问题是,如果一段DNA插入基因组某个或者某些位置了,但是我们不知道其具体位置,希望通过测序的方法来检测这些位置信息。
最简单直接的办法当然是全基因组测序(最好还要是长度长的三代测序的),然后比对插入基因序列,找边缘序列(类似于嵌合体,一半是插入的基因序列,一半是基因组的序列)。但是这个办法相对来说成本比较高。那有没有相对简单的办法呢?答案当然是有的,就是Guide-seq。
其基本原理如下图所示:

图片出自Illumina官网
简述该流程步骤如下:
- 准备好加入dsODN的细胞样本或DNA样本,按照常规文库构建办法建好PE文库,其中引入UMI分子标记;
- 设计插入片段末端的特异性引物,联合P5通用引物对文库进行扩增,所得新的DNA库,进行二次扩增,完善P7端接头序列,即是含有插入片段和原本基因片段的文库。
- 进行比对分析,确定插入位点。
分析思路如下图:
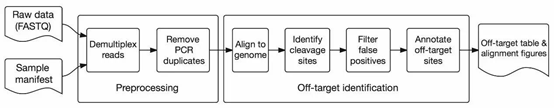
注意其中分析流程中需要去除冗余重复。
个人的一些理解:
- UMI模式不一定测序厂商都会愿意测,因此UMI可以考虑设置在特异性引物外侧;
- 特异性引物设计一定要经过确认;
- 分析的时候注意过滤掉假阳性结果。
该方法的优点是,快速,容易操作,缺点是数据分析控制不好,实验过程中,也可能因为因为设计原因或者扩增原因导致一部分位点遗漏。分析流程也许需要慎重考虑。





















 2万+
2万+











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








