欢迎关注我的CSDN:https://spike.blog.csdn.net/
本文地址:https://blog.csdn.net/caroline_wendy/article/details/131384199
免责声明:本文来源于个人知识与开源资料,仅用于学术交流,不包含任何商业技术,欢迎相互学习,不支持转载。
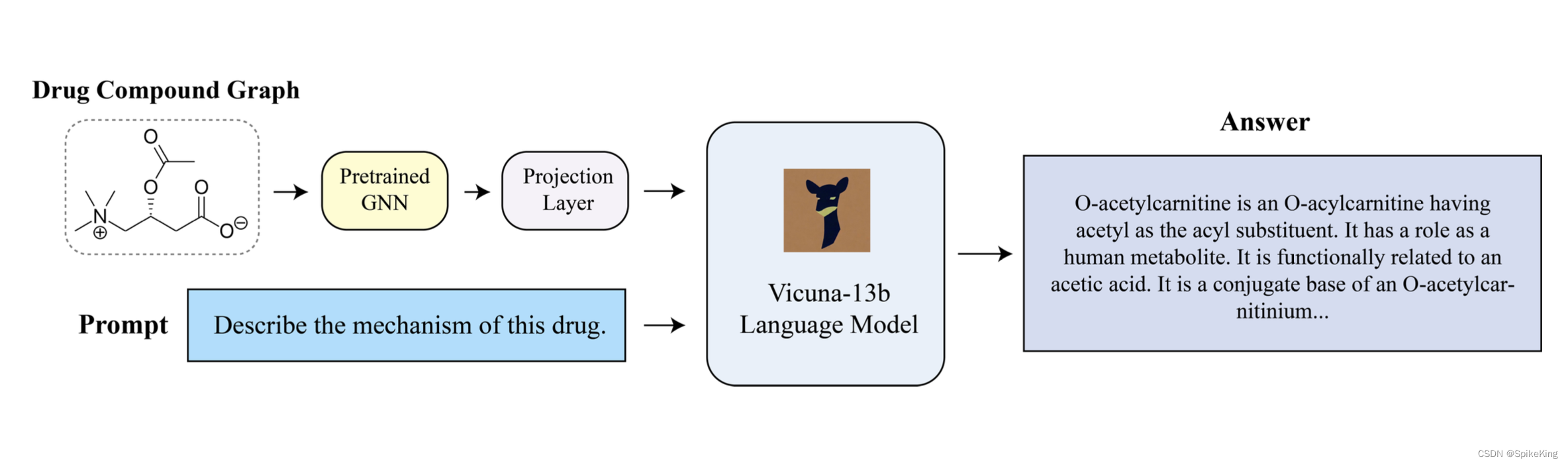
论文:DrugChat: Towards Enabling ChatGPT-Like Capabilities on Drug Molecule Graphs
DrugChat,基于图神经网








 本文深入探讨了算法的基础概念,逐步引导读者理解排序、搜索等经典算法,并介绍了高级算法如动态规划和图论的应用。通过实例解析,帮助开发者提升解决复杂问题的能力。
本文深入探讨了算法的基础概念,逐步引导读者理解排序、搜索等经典算法,并介绍了高级算法如动态规划和图论的应用。通过实例解析,帮助开发者提升解决复杂问题的能力。

 订阅专栏 解锁全文
订阅专栏 解锁全文



















 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










