探秘微生物世界:易宏基因组——你的私人宏基因组分析专家🚀
EasyMetagenomeEasy Metagenome Pipeline项目地址:https://gitcode.com/gh_mirrors/ea/EasyMetagenome
在这个生物信息学飞速发展的时代,宏基因组分析已经成为研究微生物群落结构及其功能的重要手段。今天,我们向您推荐一款强大的开源项目——易宏基因组(EasyMetagenome),这是一款专为简化宏基因组数据分析流程而设计的工具,让即使是初学者也能轻松驾驭复杂的宏基因组研究。
项目简介[Introduction]
易宏基因组(EasyMetagenome)是一个高效、直观且易于使用的宏基因组分析流程,最新版本为v1.21,于2024年5月17日更新。它提供了一个从原始测序数据到物种和功能组成的完整工作流程,如图1所示,将繁琐的数据处理过程一键化,极大地提高了研究效率。
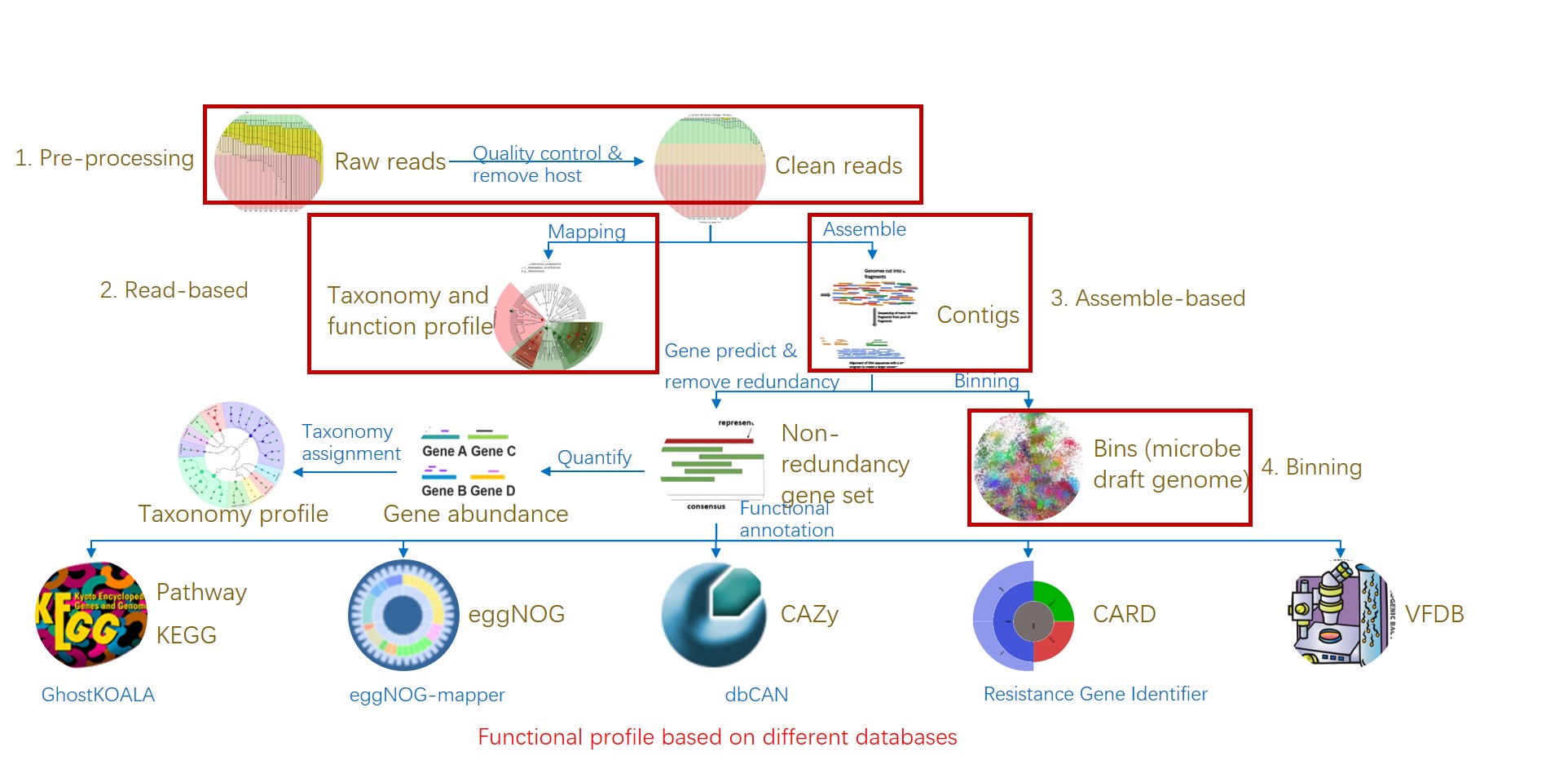
图1. 易宏基因组的工作流程:分析宏基因组测序从原始数据到物种和功能组成表。
技术解析[Technical Analysis]
EasyMetagenome基于Linux环境,提供了三个核心脚本:
0Install.sh:负责软件和数据库的安装,确保所有必需工具和资源已经就绪。1Pipeline.sh:执行实际的分析流程,包括质量控制、组装、比对、物种分类和功能注释等步骤。2StatPlot.sh:用于统计结果分析和可视化,帮助研究人员快速理解数据并生成高质量的图表。
这些Shell脚本采用Markdown格式编写,易于在多种编辑器中查看和管理,同时还带有问题解答,确保用户能够顺利进行操作。
应用场景[Application Scenarios]
无论你是想探索人体肠道微生物的多样性,还是想研究海洋深处未知微生物的生态角色,易宏基因组都是理想的选择。这款工具特别适合:
- 微生物生态学研究,以了解特定环境中微生物的种群结构和功能特性。
- 健康与疾病相关研究,通过对比不同状态下微生物群落的变化来揭示潜在的生物标志物。
- 污染修复或生物技术应用,寻找具有特定代谢功能的微生物。
项目特点[Key Features]
- 易用性:无需高级编程技能,只需要基本的Linux操作经验,就能进行完整的宏基因组分析。
- 自动化:一体化流程大大减少了手动操作,节省了宝贵的时间。
- 灵活性:支持定制化设置,可以根据研究需求调整参数。
- 透明度:所有步骤都有详细记录,保证了分析的可重复性和可靠性。
- 社区支持:背后有一个活跃的研发团队,并鼓励社区成员参与改进和扩展。
如果你正在寻找一个能够快速、准确地分析宏基因组数据的解决方案,易宏基因组无疑是最佳选择。立即加入这个开放源代码社区,释放你的微生物研究潜力吧!
Remember, citation is crucial when using EasyMetagenome:
- Yong-Xin Liu, et al. (2023). EasyAmplicon...
- Yong-Xin Liu, et al. (2021). A practical guide...
一起探索微观宇宙,开启微生物研究的新篇章!
EasyMetagenomeEasy Metagenome Pipeline项目地址:https://gitcode.com/gh_mirrors/ea/EasyMetagenome























 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










