注明:这篇遗传算法程序我在网上看到多次,很多人在转载时,都称已经修改了错误的地方,程序在matlab上能够运行。
当我在学习这段程序时,发现结果仍存在很大问题(不稳定、不准确)。我一行一行看时,发现不仅有少许语法错误,还有几处原理上的逻辑错误。
第一处
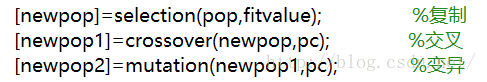
第二处

主程序中,在求每一代种群的适应度最大值时,前面一定要再计算一次种群的目标函数值和适应度值。原程序中并没有此步骤,当你运行原程序时,仔细看一下结果图,就会觉得很不对劲。
在2.4复制环节中,原主所讲的赌轮盘选择法我能够理解,但是到代码上,感觉就有点问题了。
这是我半个多月前看的程序,别的一些修改也已经记不得了。第二处错误是我昨天在作总结时发现出来的,温故知新嘛。下面代码都经过运行,结果符合预期,逻辑上应该没问题的(总结时,在逻辑上又推敲过)。我也是在自学,如果有别人发现什么问题,欢迎再讨论区留言。
博主:李帅
博客链接:http://blog.csdn.net/lee_shuai
以上为博主对原程序所做出的修正,下面贴上修改后的代码,运行无误。
本程序网上流传较广,原创作者很难找到,故不再标注转载地址。
% 求下列函数的最大值 %
% f(x)=10*sin(5x)+7*cos(4x) x∈[0,10] %
% 将 x 的值用一个10位的二值形式表示为二值问题,一个10位的二值数提供的分辨率是每为 (10-0)/(2^10-1)≈0.01
% 将变量域 [0,10] 离散化为二值域 [0,1023], x=0+10*b/1023, 其中 b 是 [0,1023] 中的一个二值数。 %
% %
%--------------------------------------------------------------------------------------------------------------%
%--------------------------------------------------------------------------------------------------------------
% 2.0 主程序
%遗传算法主程序
%Name:genmain05.m
%要求精度不大于0.01,
clear
clc
popsize=20; %群体大小
chromlength=10; %字符串长度(个体长度)
pc=0.6; %交叉概率,只有在随机数小于pc时,才会产生交叉
pm=0.001; %变异概率
pop=initpop(popsize,chromlength); %随机产生初始群体
for i=1:20 %20为遗传代数
[objvalue]=calobjvalue(pop); %计算目标函数
fitvalue=calfitvalue(objvalue); %计算群体中每个个体的适应度
[newpop]=selection(pop,fitvalue); %复制
[newpop1]=crossover(newpop,pc); %交叉
[newpop2]=mutation(newpop1,pc); %变异
[objvalue]=calobjvalue(newpop2); %计算目标函数
fitvalue=calfitvalue(objvalue); %计算群体中每个个体的适应度
[bestindividual,bestfit]=best(newpop2,fitvalue); %求出群体中适应值最大的个体及其适应值
y(i)=bestfit; %返回的 y 是自适应度值,而非函数值
x(i)=decodechrom(bestindividual,1,chromlength)*10/1023; %将自变量解码成十进制
pop=newpop2;
end
fplot('10*sin(5*x)+7*cos(4*x)',[0 10])
hold on
plot(x,y,'r*')
hold on
[z index]=max(y); %计算最大值及其位置
x5=x(index) %计算最大值对应的x值
ymax=z
% 2.1初始化(编码)
% initpop.m函数的功能是实现群体的初始化,popsize表示群体的大小,chromlength表示染色体的长度(二值数的长度),
% 长度大小取决于变量的二进制编码的长度(在本例中取10位)。
%初始化
function pop=initpop(popsize,chromlength)
pop=round(rand(popsize,chromlength));
% rand随机产生每个单元为 {0,1} 行数为popsize,列数为chromlength的矩阵,
% round对矩阵的每个单元进行圆整。这样产生的初始种群。
% 2.2.3 计算目标函数值
% calobjvalue.m函数的功能是实现目标函数的计算,其公式采用本文示例仿真,可根据不同优化问题予以修改。
%遗传算法子程序
%Name: calobjvalue.m
%实现目标函数的计算,将 二值域 中的数转化为 变量域的数
function [objvalue]=calobjvalue(pop)
temp1=decodechrom(pop,1,10); %将pop每行转化成十进制数
x=temp1*10/1023; %在精度不大于0.01时,最小整数为1023,即需要10位二进制
objvalue=10*sin(5*x)+7*cos(4*x); %计算目标函数值
%遗传算法子程序
%Name:calfitvalue.m
%计算个体的适应值
function fitvalue=calfitvalue(objvalue)
[px,py]=size(objvalue); %目标值有正有负
for i=1:px
if objvalue(i)>0
temp=objvalue(i);
else
temp=0.0;
end
fitvalue(i)=temp;
end
fitvalue=fitvalue';
% 2.4 选择复制
% 选择或复制操作是决定哪些个体可以进入下一代。程序中采用赌轮盘选择法选择,这种方法较易实现。
% 根据方程 pi=fi/∑fi=fi/fsum ,选择步骤:
% 1) 在第 t 代,由(1)式计算 fsum 和 pi
% 2) 产生 {0,1} 的随机数 rand( .),求 s=rand( .)*fsum
% 3) 求 所有fi≥s 中最小的 k ,则第 k 个个体被选中
% 4) 进行 N 次2)、3)操作,得到 N 个个体,成为第 t=t+1 代种群
%遗传算法子程序
%Name: selection.m
%选择复制
totalfit=sum(fitvalue); %求适应值之和
fitvalue=fitvalue/totalfit; %单个个体被选择的概率
fitvalue=cumsum(fitvalue); %如 fitvalue=[1 2 3 4],则 cumsum(fitvalue)=[1 3 6 10],不明白为什么要累加
[px,py]=size(pop); %20*10
ms=sort(rand(px,1)); %从小到大排列
fitin=1;
newin=1;
while newin<=px %选出20个新个体,有重复情况,和上面介绍的方法不太一样
if(ms(newin))<fitvalue(fitin)
newpop(newin,:)=pop(fitin,:);
newin=newin+1;
else
fitin=fitin+1;
end
end
% 2.5 交叉
% 交叉(crossover),群体中的每个个体之间都以一定的概率 pc 交叉,即两个个体从各自字符串的某一位置
% (一般是随机确定)开始互相交换,这类似生物进化过程中的基因分裂与重组。例如,假设2个父代个体x1,x2为:
% x1=0100110
% x2=1010001
% 从每个个体的第3位开始交叉,交又后得到2个新的子代个体y1,y2分别为:
% y1=0100001
% y2=1010110
% 这样2个子代个体就分别具有了2个父代个体的某些特征。利用交又我们有可能由父代个体在子代组合成具有更高适合度的个体。
% 事实上交叉是遗传算法区别于其它传统优化方法的主要特点之一。
%遗传算法子程序
%Name: crossover.m
%交叉
[px,py]=size(pop);
newpop=ones(size(pop));
for i=1:2:px-1 %步长为2,是将相邻的两个个体进行交叉
if(rand<pc)
cpoint=round(rand*py);
newpop(i,:)=[pop(i,1:cpoint),pop(i+1,cpoint+1:py)];
newpop(i+1,:)=[pop(i+1,1:cpoint),pop(i,cpoint+1:py)];
else
newpop(i,:)=pop(i,:);
newpop(i+1,:)=pop(i+1,:);
end
end
% 2.6 变异
% 变异(mutation),基因的突变普遍存在于生物的进化过程中。变异是指父代中的每个个体的每一位都以概率 pm 翻转,
%即由“1”变为“0”,或由“0”变为“1”。
%遗传算法的变异特性可以使求解过程随机地搜索到解可能存在的整个空间,因此可以 在一定程度上 求得全局最优解。
%遗传算法子程序
%Name: mutation.m
%变异
[px,py]=size(pop);
newpop=ones(size(pop));
for i=1:px
if(rand<pm)
mpoint=round(rand*py); %产生的变异点在1-10之间
if mpoint<=0
mpoint=1; %变异位置
end
newpop(i,:)=pop(i,:);
if any(newpop(i,mpoint))==0
newpop(i,mpoint)=1;
else
newpop(i,mpoint)=0;
end
else
newpop(i,:)=pop(i,:);
end
end
% 2.7 求出群体中最大得适应值及其个体
%遗传算法子程序
%Name: best.m
%求出第 t 代群体中适应值最大的值
function [bestindividual,bestfit]=best(pop,fitvalue)
[px,py]=size(pop);
bestindividual=pop(1,:);
bestfit=fitvalue(1);
for i=2:px
if fitvalue(i)>bestfit
bestindividual=pop(i,:);
bestfit=fitvalue(i);
end
end
% 2.2 计算目标函数值
% 2.2.1 将二进制数转化为十进制数(1)
%遗传算法子程序
%Name: decodebinary.m
%产生 [2^n 2^(n-1) ... 1] 的行向量,然后求和,将二进制转化为十进制
[px,py]=size(pop); %求pop行和列数
for i=1:py
pop1(:,i)=2.^(py-i).*pop(:,i);
end
pop2=sum(pop1,2); %求pop1的每行之和
% 2.2.2 将二进制编码转化为十进制数(2)
% decodechrom.m函数的功能是将染色体(或二进制编码)转换为十进制,参数spoint表示待解码的二进制串的起始位置
% (对于多个变量而言,如有两个变量,采用20为表示,每个变量10为,则第一个变量从1开始,另一个变量从11开始。本例为1),
% 参数1ength表示所截取的长度(本例为10)。
%遗传算法子程序
%Name: decodechrom.m
%将二进制编码转换成十进制
pop1=pop(:,spoint:spoint+length-1);
pop2=decodebinary(pop1); %将pop每行转换成十进制值,结果是20*1的矩阵
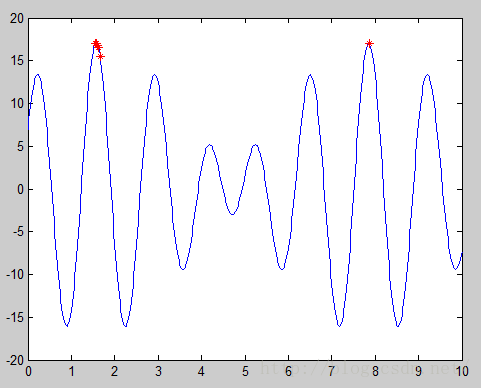
2.8 最终结果
每次运行主程序后,绘出的结果图都是不完全一样的,但最终的所求得的函数在区间[0,10]内的最大值几乎是完全相等的。
























 56万+
56万+

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








