“聚类分析是一种数据归约技术,旨在揭露一个数据集中观测值的子集。它可以把大量的观测值归约为若干个类。这里的类被定义为若干个观测值组成的群组,群组内观测值的相似度比群间相似度高。”——《R 语言实战》第二版
常用的两种聚类方法有:
- 层次聚类(hierachical clustering):每个数据点为一小类,两两通过树的方式合并,直到所有的数据点汇成一类。常用算法:
- 单联动(single linkage):类 A 中的点与类 B 中的点间的最小距离。适合于细长的类。
- 全联动(complete linkage ):类 A 中的点与类 B 中的点间的最大距离。适合于相似半径的紧凑类,对异常值敏感。
- 平均联动(average linkage):类 A 中的点与类 B 中的点间的平均距离,也称为 UPGMA。适合于聚合方差小的类。
- 质心(centroid):类 A 与类 B 的质心的距离。质心的定义是“类的变量均值向量”。对异常值不敏感,但表现可能稍弱。
- Ward 法(ward.D):两类之间的所有变量的方差分析平方和。适合于仅聚合少量值、类别数接近数据点数目的情况。
- 划分聚类(partitioning clustering):事先指定类数 KK,然后聚类。
- K均值(K-means):
- 中心划分(Partitioning Around Medoids,即 PAM):
聚类步骤
聚类是一个多步骤过程。典型的步骤有 11 步。
- 变量选取:例如你需要对实验数据进行聚类,那么你需要仔细思考哪些变量会对聚类产生影响,而哪些变量是不需加入分析的。
- 缩放数据:最常用的方法是标准化,将所有变量变为 ¯¯¯x=0,SE(x)=1x¯=0,SE(x)=1 的变量。
- 筛选异常:筛选和删除异常数据对于某些聚类方法是很重要的,这可以借助 R 的
outliers/mvoutlier包。或者,你可以换用一种受异常值干扰小的方法,比如中心划分聚类。 - 距离计算:两个数据点间的距离度量有若干种,我们在下一小节专门讨论。
- 选择聚类方法:每个方法都有其优缺点,请仔细斟酌。
- 确定一种或多种聚类方法
- 确定类数:常用的方法是尝试使用不同的类数进行聚类,然后比较结果。R 中的 NbClust 包提供了一个拥有超过30个指标的 NbClust() 函数。
- 最终方案
- 可视化:层次聚类使用树状图;划分聚类使用可视化双变量聚类图。
- 解释每个类:通常会对每个类进行汇总统计(如果是连续型数据),或者返回类的众数/类别分布(如果含类别型数据)。
- 验证:聚类结果有意义吗?更换聚类方法能得到类似结果吗?R 中的 fpc, clv 与 clValid 包给出了评估函数。
距离计算:dist() 函数
数据点之间的距离有多种度量方法。在 R 的 dist() 函数参数中,默认选项 method=euclidean。函数中内置的距离方法选项有:
-
欧几里得距离(euclidean):L2L2 norm. 在拥有 nn 个变量的数据集中,数据点 ii 与 jj 的欧式距离是
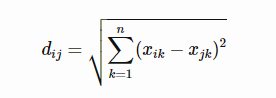
-
最大距离(maximun):L∞L∞ norm. 两点之间的最大距离,即p→∞p→∞ 时的明科夫斯基距离。
-
曼哈顿距离(manhattan): L1L1 norm.
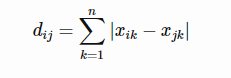
-
堪培拉距离(canberra):
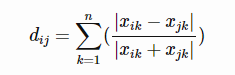
-
二进制距离(binary):非 0 变量为 1,为 0 变量为 0.然后根据 0 的比例确定距离。
-
明科夫斯基距离(minkowski):LpLp norm.
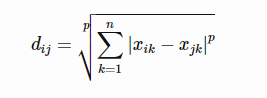
当 p=1p=1 时,即曼哈顿距离;p=2p=2 时,欧几里得距离;p→∞p→∞ 时,切比雪夫距离。
本文利用 Iris data,数据内容是萼片、花瓣的长与宽。先读取数据:
datapath <- paste(getwd(), '/data/iris.data.csv', sep='') # 我将其改成了 csv 格式
iris.raw <- read.csv(datapath, head=F)
head(iris.raw)
# 去掉非数值的第 5 列
iris <- iris.raw[,-c(5)]
| V1 | V2 | V3 | V4 | V5 |
|---|---|---|---|---|
| 5.1 | 3.5 | 1.4 | 0.2 | Iris-setosa |
| 4.9 | 3.0 | 1.4 | 0.2 | Iris-setosa |
| 4.7 | 3.2 | 1.3 | 0.2 | Iris-setosa |
| 4.6 | 3.1 | 1.5 | 0.2 | Iris-setosa |
| 5.0 | 3.6 | 1.4 | 0.2 | Iris-setosa |
| 5.4 | 3.9 | 1.7 | 0.4 | Iris-setosa |
算例:欧式距离
R 内置的 dist() 函数默认使用欧式距离,以下与 dist(iris, method='euclidean') 等同。比如我们来计算 iris 的欧氏距离:
iris.e <- dist(iris)
# 显示前 3 个数据点间的欧式距离。这是一个对角线全0的对称矩阵
as.matrix(iris.e)[1:3, 1:3]
| # | 1 | 2 | 3 |
|---|---|---|---|
| 1 | 0.0000000 | 0.5385165 | 0.509902 |
| 2 | 0.5385165 | 0.0000000 | 0.300000 |
| 3 | 0.5099020 | 0.3000000 | 0.000000 |
层次聚类算例
层次聚类(HC)的逻辑是:依次把距离最近的两类合并为一个新类,直至所有数据点合并为一个类。
层次聚类的 R 函数是 hclust(d, method=) ,其中 d 通常是一个 dist() 函数的运算结果。
仍然使用上文的 Iris data 数据。
标准化
尽管标准化不一定会用到,但是这是通常的手段之一。
iris.scaled <- scale(iris)
head(iris)
head(iris.scaled)
| V1 | V2 | V3 | V4 |
|---|---|---|---|
| 5.1 | 3.5 | 1.4 | 0.2 |
| 4.9 | 3.0 | 1.4 | 0.2 |
| 4.7 | 3.2 | 1.3 | 0.2 |
| 4.6 | 3.1 | 1.5 | 0.2 |
| 5.0 | 3.6 | 1.4 | 0.2 |
| 5.4 | 3.9 | 1.7 | 0.4 |
| V1 | V2 | V3 | V4 |
|---|---|---|---|
| -0.8976739 | 1.0286113 | -1.336794 | -1.308593 |
| -1.1392005 | -0.1245404 | -1.336794 | -1.308593 |
| -1.3807271 | 0.3367203 | -1.393470 | -1.308593 |
| -1.5014904 | 0.1060900 | -1.280118 | -1.308593 |
| -1.0184372 | 1.2592416 | -1.336794 | -1.308593 |
| -0.5353840 | 1.9511326 | -1.166767 | -1.046525 |
树状图与热力图
层次聚类中的树状图是不可少的。一般使用欧式距离,聚类方法另行确定。
热力图不是必须的。
# 选择聚类方法
dist_method <- "euclidean"
cluster_method <- "ward.D"
iris.e <- dist(iris.scaled, method=dist_method)
iris.hc <- hclust(iris.e, method=cluster_method)
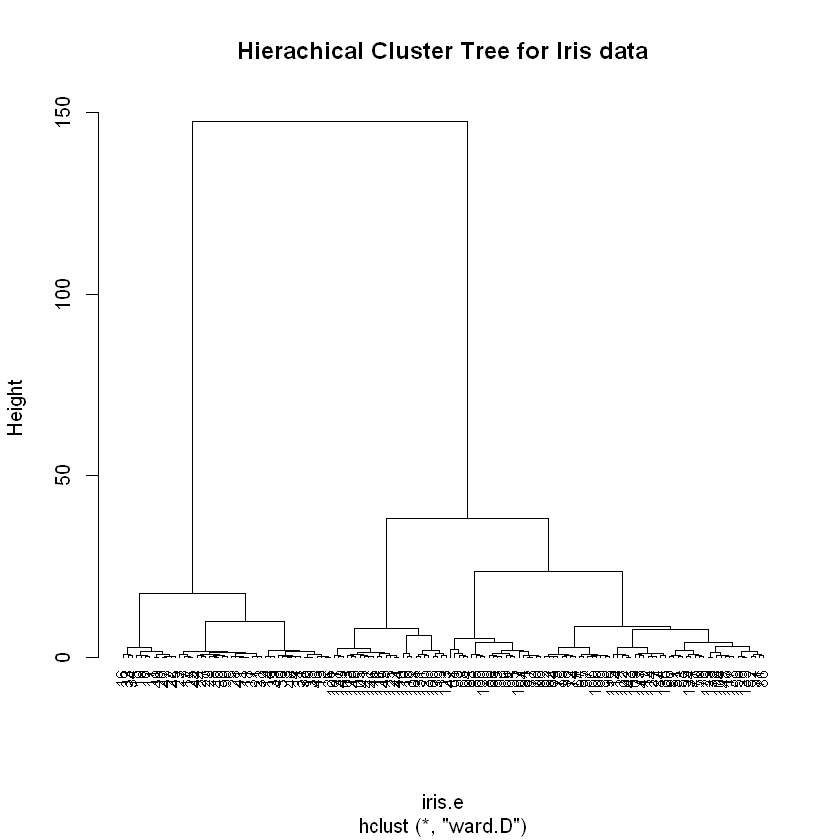
plot(iris.hc, hang=-1, cex=.8, main="Hierachical Cluster Tree for Iris data")
heatmap(as.matrix(iris.e),labRow = F, labCol = F)

确定聚类个数
使用 NbClust 包。
library(NbClust)
nc <- NbClust(iris.scaled, distance=dist_method,
min.nc=2, max.nc=10, method=cluster_method)
*** : The Hubert index is a graphical method of determining the number of clusters.
In the plot of Hubert index, we seek a significant knee that corresponds to a
significant increase of the value of the measure i.e the significant peak in Hubert
index second differences plot.
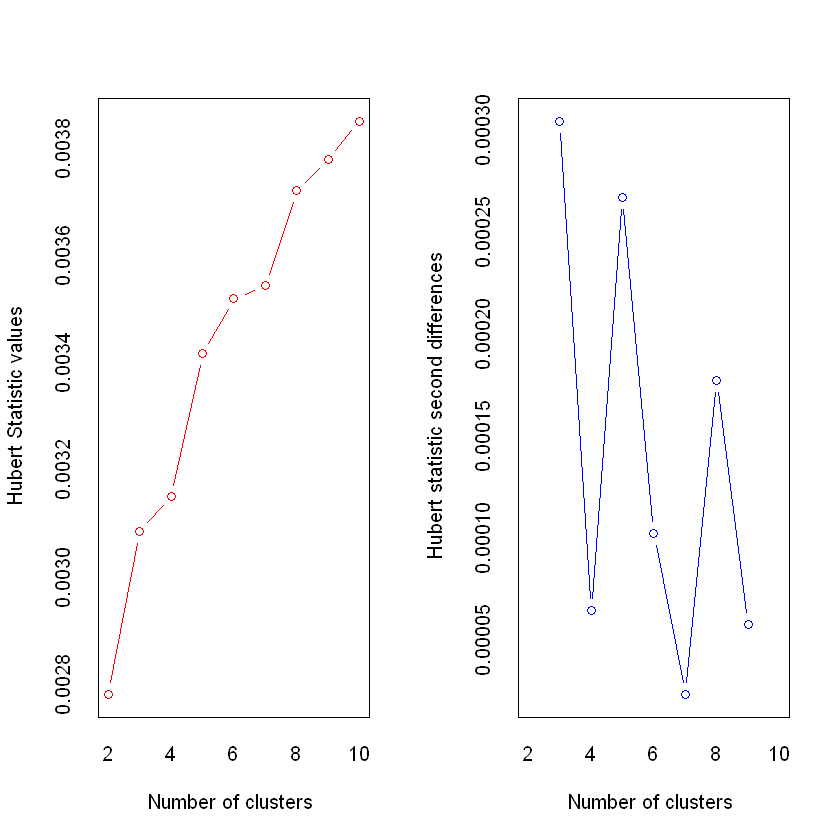
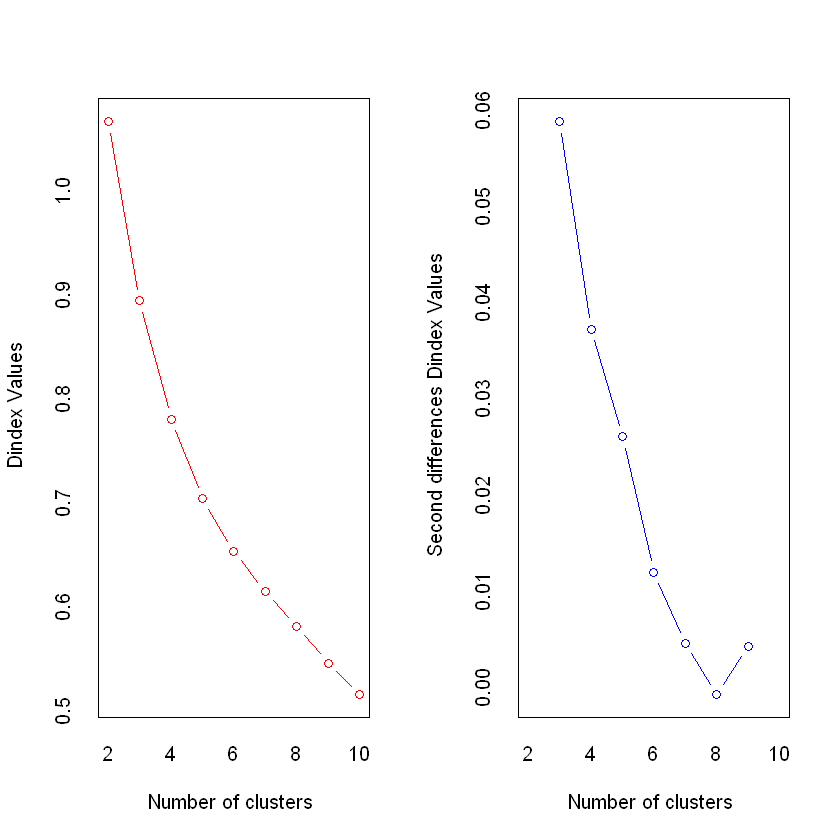
*** : The D index is a graphical method of determining the number of clusters.
In the plot of D index, we seek a significant knee (the significant peak in Dindex
second differences plot) that corresponds to a significant increase of the value of
the measure.
*******************************************************************
* Among all indices:
* 9 proposed 2 as the best number of clusters
* 5 proposed 3 as the best number of clusters
* 4 proposed 5 as the best number of clusters
* 2 proposed 6 as the best number of clusters
* 1 proposed 8 as the best number of clusters
* 3 proposed 10 as the best number of clusters
***** Conclusion *****
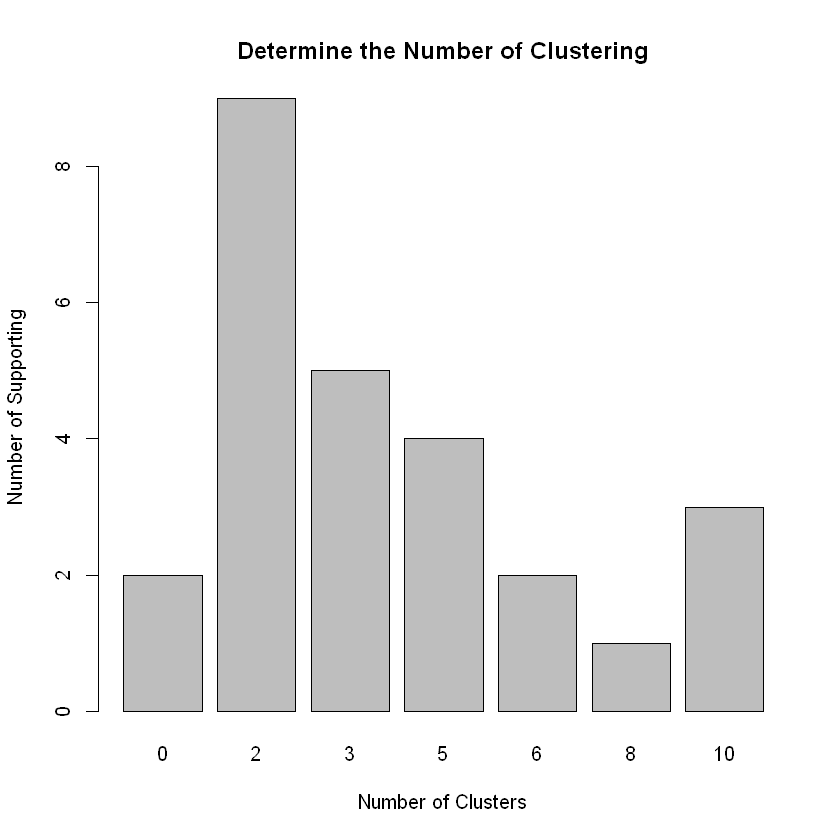
* According to the majority rule, the best number of clusters is 2
*******************************************************************
# 每个类数的投票数
table(nc$Best.n[1,])
barplot(table(nc$Best.n[1,]), xlab="Number of Clusters", ylab="Number of Supporting",
main="Determine the Number of Clustering")
0 2 3 5 6 8 10
2 9 5 4 2 1 3
完成聚类
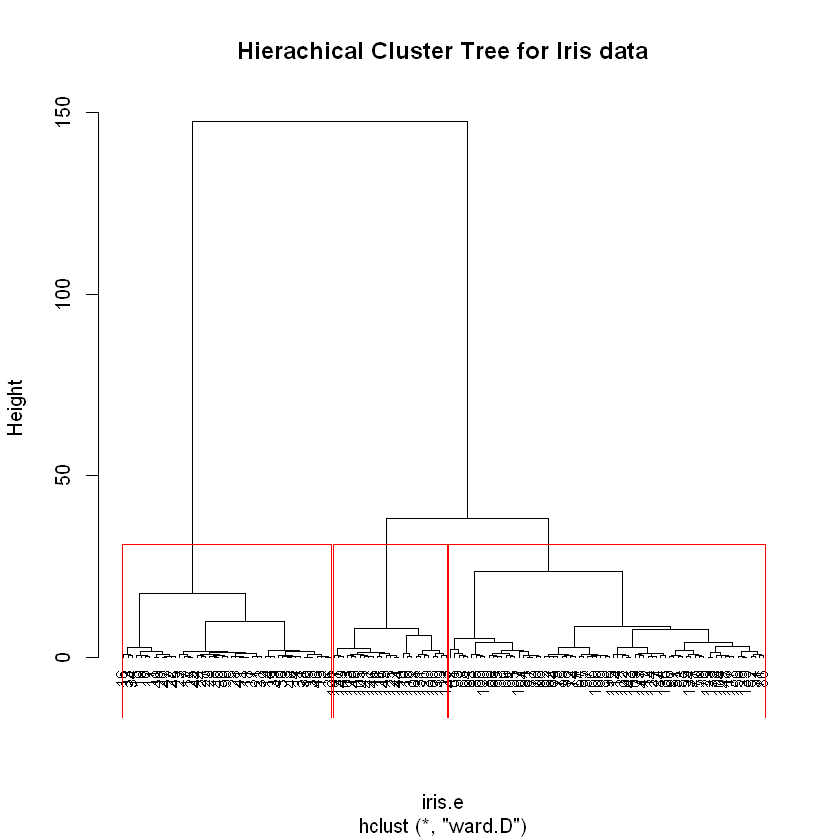
从上图我们可以确定聚类数量(两类),但是原数据指出应该是三类。以下 cutree 以及最后一个函数中使用3类。
注:类别已确定是 3 种。在此前提下,ward.D 下的 HC 聚类效果最好,但是 NbClust 投票建议仍是分为 2 类。 complete 下的 HC 聚类投票建议是 3 类,但是效果反而不如 ward 法。
cluster_num <- 3
clusters <- cutree(iris.hc, k=cluster_num)
table(clusters) # 每类多少个值
clusters
1 2 3
49 74 27
# 每类的各变量中位数
aggregate(iris, by=list(cluster=clusters), median)
| cluster | V1 | V2 | V3 | V4 |
|---|---|---|---|---|
| 1 | 5.0 | 3.4 | 1.5 | 0.20 |
| 2 | 6.0 | 2.8 | 4.5 | 1.45 |
| 3 | 6.9 | 3.1 | 5.8 | 2.20 |
# 画出矩形框
plot(iris.hc, hang=-1, cex=.8, main="Hierachical Cluster Tree for Iris data")
rect.hclust(iris.hc, k=cluster_num)
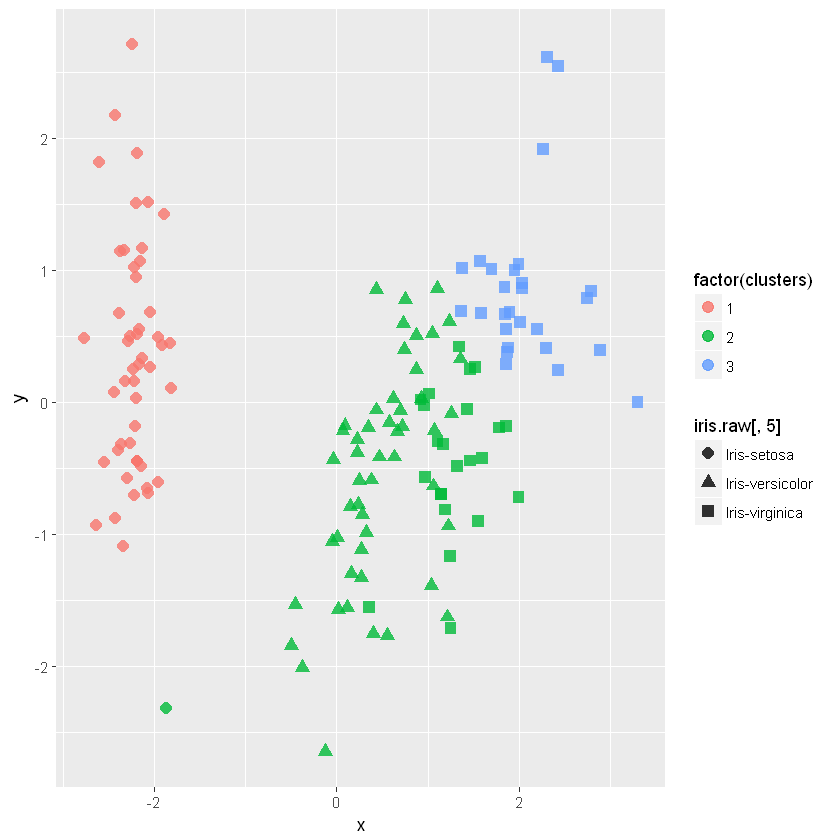
用 MDS 可视化结果
使用多维缩放(Multidimensional Scaling)方法进行可视化。原数据的三个种类被标记为三种不同的点形状,聚类结果则以颜色显示。
可以看到setose品种聚类很成功,但有一些virginica品种的花被错误和virginica品种聚类到一起。
mds=cmdscale(iris.e,k=2,eig=T)
x = mds$points[,1]
y = mds$points[,2]
library(ggplot2)
p=ggplot(data.frame(x,y),aes(x,y))
p+geom_point(size=3, alpha=0.8, aes(colour=factor(clusters),
shape=iris.raw[,5]))
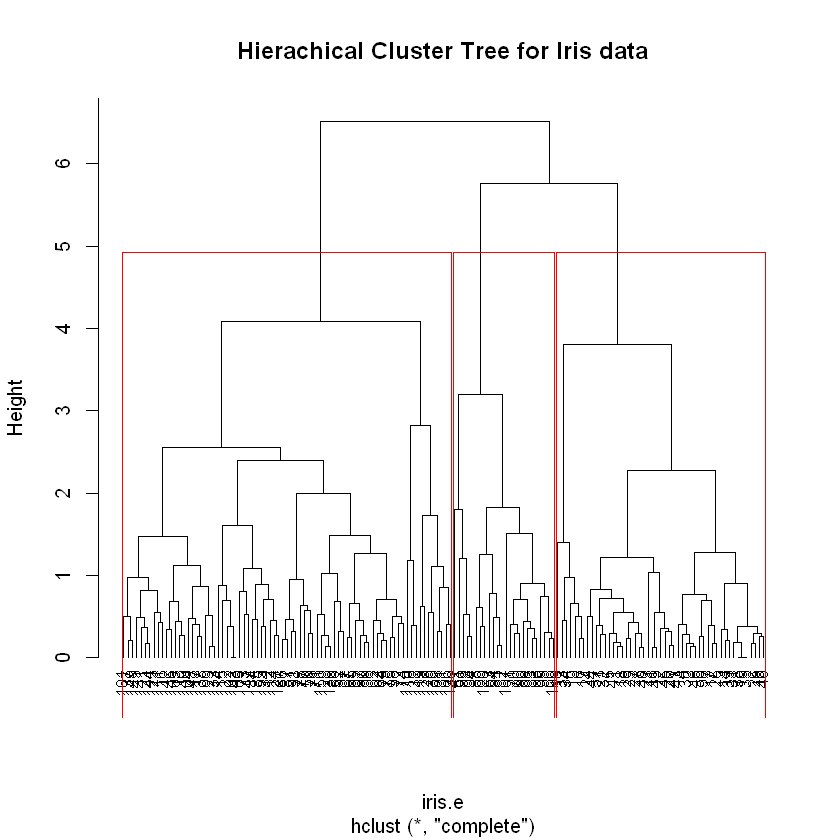
附:全联动HC聚类图
作为对比。全联动 NbClust 投票结果是3类,在此不再列出。
dist_method <- "euclidean"
cluster_method <- "complete"
iris.e <- dist(iris.scaled, method=dist_method)
iris.hc <- hclust(iris.e, method=cluster_method)
cluster_num <- 3
clusters <- cutree(iris.hc, k=cluster_num)
table(clusters) # 每类多少个值
# 画出矩形框
plot(iris.hc, hang=-1, cex=.8, main="Hierachical Cluster Tree for Iris data")
rect.hclust(iris.hc, k=cluster_num)
clusters
1 2 3
49 24 77
mds=cmdscale(iris.e,k=2,eig=T)
x = mds$points[,1]
y = mds$points[,2]
p=ggplot(data.frame(x,y),aes(x,y))
p+geom_point(size=3, alpha=0.8, aes(colour=factor(clusters),
shape=iris.raw[,5]))
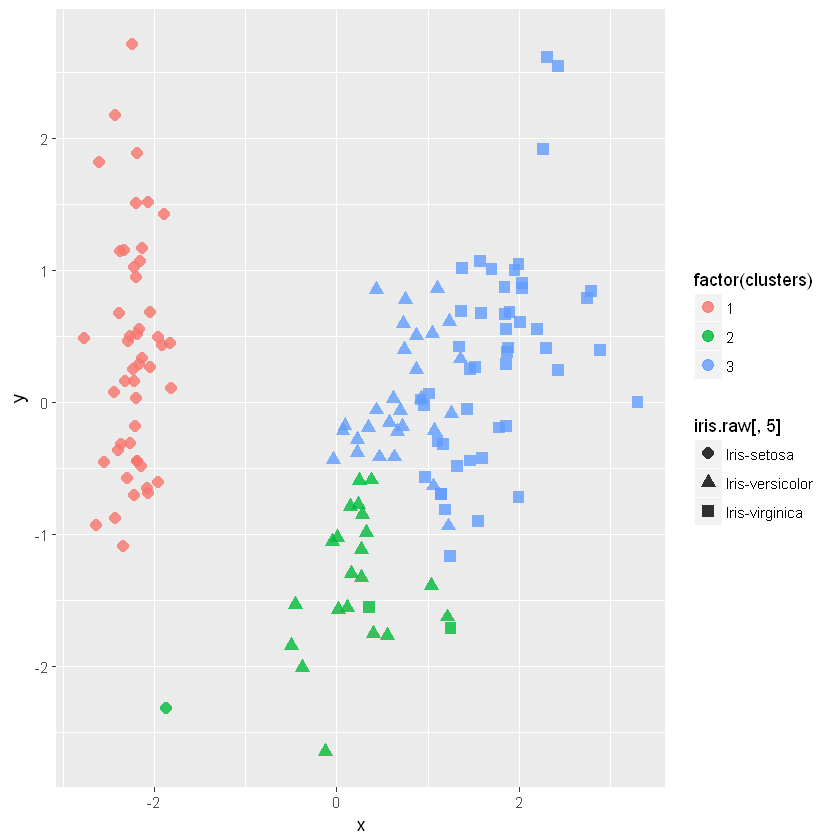
可以看出,setosa 聚类非常好; virginica 与 versicolor 的效果则是惨不忍睹。
本文内容大量参考:
- 《R 语言实战》第二版 第16章。
- 此网页
























 1852
1852

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








