探索抗菌药物耐药性的统一视角:hAMRonization项目解读
项目地址:https://gitcode.com/pha4ge/hAMRonization
项目介绍
在抗生素耐药性研究的前沿阵地上,hAMRonization犹如一位智慧的整合者,将各种不同的抗菌基因检测工具的输出统一起来。这个开源项目始于2022年,至今已支持18种(至2022年9月25日)主流的抗药性基因检测工具的结果转换,旨在提供一个标准化的数据格式,使得跨工具的比较和分析成为可能。
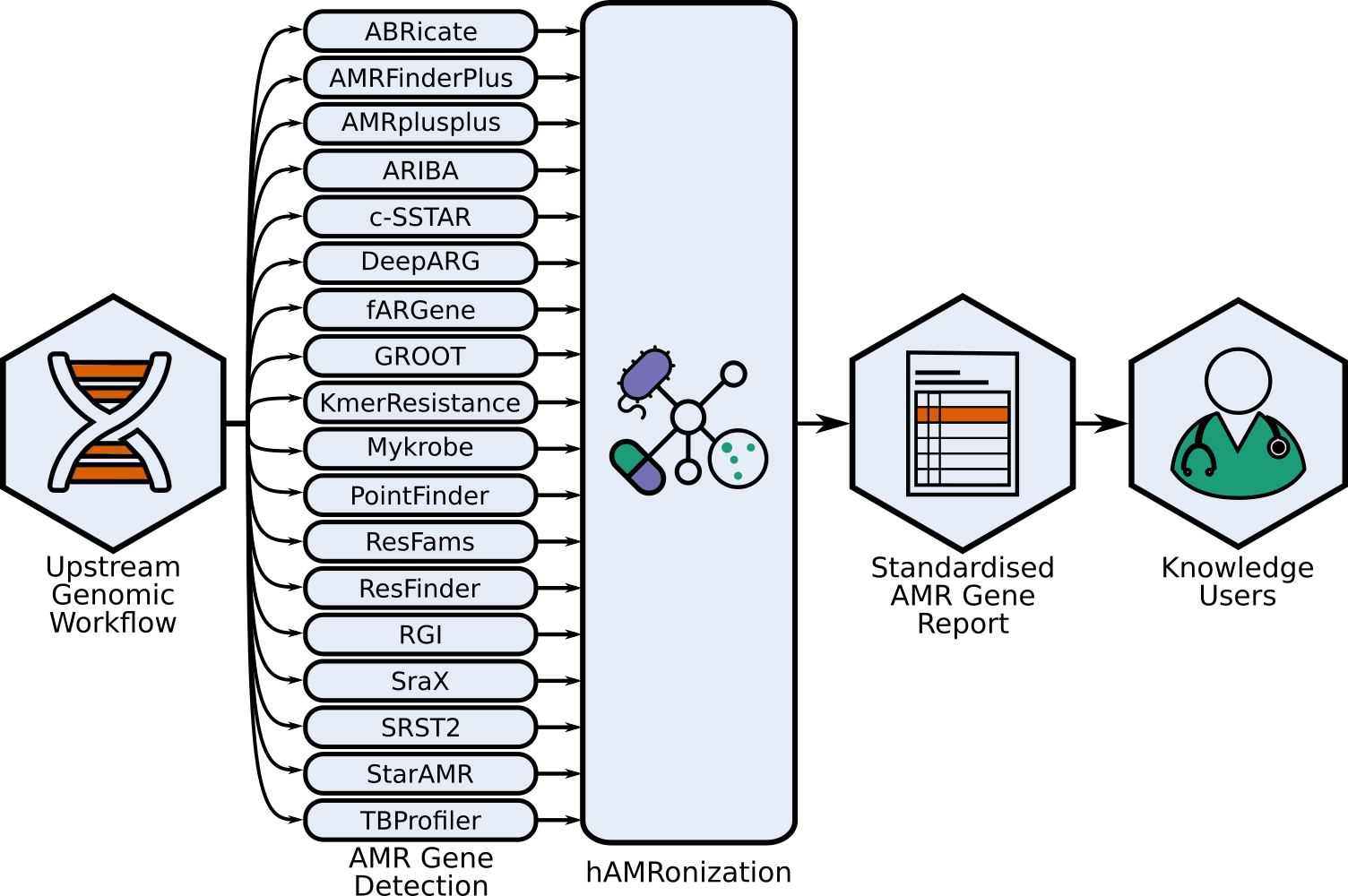
通过实现hAMRonization AMR检测规范方案,该项目不仅处理基因存在/缺失型抗性,还能处理由底层工具支持的突变抗性,为研究人员和数据分析师提供了强大的工具箱。
技术分析
hAMRonization构建于Python 3.7及以上版本之上,并依赖于pandas库,确保了其在大数据处理上的高效性能。它的设计思路简洁明了,利用模块化和命令行接口(CLI),用户可以轻松地将各种工具如abricate、amrfinderplus、rgi等的输出转换成统一的规格格式。项目中包含了详细的文档,包括英语和西班牙语版本,以及一个直观的交互式报告示例,这些都大大提升了用户体验和技术透明度。
安装过程多样化,涵盖了pip、conda、Docker和Galaxy Toolshed等多种途径,适应不同开发者和生物信息学家的工作环境和偏好。
应用场景
这一项目特别适合于微生物学、流行病学和抗菌药物耐药性研究领域。当研究人员使用不同的工具进行同一样本的抗药性基因分析时,hAMRonization能消除数据孤岛效应,使结果可比性增强,便于综合分析。无论是公共卫生部门监控抗生素耐药性的动态变化,还是科研人员在实验室间共享研究成果,hAMRonization都是连接这些数据的关键桥梁。
项目特点
- 兼容性强:能够整合市面上多种主流抗药性检测工具的输出,简化多源数据分析难题。
- 标准化输出:定义了一套统一的AMR数据规格,提高了数据的一致性和互操作性。
- 灵活性高:支持多种安装方式和输出格式(TSV、JSON),适应不同的工作流程和偏好。
- 互动式报告:提供的交互式总结报告,让用户能更直观地探索和理解数据。
- 易集成到脚本:对于自动化工作流,可以直接通过Python API调用,便于编程集成。
hAMRonization不仅仅是一个工具,它是对抗生素耐药性全球挑战的一个响应,也是促进生命科学领域数据共享与合作的重要一步。对于从事细菌基因组学研究、疾病防控及药物研发的团队来说,拥抱hAMRonization意味着拥有了更强大、更灵活的分析框架,进而加速科学发现的过程。






















 702
702











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










