什么是PCA?
数据降维
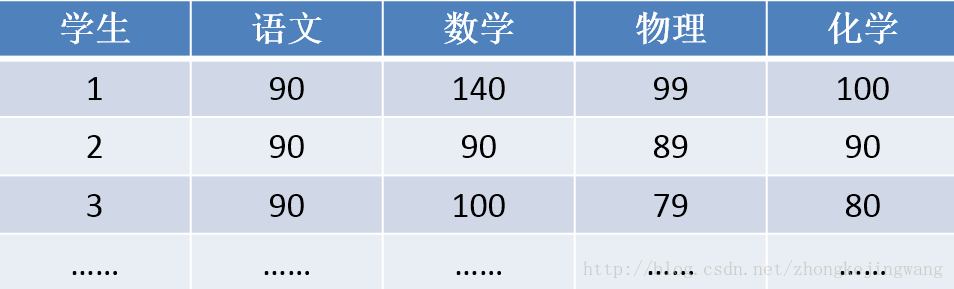
下面是一些学生的成绩:
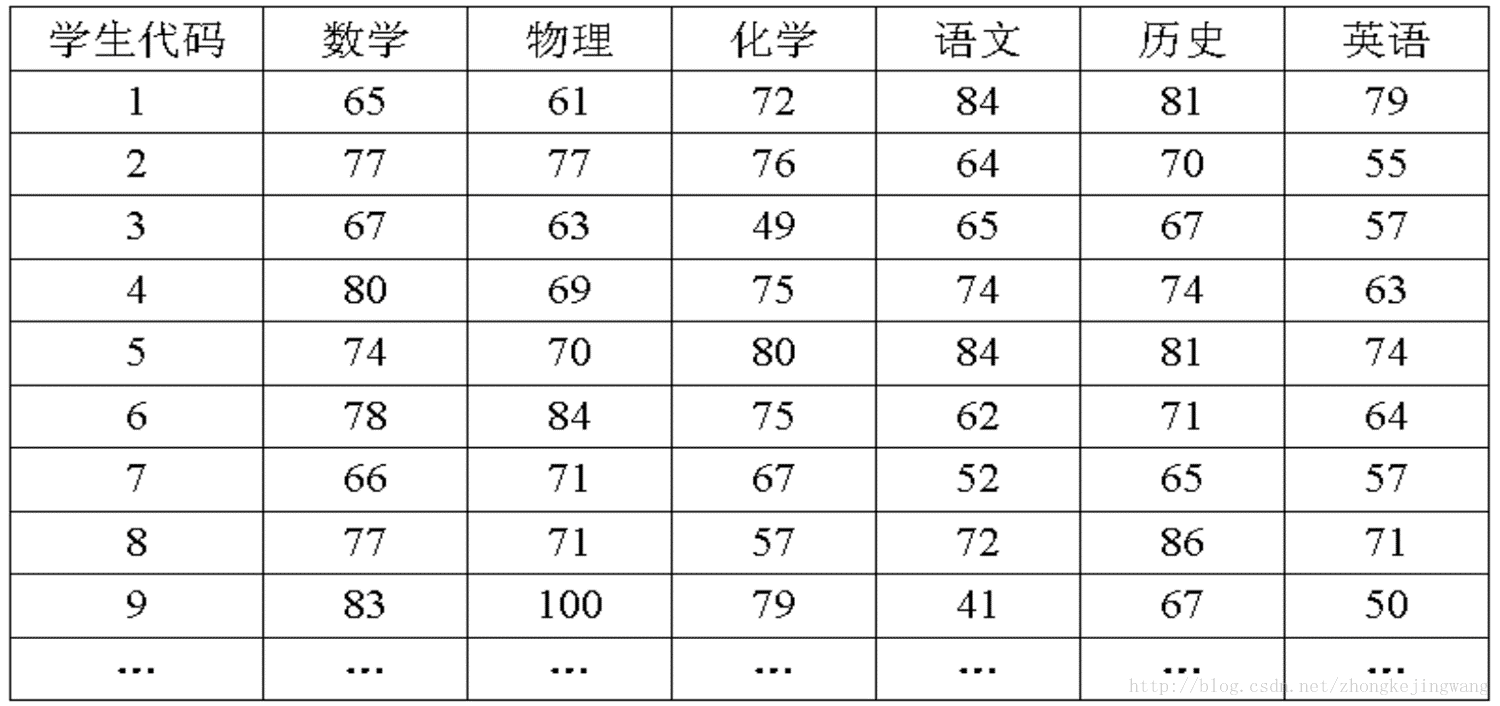
首先,假设这些科目成绩不相关,也就是说某一科考多少份与其他科没有关系。那么一眼就能看出来,数学、物理、化学这三门成绩构成了这组数据的主成分(很显然,数学作为第一主成分,因为数学成绩拉的最开)。为什么一眼能看出来?因为坐标轴选对了!下面再看一组数据,还能不能一眼看出来:
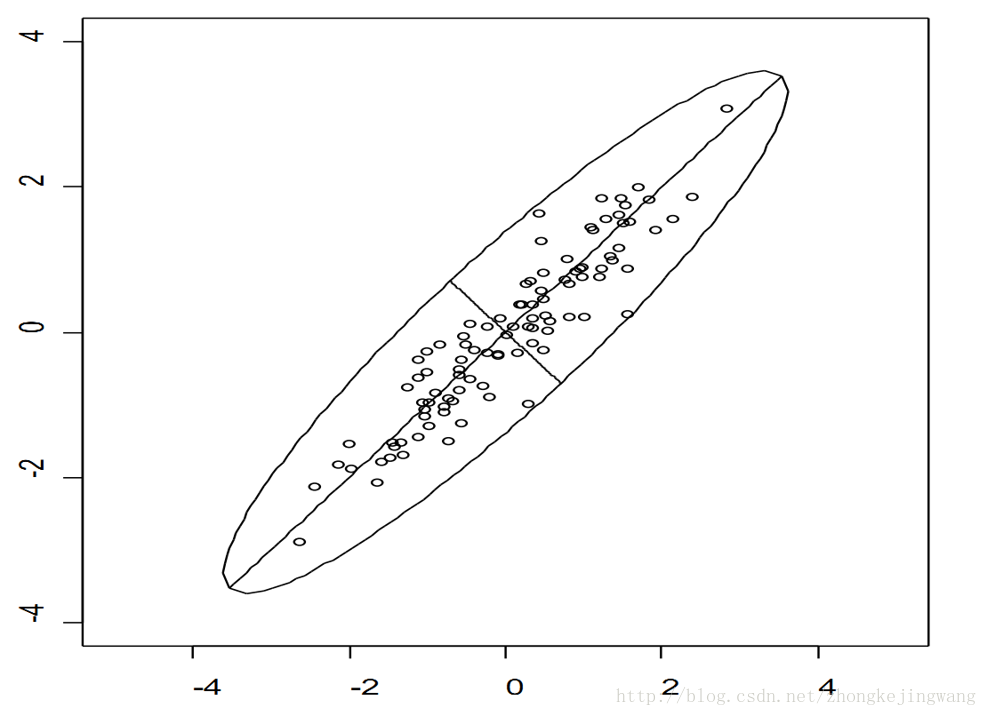
是不是有点凌乱了?你还能看出来数据的主成分吗?显然不能,因为在这坐标系下数据分布很散乱。所以说,看到事物的表象而看不到其本质,是因为看的角度有问题!如果把这些数据在空间中画出来,也许你一眼就能看出来。但是,对于高维数据,能想象其分布吗?就算能描述分布,如何精确地找到这些主成分的轴?如何衡量你提取的主成分到底占了整个数据的多少信息?要回答这些问题,需要将上面的分析上升到理论层面。接下来就是PCA的理论分析。
PCA推导
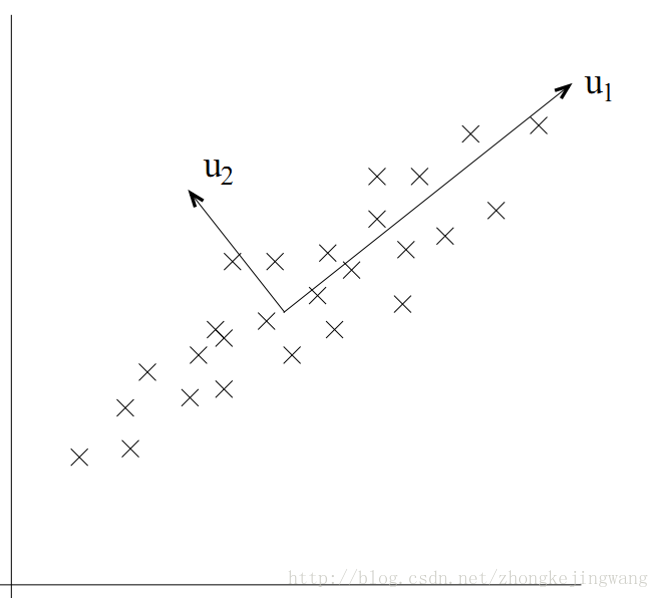
上面是二维空间中的一组数据,很明显,数据的分布让我们很容易就能看出来主成分的轴(简称主轴)的大致方向。下面的问题就是如何通过数学计算找出主轴的方向。来看这张图:
现在要做的事情就是寻找u1的方向,对于这点,我想好多人都有经验,这不就是以前用最小二乘法拟合数据时做的事情吗!对,最小二乘法求出来的直线(二维)的方向就是u1的方向!那u2的方向呢?因为这里是二维情况,所以u2方向就是跟u1垂直的方向。
先来看看svd分解
这个可以应用在数据降维压缩上!在数据相关性特别大的情况下存储X和Y矩阵比存储A矩阵占用空间更小!
正交矩阵
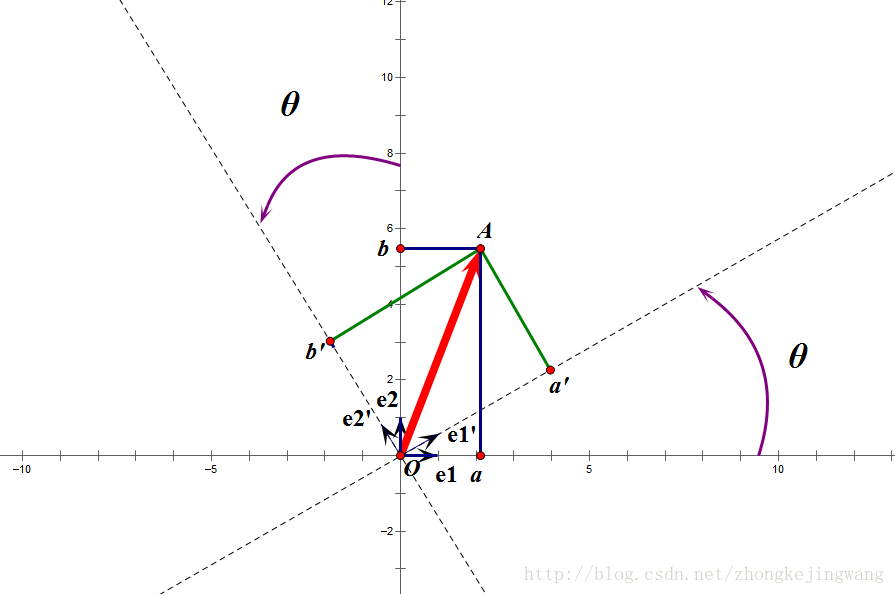
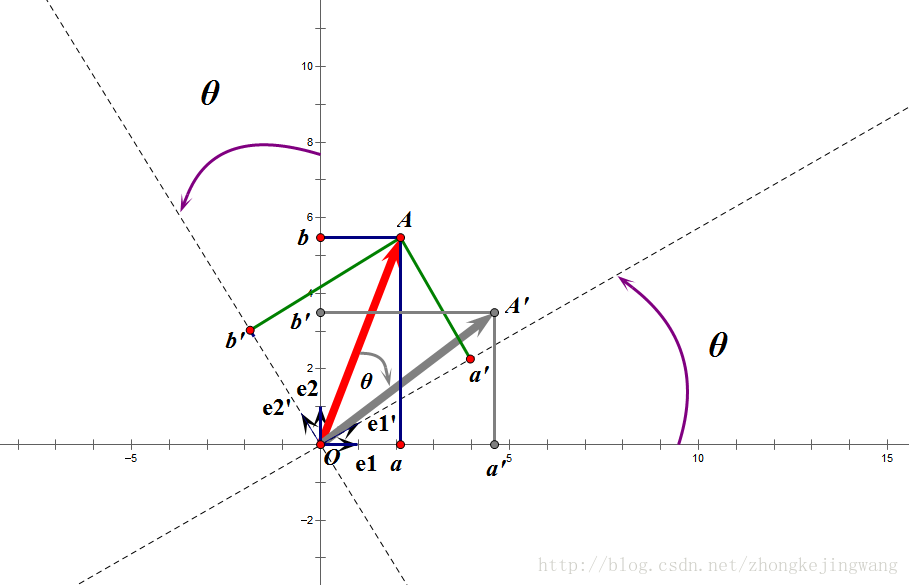
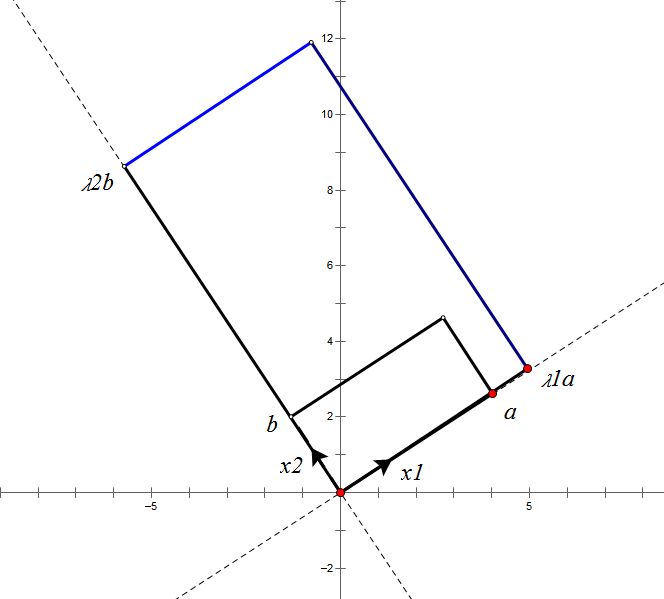
假设二维空间中的一个向量OA,它在标准坐标系也即e1、e2表示的坐标是中表示为(a,b)'(用'表示转置),现在把它用另一组坐标e1'、e2'表示为(a',b')',存在矩阵U使得(a',b')'=U(a,b)',则U即为正交矩阵。从图中可以看到,正交变换只是将变换向量用另一组正交基表示,在这个过程中并没有对向量做拉伸,也不改变向量的空间位置,加入对两个向量同时做正交变换,那么变换前后这两个向量的夹角显然不会改变。上面的例子只是正交变换的一个方面,即旋转变换,可以把e1'、e2'坐标系看做是e1、e2坐标系经过旋转某个斯塔角度得到,怎么样得到该旋转矩阵U呢?如下
a'和b'实际上是x在e1'和e2'轴上的投影大小,所以直接做内积可得,then
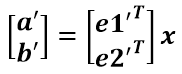
从图中可以看到
所以
正交阵U行(列)向量之间都是单位正交向量。上面求得的是一个旋转矩阵,它对向量做旋转变换!也许你会有疑问:刚才不是说向量空间位置不变吗?怎么现在又说它被旋转了?对的,这两个并没有冲突,说空间位置不变是绝对的,但是坐标是相对的,加入你站在e1上看OA,随着e1旋转到e1',看OA的位置就会改变。如下图:
如图,如果我选择了e1'、e2'作为新的标准坐标系,那么在新坐标系中OA(原标准坐标系的表示)就变成了OA',这样看来就好像坐标系不动,把OA往顺时针方向旋转了“斯塔”角度,这个操作实现起来很简单:将变换后的向量坐标仍然表示在当前坐标系中。
旋转变换是正交变换的一个方面,这个挺有用的,比如在开发中需要实现某种旋转效果,直接可以用旋转变换实现。正交变换的另一个方面是反射变换,也即e1'的方向与图中方向相反,这个不再讨论。
总结:正交矩阵的行(列)向量都是两两正交的单位向量,正交矩阵对应的变换为正交变换,它有两种表现:旋转和反射。正交矩阵将标准正交基映射为标准正交基(即图中从e1、e2到e1'、e2')
特征值分解——EVD
对应的单位特征向量为
则有
进而
所以可得到A的特征值分解(由于对称阵特征向量两两正交,所以U为正交阵,正交阵的逆矩阵等于其转置)
这里假设A有m个不同的特征值,实际上,只要A是对称阵其均有如上分解。
矩阵A分解了,相应的,其对应的映射也分解为三个映射。现在假设有x向量,用A将其变换到A的列空间中,那么首先由U'先对x做变换:
U是正交阵U'也是正交阵,所以U'对x的变换是正交变换,它将x用新的坐标系来表示,这个坐标系就是A的所有正交的特征向量构成的坐标系。比如将x用A的所有特征向量表示为:
则通过第一个变换就可以把x表示为[a1 a2 ... am]':
紧接着,在新的坐标系表示下,由中间那个对角矩阵对新的向量坐标换,其结果就是将向量往各个轴方向拉伸或压缩:
从上图可以看到,如果A不是满秩的话,那么就是说对角阵的对角线上元素存在0,这时候就会导致维度退化,这样就会使映射后的向量落入m维空间的子空间中。
最后一个变换就是U对拉伸或压缩后的向量做变换,由于U和U'是互为逆矩阵,所以U变换是U'变换的逆变换。
因此,从对称阵的分解对应的映射分解来分析一个矩阵的变换特点是非常直观的。假设对称阵特征值全为1那么显然它就是单位阵,如果对称阵的特征值有个别是0其他全是1,那么它就是一个正交投影矩阵,它将m维向量投影到它的列空间中。
根据对称阵A的特征向量,如果A是2*2的,那么就可以在二维平面中找到这样一个矩形,是的这个矩形经过A变换后还是矩形:
这个矩形的选择就是让其边都落在A的特征向量方向上,如果选择其他矩形的话变换后的图形就不是矩形了!
奇异值分解——SVD
则A矩阵将这组基映射为:
如果要使他们两两正交,即
根据假设,存在
所以如果正交基v选择为A'A的特征向量的话,由于A'A是对称阵,v之间两两正交,那么
这样就找到了正交基使其映射后还是正交基了,现在,将映射后的正交基单位化:
因为
所以有
所以取单位向量
由此可得
当k < i <= m时,对u1,u2,...,uk进行扩展u(k+1),...,um,使得u1,u2,...,um为m维空间中的一组正交基,即
同样的,对v1,v2,...,vk进行扩展v(k+1),...,vn(这n-k个向量存在于A的零空间中,即Ax=0的解空间的基),使得v1,v2,...,vn为n维空间中的一组正交基,即
则可得到
继而可以得到A矩阵的奇异值分解:
现在可以来对A矩阵的映射过程进行分析了:如果在n维空间中找到一个(超)矩形,其边都落在A'A的特征向量的方向上,那么经过A变换后的形状仍然为(超)矩形!
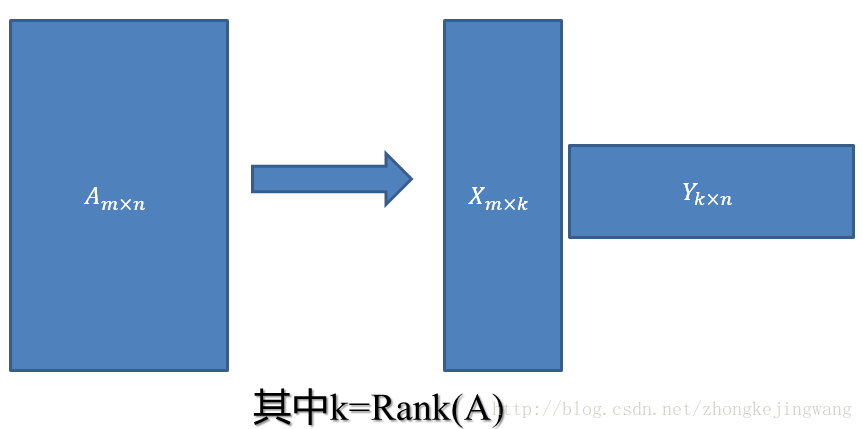
vi为A'A的特征向量,称为A的右奇异向量,ui=Avi实际上为AA'的特征向量,称为A的左奇异向量。下面利用SVD证明文章一开始的满秩分解:
利用矩阵分块乘法展开得:
可以看到第二项为0,有
令
则A=XY即是A的满秩分解。
整个SVD的推导过程就是这样,后面会介绍SVD在推荐系统中的具体应用,也就是复现Koren论文中的算法以及其推导过程。
一下是我从别人博客转载过来的,分析的特别好
首先, 我们定义样本和特征, 假定有 m 个样本, 每个样本有 n 个特征, 可以如下表示:
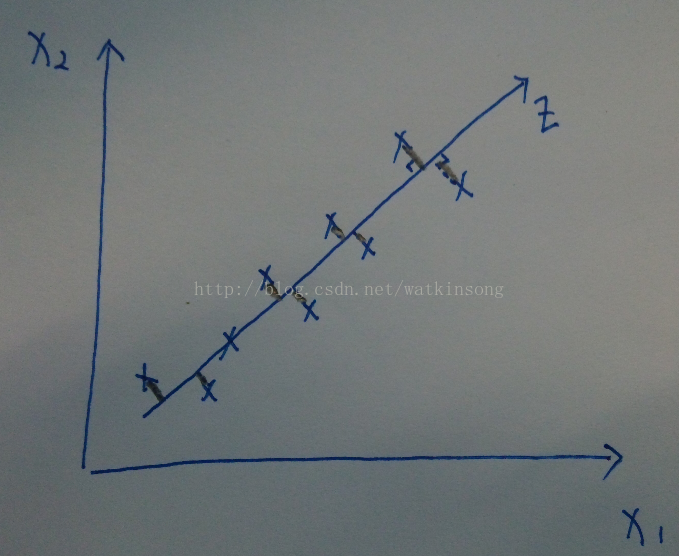
由简到难, 先看一下从2D 降维到1D的比较直观的表示:
在上图中, 假设只有两个特征x1, x2, 然后需要降维到1D, 这个时候我们可以观察途中X所表示的样本点基本上分布在一条直线上, 那么就可以将所有的用(x1, x2)平面表示的坐标映射到图像画出的直线z上, 上图中的黑色铅笔线表示样本点映射的过程。
映射到直线Z后, 如果只用直线Z表示样本的空间分布, 就可以用1个坐标表示每个样本了, 这样就将2D的特征降维到1D的特征。 同样的道理, 如果将3D的特征降维到2D, 就是将具有3D特征的样本从一个三维空间中映射到二维空间。
在上图中, 将所有的二维特征的样本点映射到了一维直线上, 这样, 从上图中可以看出在映射的过程中存在映射误差。
在上图中, 用圆圈表示了样本映射后的坐标位置。这些位置可以叫做近似位置, 以后还要用到这些位置计算映射误差。
因为在降维映射的过程中, 存在映射误差, 所有在对高维特征降维之前, 需要做特征归一化(feature normalization), 这个归一化操作包括: (1) feature scaling (让所有的特征拥有相似的尺度, 要不然一个特征特别小, 一个特征特别大会影响降维的效果) (2) zero mean normalization (零均值归一化)。
在上图中, 也可以把降维的过程看作找到一个或者多个向量u1, u2, ...., un, 使得这些向量构成一个新的向量空间(需要学习矩阵分析哦), 然后把需要降维的样本映射到这个新的样本空间上。
对于2D -> 1D 的降维过程, 可以理解为找到一个向量u1, u1表示了一个方向, 然后将所有的样本映射到这个方向上, 其实, 一个向量也可以表示一个样本空间。
对于3D -> 2D 的降维过程, 可以理解为找到两个向量u1, u2, (u1, u2) 这两个向量定义了一个新的特征空间, 然后将原样本空间的样本映射到新的样本空间。
对于n-D -> k-D 的降维过程, 可以理解为找到 k 个向量 u1, u2, ..., uk, 这k个向量定义了新的向量空间, 然后进行样本映射。
3.2 Cost Function
既然样本映射存在误差, 就需要计算每次映射的误差大小。 采用以下公式计算误差大小:
X-approx表示的是样本映射以后的新的坐标, 这个坐标如果位置如果用当前的样本空间表示, 维度和 样本X是一致的。
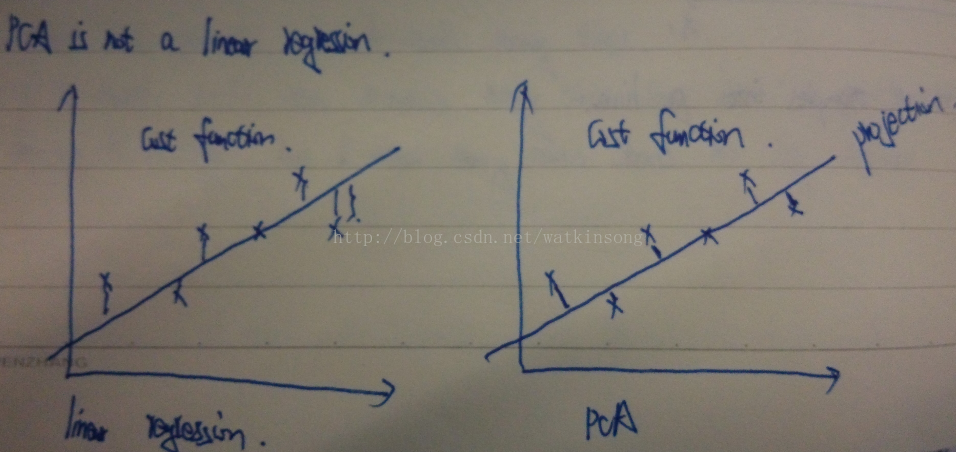
要特别注意, PCA降维和linear regression是不一样的, 虽然看上去很一致, 但是linear regression的cost function的计算是样本上线垂直的到拟合线的距离, 而PCA的cost function 是样本点到拟合线的垂直距离。 差别如下图所示:
3.3 PCA 计算过程
(A) Feature Normalization
- function [X_norm, mu, sigma] = featureNormalize(X)
- %FEATURENORMALIZE Normalizes the features in X
- % FEATURENORMALIZE(X) returns a normalized version of X where
- % the mean value of each feature is 0 and the standard deviation
- % is 1. This is often a good preprocessing step to do when
- % working with learning algorithms.
- mu = mean(X);
- X_norm = bsxfun(@minus, X, mu);
- sigma = std(X_norm);
- X_norm = bsxfun(@rdivide, X_norm, sigma);
- % ============================================================
- end
注意: 这里的X是一个m * n 的矩阵, 有 m 个样本, 每个样本包含 n 个特征, 每一行表示一个样本。 X_norm是最终得到的特征, 首先计算了所有训练样本每个特征的均值, 然后减去均值, 然后除以标准差。
(B) 计算降维矩阵



3.4 贡献率 (降维的k的值的选择)
在 http://blog.csdn.net/watkinsong/article/details/8234766 这篇文章中, 很多人问了关于贡献率的问题, 这就是相当于选择k的值的大小。 也就是选择降维矩阵 U 中的特征向量的个数。


- %% Initialization
- clear ; close all; clc
- fprintf('this code will load 12 images and do PCA for each face.\n');
- fprintf('10 images are used to train PCA and the other 2 images are used to test PCA.\n');
- m = 4000; % number of samples
- trainset = zeros(m, 32 * 32); % image size is : 32 * 32
- for i = 1 : m
- img = imread(strcat('./img/', int2str(i), '.bmp'));
- img = double(img);
- trainset(i, :) = img(:);
- end
- %% before training PCA, do feature normalization
- mu = mean(trainset);
- trainset_norm = bsxfun(@minus, trainset, mu);
- sigma = std(trainset_norm);
- trainset_norm = bsxfun(@rdivide, trainset_norm, sigma);
- %% we could save the mean face mu to take a look the mean face
- imwrite(uint8(reshape(mu, 32, 32)), 'meanface.bmp');
- fprintf('mean face saved. paused\n');
- pause;
- %% compute reduce matrix
- X = trainset_norm; % just for convience
- [m, n] = size(X);
- U = zeros(n);
- S = zeros(n);
- Cov = 1 / m * X' * X;
- [U, S, V] = svd(Cov);
- fprintf('compute cov done.\n');
- %% save eigen face
- for i = 1:10
- ef = U(:, i)';
- img = ef;
- minVal = min(img);
- img = img - minVal;
- max_val = max(abs(img));
- img = img / max_val;
- img = reshape(img, 32, 32);
- imwrite(img, strcat('eigenface', int2str(i), '.bmp'));
- end
- fprintf('eigen face saved, paused.\n');
- pause;
- %% dimension reduction
- k = 100; % reduce to 100 dimension
- test = zeros(10, 32 * 32);
- for i = 4001:4010
- img = imread(strcat('./img/', int2str(i), '.bmp'));
- img = double(img);
- test(i - 4000, :) = img(:);
- end
- % test set need to do normalization
- test = bsxfun(@minus, test, mu);
- % reduction
- Uk = U(:, 1:k);
- Z = test * Uk;
- fprintf('reduce done.\n');
- %% reconstruction
- %% for the test set images, we only minus the mean face,
- % so in the reconstruct process, we need add the mean face back
- Xp = Z * Uk';
- % show reconstructed face
- for i = 1:5
- face = Xp(i, :) + mu;
- face = reshape((face), 32, 32);
- imwrite(uint8(face), strcat('./reconstruct/', int2str(4000 + i), '.bmp'));
- end
- %% for the train set reconstruction, we minus the mean face and divide by standard deviation during the train
- % so in the reconstruction process, we need to multiby standard deviation first,
- % and then add the mean face back
- trainset_re = trainset_norm * Uk; % reduction
- trainset_re = trainset_re * Uk'; % reconstruction
- for i = 1:5
- train = trainset_re(i, :);
- train = train .* sigma;
- train = train + mu;
- train = reshape(train, 32, 32);
- imwrite(uint8(train), strcat('./reconstruct/', int2str(i), 'train.bmp'));
- end
- fprintf('job done.\n');








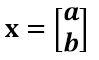
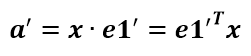
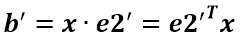
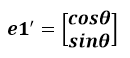
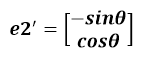
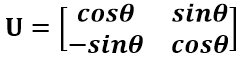
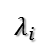
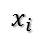
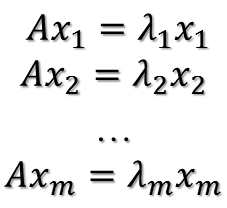
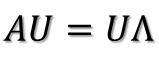
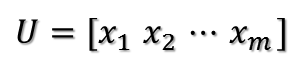
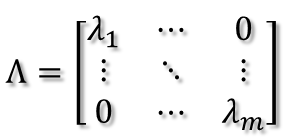
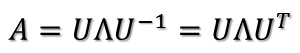
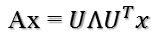
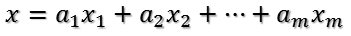
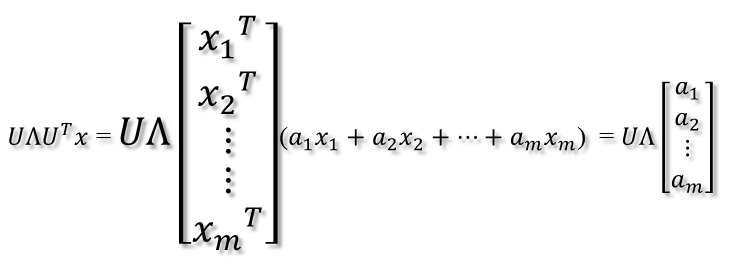
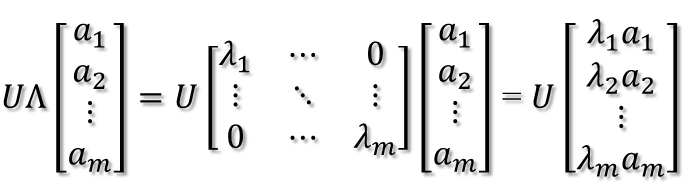
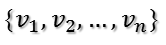
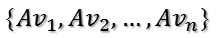
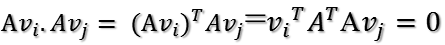
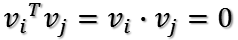
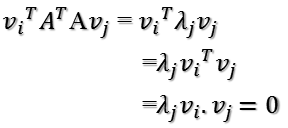
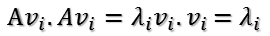
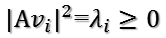
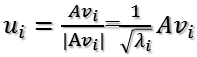
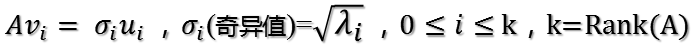
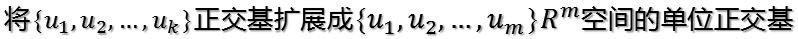
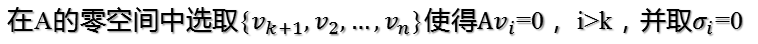
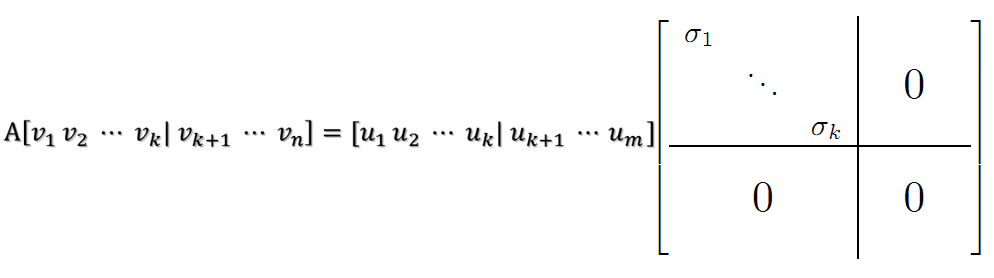
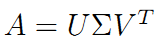
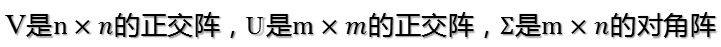
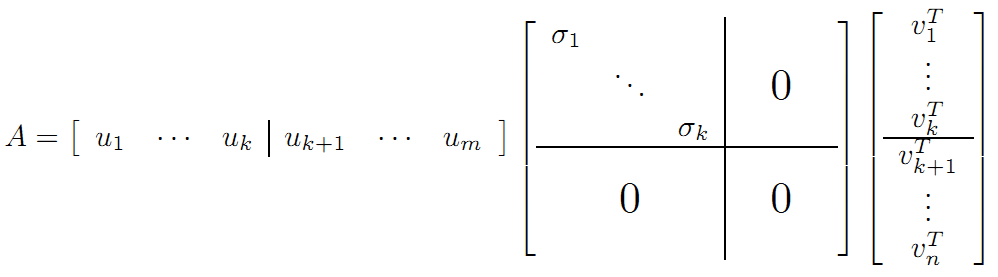
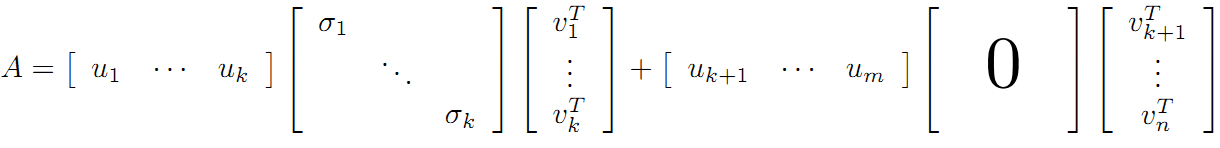
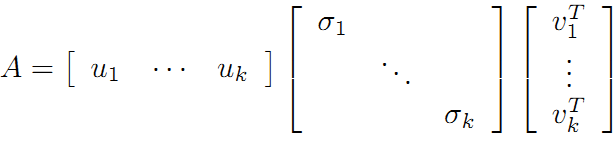
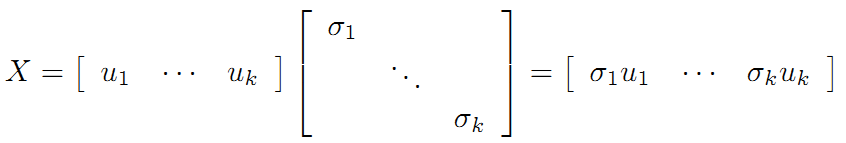
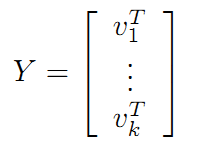

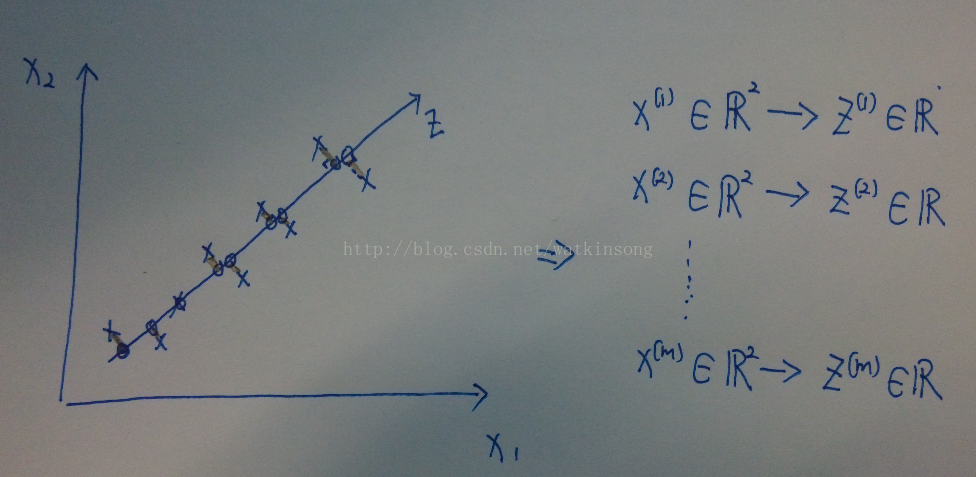















 2617
2617

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








