实操 | 合并VCF文件的几种方法及注意事项
多款软件进行vcf合并-gatk、vcftools、bcftools
Import all genotype data from the 1000 genome project
本文系在尝试使用GATK 两种合并 1000G不同染色体位置的VCF文件未果后,尝试使用vcftools解决,
在此过程中所面临的安装python第三方库 variant_tools遇到的一系列问题
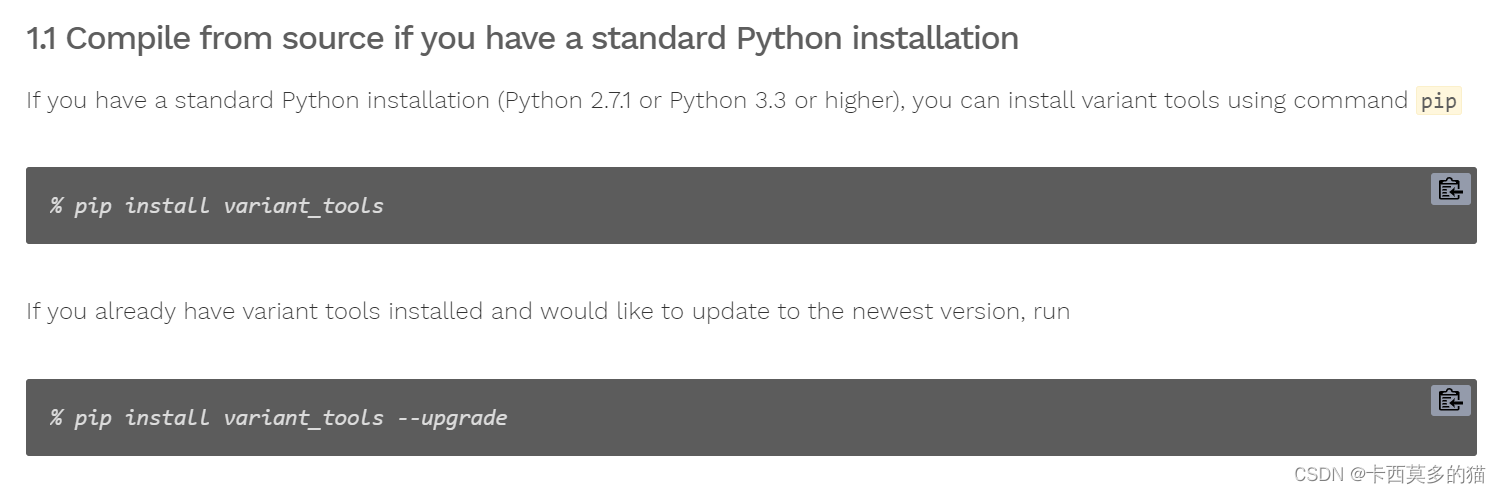
首先在本地进行安装测试,
发现通过pycharm直接在工作环境中安装报错
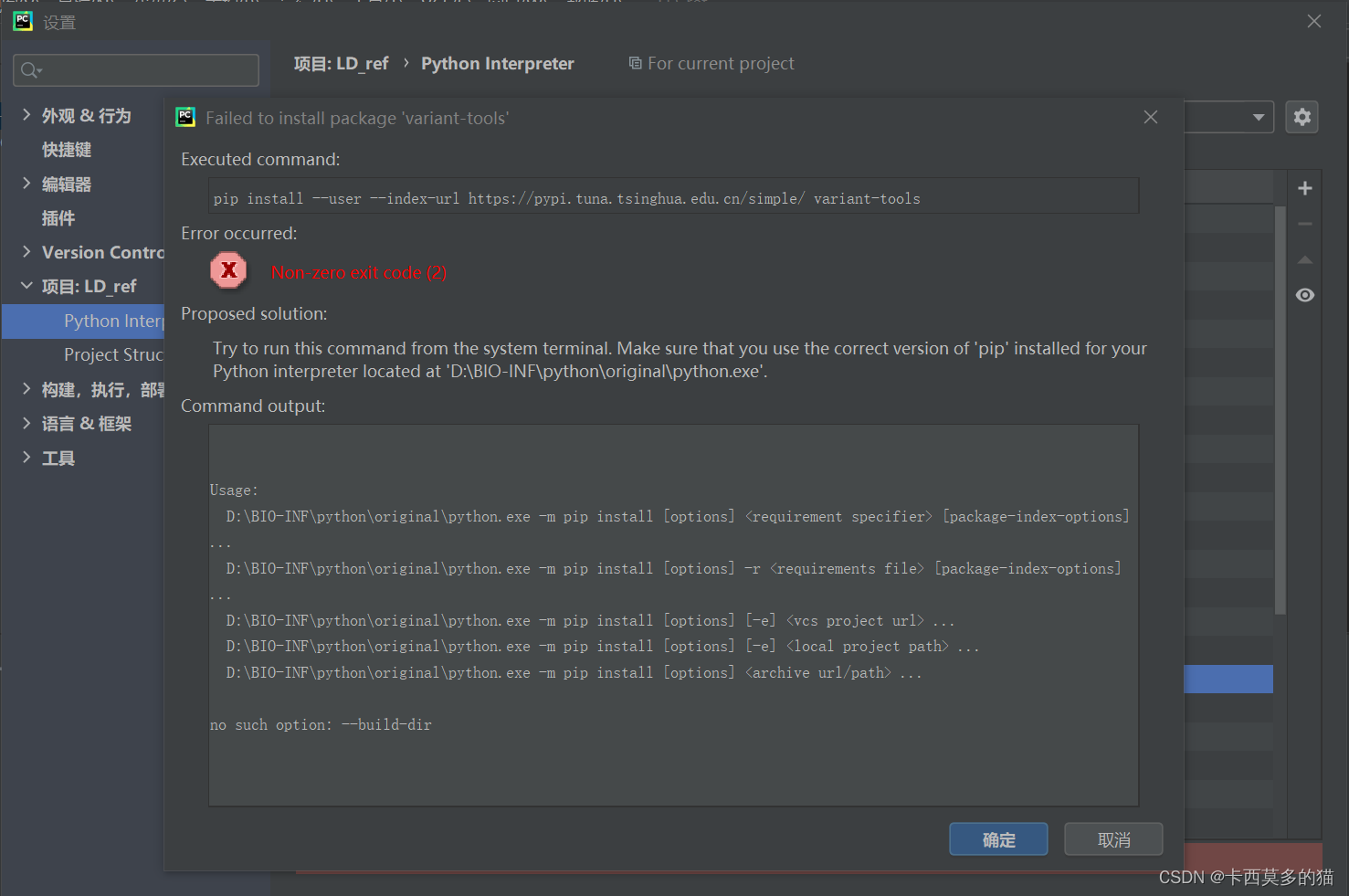
后阅读博客
发现可能是当前工作环境中pip版本或是否存在的问题,
此报错在我日常本地工作时也遇到过,但都可通过在终端安装解决
考虑到最后在服务器上安装,所以在未从此角度对问题进行探索
在终端安装时,出现了之前本地工作不存在的报错
D:\BIO-INF\毕设project\LD_ref>pip install variant_tools
Looking in indexes: https://pypi.tuna.tsinghua.edu.cn/simple
Collecting variant_tools
Using cached https://pypi.tuna.tsinghua.edu.cn/packages/b1/2c/0d52fe61b5e9915cde9894ec2bc853f5225ff86354a4474f192b65904fa9/variant_tools-3.1.3.tar.gz (3.
0 MB)
Preparing metadata (setup.py) ... error
error: subprocess-exited-with-error 👈
× python setup.py egg_info did not run successfully.
│ exit code: 1
╰─> [6 lines of output]
Traceback (most recent call last):
File "<string>", line 36, in <module>
File "<pip-setuptools-caller>", line 34, in <module>
File "C:\Users\18369\AppData\Local\Temp\pip-install-ihlfstdx\variant-tools_377f3ed474314b19a30d1d4fddc577e4\setup.py", line 27, in <module>
from Cython.Build import cythonize
ModuleNotFoundError: No module named 'Cython'👈
[end of output]
note: This error originates from a subprocess, and is likely not a problem with pip.
error: metadata-generation-failed
× Encountered error while generating package metadata.
╰─> See above for output.
note: This is an issue with the package mentioned above, not pip.
hint: See above for details.
error: subprocess-exited-with-error
首先尝试从此处入手解决,查到此博客
但是对所提供的解决办法都进行了尝试,都未解决

(第三条对其他日常安装有参考价值)
其中第三种将git clone到本地,报错
C:\Users\18369>pip install -e varianttools
Looking in indexes: https://pypi.tuna.tsinghua.edu.cn/simple
Obtaining file:///C:/Users/18369/varianttools # clone到本地的git
Preparing metadata (setup.py) ... error
error: subprocess-exited-with-error
× python setup.py egg_info did not run successfully.👈
│ exit code: 1
╰─> [6 lines of output]
Traceback (most recent call last):
File "<string>", line 36, in <module>
File "<pip-setuptools-caller>", line 34, in <module>
File "C:\Users\18369\varianttools\setup.py", line 27, in <module>
from Cython.Build import cythonize
ModuleNotFoundError: No module named 'Cython'
[end of output]
note: This error originates from a subprocess, and is likely not a problem with pip.
error: metadata-generation-failed
× Encountered error while generating package metadata.
╰─> See above for output.
note: This is an issue with the package mentioned above, not pip.
hint: See above for details.
ModuleNotFoundError: No module named ‘Cython’
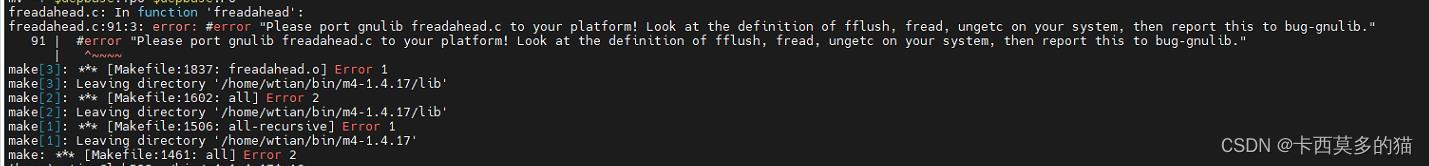
尝试从此入手,发现可能存在本地无所需module的情况
再加上博客
× python setup.py egg_info did not run successfully.
所提到的gcc版本问题
尝试自行安装gcc到非root账号家目录下
根据博客Linux环境下非root用户安装GCC
仍未果
回到软件网站寻找其它安装方式
尝试通过conda下载
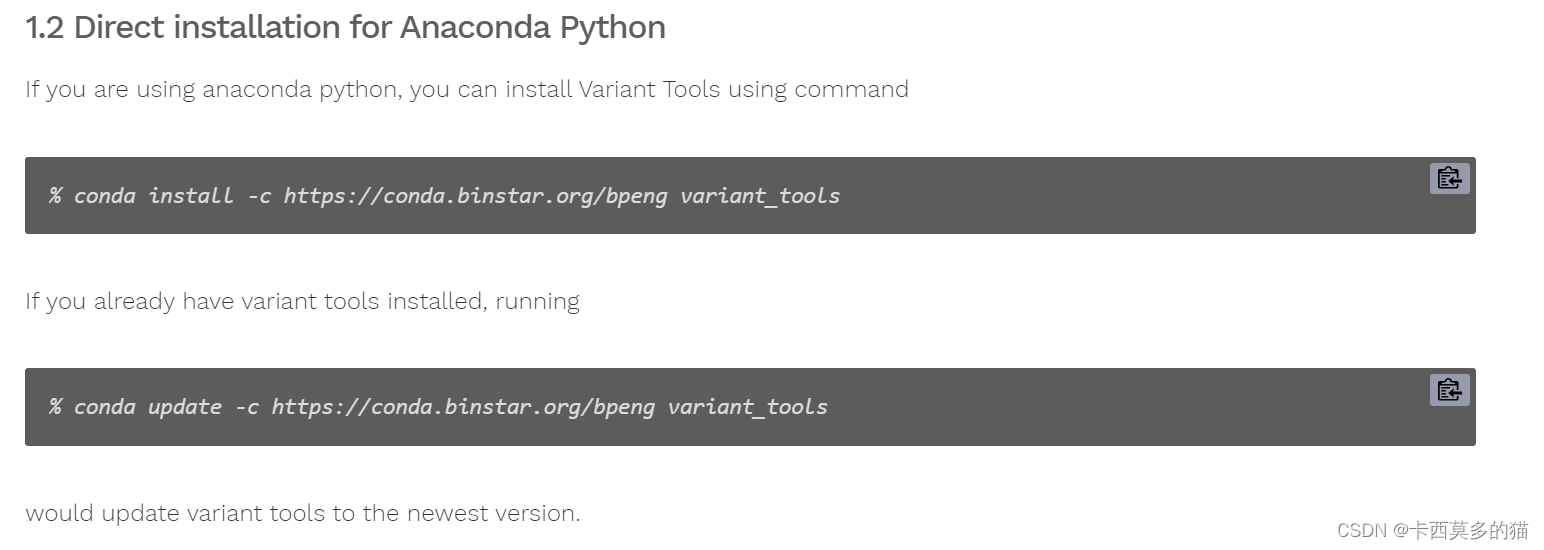
channel报错,怀疑是未添加channel的原因(未进行尝试添加bpeng)
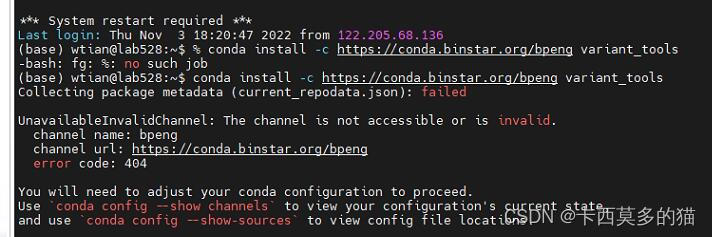
通过conda.org直接进行检索

发现bpeng/ 对应的官网时之前的文件网站
在文件网站中存在此说明

所指向的github与下载量最多的binconda/ 下包地址相同
判断为同一第三方库
conda优势
自动寻找compatible
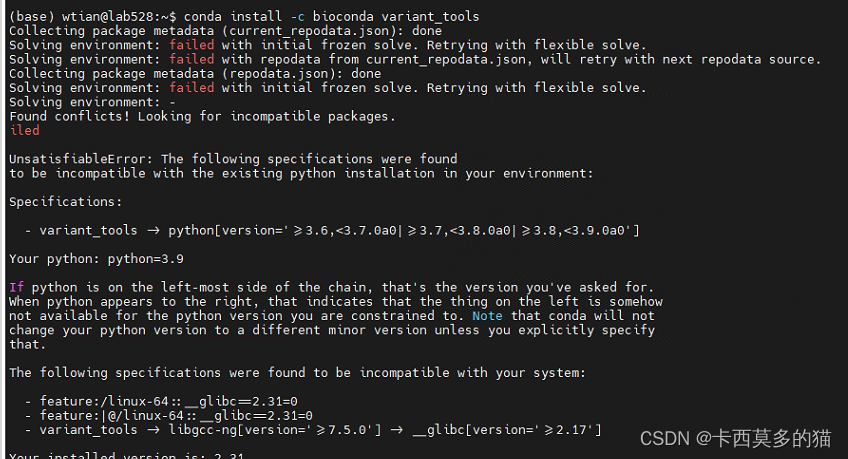
summary:
①文件官网
②GitHub
③conda
或者
查看
/usr/bin中存不存在
最终发现可能自己安装的这个过程还是没有完成
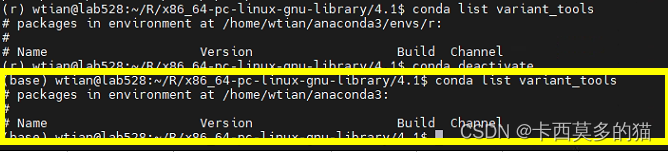
(在base环境下对python包进行安装的)
联系结果
猜测和已存在有关
但仍不知为何最终以命令行(软件)形式出现

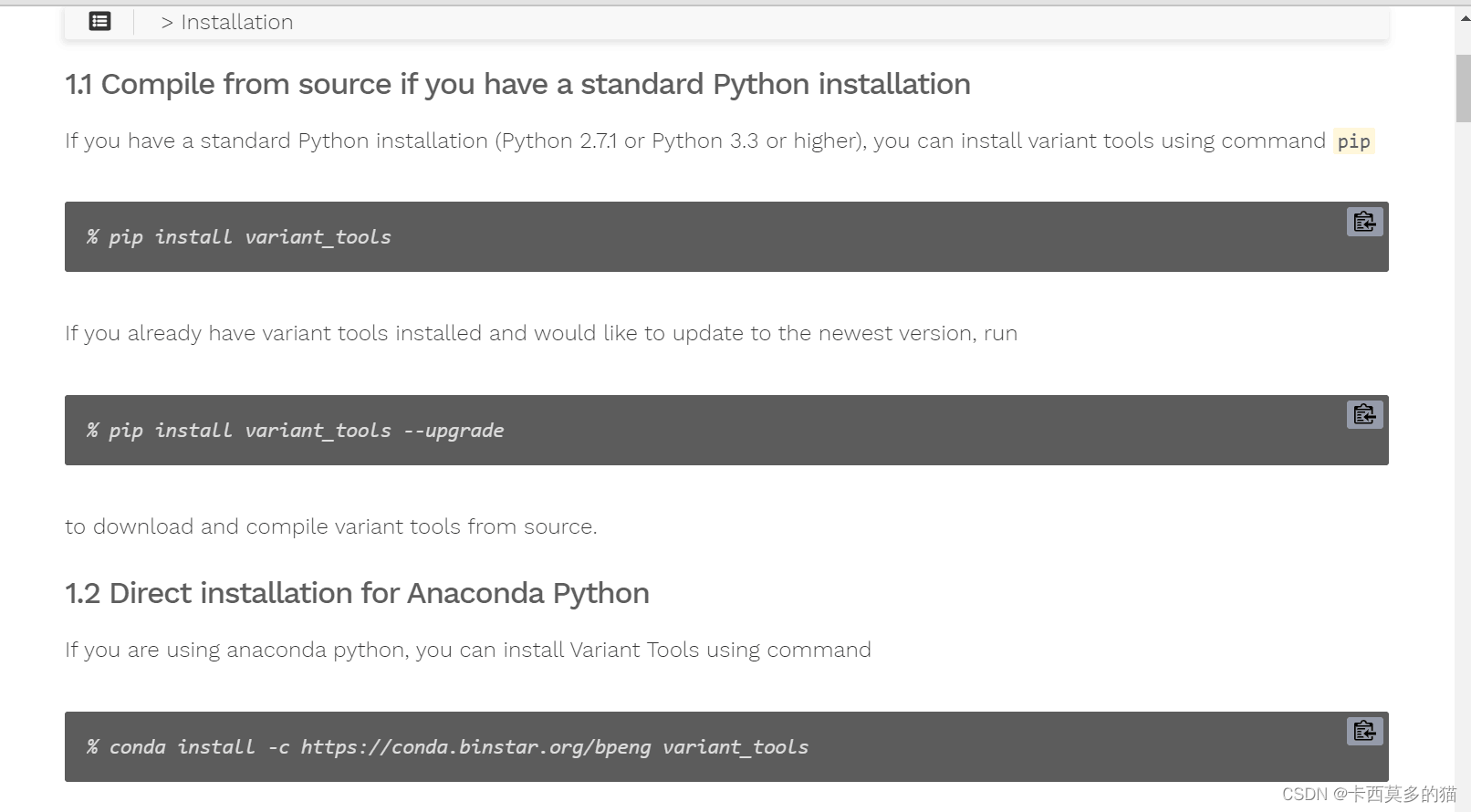
可仔细研读文件网站说明





















 3917
3917











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








