
2019年7月发表的PNAS文章:

https://www.pnas.org/content/pnas/116/37/18561.full.pdf
附件:
https://www.pnas.org/content/pnas/suppl/2019/08/23/1905221116.DCSupplemental/pnas.1905221116.sapp.pdf
对于使用数据和方法的描述:
Normalized RNA-seq data for genes MIR-199 and CDK2 were retrieved from HTSeq FPKM-UQ (Fragments Per Kilobase of transcript per Million mapped reads Upper Quartile) from The Cancer Genome Atlas (TCGA) RNA-seq data from NCI's Genomic Data Commons (GDC). Pearson correlation coefficiency and p-value between MIR-199 and CDK2 in each cancer type were calculated using log2 transformed FPKM-UQ data.
如上文所述,你看到的是MIR-199,但图中显示的是hsa-miRNA-199a-1(下图左)和miRNA-199a-2(下图右):
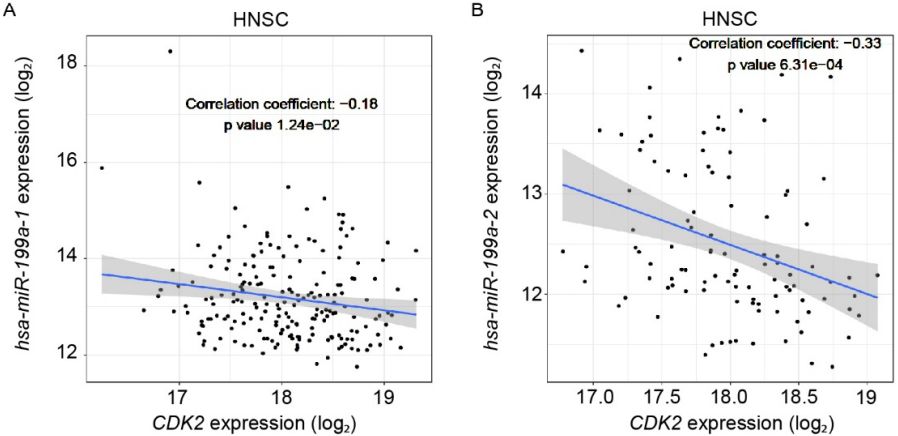
玄机在哪?是不是作者没明说,但是又暗自下载了 [成熟体miRNA表达数据] ?
小编尝试了,答案不是!
那么,这个数据是怎么来的呢?
经过长年累月的 [数据虐我千百遍] 小编现在已经练就了一身侦察推理的本领。
我们以左图为例进行绘制,最终得到的结果如下:
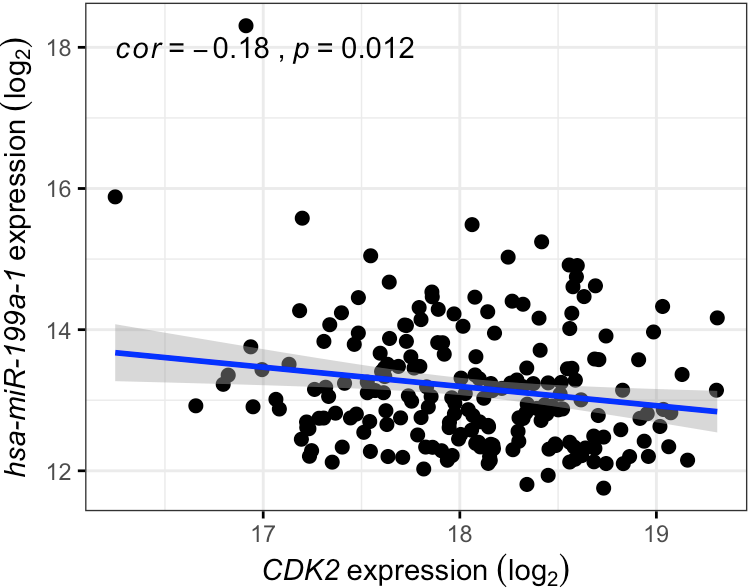
虽然费了一番功夫,但是统计结果完全一致,就连图中点的分布都一样,就连坐标名斜体都考虑了,除了我个人觉得上图中的统计结果展示更简洁有效。看到出图的那一刻,舒适感呲呲往外冒...
嗯
以后的相关性分析就跟着PNAS做了
不担心有问题!
文章、代码和数据已为大家备好:

领取方法:
将本文转发朋友圈,或超过80人相关医学群,截图给小编(文末添加二维码)即可领取!
 如果大家有分析绘图需求,欢迎来扰
如果大家有分析绘图需求,欢迎来扰
数据挖掘系列·往期精彩
数据挖掘 | 搞定TCGA批次效应!?
数据挖掘 | CELL证实了我的发现,巴适!
相煎何太急 https://www...
数据挖掘 | KEGG通路与基因的对应关系
数据挖掘 | C-index的概念和计算
数据挖掘 | 赶紧丢掉你手里的edgeR分析脚本
数据挖掘 | 快速实现生存分析森林图
数据挖掘 | TCGA数据库RNA表达数据整理
数据挖掘 | 被忽视的PPI蛋白互作网络
数据挖掘 | cBioPortal请慎用!!
数据挖掘 | TCGA数据挖掘如何入门?
太多了,不粘了,多看历史...





















 2825
2825











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








