关注公众号,点击加群,群中有系列代码推荐、前沿会议、各种科研资料分享交流(为防止一些广告微信的加入,请大家一定备注好加单细胞群 学校/单位+ 研究方向 )

文献来源
Chu, Y. and E. Dai, et al. (2023). "Pan-cancer T cell atlas links a cellular stress response state to immunotherapy resistance." Nature medicine 29(6): 1550-1562.

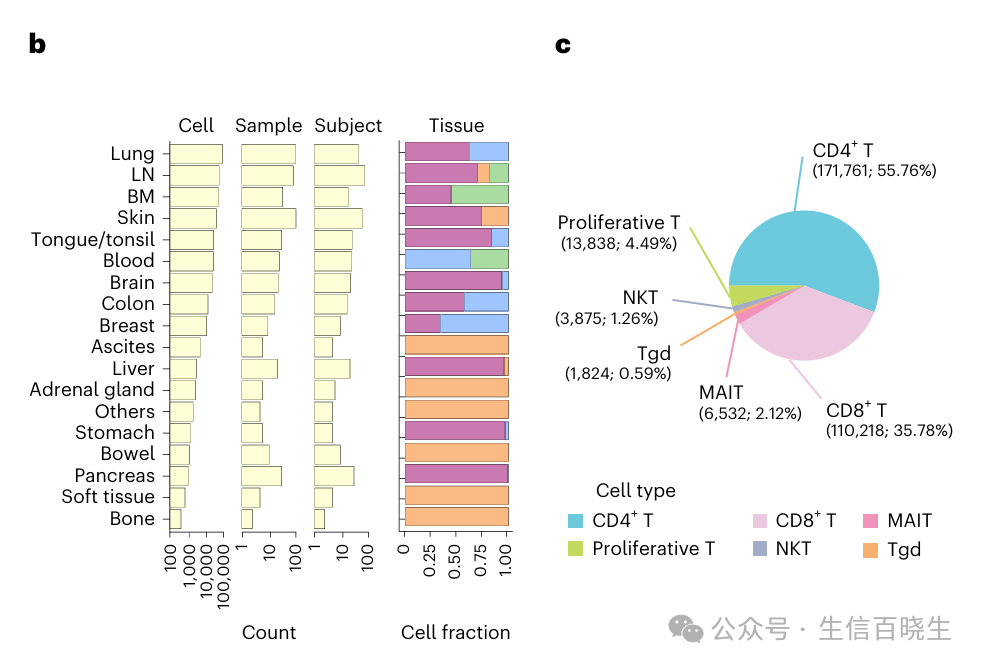
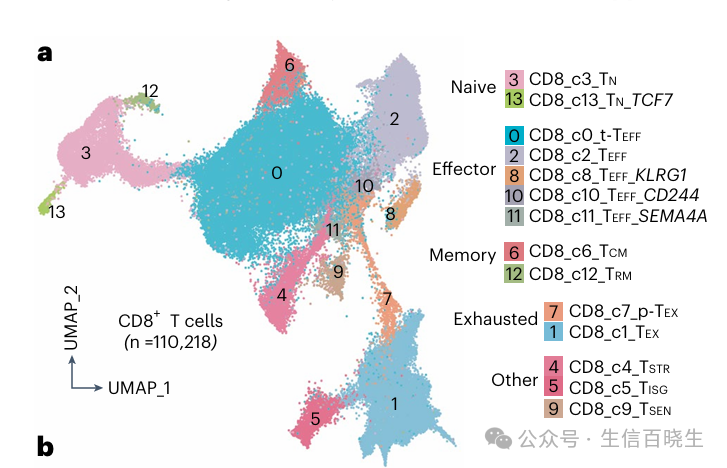
肿瘤浸润性T细胞为癌症治疗提供了一条很有希望的途径,但它们的状态仍有待充分表征。在这里,我们展示了来自16种癌症类型的308,048个转录本的T细胞的单细胞图谱,揭示了以前未描述的T细胞状态和不同亚群的滤泡辅助T细胞、调节T细胞和增殖T细胞。我们确定了一种独特的应激反应状态,TSTR,以热休克基因表达为特征。在各种癌症类型的肿瘤微环境中,TSTR细胞都可被原位检测到,主要位于肿瘤床或周围肿瘤边缘的淋巴细胞聚集体或潜在的三级淋巴样结构中。在23个队列的375名患者中,包括171名接受免疫检查点阻断治疗的患者,T细胞状态/组成与基因组、病理和临床特征相关。我们还发现,免疫检查点阻断治疗后,肿瘤内的CD4/CD8+细胞中热休克基因的表达显著上调,特别是在无反应的肿瘤中,这表明TSTR细胞在免疫治疗抵抗中可能发挥作用。我们注释良好的T细胞参考图、网络门户和自动比对/注释工具可以为T细胞治疗优化和生物标记物发现提供有价值的资源。
code
The R script TCellMap is available at GitHub (https://github.com/ Coolgenome/TCM).
-
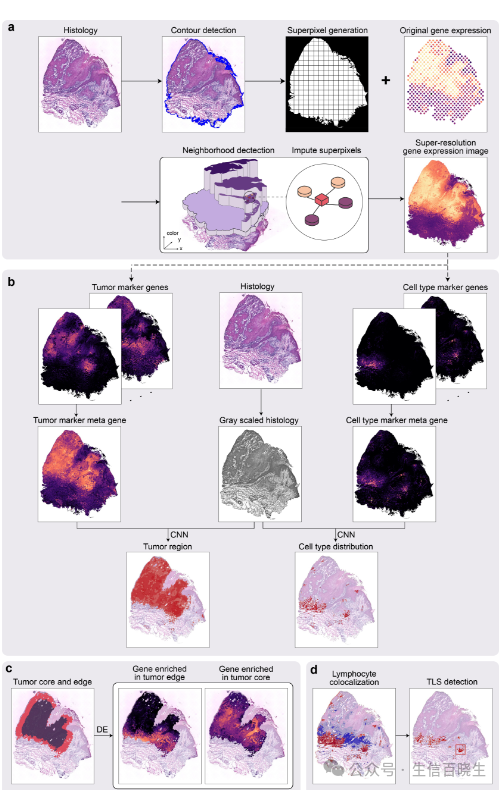
An open-source implementation of the TESLA algorithm in Python can be downloaded from https://github.com/ jianhuupenn/TESLA.
-
The custom script used to overlay the spatial loca tions of the hypoxia signal and TSTR cells on the same histology image is available at GitHub (https://github.com/Coolgenome/TCM/blob/main/ res_largerT.py#L230).
-
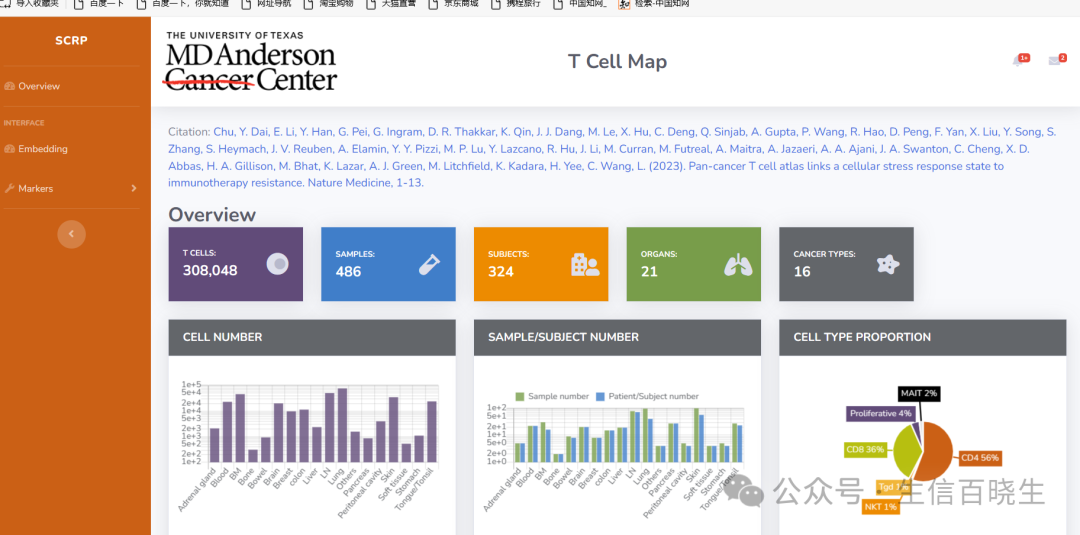
Additionally, we have built a user-friendly and interactive online data portal, the SCRP (https://singlecell.mdander son.org/),
-
for visualizing scRNA-seq data. All scRNA-seq data used to build T cell reference maps in this study can be visualized via the SCRP and queried at https://singlecell.mdanderson.org/TCM/.
https://github.com/Coolgenome/TCM
TESLA: Deciphering tumor ecosystems at super-resolution from spatial transcriptomics
https://github.com/jianhuupenn/TESLA
https://singlecell.mdanderson.org/TCM/

























 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








