最近在研究支持向量机,这里转载几篇由ChenLee_1大神写的LIBSVM的使用方法。
原文请见:
http://blog.csdn.net/carson2005/article/details/6527055
http://blog.csdn.net/carson2005/article/details/6539192
http://blog.csdn.net/carson2005/article/details/6539218
libSVM是台湾大学林智仁教授等研究人员开发的一个用于支持向量机分类,回归分析及分布估计的c/c++开源库。另外,它也可以用于解决多类分类问题。 libSVM最新的版本是2011年4月发布的3.1版。林智仁教授设计开发该SVM库的目的是为了让其它非专业人士可以更加方便快捷的使用SVM这个统计学习工具。libSVM提供了一些简单易用的接口,从而使得用户可以方便的使用,而不必关心其内部复杂的数学模型和运算过程。libSVM的主要特点有:
(1)各种SVM的表达公式;
(2)有效的多类分类能力;
(3)交叉验证功能;
(4)各种核函数,包括预先计算得到的核矩阵;
(5)用于非平衡数据的加权svm;
(6)提供c++和java源代码;
(7)用于演示SVM分类与回归能力的GUI界面;
.....
很多初学者往往按照以下的步骤使用libSVM:
(1)将数据转换到libSVM指定的格式;
(2)随机选择一个核函数和一些参数;
(3)测试;
这种方法虽然可行,但却不一定能很快达到好的效果。为此,林智仁教授推荐按照以下的步骤来使用libSVM:
(1)将数据转换到libSVM指定的格式;
(2)对数据进行尺度操作(一般指数据的归一化);
(3)考虑RBF(径向基)核函数;
(4)利用交叉验证来得到最好的参数C和r;
(5)用最好的C和r来训练所有训练集合;
(6)测试;
之所以推荐首选径向基核函数,是由于该核可以将数据非线性地映射到高维空间,而且,它还能处理那种特征(数据)及其属性之间呈现非线性关系的情况,而线性核函数只是径向基核函数的一个特例。另外,相比而言,多项式核函数在高维空间有着更多的参数,从而使得模型更加复杂。同时,需要提醒的是,径向基核函数并非万能的,尤其当特征数据的数值本身比较大的时候,线性核函数要更实用一些。
任何人可以在http://www.csie.ntu.edu.tw/~cjlin/libsvm 来下载libSVM开源库。不过,按照开发者的要求,在使用之前,请务必阅读其copyright,并按照其要求进行相应的引用和说明。另外,在使用之前,强烈推荐大家阅读libSVM.zip里面的readme文件。该文件详细描述了libSVM的使用方法及注意事项。
鉴于libSVM中的readme文件有点长,而且,都是采用英文书写,这里,我把其中重要的内容提炼出来,并给出相应的例子来说明其用法,大家可以直接参考我的代码来调用libSVM库。
第一部分,利用libSVM自带的简易工具来演示SVM的两类分类过程。(以下内容只是利用libSVM自带的一个简易的工具供大家更好的理解SVM,如果你对SVM已经有了一定的了解,可以直接跳过这部分内容)
首先,你要了解的是libSVM只是众多SVM实现版本中的其中之一。而SVM是一种进行两类分类的分类器,在libSVM最新版(libSVM3.1)里面,已经自带了简单的工具,可以对二分类进行演示。以windows平台为例,将libSVM.zip解压之后,有一个名为windows的子文件夹,里面有一个名为svm-toy.exe的可执行文件。直接双击,运行该可执行文件,显示如下的界面
点击第二个按钮“Run”,然后,在左上部分,用鼠标左键随机点几下,代表你选择的第一类模式的数据分布,下图是我随即点了几下的结果:

之后,点击“Change”,接着,用鼠标左键在窗口右下方随便点击几下,代表你选择的第二类模式的数据分布,如下图所示:
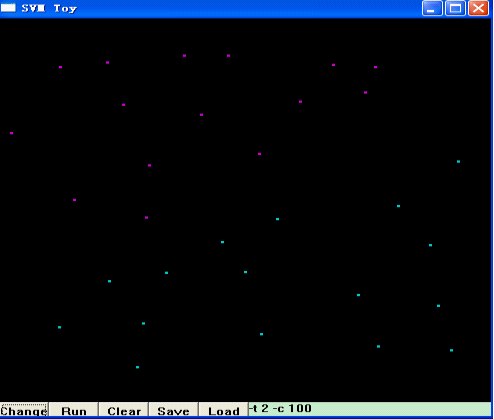
接着,点击“Run”,libSVM就帮你把这两类模式分开了,并用两种不同的颜色区域来代表两类不同的模式,如下图所示:

图中左上方紫色的区域,是第一类模式所在的区域,右下方的蓝色区域,是你选择的第二类模式所在的的区域,而两者的分界面,也就是SVM的最优分类面。当然,SVM是通过核函数将原始数据映射到高维空间,在高维空间进行线性分类。换句话说,在高维空间,这两类数据应该是线性可分的,即:最优分类面应该是一条直线,而这里看到的,是将高维空间分类的结果又映射回原始空间所呈现的分类结果,即:非线性的分类面。细心的朋友可能已经发现,在上述界面的右下角,有一个编辑框,里面写着“-t 2 -c 100”,显然,这是libSVM的一些参数,你也可以试着更改这些参数,来选择不同的核函数、不同的SVM类型等来达到最好的分类效果。
第二部分:libSVM中的小工具
libSVM中包含以下可执行程序文件(小工具):
(1)svm-scale:一个用于对输入数据进行归一化的简易工具
(2)svm-toy:一个带有图形界面的交互式SVM二分类功能演示小工具;
(3)svm-train:对用户输入的数据进行SVM训练。其中,训练数据是按照以下格式输入的:
<类别号> <索引1>:<特征值1> <索引2>:<特征值2>...
(4)svm-predict:根据SVM训练得到的模型,对输入数据进行预测,即分类。
第三部分:libSVM用法介绍:`
libSVM的所有函数申明及结构体定义均包含在libSVM.h文件当中,在使用过程中,你必须要包含该头文件,并且,对libSVM.cpp进行相应的链接。在对libSVM中的函数用法进行详细介绍之前,我们不妨先简单了解一下libSVM.h中一些结构体的含义。
struct svm_node
{
int index;
double value;
};
该结构体,定义了一个“SVM节点”,即:索引i及其所对应的第i个特征值。这样n个相同类别号的SVM节点,就构成了一个SVM输入向量。即:一个SVM输入向量可以表示为如下的形式:
类别标签 索引1:特征值1 索引2:特征值2 索引3:特征值3...
我们可以将若干个这样的输入向量输入到libSVM进行训练,或者,输入一个类别标签未知的向量对其进行预测。
struct svm_problem
{
int l;
double *y;
struct svm_node **x;
};
该结构体中的l代表训练样本的个数;double型指针y代表l个训练样本中每个训练样本的类别号,也就是我们常说的“标签”;而"SVM节点"x,则是一个指针的指针(如果你对指针的指针不熟悉,完全可以把x理解为一个矩阵),x所指向的内容就是所有训练样本所有的特征值数据。
假如我们有下面的训练样本数据:
类别标签 特征值1 特征值2 特征值3 特征值4 特征值5
1 0 0.1 0.2 0 0
2 0 0.1 0.3 -1.2 0
1 0.4 0 0 0 0
2 0 0.1 0 1.4 0.5
1 -0.1 -0.2 0.1 1.1 0.1
那么,svm_problem结构体中的l=5(共有5个训练样本),y=[1,2,1,2,1];指针x所指向的内容可以视为5个行向量,每个行向量有5列,即:x指代一个5*5的矩阵,其值为:
(1,0)(2,0.1)(3,0.2)(4,0)(5,0)(-1,?)
(1,0)(2,0.1)(3,0.3)(4,-1.2)(5,0)(-1,?)
(1,0.4)(2,0)(3,0)(4,0)(5,0)(-1,?)
(1,0)(2,0.1)(3,0)(4,1.4)(5,0.5)(-1,?)
(1,-0.1)(2,-0.2)(3,0.1)(4,1.1)(5,0.1)(-1,?)
需要提醒的是,这里,每一行最后一列都是以“-1”开头,这是libSVM规定的特征值向量的结束标识;此外,索引应该按照升序方式进行排列。
enum { C_SVC, NU_SVC, ONE_CLASS, EPSILON_SVR, NU_SVR };//libSVM规定的SVM类型
enum { LINEAR, POLY, RBF, SIGMOID, PRECOMPUTED };//libSVM规定的核函数的类型
struct svm_parameter
{
int svm_type;//取值为前面提到的枚举类型中的值
int kernel_type;//取值为前面提到的枚举类型中的值
int degree; //用于多项式核函数/
double gamma;//用于多项式、径向基、S型核函数
double coef0;//用于多项式和S型核函数
/* 以下参数仅仅用于训练阶段 */
double cache_size; //核缓存大小,以MB为单位
double eps; //误差精度小于eps时,停止训练
double C; //用于C_SVC,EPSILON_SVR,NU_SVR
int nr_weight; //用于C_SVC
int *weight_label;//用于C_SVC
double* weight;//用于C_SVC
double nu;//用于NU_SVC,ONE_CLASS,NU_SVR
double p;//用于EPSILON_SVR
int shrinking; //等于1代表执行启发式收缩
int probability;//等于1代表模型的分布概率已知
};
该结构体定义了libSVM中的用到的SVM参数。其中svm_type可以是C_SVC, NU_SVC, ONE_CLASS, EPSILON_SVR, NU_SVR中的任意一种,代表着SVM的类型;
C_SVC: C-SVM classification
NU_SVC: nu-SVM classification
ONE_CLASS: one-class-SVM
EPSILON_SVR: epsilon-SVM regression
NU_SVR: nu-SVM regression
kernel_type可以是LINEAR, POLY, RBF, SIGMOID中的一种,代表着核函数的类型;
LINEAR: u'*v,线性核函数;
POLY: (gamma*u'*v + coef0)^degree,多项式核函数;
RBF: exp(-gamma*|u-v|^2),径向基核函数;
SIGMOID: tanh(gamma*u'*v + coef0),S型核函数;
PRECOMPUTED: kernel values in training_set_file,自定义的核函数;
nr_weight, weight_label, and weight这三个参数用于改变某些类的惩罚因子。当输入数据不平衡,或者误分类的风险代价不对称的时候,这三个参数将会对样本训练起到非常重要的调节作用。
nr_weight是weight_label和weight的元素个数,或者称之为维数。Weight[i]与weight_label[i]之间是一一对应的,weight[i]代表着类别weight_label[i]的惩罚因子的系数是weight[i]。如果你不想设置惩罚因子,直接把nr_weight设置为0即可。
为了防止错误的参数设置,你还可以调用libSVM提供的接口函数svm_check_parameter()来对输入参数进行检查。
在使用libSVM进行分类之前,你需要通过样本学习,构建一个SVM分类模型。该分类模型也可以理解为生成一些用于分类的“数据”。当然,构建的分类模型需要保存为文件,以便后续使用。用于libSVM训练的函数,其申明如下所示:
struct svm_model *svm_train(const struct svm_problem *prob, const struct svm_parameter *param);
显然,该函数的输入,就是svm_problem结构体的prob指针所指向的内容。该结构体在前面已经介绍过,其内部,不仅包含了训练样本的个数,还包含每个训练样本的“标签”及该训练样本对应的特征数据。而svm_parameter类型的param指针则指定了libSVM所用到的诸如SVM类型,核函数类型,惩罚因子之类的参数。另外,该函数的返回值是一个svm_model结构体,该结构体的定义,在libSVM.cpp当中:
struct svm_model
{
svm_parameter param; //SVM参数设置
int nr_class; //类别数量,对于regression和ne-class SVM这两种情况,该值为2
int l; //支持向量的个数
svm_node **SV; //支持向量
double **sv_coef; //用于决策函数的支持向量系数
double *rho; //决策函数中的常数项
double *probA; // pariwise probability information
double *probB;
// for classification only
int *label; // 每个类类别标签
int *nSV; //每个类的支持向量个数
int free_sv; //如果svm_model已经通过svm_load_model创建,则该值为1;如果svm_model是通过svm_train创建的,该值为0
};
需要提醒的是,libSVM支持多类分类问题,当有k个待分类问题时,libSVM构建k*(k-1)/2种分类模型来进行分类,即:libSVM采用一对一的方式来构建多类分类器,如下所示:
1 vs 2, 1 vs 3, ..., 1 vs k, 2 vs 3, ..., 2 vs k, ..., k-1 vs k。
用户在得到SVM分类模型之后,需要将其进行保存。在这里,libSVM已经提供了相应的函数接口:
int svm_save_model(const char *model_file_name, const struct svm_model *model);
在调用训练函数之后,只需要指定保存位置,直接调用该函数,就可以进行相应的保存。
在对样本进行训练得到分类模型之后,就可以利用该分类模型对未知输入数据进行类别判断了,也就是我们常说的“预测”。用于libSVM预测的函数,其申明如下所示:
double svm_predict(const struct svm_model *model, const struct svm_node *x);
该函数的第一个参数就是利用样本训练得到的SVM分类模型,第二个参数,是输入的未知模式的特征数据,即:得到了表征某一类别的特征数据,根据这些数据,来判断它所对应的类别标签。而SVM分类模型,可以由libSVM定义的下面这个接口函数来进行加载:
struct svm_model *svm_load_model(const char *model_file_name);
此外,在使用上述函数过程中,需要对svm_model及svm_parameter申请内存,而不使用它们的时候,用户需要调用以下两个函数进行内存释放:
void svm_destroy_model(struct svm_model *model);
void svm_destroy_param(struct svm_parameter *param);
前面提到,很多人看到libSVM这么多的参数,估计要犯晕了。没关系,我之前把相关的libSVM参数已经讲解了一遍,这里,再给出libSVM的用法。如果你不想花时间去仔细研究libSVM,完全可以参照我的函数来直接调用libSVM完成你的工作。
首先是训练SVM得到模型;假设,有10个训练样本,每个训练样本,有12个特征值,即:每个训练样本的维数是12,也就是说,训练样本构成了一个10*12的矩阵(当然,所有数据应该被归一化到[-1,1]或[0,1]范围内),另外,所有训练样本,应该有一个明确的类别标签,以此来表明当前样本所属的类别。所以,完整的训练样本,应该是10*13的矩阵,这里,我们给出一个10*13的矩阵,并认为,它就是训练样本。每个训练样本是个行向量,而该矩阵的第一列则代表训练样本的“标签”。即:第一个训练样本,类别标签为“1”,第二个训练样本类别标签为“-1”。第一个训练样本的第一个特征值为0.708333,第二个特征值为1,第三个特征值为1...
double inputArr[10][13] =
{
1,0.708333,1,1,-0.320755,-0.105023,-1,1,-0.419847,-1,-0.225806,0,1,
-1,0.583333,-1,0.333333,-0.603774,1,-1,1,0.358779,-1,-0.483871,0,-1,
1,0.166667,1,-0.333333,-0.433962,-0.383562,-1,-1,0.0687023,-1,-0.903226,-1,-1,
-1,0.458333,1,1,-0.358491,-0.374429,-1,-1,-0.480916,1,-0.935484,0,-0.333333,
-1,0.875,-1,-0.333333,-0.509434,-0.347032,-1,1,-0.236641,1,-0.935484,-1,-0.333333,
-1,0.5,1,1,-0.509434,-0.767123,-1,-1,0.0534351,-1,-0.870968,-1,-1,
1,0.125,1,0.333333,-0.320755,-0.406393,1,1,0.0839695,1,-0.806452,0,-0.333333,
1,0.25,1,1,-0.698113,-0.484018,-1,1,0.0839695,1,-0.612903,0,-0.333333,
1,0.291667,1,1,-0.132075,-0.237443,-1,1,0.51145,-1,-0.612903,0,0.333333,
1,0.416667,-1,1,0.0566038,0.283105,-1,1,0.267176,-1,0.290323,0,1
};
另外,我们给出一个待分类的输入向量,并用行向量形式表示:
double testArr[]=
{
0.25,1,1,-0.226415,-0.506849,-1,-1,0.374046,-1,-0.83871,0,-1
};
下面,给出完整的SVM训练及预测程序:
#include "stdafx.h"
#include "svm.h"
#include "iostream"
#include "fstream"
using namespace std;
double inputArr[10][13] =
{
1,0.708333,1,1,-0.320755,-0.105023,-1,1,-0.419847,-1,-0.225806,0,1,
-1,0.583333,-1,0.333333,-0.603774,1,-1,1,0.358779,-1,-0.483871,0,-1,
1,0.166667,1,-0.333333,-0.433962,-0.383562,-1,-1,0.0687023,-1,-0.903226,-1,-1,
-1,0.458333,1,1,-0.358491,-0.374429,-1,-1,-0.480916,1,-0.935484,0,-0.333333,
-1,0.875,-1,-0.333333,-0.509434,-0.347032,-1,1,-0.236641,1,-0.935484,-1,-0.333333,
-1,0.5,1,1,-0.509434,-0.767123,-1,-1,0.0534351,-1,-0.870968,-1,-1,
1,0.125,1,0.333333,-0.320755,-0.406393,1,1,0.0839695,1,-0.806452,0,-0.333333,
1,0.25,1,1,-0.698113,-0.484018,-1,1,0.0839695,1,-0.612903,0,-0.333333,
1,0.291667,1,1,-0.132075,-0.237443,-1,1,0.51145,-1,-0.612903,0,0.333333,
1,0.416667,-1,1,0.0566038,0.283105,-1,1,0.267176,-1,0.290323,0,1
};
double testArr[]=
{
0.25,1,1,-0.226415,-0.506849,-1,-1,0.374046,-1,-0.83871,0,-1
};
void DefaultSvmParam(struct svm_parameter *param)
{
param->svm_type = C_SVC;
param->kernel_type = RBF;
param->degree = 3;
param->gamma = 0; // 1/num_features
param->coef0 = 0;
param->nu = 0.5;
param->cache_size = 100;
param->C = 1;
param->eps = 1e-3;
param->p = 0.1;
param->shrinking = 1;
param->probability = 0;
param->nr_weight = 0;
param->weight_label = NULL;
param->weight = NULL;
}
void SwitchForSvmParma(struct svm_parameter *param, char ch, char *strNum, int nr_fold, int cross_validation)
{
switch(ch)
{
case 's':
{
param->svm_type = atoi(strNum);
break;
}
case 't':
{
param->kernel_type = atoi(strNum);
break;
}
case 'd':
{
param->degree = atoi(strNum);
break;
}
case 'g':
{
param->gamma = atof(strNum);
break;
}
case 'r':
{
param->coef0 = atof(strNum);
break;
}
case 'n':
{
param->nu = atof(strNum);
break;
}
case 'm':
{
param->cache_size = atof(strNum);
break;
}
case 'c':
{
param->C = atof(strNum);
break;
}
case 'e':
{
param->eps = atof(strNum);
break;
}
case 'p':
{
param->p = atof(strNum);
break;
}
case 'h':
{
param->shrinking = atoi(strNum);
break;
}
case 'b':
{
param->probability = atoi(strNum);
break;
}
case 'q':
{
break;
}
case 'v':
{
cross_validation = 1;
nr_fold = atoi(strNum);
if (nr_fold < 2)
{
cout<<"nr_fold should > 2!!! file: "<<__FILE__<<" function: ";
cout<<__FUNCTION__<<" line: "<<__LINE__<<endl;
}
break;
}
case 'w':
{
++param->nr_weight;
param->weight_label = (int *)realloc(param->weight_label,sizeof(int)*param->nr_weight);
param->weight = (double *)realloc(param->weight,sizeof(double)*param->nr_weight);
param->weight_label[param->nr_weight-1] = atoi(strNum);
param->weight[param->nr_weight-1] = atof(strNum);
break;
}
default:
{
break;
}
}
}
void SetSvmParam(struct svm_parameter *param, char *str, int cross_validation, int nr_fold)
{
DefaultSvmParam(param);
cross_validation = 0;
char ch = ' ';
int strSize = strlen(str);
for (int i=0; i<strSize; i++)
{
if (str[i] == '-')
{
ch = str[i+1];
int length = 0;
for (int j=i+3; j<strSize; j++)
{
if (isdigit(str[j]))
{
length++;
}
else
{
break;
}
}
char *strNum = new char[length+1];
int index = 0;
for (int j=i+3; j<i+3+length; j++)
{
strNum[index] = str[j];
index++;
}
strNum[length] = '/0';
SwitchForSvmParma(param, ch, strNum, nr_fold, cross_validation);
delete strNum;
}
}
}
void SvmTraining(char *option)
{
struct svm_parameter param;
struct svm_problem prob;
struct svm_model *model;
struct svm_node *x_space;
int cross_validation = 0;
int nr_fold = 0;
int sampleCount = 10;
int featureDim = 12;
prob.l = sampleCount;
prob.y = new double[sampleCount];
prob.x = new struct svm_node*[sampleCount];
x_space = new struct svm_node[(featureDim+1)*sampleCount];
SetSvmParam(¶m, option, cross_validation, nr_fold);
for (int i=0; i<sampleCount; i++)
{
prob.y[i] = inputArr[i][0];
}
int j = 0;
for (int i=0; i<sampleCount; i++)
{
prob.x[i] = &x_space[j];
for (int k=1; k<=featureDim; k++)
{
x_space[i*featureDim+k].index = k;
x_space[i*featureDim+k].value = inputArr[i][k];
}
x_space[(i+1)*featureDim].index = -1;
j = (i+1)*featureDim + 1;
}
model = svm_train(&prob, ¶m);
const char* model_file_name = "C://Model.txt";
svm_save_model(model_file_name, model);
svm_destroy_model(model);
svm_destroy_param(¶m);
delete[] prob.y;
delete[] prob.x;
delete[] x_space;
}
int SvmPredict(const char* modelAdd)
{
struct svm_node *testX;
struct svm_model* testModel;
testModel = svm_load_model(modelAdd);
int featureDim = 12;
testX = new struct svm_node[featureDim+1];
for (int i=0; i<featureDim; i++)
{
testX[i].index = i+1;
testX[i].value = testArr[i];
}
testX[featureDim].index = -1;
double p = svm_predict(testModel, testX);
svm_destroy_model(testModel);
delete[] testX;
if (p > 0.5)
{
return 1;
}
else
{
return -1;
}
}
int _tmain(int argc, _TCHAR* argv[])
{
SvmTraining("-c 100 -t 1 -g 4 -r 1 -d 4");
int flag = SvmPredict("c://model.txt");
cout<<"flag = "<<flag<<endl;
system("pause");
return 0;
}





















 4万+
4万+

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








