VTK 实现对vtkpolyata 膨胀放缩
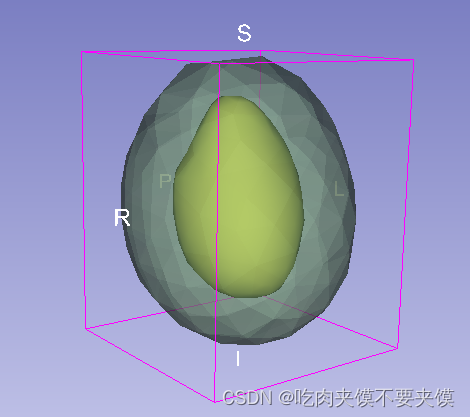
实现VTKpolydata 向外扩大, 目前了解到的有两种方法
- 方法1
使用vtkWarpVector 通过设置放缩因子和normals,使得vtkpolyata向外膨胀的效果
但是该种方式更多的是成比例的膨胀,即膨胀多少倍等,很难做到具体的控制膨胀多少距离
另外,注意放缩后可能没那么平滑了, 或许需要进行stripper去除表面多边形
def update_edge_size(input_polydata, scaleFactor, iteration=50):
"""vtkWarpVector 放缩 vtkpolyata"""
# 先将polydata表面进行一定平滑处理
smooth_filter = vtk.vtkSmoothPolyDataFilter()
smooth_filter.SetInputData(input_polydata)
smooth_filter.SetNumberOfIterations(iteration)
smooth_filter.SetRelaxationFactor(0.2)
smooth_filter.Update()
# 清理polydata 数据中的冗余信息,包括重复的点等,简化数据集
clean = vtk.vtkCleanPolyData()
clean.SetInputData(smooth_filter.GetOutput())
normals = vtk.vtkPolyDataNormals()
normals.SetInputConnection(clean.GetOutputPort())
normals.SplittingOff()
# 使用vtkWarpVector 进行放缩
warp = vtk.vtkWarpVector()
warp.SetInputConnection(normals.GetOutputPort())
warp.SetInputArrayToProcess(
0, 0, 0,
vtk.vtkDataObject().FIELD_ASSOCIATION_POINTS,
vtk.vtkDataSetAttributes().NORMALS
)
warp.SetScaleFactor(scaleFactor)
warp.Update()
warped_polydata = warp.GetOutput()
return warped_polydata
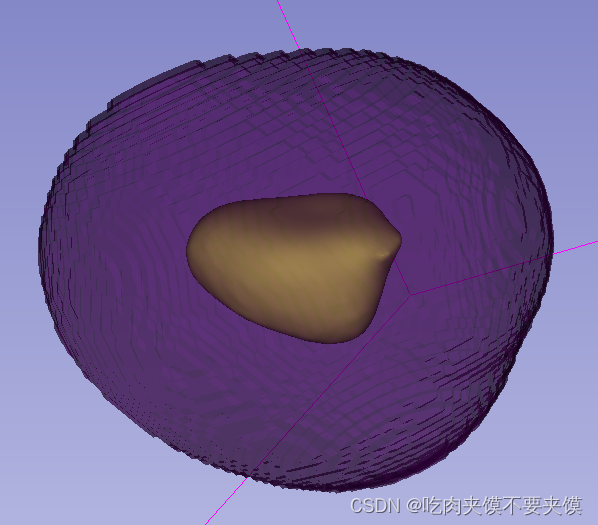
- 方法2
使用 vtkImplicitPolyDataDistance 计算一个有向距离场(signed distance field), 距离场的数据表示距离polydata表面的距离,在polydata外部值为正数, 内部值为负数,表面值为0
具体官方例子可见 这里
官方例子中还是以点的形式展示了有向距离场
但是我的目的是通过SDF 实现对polydata按照指定长度的膨胀,就是说膨胀3mm的时候,希望膨胀后的polydata表面距离原先polydata表面的平均距离也是3mm
考虑了一下大致思路是, 通过vtkImplicitPolyDataDistance 得到一个有向距离场的矩阵,然后根据希望放大的长度删选除膨胀后的点数据,得到一个mask,再将mask转换为polydata,得到膨胀了指定距离的polydata
def sdf_polydata(polydata:vtk.vtkPolyData, volume_sitk_img: sitk.Image,target_size=20):
"""
通过SDF 膨胀 polydata
params:
polydata: 输入待膨胀的polydata
volume_sitk_img: sitk.Image 相应的体数据,主要是为了得到矩阵大小以及进行RAS坐标和IJK世界坐标的转换,如果有指定的矩阵大小和RAS坐标和IJK坐标转换则不需要
target_size: 希望膨胀的大小
"""
if not target_size or target_size <= 1:
return None
volume_arr = sitk.GetArrayFromImage(volume_sitk_img)
sdf_arr = np.zeros_like(volume_arr, np.float16)
origin = volume_sitk_img.GetOrigin()
spacing = volume_sitk_img.GetSpacing()
volume_shape = volume_arr.shape
# 膨胀后 mask的包围盒
polydata_bounds = [0] * 6
polydata.GetBounds(polydata_bounds)
ras_x_min, ras_x_max, ras_y_min, ras_y_max, ras_z_min, ras_z_max = polydata_bounds
ras_x_min, ras_y_min, ras_z_min = (
ras_x_min - target_size - 1,
ras_y_min - target_size - 1,
ras_z_min - target_size - 1
)
ras_x_max, ras_y_max, ras_z_max = (
ras_x_max + target_size + 1,
ras_y_max + target_size + 1,
ras_z_max + target_size + 1
)
impl_distance = vtk.vtkImplicitPolyDataDistance()
impl_distance.SetInput(polydata)
min_ijk_point = volume_sitk_img.TransformPhysicalPointToIndex([ras_x_min, ras_y_min, ras_z_min])
max_ijk_point = volume_sitk_img.TransformPhysicalPointToIndex([ras_x_max, ras_y_max, ras_z_max])
# 这部分比较耗时
# 遍历包围盒,计算包围盒中每个值保存的是当前点距离polydata表面的距离
for x in range(min_ijk_point[0], max_ijk_point[0]):
for y in range(min_ijk_point[1], max_ijk_point[1]):
for z in range(min_ijk_point[2], max_ijk_point[2]):
tmp_ijk_point = [x, y, z]
tmp_ras_point = volume_sitk_img.TransformIndexToPhysicalPoint(tmp_ijk_point)
if not 0 <= tmp_ijk_point[0] <= volume_shape[2] or not 0 <= tmp_ijk_point[1] <= volume_shape[
1] or not 0 <= tmp_ijk_point[2] <= volume_shape[0]:
print(f"point {tmp_ijk_point} is over rand {volume_shape}")
continue
# 计算当前点到polydata表面的距离, 由于计算需要ras坐标,所以把索引下标再转回了ras
distance = impl_distance.EvaluateFunction(tmp_ras_point)
sdf_arr[tmp_ijk_point[2], tmp_ijk_point[1], tmp_ijk_point[0]] = round(distance, 2)
# 得到膨胀后mask
new_mask = np.zeros_like(sdf_arr, np.uint8)
logic = np.logical_and(sdf_arr <= target_size, sdf_arr != 0)
new_mask[logic] = 1
# 进行开运算,去掉膨胀后mask中间的一些空洞
for i in range(0, new_mask.shape[0]):
new_mask[i] = open_compute(new_mask[i], 3)
# 得到膨胀后的polydatamask之后需要将其转为polydata
# 分两步走。 1,mask转为imagedata; 2, imagedata转为polydata
# 将膨胀后mask转为imagedata
tmp_imagedata = vtk.vtkImageData()
tmp_imagedata.SetDimensions(*volume_sitk_img.GetSize())
tmp_imagedata.SetOrigin(origin)
tmp_imagedata.SetSpacing(spacing)
vtk_array = numpy_support.numpy_to_vtk(new_mask.flatten(), array_type=vtk.VTK_INT)
tmp_imagedata.GetPointData().SetScalars(vtk_array)
# imagedata转为polydata
marching_cubes = vtk.vtkDiscreteMarchingCubes()
marching_cubes.SetInputData(tmp_imagedata)
marching_cubes.SetValue(0, 1)
# 设置法向量计算开启
marching_cubes.ComputeNormalsOn()
marching_cubes.ComputeScalarsOn()
marching_cubes.Update()
res_polydata = marching_cubes.GetOutput()
return res_polydata
def open_compute(img_arr, kernel_size=3, iterations=1):
# 开运算
kernel = np.ones((kernel_size, kernel_size), np.int8)
dilated_arr = cv2.dilate(img_arr, kernel, iterations=iterations)
erode_arr = cv2.erode(dilated_arr, kernel, iterations=iterations)
return erode_arr
补充:
使用vtkImplicitPolyDataDistance 计算时候可能会受到 polydata的normals的影响,当法线指向内部时候, 外部的距离变为负数,内部变为正数。 所以需要法线指向外部(更方便计算处理)
修正polydata 法线:
def updatepolydata_normals(polydata):
normals = vtk.vtkPolyDataNormals()
normal_filter.SetInputData(polydata)
normal_filter.SetComputePointNormals(0)
normal_filter.SetComputeCellNormals(1)
normal_filter.SetAutoOrientNormals(1)
normal_filter.Update()
polydata = normal_filter.GetOutput()
return polydata
























 5223
5223











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










