@浙大疏锦行
知识点
1. 聚类的指标
2. 聚类常见算法:kmeans聚类、dbscan聚类、层次聚类
3. 三种算法对应的流程
实际在论文中聚类的策略不一定是针对所有特征,可以针对其中几个可以解释的特征进行聚类,得到聚类后的类别,这样后续进行解释也更加符合逻辑。
聚类的流程
1. 标准化数据
2. 选择合适的算法,根据评估指标调参( )
KMeans 和层次聚类的参数是K值,选完k指标就确定
DBSCAN 的参数是 eps 和min_samples,选完他们出现k和评估指标
以及层次聚类的 linkage准则等都需要仔细调优。
除了经典的评估指标,还需要关注聚类出来每个簇对应的样本个数,避免太少没有意义。
3. 将聚类后的特征添加到原数据中
4. 原则t-sne或者pca进行2D或3D可视化
题目: 对心脏病数据集进行聚类。
import pandas as pd #用于数据处理和分析,可处理表格数据。
import numpy as np #用于数值计算,提供了高效的数组操作。
import matplotlib.pyplot as plt #用于绘制各种类型的图表
import seaborn as sns #基于matplotlib的高级绘图库,能绘制更美观的统计图形。
from sklearn.model_selection import train_test_split
from sklearn.ensemble import RandomForestClassifier
from sklearn.model_selection import StratifiedKFold, cross_validate # 引入分层 K 折和交叉验证工具
from sklearn.metrics import make_scorer, accuracy_score, precision_score, recall_score, f1_score, confusion_matrix, classification_report
import time
import warnings
warnings.filterwarnings("ignore")
# 设置中文字体(解决中文显示问题)
plt.rcParams['font.sans-serif'] = ['SimHei'] # Windows系统常用黑体字体
plt.rcParams['axes.unicode_minus'] = False # 正常显示负号
data = pd.read_csv('heart.csv')
# 提取连续值特征
continuous_features = ['age', 'trestbps', 'chol', 'thalach', 'oldpeak']
# 提取离散值特征
discrete_features = ['sex', 'cp', 'fbs', 'restecg', 'exang', 'slope', 'ca', 'thal', 'target']
# 使用映射字典进行转换
mapping = {
'cp': {0: 0, 1: 1, 2: 2, 3: 3},
'restecg': {0: 0, 1: 1, 2: 2},
'slope': {0: 0, 1: 1, 2: 2},
'ca': {0: 0, 1: 1, 2: 2, 3: 3, 4: 4},
'thal': {0: 0, 1: 1, 2: 2, 3: 3}
}
for feature, mapping in mapping.items():
data[feature] = data[feature].map(mapping)
# Purpose 独热编码
columns_to_encode = ['sex','fbs','exang']
data = pd.get_dummies(data, columns=columns_to_encode)
data2 = pd.read_csv("heart.csv") # 重新读取数据,用来做列名对比
list_final = [] # 新建一个空列表,用于存放独热编码后新增的特征名
for i in data.columns:
if i not in data2.columns:
list_final.append(i) # 这里打印出来的就是独热编码后的特征名
for i in list_final:
data[i] = data[i].astype(int) # 这里的i就是独热编码后的特征名
# 划分训练集和测试机
X = data.drop(['target'], axis=1) # 特征,axis=1表示按列删除
y = data['target'] # 标签
import numpy as np
import pandas as pd
from sklearn.cluster import KMeans, DBSCAN, AgglomerativeClustering
from sklearn.preprocessing import StandardScaler
from sklearn.decomposition import PCA
from sklearn.metrics import silhouette_score, calinski_harabasz_score, davies_bouldin_score
import matplotlib.pyplot as plt
import seaborn as sns
# 标准化数据(聚类前通常需要标准化)
scaler = StandardScaler()
X_scaled = scaler.fit_transform(X)
# 评估不同 k 值下的指标
k_range = range(2, 11) # 测试 k 从 2 到 10
inertia_values = []
silhouette_scores = []
ch_scores = []
db_scores = []
for k in k_range:
kmeans = KMeans(n_clusters=k, random_state=42)
kmeans_labels = kmeans.fit_predict(X_scaled)
inertia_values.append(kmeans.inertia_) # 惯性(肘部法则)
silhouette = silhouette_score(X_scaled, kmeans_labels) # 轮廓系数
silhouette_scores.append(silhouette)
ch = calinski_harabasz_score(X_scaled, kmeans_labels) # CH 指数
ch_scores.append(ch)
db = davies_bouldin_score(X_scaled, kmeans_labels) # DB 指数
db_scores.append(db)
print(f"k={k}, 惯性: {kmeans.inertia_:.2f}, 轮廓系数: {silhouette:.3f}, CH 指数: {ch:.2f}, DB 指数: {db:.3f}")
# 绘制评估指标图
plt.figure(figsize=(15, 10))
# 肘部法则图(Inertia)
plt.subplot(2, 2, 1)
plt.plot(k_range, inertia_values, marker='o')
plt.title('肘部法则确定最优聚类数 k(惯性,越小越好)')
plt.xlabel('聚类数 (k)')
plt.ylabel('惯性')
plt.grid(True)
# 轮廓系数图
plt.subplot(2, 2, 2)
plt.plot(k_range, silhouette_scores, marker='o', color='orange')
plt.title('轮廓系数确定最优聚类数 k(越大越好)')
plt.xlabel('聚类数 (k)')
plt.ylabel('轮廓系数')
plt.grid(True)
# CH 指数图
plt.subplot(2, 2, 3)
plt.plot(k_range, ch_scores, marker='o', color='green')
plt.title('Calinski-Harabasz 指数确定最优聚类数 k(越大越好)')
plt.xlabel('聚类数 (k)')
plt.ylabel('CH 指数')
plt.grid(True)
# DB 指数图
plt.subplot(2, 2, 4)
plt.plot(k_range, db_scores, marker='o', color='red')
plt.title('Davies-Bouldin 指数确定最优聚类数 k(越小越好)')
plt.xlabel('聚类数 (k)')
plt.ylabel('DB 指数')
plt.grid(True)
plt.tight_layout()
plt.show()
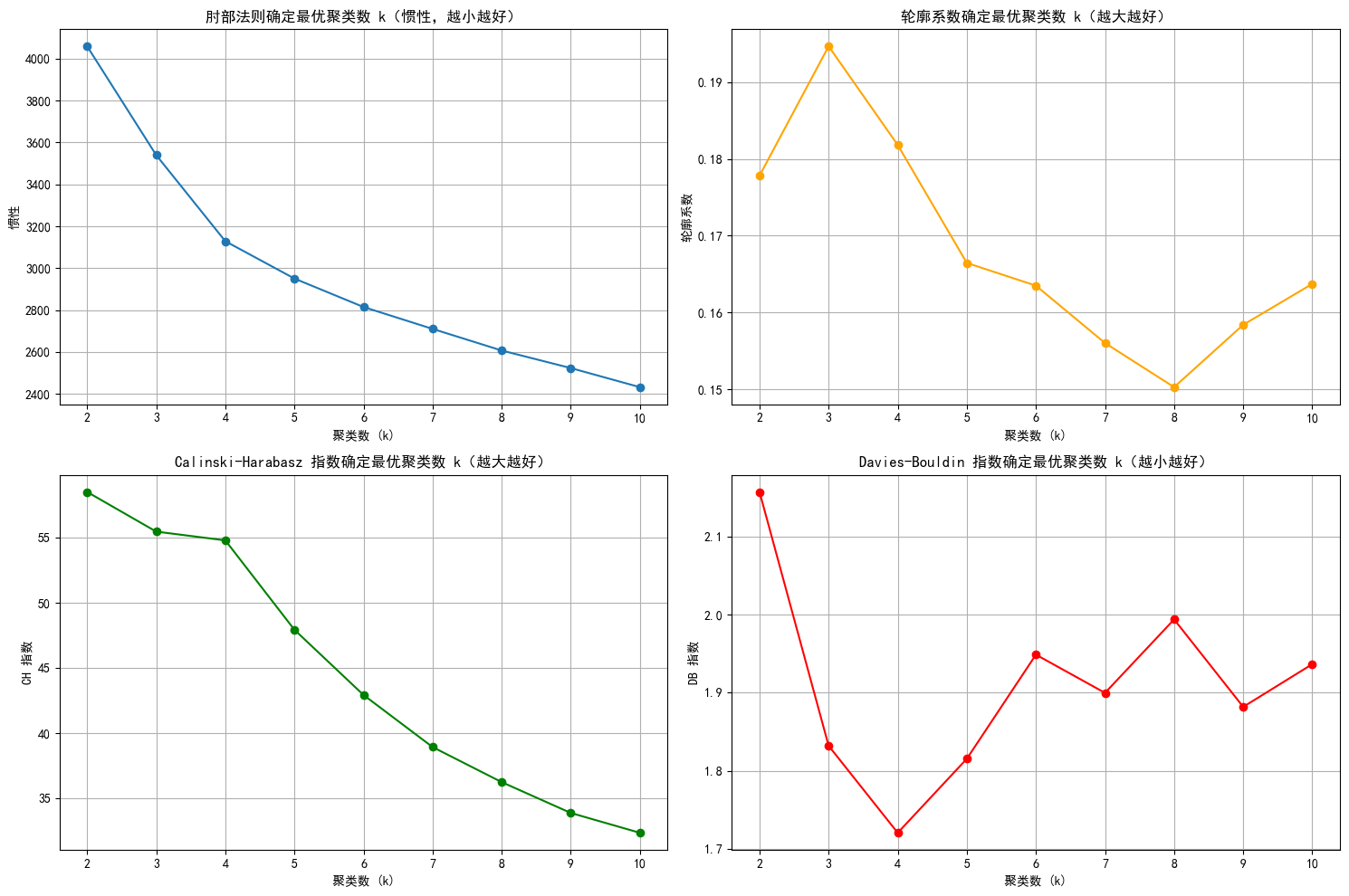
# 提示用户选择 k 值
selected_k = 4
# 使用选择的 k 值进行 KMeans 聚类
kmeans = KMeans(n_clusters=selected_k, random_state=42)
kmeans_labels = kmeans.fit_predict(X_scaled)
X['KMeans_Cluster'] = kmeans_labels
# 使用 PCA 降维到 2D 进行可视化
pca = PCA(n_components=2)
X_pca = pca.fit_transform(X_scaled)
# KMeans 聚类结果可视化
plt.figure(figsize=(6, 5))
sns.scatterplot(x=X_pca[:, 0], y=X_pca[:, 1], hue=kmeans_labels, palette='viridis')
plt.title(f'KMeans Clustering with k={selected_k} (PCA Visualization)')
plt.xlabel('PCA Component 1')
plt.ylabel('PCA Component 2')
plt.show()
# 打印 KMeans 聚类标签的前几行
print(f"KMeans Cluster labels (k={selected_k}) added to X:")
print(X[['KMeans_Cluster']].value_counts())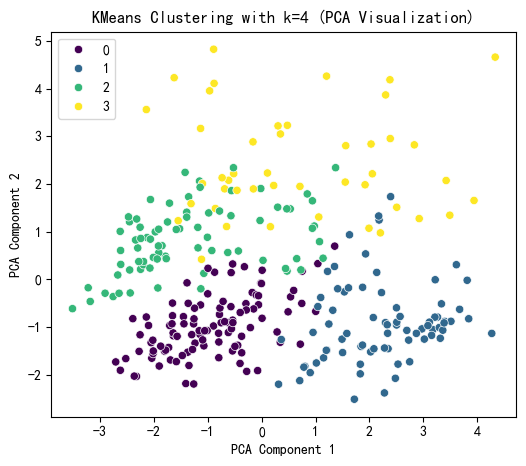
eps_range = np.arange(0.3, 2.0, 0.1) # 测试 eps 从 0.3 到 0.7
min_samples_range = range(3, 20) # 测试 min_samples 从 3 到 7
results = []
for eps in eps_range:
for min_samples in min_samples_range:
dbscan = DBSCAN(eps=eps, min_samples=min_samples)
dbscan_labels = dbscan.fit_predict(X_scaled)
# 计算簇的数量(排除噪声点 -1)
n_clusters = len(np.unique(dbscan_labels)) - (1 if -1 in dbscan_labels else 0)
# 计算噪声点数量
n_noise = list(dbscan_labels).count(-1)
# 只有当簇数量大于 1 且有有效簇时才计算评估指标
if n_clusters > 1:
# 排除噪声点后计算评估指标
mask = dbscan_labels != -1
if mask.sum() > 0: # 确保有非噪声点
silhouette = silhouette_score(X_scaled[mask], dbscan_labels[mask])
ch = calinski_harabasz_score(X_scaled[mask], dbscan_labels[mask])
db = davies_bouldin_score(X_scaled[mask], dbscan_labels[mask])
results.append({
'eps': eps,
'min_samples': min_samples,
'n_clusters': n_clusters,
'n_noise': n_noise,
'silhouette': silhouette,
'ch_score': ch,
'db_score': db
})
print(f"eps={eps:.1f}, min_samples={min_samples}, 簇数: {n_clusters}, 噪声点: {n_noise}, "
f"轮廓系数: {silhouette:.3f}, CH 指数: {ch:.2f}, DB 指数: {db:.3f}")
else:
print(f"eps={eps:.1f}, min_samples={min_samples}, 簇数: {n_clusters}, 噪声点: {n_noise}, 无法计算评估指标")
# 将结果转为 DataFrame 以便可视化和选择参数
results_df = pd.DataFrame(results)
# 绘制评估指标图,增加点论文中的工作量
plt.figure(figsize=(15, 10))
# 轮廓系数图
plt.subplot(2, 2, 1)
for min_samples in min_samples_range:
subset = results_df[results_df['min_samples'] == min_samples] #
plt.plot(subset['eps'], subset['silhouette'], marker='o', label=f'min_samples={min_samples}')
plt.title('轮廓系数确定最优参数(越大越好)')
plt.xlabel('eps')
plt.ylabel('轮廓系数')
plt.legend()
plt.grid(True)
# CH 指数图
plt.subplot(2, 2, 2)
for min_samples in min_samples_range:
subset = results_df[results_df['min_samples'] == min_samples]
plt.plot(subset['eps'], subset['ch_score'], marker='o', label=f'min_samples={min_samples}')
plt.title('Calinski-Harabasz 指数确定最优参数(越大越好)')
plt.xlabel('eps')
plt.ylabel('CH 指数')
plt.legend()
plt.grid(True)
# DB 指数图
plt.subplot(2, 2, 3)
for min_samples in min_samples_range:
subset = results_df[results_df['min_samples'] == min_samples]
plt.plot(subset['eps'], subset['db_score'], marker='o', label=f'min_samples={min_samples}')
plt.title('Davies-Bouldin 指数确定最优参数(越小越好)')
plt.xlabel('eps')
plt.ylabel('DB 指数')
plt.legend()
plt.grid(True)
# 簇数量图
plt.subplot(2, 2, 4)
for min_samples in min_samples_range:
subset = results_df[results_df['min_samples'] == min_samples]
plt.plot(subset['eps'], subset['n_clusters'], marker='o', label=f'min_samples={min_samples}')
plt.title('簇数量变化')
plt.xlabel('eps')
plt.ylabel('簇数量')
plt.legend()
plt.grid(True)
plt.tight_layout()
plt.show()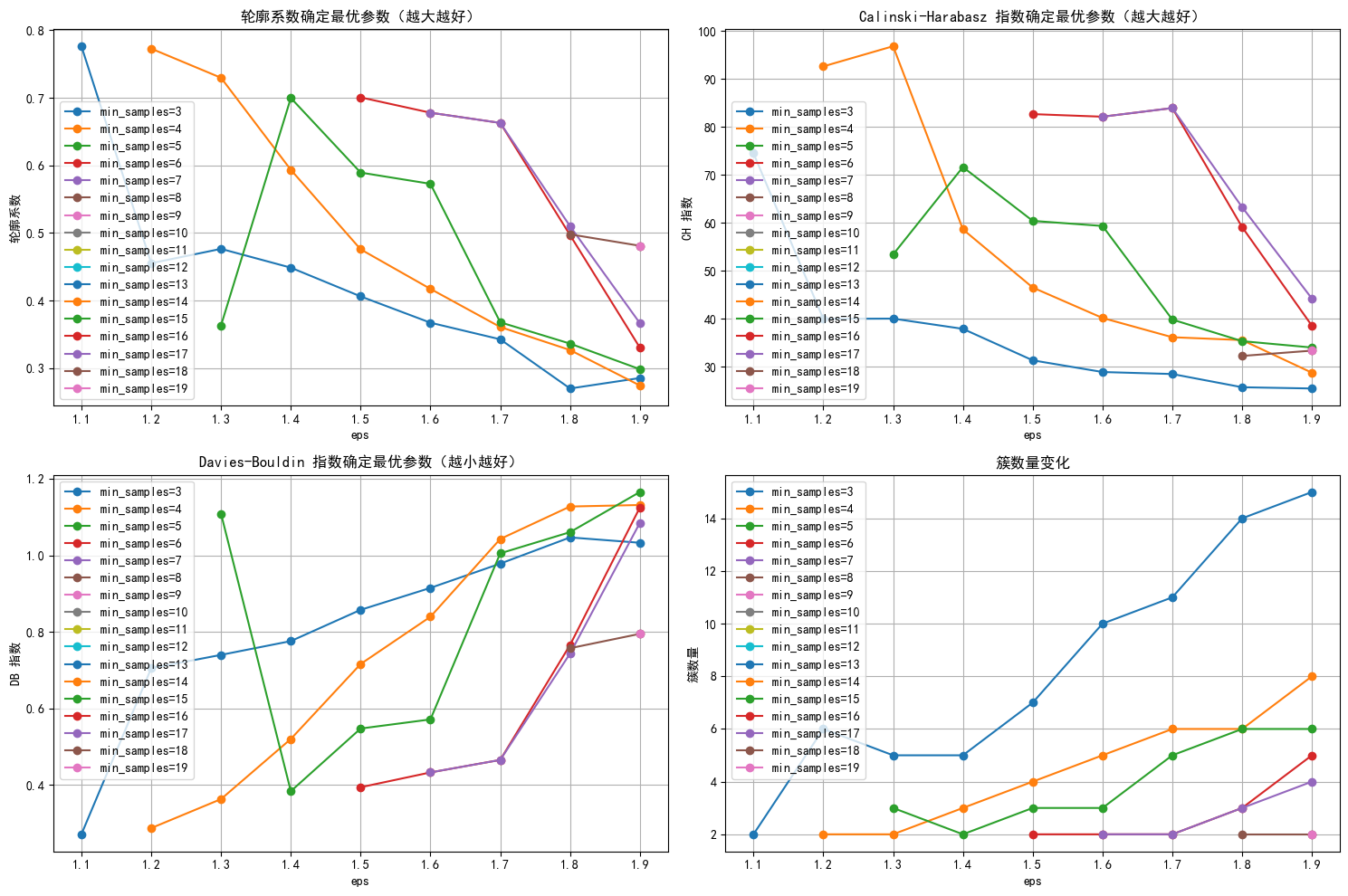
# 选择 eps 和 min_samples 值(根据图表选择最佳参数)
selected_eps = 1.2 # 根据图表调整
selected_min_samples = 4 # 根据图表调整
# 使用选择的参数进行 DBSCAN 聚类
dbscan = DBSCAN(eps=selected_eps, min_samples=selected_min_samples)
dbscan_labels = dbscan.fit_predict(X_scaled)
X['DBSCAN_Cluster'] = dbscan_labels
# 使用 PCA 降维到 2D 进行可视化
pca = PCA(n_components=2)
X_pca = pca.fit_transform(X_scaled)
# DBSCAN 聚类结果可视化
plt.figure(figsize=(6, 5))
sns.scatterplot(x=X_pca[:, 0], y=X_pca[:, 1], hue=dbscan_labels, palette='viridis')
plt.title(f'DBSCAN Clustering with eps={selected_eps}, min_samples={selected_min_samples} (PCA Visualization)')
plt.xlabel('PCA Component 1')
plt.ylabel('PCA Component 2')
plt.show()
# 打印 DBSCAN 聚类标签的分布
print(f"DBSCAN Cluster labels (eps={selected_eps}, min_samples={selected_min_samples}) added to X:")
print(X[['DBSCAN_Cluster']].value_counts())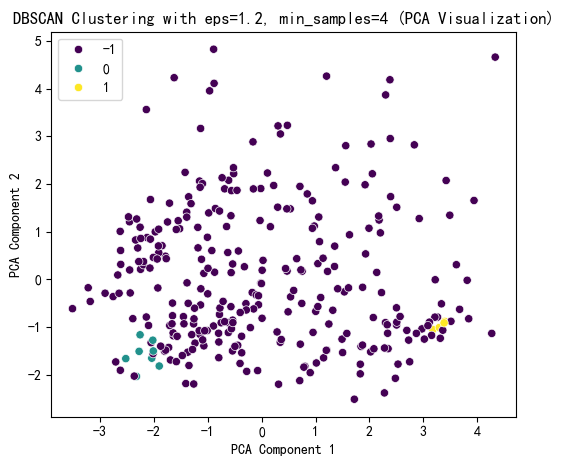
# 评估不同 n_clusters 下的指标
n_clusters_range = range(2, 11) # 测试簇数量从 2 到 10
silhouette_scores = []
ch_scores = []
db_scores = []
for n_clusters in n_clusters_range:
agglo = AgglomerativeClustering(n_clusters=n_clusters, linkage='ward') # 使用 Ward 准则合并簇
agglo_labels = agglo.fit_predict(X_scaled)
# 计算评估指标
silhouette = silhouette_score(X_scaled, agglo_labels)
ch = calinski_harabasz_score(X_scaled, agglo_labels)
db = davies_bouldin_score(X_scaled, agglo_labels)
silhouette_scores.append(silhouette)
ch_scores.append(ch)
db_scores.append(db)
print(f"n_clusters={n_clusters}, 轮廓系数: {silhouette:.3f}, CH 指数: {ch:.2f}, DB 指数: {db:.3f}")
# 绘制评估指标图
plt.figure(figsize=(15, 5))
# 轮廓系数图
plt.subplot(1, 3, 1)
plt.plot(n_clusters_range, silhouette_scores, marker='o')
plt.title('轮廓系数确定最优簇数(越大越好)')
plt.xlabel('簇数量 (n_clusters)')
plt.ylabel('轮廓系数')
plt.grid(True)
# CH 指数图
plt.subplot(1, 3, 2)
plt.plot(n_clusters_range, ch_scores, marker='o')
plt.title('Calinski-Harabasz 指数确定最优簇数(越大越好)')
plt.xlabel('簇数量 (n_clusters)')
plt.ylabel('CH 指数')
plt.grid(True)
# DB 指数图
plt.subplot(1, 3, 3)
plt.plot(n_clusters_range, db_scores, marker='o')
plt.title('Davies-Bouldin 指数确定最优簇数(越小越好)')
plt.xlabel('簇数量 (n_clusters)')
plt.ylabel('DB 指数')
plt.grid(True)
plt.tight_layout()
plt.show()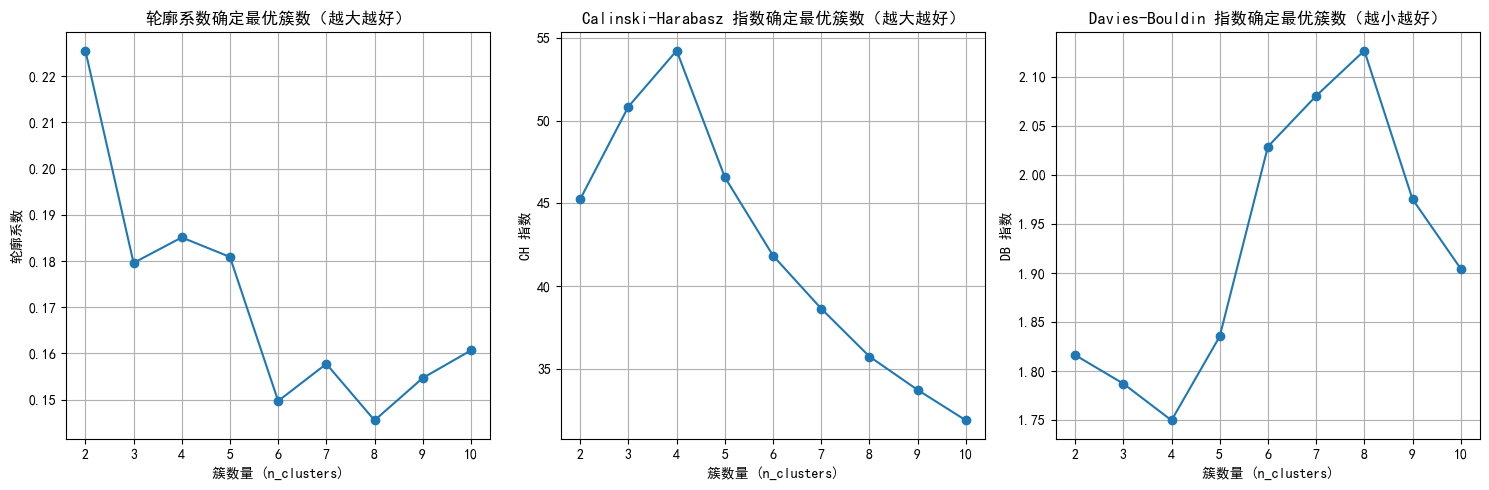
# 提示用户选择 n_clusters 值(这里可以根据图表选择最佳簇数)
selected_n_clusters = 4 # 示例值,根据图表调整
# 使用选择的簇数进行 Agglomerative Clustering 聚类
agglo = AgglomerativeClustering(n_clusters=selected_n_clusters, linkage='ward')
agglo_labels = agglo.fit_predict(X_scaled)
X['Agglo_Cluster'] = agglo_labels
# 使用 PCA 降维到 2D 进行可视化
pca = PCA(n_components=2)
X_pca = pca.fit_transform(X_scaled)
# Agglomerative Clustering 聚类结果可视化
plt.figure(figsize=(6, 5))
sns.scatterplot(x=X_pca[:, 0], y=X_pca[:, 1], hue=agglo_labels, palette='viridis')
plt.title(f'Agglomerative Clustering with n_clusters={selected_n_clusters} (PCA Visualization)')
plt.xlabel('PCA Component 1')
plt.ylabel('PCA Component 2')
plt.show()
# 打印 Agglomerative Clustering 聚类标签的分布
print(f"Agglomerative Cluster labels (n_clusters={selected_n_clusters}) added to X:")
print(X[['Agglo_Cluster']].value_counts())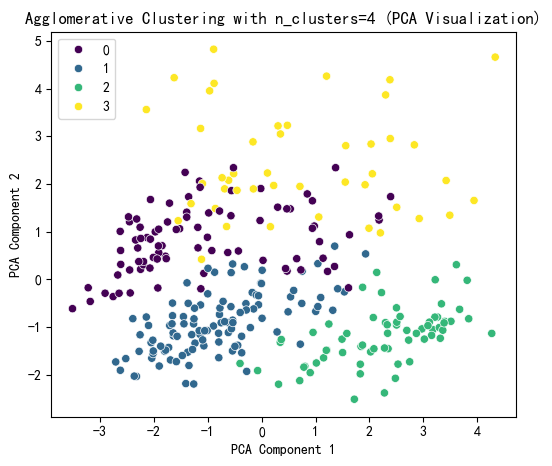
# 层次聚类的树状图可视化
from scipy.cluster import hierarchy
import matplotlib.pyplot as plt
# 假设 X_scaled 是标准化后的数据
# 计算层次聚类的链接矩阵
Z = hierarchy.linkage(X_scaled, method='ward') # 'ward' 是常用的合并准则
# 绘制树状图
plt.figure(figsize=(10, 6))
hierarchy.dendrogram(Z, truncate_mode='level', p=4) # p 控制显示的层次深度
# hierarchy.dendrogram(Z, truncate_mode='level') # 不用p这个参数,可以显示全部的深度
plt.title('Dendrogram for Agglomerative Clustering')
plt.xlabel('Cluster Size')
plt.ylabel('Distance')
plt.show()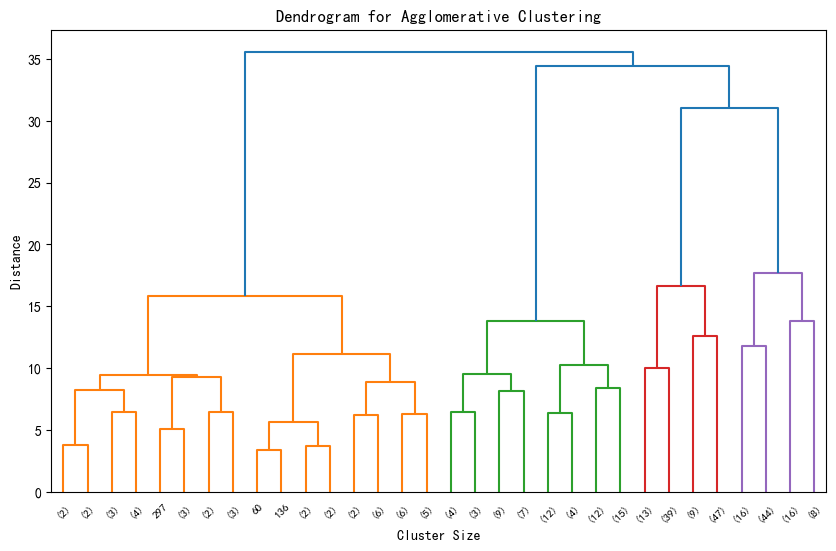
























 147
147

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








