当我分析CyTOF数据的时候,走到差异分析得时候,
topTable(da_res1, show_props = TRUE, format_vals = TRUE, digits = 2)出现了错误:
Error in topTable(da_res1, show_props = TRUE, format_vals = TRUE, digits = 2) :
unused arguments (show_props = TRUE, format_vals = TRUE, digits = 2)然后我以为里面的参数弄错了,我就??topTable,然后选择diffcyt,因为差异分析我用的是这个包,所以想当然我查看得就是这个包里的topTable函数,
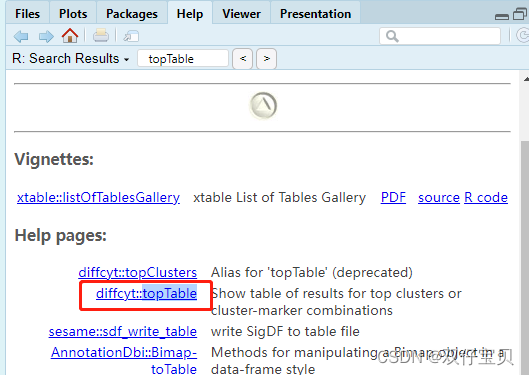
然后查看里面的参数,

没有问题
但我还是以为哪个参数用错了,我就把后面的参数都去掉了
topTable(da_res1)还是报错,但报错内容变了【更新了找不到了】
但里面有个fit什么的,我就很奇怪,参数里也没有这个,
然后我就想会不会是其他包里的函数,把diffcyt包里的topTable给我覆盖了,然后我就在??topTable下搜索,果然有个limma,

点进去之后,发现了!!!!

并且,我在运行这个的时候发现,就是这样的,实锤了!
> args(topTable)
function (fit, coef = NULL, number = 10, genelist = fit$genes,
adjust.method = "BH", sort.by = "B", resort.by = NULL, p.value = 1,
lfc = 0, confint = FALSE)
NULL接下来就是
detach("package:limma", unload = TRUE)然后在运行
topTable(da_res1, show_props = TRUE, format_vals = TRUE, digits = 2)
topTable(da_res1, show_props = TRUE, format_vals = TRUE, digits = 2)非常顺利,没有报错,嘿嘿!





















 1万+
1万+











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








