本文将介绍使用FMRIB Software Library(FSL)做VBM(voxel-based morphometry)分析。
操作系统:linux系统;
本教程使用的环境是ubuntu-18.04.1;虽然ubuntu目前的最新版本是18.10,但最好不要安装最新版本,相关的配套插件尚未完善,FSL运行要报错。
FSL版本号为FSL 6.0.0。
一、准备原始数据
(1)新建一个文件夹(假设命名为VBMtest)作为分析目录,并将所有被试的原始 T1 像放到该文件夹下。这里的文件是nii.gz格式,从磁共振机器拷贝出来的是dicom格式,需要将其压缩成nii.gz格式。具体压缩的软件有很多,熟悉windows系统的同学可以在windows系统使用相关软件完成压缩过程;在本教程中,是在linux环境下的dcm2niix程序完成压缩的。具体请参考:https://github.com/rordenlab/dcm2niix/releases
这里有两组被试,第一组健康对照组22 人, 命名为control*.nii.gz (*表示不同的subjects... ),第二组病人组16 人,命名为pa*.nii.gz (*表示不同的subjects... );见图1。
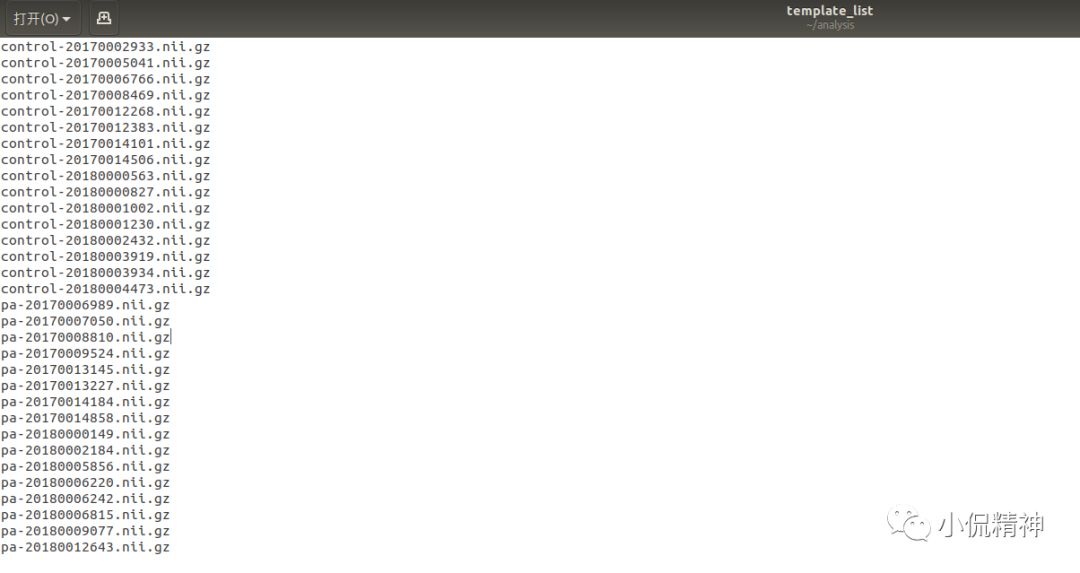
(2)构建组模板。将被试的名字,即 control*.nii.gz...,pa*.nii.gz...放到一个名为template_list 的文件里。如果两组被试数目不一样,就从被试数目较多的一组中随机选择部分被试,使得两组被试数据相等,这是为了保证构建的组模板不会偏向于某一组;具体操作:打开终端,cd到VBMtest目录(或者在VBMtest目录里点击右键,打开终端会自动到该目录),输入:gedit template_list,输入subjects的文件名,然后保存。见图2。
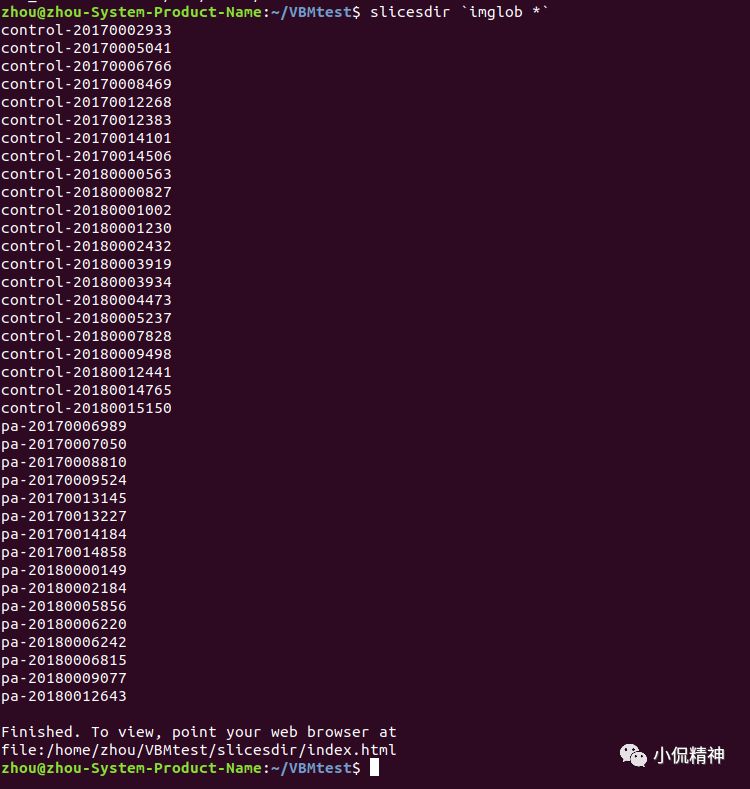
(3)[这部分并非VBM所必须]在命令行下运行slicesdir `imglob *` ,这里*表示所有的subjects. 即当前文件夹下所有被试的文件。见图3。
这行命令的作用是产生了一个slicesdir的文件夹,在里面截取每个被试的 T1 图像,并生成一个名为index.html的文件。见图4。
二、构建GLM模型,用于组间比较
(1)设计矩阵中被试的顺序应该与subjects的文件名一致。比如这里健康组的文件名命名为 control* ,而病人组名为pa*, control*在pa*前面(默认排序),所以设计矩阵中前22个应为健康对照








 最低0.47元/天 解锁文章
最低0.47元/天 解锁文章















 1万+
1万+











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








