1. 数据集
1.1 特征
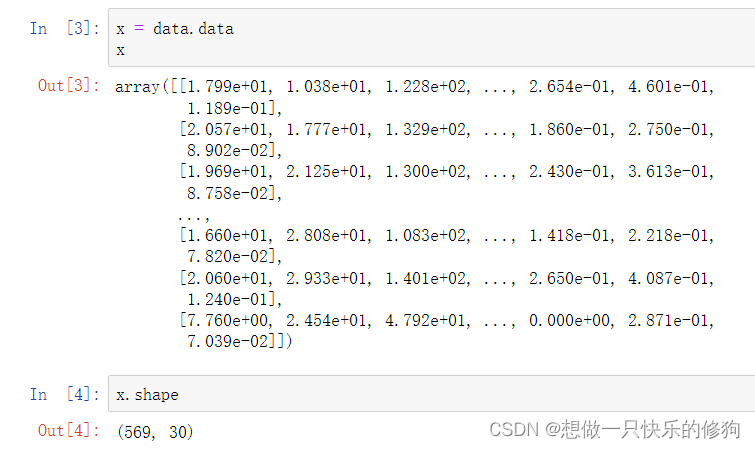
共有30个特征。
1.2 目标值
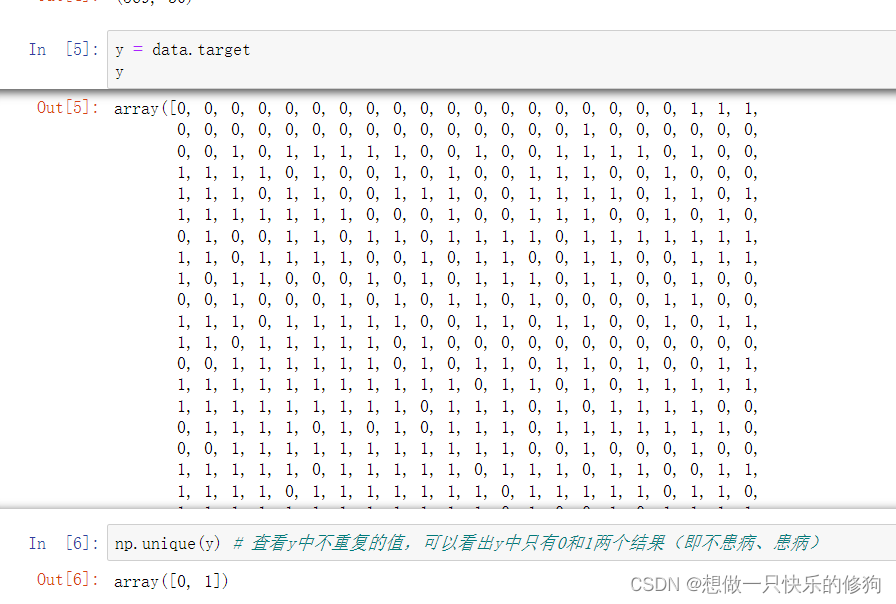
1.3 数据分布
1.3.1 选择前两维特征绘制散点图
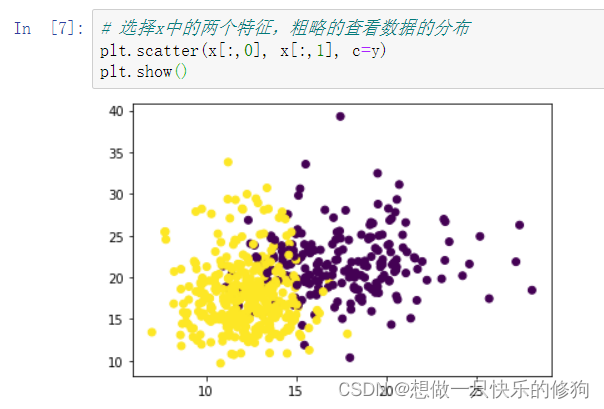
1.3.2 使用PCA降维到2维,再绘制散点图
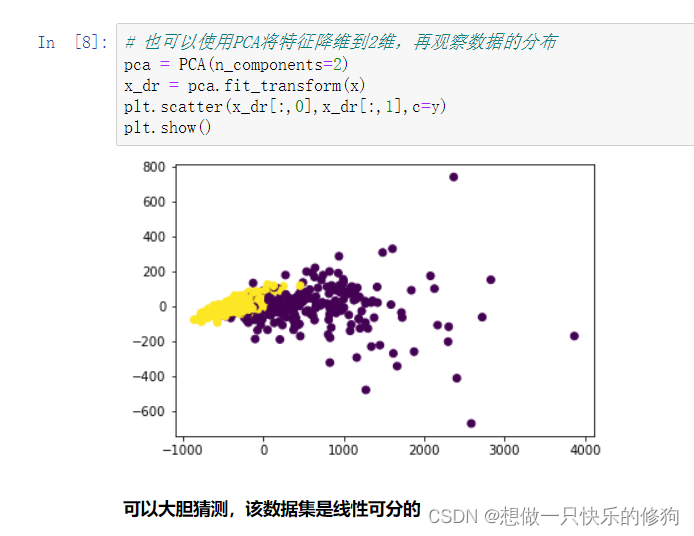
2. 代码实现
2.1 不做数据预处理,直接选择核函数
代码;
# 划分数据集
x_train, x_test, y_train, y_test = train_test_split(x, y, test_size=0.3, random_state=420)
kernel = ['linear', 'poly', 'rbf','sigmoid']
for kernel in kernel:
# 开始时间
time0 = time()
clf = SVC(kernel=kernel
,gamma='auto'
,cache_size = 1000 # 单位是MB,使用计算机的内存
).fit(x_train, y_train)
print('在%s作为kernel的条件下,准确率为%f'%(kernel, clf.score(x_test, y_test)))
print('运行时间为:', datetime.datetime.fromtimestamp(time()-time0).strftime('%M:%S:%f')) # 分钟:秒:毫秒
发现结果一直停在线性函数不动,因为poly作为核函数,要花费很长时间。
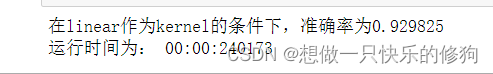
将poly核函数去掉,结果:
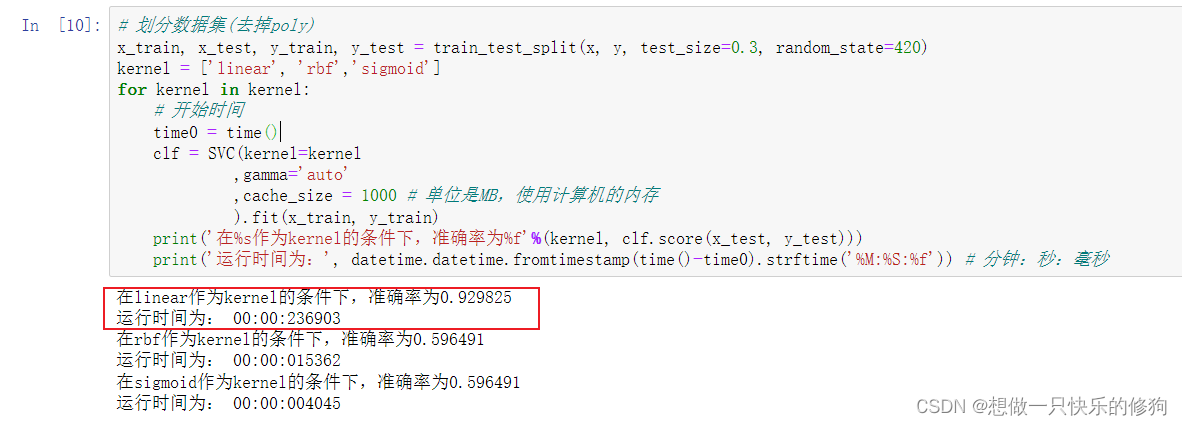
如果数据是线性的,那如果我们把degree参数调整为1,多项式核函数应该也可以得到不错的结果:
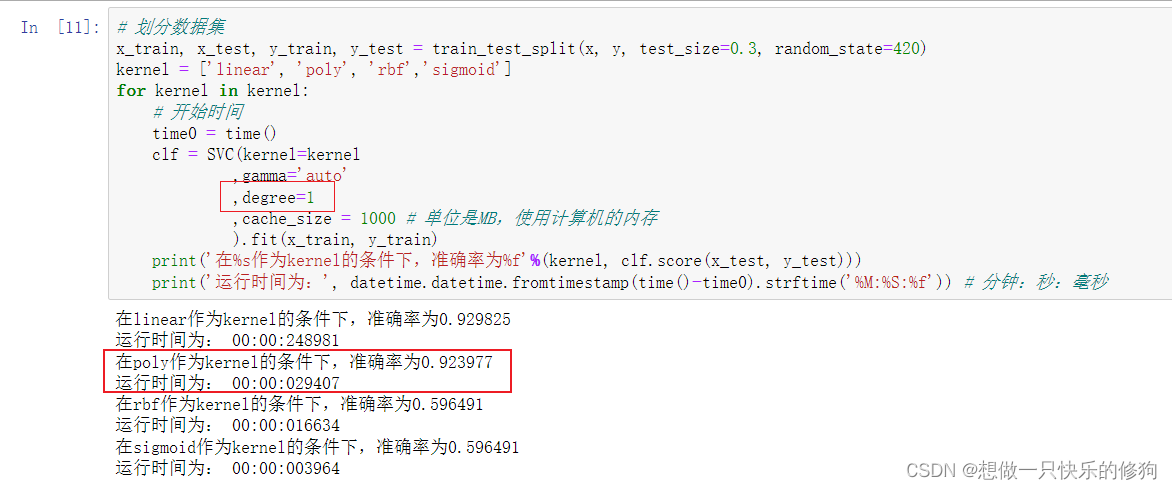
- 这样就直接选择linear了吗?可以再探索探索。
2.2 进行数据标准化,再选择核函数
2.2.1 为什么要对乳腺癌数据集进行标准化?
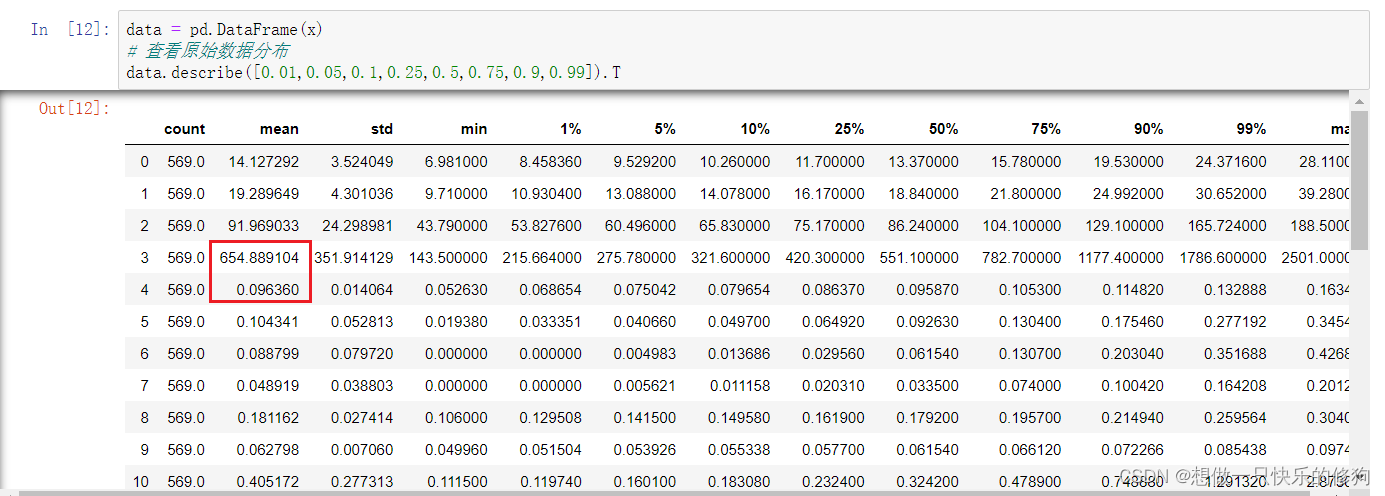
就从框出来的那个地方看,就能看出来数据量钢化差别太大,所以要进行数据标准化。
对数据进行标准化以后,再查看数据的分布:
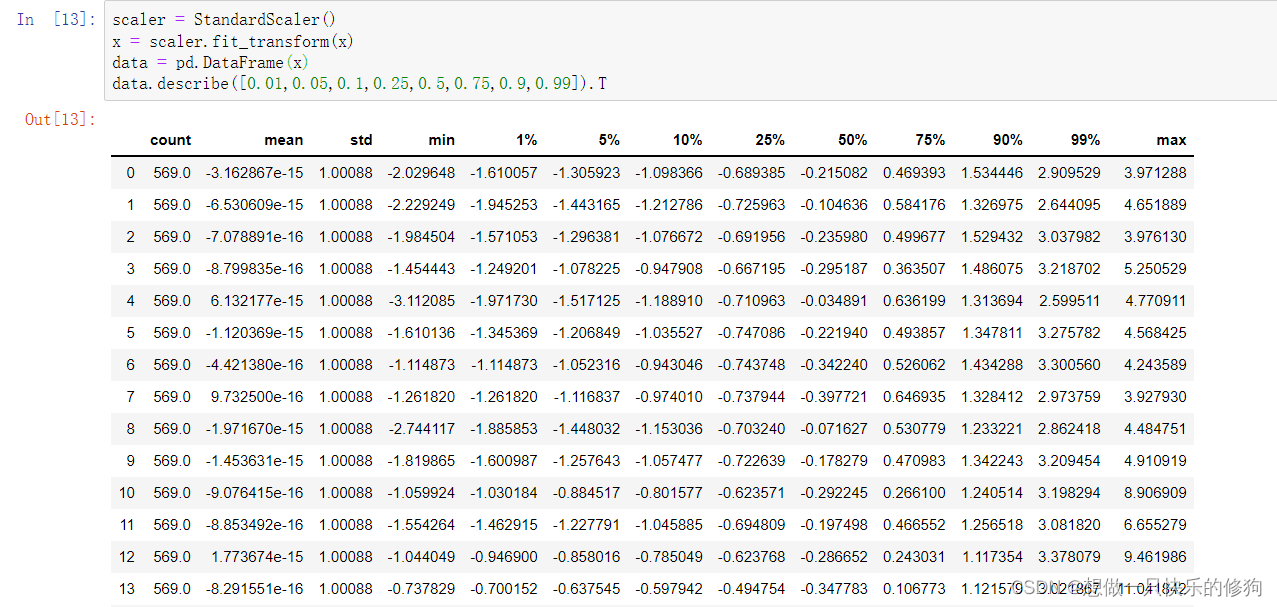
2.2.2 代码实现
# 划分数据集(degree设置为1)
x_train, x_test, y_train, y_test = train_test_split(x, y, test_size=0.3, random_state=420)
kernel = ['linear', 'poly', 'rbf','sigmoid']
for kernel in kernel:
# 开始时间
time0 = time()
clf = SVC(kernel=kernel
,gamma='auto'
,degree=1
,cache_size = 1000 # 单位是MB,使用计算机的内存
).fit(x_train, y_train)
print('在%s作为kernel的条件下,准确率为%f'%(kernel, clf.score(x_test, y_test)))
print('运行时间为:', datetime.datetime.fromtimestamp(time()-time0).strftime('%M:%S:%f')) # 分钟:秒:毫秒
结果:
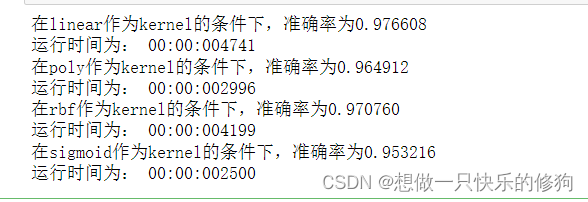
可以见到,在rbf作为核函数的结果中精确度已经提高了,跟linear作为核函数差距没有那么大了。
那么,接下来我们就继续在rbf核函数上继续探索吧!
2.3 rbf作为核函数,继续进行调参
首先,看一下SVM中各个核函数所要调节的参数。

2.3.1 调节gamma —— 绘制学习曲线
score = []
gamma_range = np.logspace(-10,1,50) # 对数刻度上均匀间隔的数字
for i in gamma_range:
clf = SVC(kernel='rbf', gamma=i, cache_size=1000).fit(x_train, y_train)
score.append(clf.score(x_test,y_test))
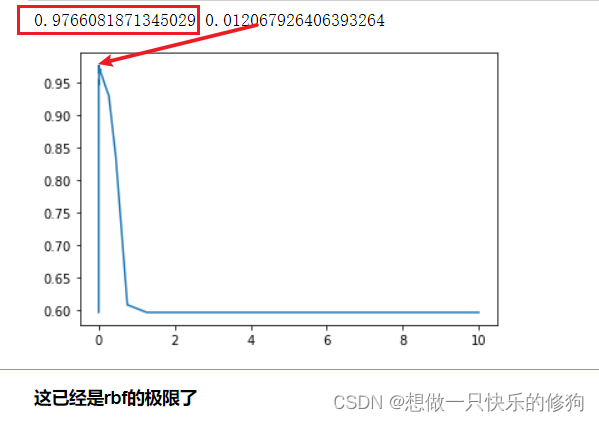
print(max(score), gamma_range[score.index(max(score))])
plt.plot(gamma_range, score)
plt.show()
结果:
2.4 kernel为poly,继续进行探索 —— 网格搜索
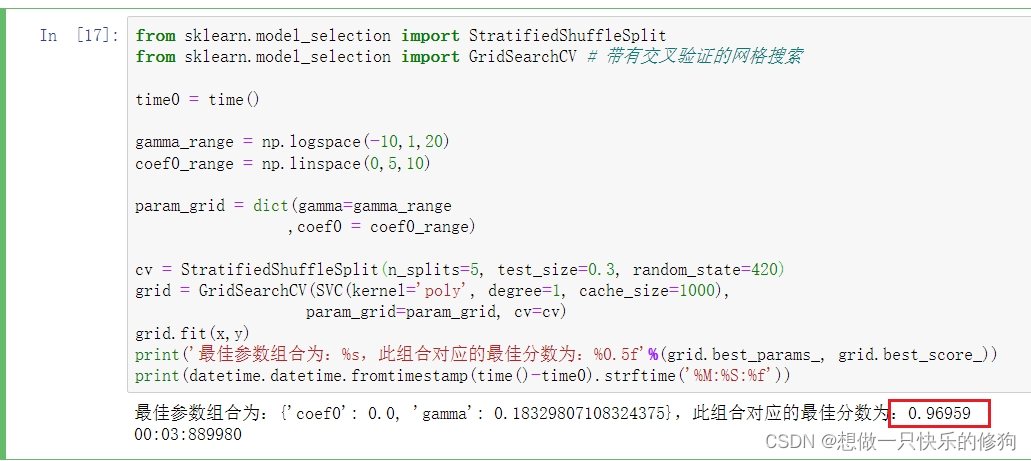
放弃poly作为核函数吧。。。
2.5 最后的挣扎,调整惩罚项系数C(linear和rbf做最后的比拼)
2.5.1 线性函数作为核函数
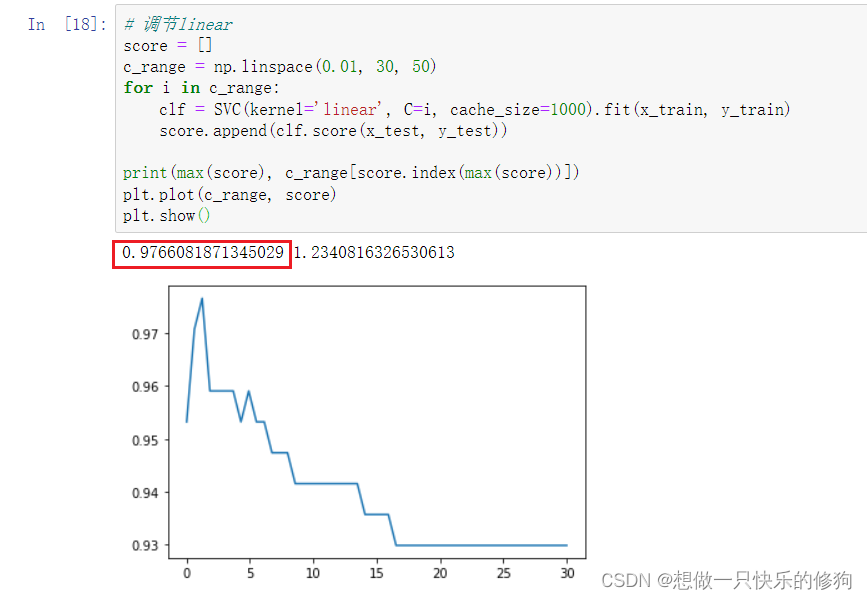
2.5.2 rbf作为核函数
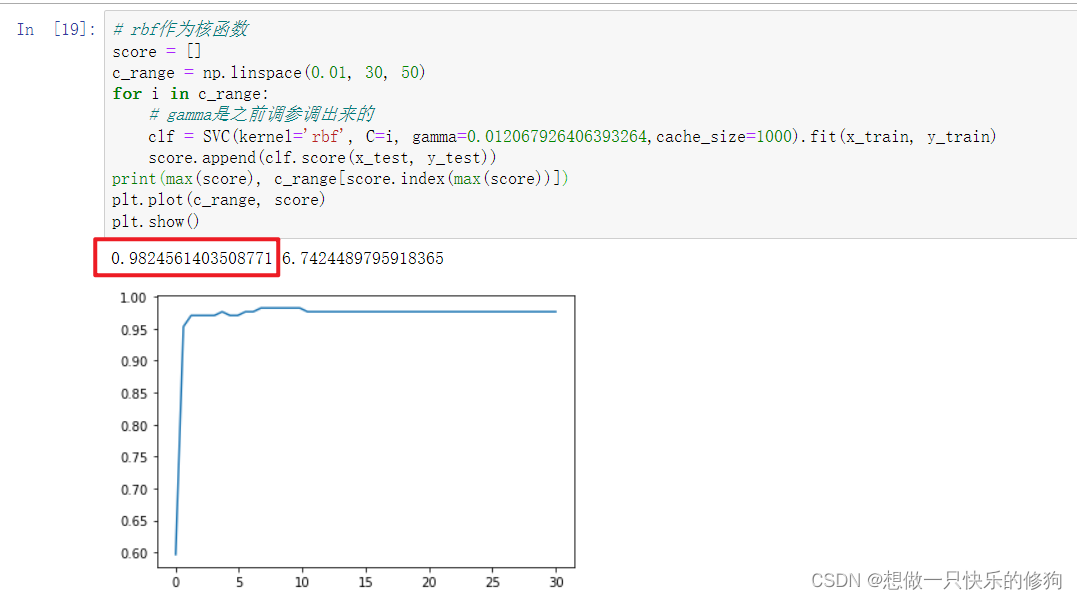
啊啊啊啊啊啊啊啊啊啊,努力没有白费啊!
结论
针对sklearn中的乳腺癌数据集,使用SVC作为算法模型,进行调参,最优的参数组合为:
| 核函数 | gamma | 惩罚项C |
|---|---|---|
| rbf | 0.012067926406393264 | 6.7424489795918365 |
【PS】这是我看看sklearn菜菜的视频学习笔记~





















 1890
1890











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










