MOE里的是内置的SVL代码、没时间学了…就找了一套流程去实现MOE里的数据和Python去交互:
具体负责操作的是MDB文件(MOE内置的文件格式,与微软的数据库文件没有任何关系!这种文件很难用非MOE软件打开…)。但是MDB可以保存成下列文件: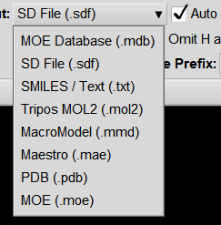
于是我们可以用SDF文件作为媒介实现交互,我们把MDB文件另存为SDF文件,就可以实现python读取了!然后要是再用SDF文件的话就再用MOE打开,点击Import to Database就出现MDB文件了:

from rdkit.Chem import PandasTools
import rdkit.Chem.Draw as Draw
import matplotlib.pyplot as plt
########1.导入数据########
SDFfile=PandasTools.LoadSDF("E:/MOE/moe_2019.0102-3.10install/sample/mol/QSAR_STUDY/bbb.sdf")
########2.对列处理########
SDFfile_colnames=SDFfile.columns
#axis=1 是对列处理,axis=0 是对行处理;还要加inplace去更新内存
#SDFfile.drop(['ID'],axis=1,inplace=True)
#把原来的ID 换成index
SDFfile['ID']=SDFfile.index
########3.查看分子的图片,先保存再查看图片
Draw.MolToImage(SDFfile['ROMol'][1])
Draw.MolToImage(SDFfile['ROMol'][1]).save("E:/MOE/moe_2019.0102-3.10install/sample/mol/QSAR_STUDY/MOL_1.jpg")
######4 dataframe画图
fig =plt.figure(100)
x=SDFfile['ID'] #元素类型:<class 'numpy.int64'>
#y=SDFfile['logBB'] #元素类型:<class 'str'> 会导致y轴顺序发生变化
y=[np.float64(i) for i in SDFfile['logBB']]
z=[np.float64(i) for i in SDFfile['$PRED']]
plt.grid(True)
plt.plot(x, y, z )
fig.show()
########5.保存sdffile
#用这一行代码,实现代码和MOE软件的互相转换,后面的properties里写需要保存的列
PandasTools.WriteSDF(SDFfile,"E:/MOE/moe_2019.0102-3.10install/sample/mol/QSAR_STUDY/bbb_NEW.sdf", properties=['logBB'],allNumeric=True)
#######





















 1万+
1万+











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








