今天给同学们分享一篇双疾病+分子药物的生信文章“Bioinformatics and system biology approach to identify potential common pathogenesis for COVID-19 infection and osteoarthritis”,这篇文章于2023年6月8日发表在Scientific Reports期刊上,影响因子为4.996。


越来越多的证据表明,骨关节炎(OA)患者的冠状病毒2019(COVID-19)感染率较高,感染后预后较差。此外,科学家还发现,COVID-19 感染可能会导致肌肉骨骼系统发生病理变化。然而,其机制仍未完全阐明。本研究旨在进一步探索OA和COVID-19感染患者的共同发病机制,并寻找候选药物。
1. COVID-19 和 OA DEGs 的鉴定
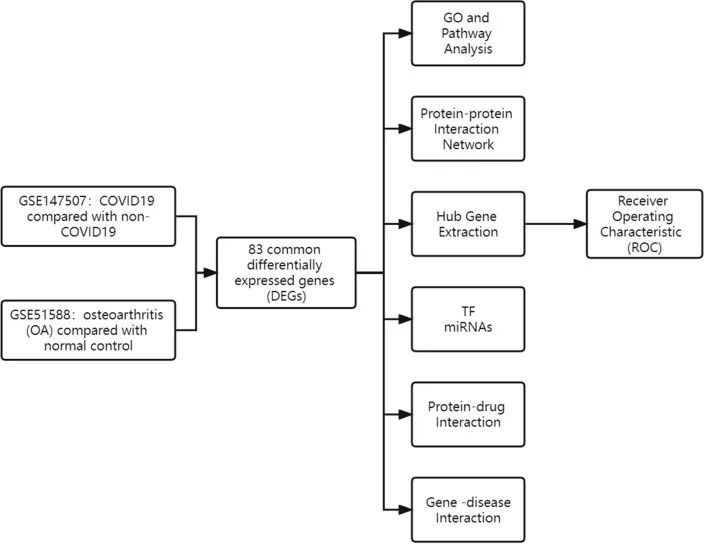
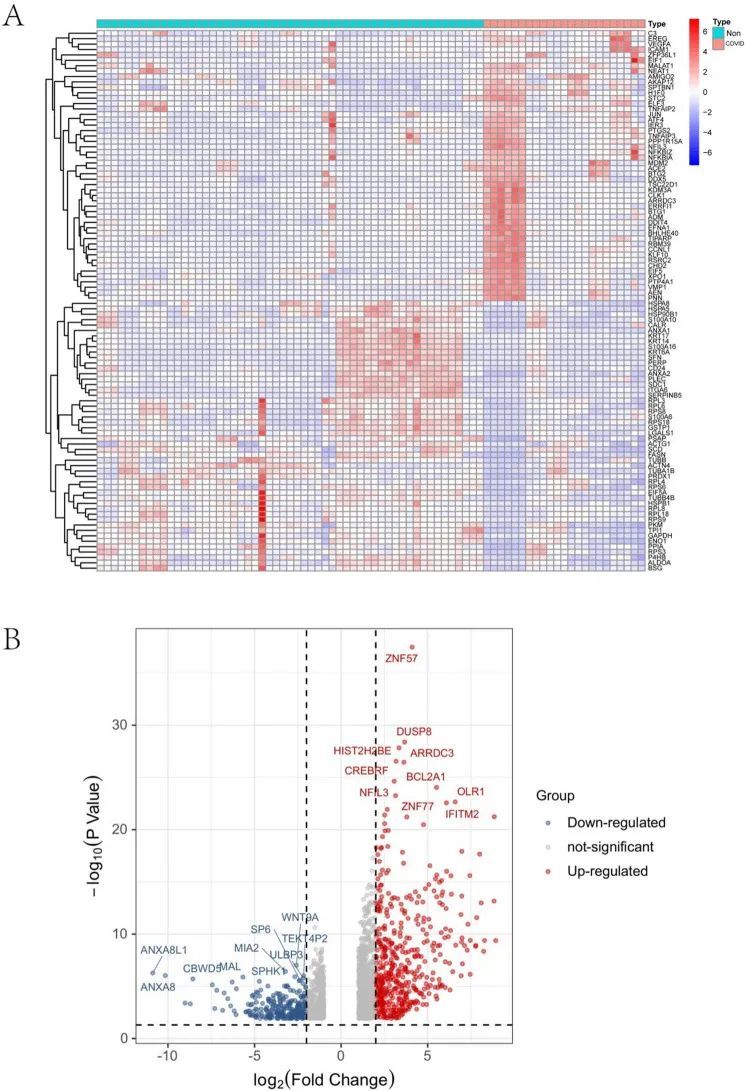
本研究的整体流程图如图 1 所示。在 GSE147507 数据集中发现了 3569 个 DEGs,在 GSE51588 数据集中发现了 861 个 DEGs。图 2 和图 3通过热图和火山图分别显示了COVID-19患者和非COVID-19患者之间以及OA患者和正常对照组之间的DEGs分布。GSE147507数据集和GSE51588数据集的DEGs交集通过维恩图直观显示,共筛选出83个共享DEGs(图4)。

图1 本研究总体工作流程示意图

图2 COVID-19 患者 DEGs 的表达特征








 研究通过生物信息学方法分析了COVID-19和骨关节炎(OA)的共同发病机制,识别了DEGs并探讨了可能的致病通路。关键基因的发现为个性化疗法和新药研发提供了线索。
研究通过生物信息学方法分析了COVID-19和骨关节炎(OA)的共同发病机制,识别了DEGs并探讨了可能的致病通路。关键基因的发现为个性化疗法和新药研发提供了线索。
 最低0.47元/天 解锁文章
最低0.47元/天 解锁文章



















 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










