【ANTs】医学影像处理工具ANTs - 即插即用的安装教程,无需编译
ANTs(Advanced Normalization Tools)是一个用于处理医学图像的先进工具集。ANTs 允许人们组织、可视化和统计探索大型生物医学图像集,具有医学图像配准、分割等强大功能。
在以往的博客里,ANTs的源码编译安装教程已经较为详细,由于网络和操作系统的缘故,安装过程可能出现一系列问题。因此,这种方法往往并不适用于初学者或具有较少Linux基础的使用者。
我将在这篇博客介绍ANTs的一种简单的安装教程,它基于官方的Releases,只需要几步便可以完成。
基于Releases的安装
-
前往ANTs项目的Github主页link
-
在右侧有Releases字样,点击此处
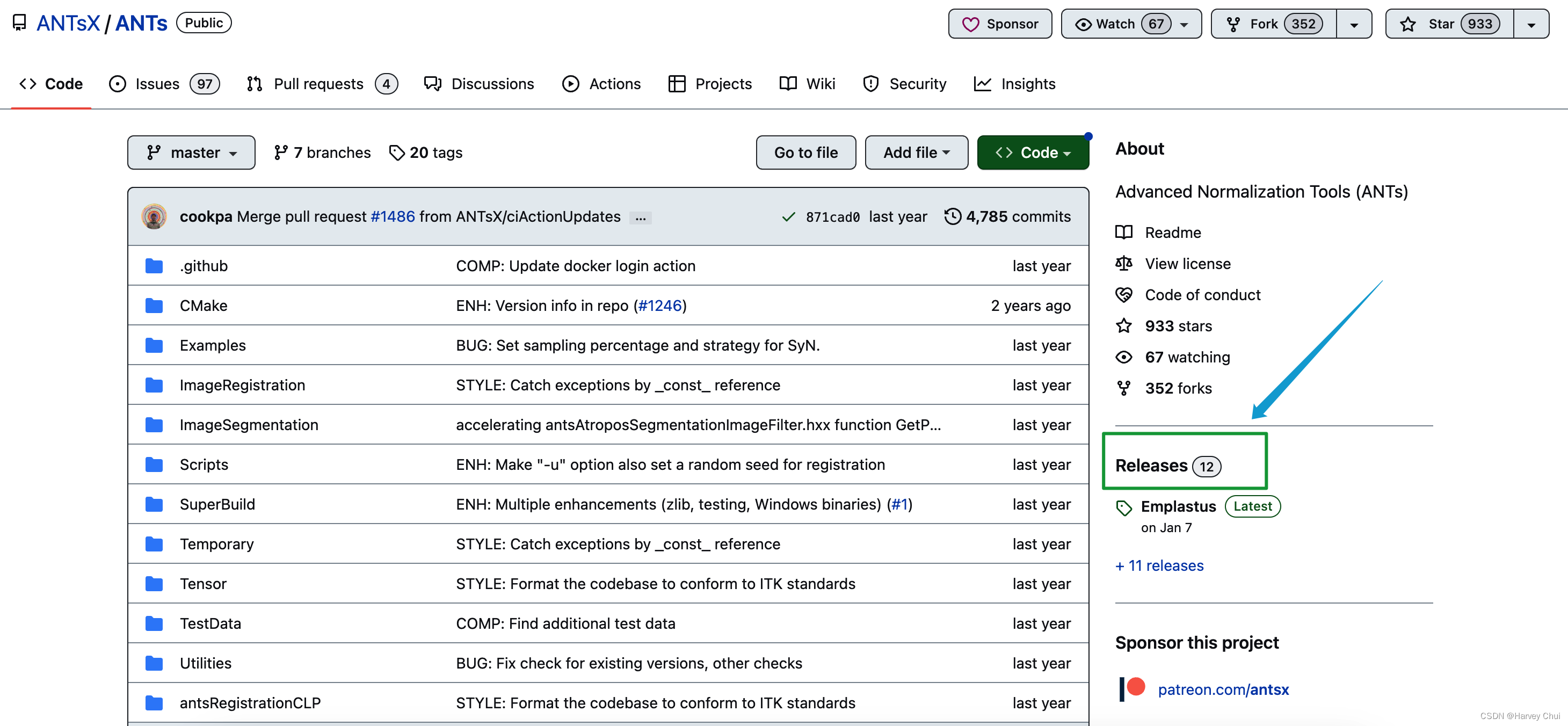
-
你将能找到来自官方的编译后的版本,选择发布日期靠前的Release,在其中的Asset部分找到适合你电脑操作系统和版本的名称,点击即可下载
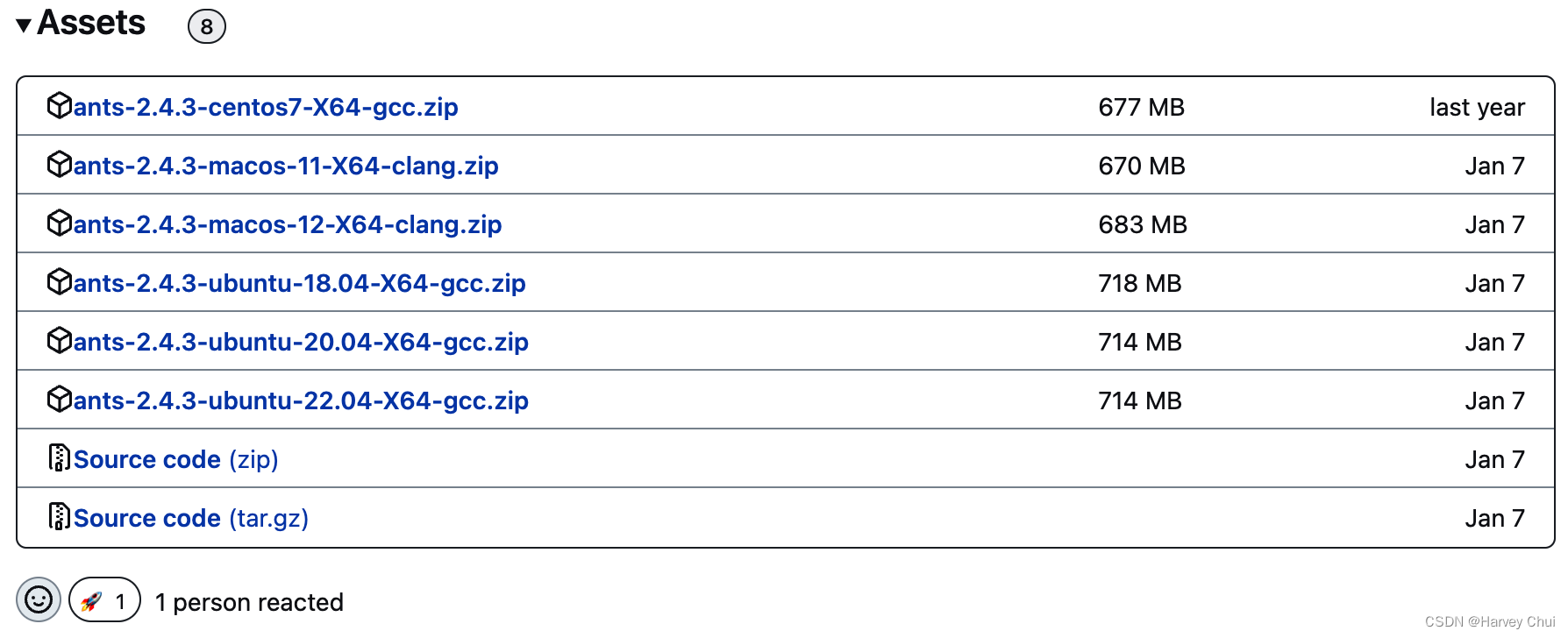
注意,目前ANTs只支持MacOS、CentOS及Ubuntu,如果是Linux的其他发行版本建议使用源码安装;对于Windows用户,建议使用Ubuntu子系统完成安装。
-
下载之后的文件夹是这样的格式:
ants-2.x.x # 版本号码 ├─ bin # 存放程序集 │ ├─ AddNoiseToImage # 可执行文件 │ ├─ antsASLProcessing.sh # ANTs具体的function,后面会用到 │ ├─ ... │ └─ WarpTimeSeriesImageMultiTransform # 可执行文件 └─ lib # 存放静态库文件 -
下载的分发版本和编译的版本文件结构略有不同,下载的分发版本是没有
/script文件夹的,所有的.sh脚本文件都存放在bin目录下 -
在运行前,需要写入
ANTSPATH作为环境变量,例如,我的ants-2.x.x文件放在了这个目录下:/Users/harvel/code/ants-2.4.3,那么需要执行:export ANTSPATH=/Users/harvel/code/ants-2.4.3/bin注意:ANTSPATH是ANTs下的bin目录;当然也可以写入
.bash_profile,这样做的好处是不需要每次使用ANTs时重新声明环境变量
ANTs使用(以配准为例)
- 然后,就可以开始使用ANTs进行分割、配准等操作了,请先进入ANTs的
bin目录作为working directory,确保当前所在目录有相关.sh文件,然后进行操作,例如:
上述命令是将antsRegistrationSyN.sh -d 3 -f target.nii.gz -m example.nii.gz -o reg_example.nii.gz配准到target.nii.gz,维度为3,输出文件开头为reg_,最终将输出五个文件,包括后者配准到前者的图像。整个过程将会执行五分钟以上。如果想要更快速执行,可以使用ANTs提供的更快的方法:
如果只想保留antsRegistrationSyNQuick.sh -d 3 -f target.nii.gz -m example.nii.gz -o reg_example.nii.gz配准到target.nii.gz的文件,可以在上一条指令执行的基础上继续执行rm "*1InverseWarp.nii.gz" rm "*1Warp.nii.gz" rm "*0GenericAffine.mat" rm "*InverseWarped.nii.gz" - 最终将保留一个名为
reg_Warp.nii.gz的文件,生成在bin目录下,可以使用mv命令每次执行之后将它重命名并转移到目标目录下,这里不再赘述。为了使用方便,你可以把脚本中的-o后换成你转换的文件标识名称,这是一个简单的使用例:#!/bin/bash input_dir="usr/data/input" output_dir="usr/data/output" for i in {1..50}; do ./antsRegistrationSyNQuick.sh -d 3 -f "${input_dir}/${i}_target.nii.gz" -m "${input_dir}/${i}.nii.gz" -o "$i" # Delete specified files rm "*1InverseWarp.nii.gz" rm "*1Warp.nii.gz" rm "*0GenericAffine.mat" rm "*InverseWarped.nii.gz" # move file mv "*Warp.nii.gz" "${output_dir}/" done
如果有问题,欢迎留言~
同样也欢迎转发,转载请注明出处,谢谢。








 ANTs是一个强大的医学影像处理工具,本文提供了一种简单的方法来安装ANTs,无需编译源码,主要针对官方Releases,适用于MacOS、CentOS及Ubuntu用户。安装完成后,通过设置ANTSPATH环境变量即可使用,文中还以配准操作为例介绍了ANTs的基本使用方法。
ANTs是一个强大的医学影像处理工具,本文提供了一种简单的方法来安装ANTs,无需编译源码,主要针对官方Releases,适用于MacOS、CentOS及Ubuntu用户。安装完成后,通过设置ANTSPATH环境变量即可使用,文中还以配准操作为例介绍了ANTs的基本使用方法。
















 1646
1646

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








