部署
去这个网址,下载ncbi-blast-2.13.0+-x64-linux.tar.gz,也就是Linux版本
第二步:
在linux上创建好文件夹,比如我在/home下创建soft文件夹,用于安装Blast软件.
第三步:把下载好的压缩包,放到文件夹下,进行解压,命令如:tar -zxvf ncbi-blast-2.13.0+-x64-linux.tar.gz
第四步:
进入程序的文件夹里面的bin目录。输入pwd ,查看当前路径,复制路径
第五步:
添加环境变量,使用vim ~/.bashrc命令,编辑文件,在最后一行添加
export PATH=刚刚复制的路径:$PATH
然后保存退出
第六步:
使用 source ~/.bashrc 命令让其生效
第七步:
使用 blastn -version 这个命令出现版本号,就安装好了
使用
在使用之前需要准备一个fasta库,也就是所有的序列信息
还有要比对的源数据,也是一个fasta文件
可以将他们存放在另一个文件夹下
第一步:建库
命令如下
makeblastdb -in SRR7.fasta -dbtype nucl
其中SRR7.fasta是数据库文件,这属于简单建库,后面还有其他参数,如下
--------------------------------------------
makeblastdb -in 数据库文件 -dbtype 序列类型 -parse_seqids -out database_name -logfile File_Name
-dbtype 后接序列类型,nucl为核苷酸,prot为蛋白
-parse_seqids 推荐加上
-out 后接数据库名 (暂时没发现这个有什么用)
-logfile 日志文件,如果没有默认输出到屏幕
第二步:进行序列比对
命令举例:
blastn -query /home/data/blast/query.fasta -db /home/data/blast/SRR7.fasta -out /home/result/result.txt -evalue 1e-5 -outfmt 6
这样就会在当前路径下生成a.txt的结果文件
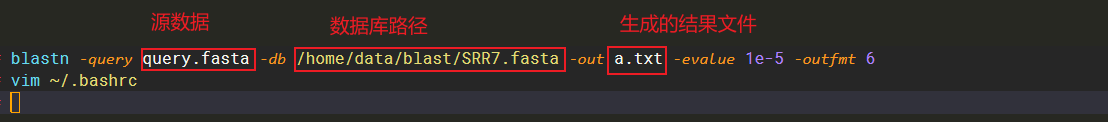
参数解释:
-query: 输入文件路径及文件名
-out:输出文件路径及文件名
-db:格式化了的数据库路径及数据库名
-outfmt:输出文件格式,总共有12种格式,6是tabular格式对应之前BLAST的m8格式
-evalue:设置输出结果的e-value值
-num_alignments 显示比对数Default = 250
-num_descriptions:单行描述的最大数目 default=50
-num_threads:线程





















 1479
1479

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








