一、通俗理解概念
NMF(Non-negative matrix factorization),即对于任意给定的一个非负矩阵 V,其能够寻找到一个非负矩阵 W 和一个非负矩阵 H,满足条件
V
=
W
×
H
V=W \times H
V=W×H,即将一个非负的矩阵分解为左右两个非负矩阵的乘积。
V
=
W
×
H
V = W \times H
V=W×H
其中,
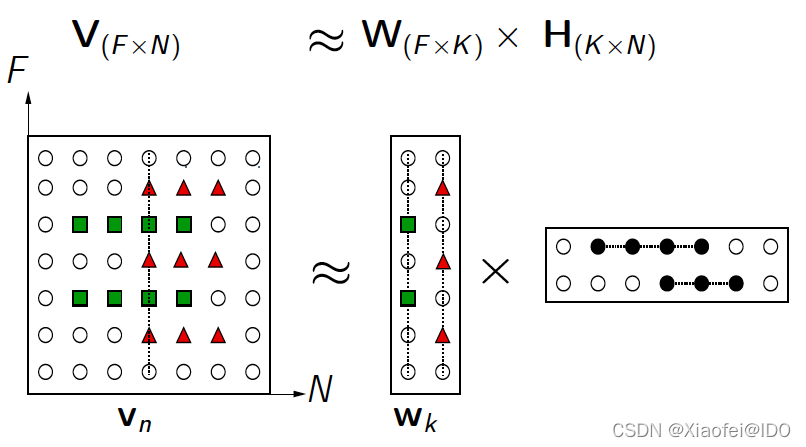
- V矩阵中每一列代表一个观测(observation),每一行代表一个特征(feature);
- W矩阵称为基矩阵或特征的权重矩阵,代表每个特征对聚类结果的贡献度;
- H矩阵称为系数矩阵或样本的权重矩阵,代表每个样本对聚类结果的贡献度;
- 此时,用系数矩阵H代替原始矩阵,就可以实现对原始矩阵进行降维,得到数据特征的降维矩阵,从而减少存储空间。
图解如下:
二、python实现
在sklearn封装了NMF的实现,但是注意sklearn中输入数据的格式是(samples, features):
from sklearn.decomposition import NMF
from sklearn.datasets import load_iris
X, _ = load_iris(True)
# can be used for example for dimensionality reduction, source separation or topic extraction
# 个人认为最重要的参数是n_components、alpha、l1_ratio、solver
nmf = NMF(n_components=2, # k value,默认会保留全部特征
init=None, # W H 的初始化方法,包括'random' | 'nndsvd'(默认) | 'nndsvda' | 'nndsvdar' | 'custom'.
solver='cd', # 'cd' | 'mu'
beta_loss='frobenius', # {'frobenius', 'kullback-leibler', 'itakura-saito'},一般默认就好
tol=1e-4, # 停止迭代的极限条件
max_iter=200, # 最大迭代次数
random_state=None,
alpha=0., # 正则化参数
l1_ratio=0., # 正则化参数
verbose=0, # 冗长模式
shuffle=False # 针对"cd solver"
)
# -----------------函数------------------------
print('params:', nmf.get_params()) # 获取构造函数参数的值,也可以nmf.attr得到,所以下面我会省略这些属性
# 下面四个函数很简单,也最核心,例子中见
nmf.fit(X)
W = nmf.fit_transform(X)
W = nmf.transform(X)
nmf.inverse_transform(W)
# -----------------属性------------------------
H = nmf.components_ # H矩阵
print('reconstruction_err_', nmf.reconstruction_err_) # 损失函数值
print('n_iter_', nmf.n_iter_) # 实际迭代次数
注意点:
- init参数中,nndsvd(默认)更适用于sparse factorization,其变体则适用于dense factorization.
- solver参数中,如果初始化中产生很多零值,Multiplicative Update (mu) 不能很好更新。所以mu一般不和nndsvd使用,而和其变体nndsvda、nndsvdar使用。
- solver参数中,cd只能优化Frobenius norm函数;而mu可以更新所有损失函数
图像特征提取
这里再举一个NMF在图像特征提取的应用,来自官方示例,根据我的需要改动了一些:
from time import time
from numpy.random import RandomState
import matplotlib.pyplot as plt
from sklearn.datasets import fetch_olivetti_faces
from sklearn import decomposition
n_row, n_col = 2, 3
n_components = n_row * n_col
image_shape = (64, 64)
rng = RandomState(0)
# #############################################################################
# Load faces data
dataset = fetch_olivetti_faces('./', True,
random_state=rng)
faces = dataset.data
n_samples, n_features = faces.shape
print("Dataset consists of %d faces, features is %s" % (n_samples, n_features))
def plot_gallery(title, images, n_col=n_col, n_row=n_row, cmap=plt.cm.gray):
plt.figure(figsize=(2. * n_col, 2.26 * n_row))
plt.suptitle(title, size=16)
for i, comp in enumerate(images):
plt.subplot(n_row, n_col, i + 1)
vmax = max(comp.max(), -comp.min())
plt.imshow(comp.reshape(image_shape), cmap=cmap,
interpolation='nearest',
vmin=-vmax, vmax=vmax)
plt.xticks(())
plt.yticks(())
plt.subplots_adjust(0.01, 0.05, 0.99, 0.93, 0.04, 0.)
# #############################################################################
estimators = [
('Non-negative components - NMF',
decomposition.NMF(n_components=n_components, init='nndsvda', tol=5e-3))
]
# #############################################################################
# Plot a sample of the input data
plot_gallery("First centered Olivetti faces", faces[:n_components])
# #############################################################################
# Do the estimation and plot it
for name, estimator in estimators:
print("Extracting the top %d %s..." % (n_components, name))
t0 = time()
data = faces
estimator.fit(data)
train_time = (time() - t0)
print("done in %0.3fs" % train_time)
components_ = estimator.components_
print('components_:', components_.shape, '\n**\n', components_)
plot_gallery('%s - Train time %.1fs' % (name, train_time),
components_)
plt.show()
#---------------------------其他注释---------------------------
V矩阵:400*4096
W矩阵:400*6
H矩阵:6*4096

























 1366
1366

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








