概述
什么是聚类分析
聚类分析是在数据中发现数据对象之间的关系,将数据进行分组,组内的相似性越大,组间的差别越大,则聚类效果越好。
不同的簇类型
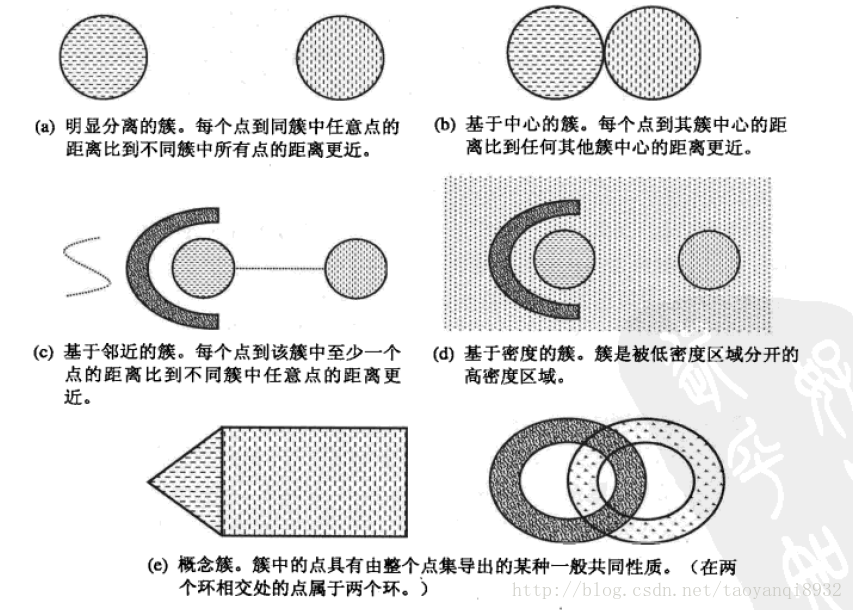
聚类旨在发现有用的对象簇,在现实中我们用到很多的簇的类型,使用不同的簇类型划分数据的结果是不同的,如下的几种簇类型。
明显分离的
可以看到(a)中不同组中任意两点之间的距离都大于组内任意两点之间的距离,明显分离的簇不一定是球形的,可以具有任意的形状。
基于原型的
簇是对象的集合,其中每个对象到定义该簇的原型的距离比其他簇的原型距离更近,如(b)所示的原型即为中心点,在一个簇中的数据到其中心点比到另一个簇的中心点更近。这是一种常见的基于中心的簇,最常用的K-Means就是这样的一种簇类型。
这样的簇趋向于球形。
基于密度的
簇是对象的密度区域,(d)所示的是基于密度的簇,当簇不规则或相互盘绕,并且有早上和离群点事,常常使用基于密度的簇定义。
关于更多的簇介绍参考《数据挖掘导论》。
基本的聚类分析算法
1. K均值:
基于原型的、划分的距离技术,它试图发现用户指定个数(K)的簇。
2. 凝聚的层次距离:
思想是开始时,每个点都作为一个单点簇,然后,重复的合并两个最靠近的簇,直到尝试单个、包含所有点的簇。
3. DBSCAN:
一种基于密度的划分距离的算法,簇的个数有算法自动的确定,低密度中的点被视为噪声而忽略,因此其不产生完全聚类。
距离量度
不同的距离量度会对距离的结果产生影响,常见的距离量度如下所示:
K-Means算法
下面介绍K均值算法:
优点:易于实现
缺点:可能收敛于局部最小值,在大规模数据收敛慢
算法思想较为简单如下所示:
选择K个点作为初始质心
repeat
将每个点指派到最近的质心,形成K个簇
重新计算每个簇的质心
until 簇不发生变化或达到最大迭代次数 这里的重新计算每个簇的质心,如何计算的是根据目标函数得来的,因此在开始时我们要考虑距离度量和目标函数。
考虑欧几里得距离的数据,使用误差平方和(Sum of the Squared Error,SSE)作为聚类的目标函数,两次运行K均值产生的两个不同的簇集,我们更喜欢SSE最小的那个。
k表示k个聚类中心,ci表示第几个中心,dist表示的是欧几里得距离。
这里有一个问题就是为什么,我们更新质心是让所有的点的平均值,这里就是SSE所决定的。
下面用Python进行实现
# dataSet样本点,k 簇的个数
# disMeas距离量度,默认为欧几里得距离
# createCent,初始点的选取
def kMeans(dataSet, k, distMeas=distEclud, createCent=randCent):
m = shape(dataSet)[0] #样本数
clusterAssment = mat(zeros((m,2))) #m*2的矩阵
centroids = createCent(dataSet, k) #初始化k个中心
clusterChanged = True
while clusterChanged: #当聚类不再变化
clusterChanged = False
for i in range(m):
minDist = inf; minIndex = -1
for j in range(k): #找到最近的质心
distJI = distMeas(centroids[j,:],dataSet[i,:])
if distJI < minDist:
minDist = distJI; minIndex = j
if clusterAssment[i,0] != minIndex: clusterChanged = True
# 第1列为所属质心,第2列为距离
clusterAssment[i,:] = minIndex,minDist**2
print centroids
# 更改质心位置
for cent in range(k):
ptsInClust = dataSet[nonzero(clusterAssment[:,0].A==cent)[0]]
centroids[cent,:] = mean(ptsInClust, axis=0)
return centroids, clusterAssment重点理解一下:
for cent in range(k):
ptsInClust = dataSet[nonzero(clusterAssment[:,0].A==cent)[0]]
centroids[cent,:] = mean(ptsInClust, axis=0) 循环每一个质心,找到属于当前质心的所有点,然后根据这些点去更新当前的质心。
nonzero()返回的是一个二维的数组,其表示非0的元素位置。
>>> from numpy import *
>>> a=array([[1,0,0],[0,1,2],[2,0,0]])
>>> a
array([[1, 0, 0],
[0, 1, 2],
[2, 0, 0]])
>>> nonzero(a)
(array([0, 1, 1, 2]), array([0, 1, 2, 0]))表示第[0,0],[1,1] … 位非零元素。第一个数组为行,第二个数组为列,两者进行组合得到的。
ptsInClust = dataSet[nonzero(clusterAssment[:,0].A==cent)[0]]
因此首先先比较clusterAssment[:,0].A==cent的真假,如果为真则记录了他所在的行,因此在用切片进行取值。
一些辅助的函数:
def loadDataSet(fileName): #general function to parse tab -delimited floats
dataMat = [] #assume last column is target value
fr = open(fileName)
for line in fr.readlines():
curLine = line.strip().split('\t')
fltLine = map(float,curLine) #map all elements to float()
dataMat.append(fltLine)
return dataMat
def distEclud(vecA, vecB):
return sqrt(sum(power(vecA - vecB, 2))) #la.norm(vecA-vecB)
def randCent(dataSet, k):
n = shape(dataSet)[1]
centroids = mat(zeros((k,n)))#create centroid mat
for j in range(n):#create random cluster centers, within bounds of each dimension
minJ = min(dataSet[:,j])
rangeJ = float(max(dataSet[:,j]) - minJ)
centroids[:,j] = mat(minJ + rangeJ * random.rand(k,1))
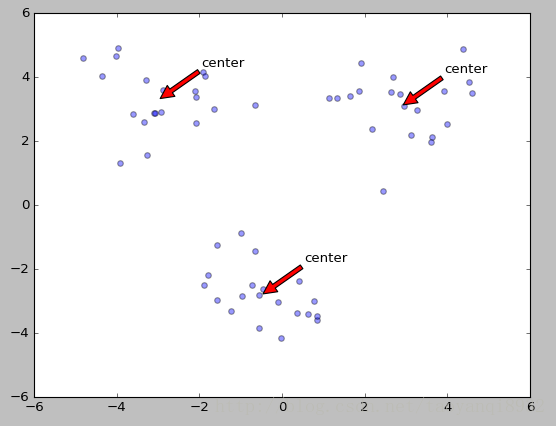
return centroids运行和结果
将上述代码写到kMeans.py中,然后打开python交互端。
>>> from numpy import *
>>> import kMeans
>>> dat=mat(kMeans.loadDataSet('testSet.txt')) #读入数据
>>> center,clust=kMeans.kMeans(dat,4)
[[ 0.90796996 5.05836784]
[-2.88425582 0.01687006]
[-3.3447423 -1.01730512]
[-0.32810867 0.48063528]]
[[ 1.90508653 3.530091 ]
[-3.00984169 2.66771831]
[-3.38237045 -2.9473363 ]
[ 2.22463036 -1.37361589]]
[[ 2.54391447 3.21299611]
[-2.46154315 2.78737555]
[-3.38237045 -2.9473363 ]
[ 2.8692781 -2.54779119]]
[[ 2.6265299 3.10868015]
[-2.46154315 2.78737555]
[-3.38237045 -2.9473363 ]
[ 2.80293085 -2.7315146 ]]
# 作图
>>>kMeans(dat,center)绘图的程序如下:
def draw(data,center):
length=len(center)
fig=plt.figure
# 绘制原始数据的散点图
plt.scatter(data[:,0],data[:,1],s=25,alpha=0.4)
# 绘制簇的质心点
for i in range(length):
plt.annotate('center',xy=(center[i,0],center[i,1]),xytext=\
(center[i,0]+1,center[i,1]+1),arrowprops=dict(facecolor='red'))
plt.show()K-Means算法的缺陷
k均值算法非常简单且使用广泛,但是其有主要的两个缺陷:
1. K值需要预先给定,属于预先知识,很多情况下K值的估计是非常困难的,对于像计算全部微信用户的交往圈这样的场景就完全的没办法用K-Means进行。对于可以确定K值不会太大但不明确精确的K值的场景,可以进行迭代运算,然后找出Cost Function最小时所对应的K值,这个值往往能较好的描述有多少个簇类。
2. K-Means算法对初始选取的聚类中心点是敏感的,不同的随机种子点得到的聚类结果完全不同
3. K均值算法并不是很所有的数据类型。它不能处理非球形簇、不同尺寸和不同密度的簇,银冠指定足够大的簇的个数是他通常可以发现纯子簇。
4. 对离群点的数据进行聚类时,K均值也有问题,这种情况下,离群点检测和删除有很大的帮助。
下面对初始质心的选择进行讨论:
拙劣的初始质心
当初始质心是随机的进行初始化的时候,K均值的每次运行将会产生不同的SSE,而且随机的选择初始质心结果可能很糟糕,可能只能得到局部的最优解,而无法得到全局的最优解。如下图所示:
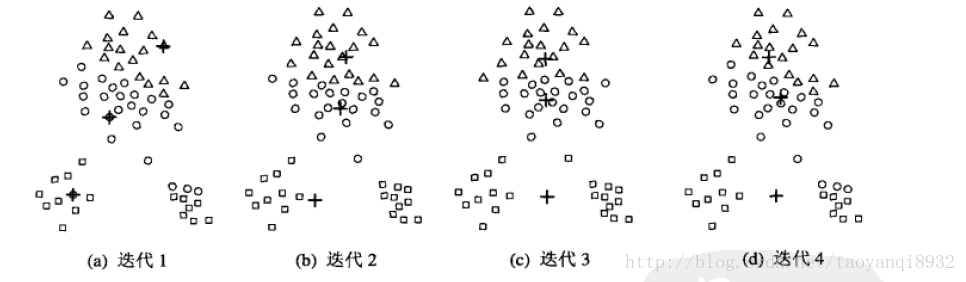
可以看到程序迭代了4次终止,其得到了局部的最优解,显然我们可以看到其不是全局最优的,我们仍然可以找到一个更小的SSE的聚类。
随机初始化的局限
你可能会想到:多次运行,每次使用一组不同的随机初始质心,然后选择一个具有最小的SSE的簇集。该策略非常的简单,但是效果可能不是很好,这取决于数据集合寻找的簇的个数。
关于更多,参考《数据挖掘导论》
K-Means优化算法
为了克服K-Means算法收敛于局部最小值的问题,提出了一种二分K-均值(bisecting K-means)
bisecting K-means
算法的伪代码如下:
将所有的点看成是一个簇
当簇小于数目k时
对于每一个簇
计算总误差
在给定的簇上进行K-均值聚类,k值为2
计算将该簇划分成两个簇后总误差
选择是的误差最小的那个簇进行划分完整的Python代码如下:
def biKmeans(dataSet, k, distMeas=distEclud):
m = shape(dataSet)[0]
# 这里第一列为类别,第二列为SSE
clusterAssment = mat(zeros((m,2)))
# 看成一个簇是的质心
centroid0 = mean(dataSet, axis=0).tolist()[0]
centList =[centroid0] #create a list with one centroid
for j in range(m): #计算只有一个簇是的误差
clusterAssment[j,1] = distMeas(mat(centroid0), dataSet[j,:])**2
# 核心代码
while (len(centList) < k):
lowestSSE = inf
# 对于每一个质心,尝试的进行划分
for i in range(len(centList)):
# 得到属于该质心的数据
ptsInCurrCluster =\ dataSet[nonzero(clusterAssment[:,0].A==i)[0],:]
# 对该质心划分成两类
centroidMat, splitClustAss = kMeans(ptsInCurrCluster, 2, distMeas)
# 计算该簇划分后的SSE
sseSplit = sum(splitClustAss[:,1])
# 没有参与划分的簇的SSE
sseNotSplit = sum(clusterAssment[nonzero(clusterAssment[:,0].A!=i)[0],1])
print "sseSplit, and notSplit: ",sseSplit,sseNotSplit
# 寻找最小的SSE进行划分
# 即对哪一个簇进行划分后SSE最小
if (sseSplit + sseNotSplit) < lowestSSE:
bestCentToSplit = i
bestNewCents = centroidMat
bestClustAss = splitClustAss.copy()
lowestSSE = sseSplit + sseNotSplit
# 较难理解的部分
bestClustAss[nonzero(bestClustAss[:,0].A == 1)[0],0] = len(centList) #change 1 to 3,4, or whatever
bestClustAss[nonzero(bestClustAss[:,0].A == 0)[0],0] = bestCentToSplit
print 'the bestCentToSplit is: ',bestCentToSplit
print 'the len of bestClustAss is: ', len(bestClustAss)
centList[bestCentToSplit] = bestNewCents[0,:].tolist()[0]#replace a centroid with two best centroids
centList.append(bestNewCents[1,:].tolist()[0])
clusterAssment[nonzero(clusterAssment[:,0].A == bestCentToSplit)[0],:]= bestClustAss#reassign new clusters, and SSE
return mat(centList), clusterAssment下面对最后的代码进行解析:
bestClustAss[nonzero(bestClustAss[:,0].A == 1)[0],0] = len(centList) #change 1 to 3,4, or whatever
bestClustAss[nonzero(bestClustAss[:,0].A == 0)[0],0] = bestCentToSplit这里是更改其所属的类别,其中bestClustAss = splitClustAss.copy()是进行k-means后所返回的矩阵,其中第一列为类别,第二列为SSE值,因为当k=2是k-means返回的是类别0,1两类,因此这里讲类别为1的更改为其质心的长度,而类别为0的返回的是该簇原先的类别。
举个例子:
例如:目前划分成了0,1两个簇,而要求划分成3个簇,则在算法进行时,假设对1进行划分得到的SSE最小,则将1划分成了2个簇,其返回值为0,1两个簇,将返回为1的簇改成2,返回为0的簇改成1,因此现在就有0,1,2三个簇了。
centList[bestCentToSplit] = bestNewCents[0,:].tolist()[0]#replace a centroid with two best centroids
centList.append(bestNewCents[1,:].tolist()[0])
clusterAssment[nonzero(clusterAssment[:,0].A == bestCentToSplit)[0],:]= bestClustAss#reassign new clusters, and SSE其中bestNewCents是k-means的返回簇中心的值,其有两个值,分别是第一个簇,和第二个簇的坐标(k=2),这里将第一个坐标赋值给 centList[bestCentToSplit] = bestNewCents[0,:].tolist()[0],将另一个坐标添加到centList中 centList.append(bestNewCents[1,:].tolist()[0])
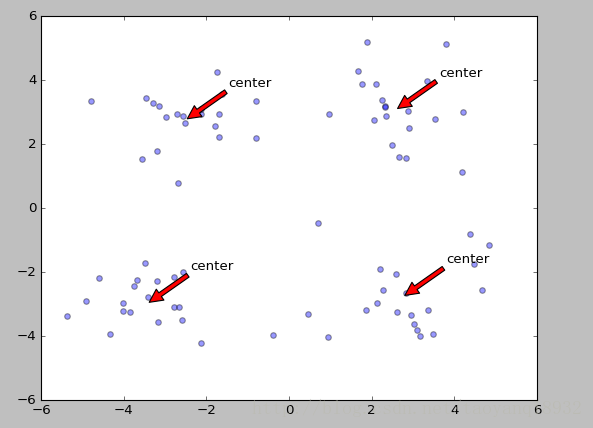
运行与结果
>>> from numpy import *
>>> import kMeans
>>> dat = mat(kMeans.loadDataSet('testSet2.txt'))
>>> cent,assment=kMeans.biKmeans(dat,3)
sseSplit, and notSplit: 570.722757425 0.0
the bestCentToSplit is: 0
the len of bestClustAss is: 60
sseSplit, and notSplit: 68.6865481262 38.0629506357
sseSplit, and notSplit: 22.9717718963 532.659806789
the bestCentToSplit is: 0
the len of bestClustAss is: 40可以看到进行了两次的划分,第一次最好的划分是在0簇,第二次划分是在1簇。
可视化如下图所示:
Mini Batch k-Means
在原始的K-means算法中,每一次的划分所有的样本都要参与运算,如果数据量非常大的话,这个时间是非常高的,因此有了一种分批处理的改进算法。
使用Mini Batch(分批处理)的方法对数据点之间的距离进行计算。
Mini Batch的好处:不必使用所有的数据样本,而是从不同类别的样本中抽取一部分样本来代表各自类型进行计算。n 由于计算样本量少,所以会相应的减少运行时间n 但另一方面抽样也必然会带来准确度的下降。










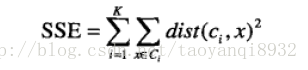















 5196
5196

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








