【中文】【吴恩达课后编程作业】Course 2 - 改善深层神经网络 - 第一周作业(1&2&3) - 初始化、正则化、梯度校验
声明
本文参考Kulbear 的 【Initialization】和【Regularization】 和 【Gradient Checking】,以及念师的【10. 初始化、正则化、梯度检查实战】,我基于以上的文章加以自己的理解发表这篇博客,力求让大家以最轻松的姿态理解吴恩达的视频,如有不妥的地方欢迎大家指正。
资料下载
- 下载点1:本文所使用的资料已上传到百度网盘【点击下载】,提取码:imgq ,请在开始之前下载好所需资料,或者在本文底部copy资料代码。
- 下载点2(数据包):**【data.mat】 **, 下载后名称为9.mat,需要手动更名为data.mat,下载来源:念师,其他的代码在文章底部。
【博主使用的python版本:3.6.2】
开始之前
老规矩,我们在开始之前说一下我们要干什么。在这篇文章中,我们要干三件事:
1. 初始化参数:
1.1:使用0来初始化参数。
1.2:使用随机数来初始化参数。
1.3:使用抑梯度异常初始化参数(参见视频中的梯度消失和梯度爆炸)。
2. 正则化模型:
2.1:使用二范数对二分类模型正则化,尝试避免过拟合。
2.2:使用随机删除节点的方法精简模型,同样是为了尝试避免过拟合。
3. 梯度校验 :对模型使用梯度校验,检测它是否在梯度下降的过程中出现误差过大的情况。
我们说完了我们要干什么,我们这就开始吧。
我们就开始导入相关的库:
import numpy as np
import matplotlib.pyplot as plt
import sklearn
import sklearn.datasets
import init_utils #第一部分,初始化
import reg_utils #第二部分,正则化
import gc_utils #第三部分,梯度校验
#%matplotlib inline #如果你使用的是Jupyter Notebook,请取消注释。
plt.rcParams['figure.figsize'] = (7.0, 4.0) # set default size of plots
plt.rcParams['image.interpolation'] = 'nearest'
plt.rcParams['image.cmap'] = 'gray'
初始化参数
我们在初始化之前,我们来看看我们的数据集是怎样的:
读取并绘制数据
train_X, train_Y, test_X, test_Y = init_utils.load_dataset(is_plot=True)
执行结果:

我们将要建立一个分类器把蓝点和红点分开,在之前我们已经实现过一个3层的神经网络,我们将对它进行初始化:
我们将会尝试下面三种初始化方法:
- 初始化为0:在输入参数中全部初始化为0,参数名为initialization = “zeros”,核心代码:
parameters['W' + str(l)] = np.zeros((layers_dims[l], layers_dims[l - 1])) - 初始化为随机数:把输入参数设置为随机值,权重初始化为大的随机值。参数名为initialization = “random”,核心代码:
parameters['W' + str(l)] = np.random.randn(layers_dims[l], layers_dims[l - 1]) * 10 - 抑梯度异常初始化:参见梯度消失和梯度爆炸的那一个视频,参数名为initialization = “he”,核心代码:
parameters['W' + str(l)] = np.random.randn(layers_dims[l], layers_dims[l - 1]) * np.sqrt(2 / layers_dims[l - 1])
首先我们来看看我们的模型是怎样的:
def model(X,Y,learning_rate=0.01,num_iterations=15000,print_cost=True,initialization="he",is_polt=True):
"""
实现一个三层的神经网络:LINEAR ->RELU -> LINEAR -> RELU -> LINEAR -> SIGMOID
参数:
X - 输入的数据,维度为(2, 要训练/测试的数量)
Y - 标签,【0 | 1】,维度为(1,对应的是输入的数据的标签)
learning_rate - 学习速率
num_iterations - 迭代的次数
print_cost - 是否打印成本值,每迭代1000次打印一次
initialization - 字符串类型,初始化的类型【"zeros" | "random" | "he"】
is_polt - 是否绘制梯度下降的曲线图
返回
parameters - 学习后的参数
"""
grads = {}
costs = []
m = X.shape[1]
layers_dims = [X.shape[0],10,5,1]
#选择初始化参数的类型
if initialization == "zeros":
parameters = initialize_parameters_zeros(layers_dims)
elif initialization == "random":
parameters = initialize_parameters_random(layers_dims)
elif initialization == "he":
parameters = initialize_parameters_he(layers_dims)
else :
print("错误的初始化参数!程序退出")
exit
#开始学习
for i in range(0,num_iterations):
#前向传播
a3 , cache = init_utils.forward_propagation(X,parameters)
#计算成本
cost = init_utils.compute_loss(a3,Y)
#反向传播
grads = init_utils.backward_propagation(X,Y,cache)
#更新参数
parameters = init_utils.update_parameters(parameters,grads,learning_rate)
#记录成本
if i % 1000 == 0:
costs.append(cost)
#打印成本
if print_cost:
print("第" + str(i) + "次迭代,成本值为:" + str(cost))
#学习完毕,绘制成本曲线
if is_polt:
plt.plot(costs)
plt.ylabel('cost')
plt.xlabel('iterations (per hundreds)')
plt.title("Learning rate =" + str(learning_rate))
plt.show()
#返回学习完毕后的参数
return parameters
模型我们可以简单地看一下,我们这就开始尝试一下这三种初始化。
初始化为零
def initialize_parameters_zeros(layers_dims):
"""
将模型的参数全部设置为0
参数:
layers_dims - 列表,模型的层数和对应每一层的节点的数量
返回
parameters - 包含了所有W和b的字典
W1 - 权重矩阵,维度为(layers_dims[1], layers_dims[0])
b1 - 偏置向量,维度为(layers_dims[1],1)
···
WL - 权重矩阵,维度为(layers_dims[L], layers_dims[L -1])
bL - 偏置向量,维度为(layers_dims[L],1)
"""
parameters = {}
L = len(layers_dims) #网络层数
for l in range(1,L):
parameters["W" + str(l)] = np.zeros((layers_dims[l],layers_dims[l-1]))
parameters["b" + str(l)] = np.zeros((layers_dims[l],1))
#使用断言确保我的数据格式是正确的
assert(parameters["W" + str(l)].shape == (layers_dims[l],layers_dims[l-1]))
assert(parameters["b" + str(l)].shape == (layers_dims[l],1))
return parameters
我们这就来测试一下:
parameters = initialize_parameters_zeros([3,2,1])
print("W1 = " + str(parameters["W1"]))
print("b1 = " + str(parameters["b1"]))
print("W2 = " + str(parameters["W2"]))
print("b2 = " + str(parameters["b2"]))
测试结果:
W1 = [[ 0. 0. 0.]
[ 0. 0. 0.]]
b1 = [[ 0.]
[ 0.]]
W2 = [[ 0. 0.]]
b2 = [[ 0.]]
我们可以看到W和b全部被初始化为0了,那么我们使用这些参数来训练模型,结果会怎样呢?
parameters = model(train_X, train_Y, initialization = "zeros",is_polt=True)
执行结果:
第0次迭代,成本值为:0.69314718056
第1000次迭代,成本值为:0.69314718056
第2000次迭代,成本值为:0.69314718056
第3000次迭代,成本值为:0.69314718056
第4000次迭代,成本值为:0.69314718056
第5000次迭代,成本值为:0.69314718056
第6000次迭代,成本值为:0.69314718056
第7000次迭代,成本值为:0.69314718056
第8000次迭代,成本值为:0.69314718056
第9000次迭代,成本值为:0.69314718056
第10000次迭代,成本值为:0.69314718056
第11000次迭代,成本值为:0.69314718056
第12000次迭代,成本值为:0.69314718056
第13000次迭代,成本值为:0.69314718056
第14000次迭代,成本值为:0.69314718056

从上图中我们可以看到学习率一直没有变化,也就是说这个模型根本没有学习。我们来看看预测的结果怎么样:
print ("训练集:")
predictions_train = init_utils.predict(train_X, train_Y, parameters)
print ("测试集:")
predictions_test = init_utils.predict(test_X, test_Y, parameters)
执行结果:
训练集:
Accuracy: 0.5
测试集:
Accuracy: 0.5
性能确实很差,而且成本并没有真正降低,算法的性能也比随机猜测要好。为什么?让我们看看预测和决策边界的细节:
print("predictions_train = " + str(predictions_train))
print("predictions_test = " + str(predictions_test))
plt.title("Model with Zeros initialization")
axes = plt.gca()
axes.set_xlim([-1.5, 1.5])
axes.set_ylim([-1.5, 1.5])
init_utils.plot_decision_boundary(lambda x: init_utils.predict_dec(parameters, x.T), train_X, train_Y)
执行结果:
predictions_train = [[0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0
0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0
0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0
0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0
0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0
0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0
0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0
0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0
0 0 0 0]]
predictions_test = [[0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0
0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0
0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0 0]]

分类失败,该模型预测每个都为0。通常来说,零初始化都会导致神经网络无法打破对称性,最终导致的结果就是无论网络有多少层,最终只能得到和Logistic函数相同的效果。
随机初始化
为了打破对称性,我们可以随机地把参数赋值。在随机初始化之后,每个神经元可以开始学习其输入的不同功能,我们还会设置比较大的参数值,看看会发生什么。
def initialize_parameters_random(layers_dims):
"""
参数:
layers_dims - 列表,模型的层数和对应每一层的节点的数量
返回
parameters - 包含了所有W和b的字典
W1 - 权重矩阵,维度为(layers_dims[1], layers_dims[0])
b1 - 偏置向量,维度为(layers_dims[1],1)
···
WL - 权重矩阵,维度为(layers_dims[L], layers_dims[L -1])
b1 - 偏置向量,维度为(layers_dims[L],1)
"""
np.random.seed(3) # 指定随机种子
parameters = {}
L = len(layers_dims) # 层数
for l in range(1, L):
parameters['W' + str(l)] = np.random.randn(layers_dims[l], layers_dims[l - 1]) * 10 #使用10倍缩放
parameters['b' + str(l)] = np.zeros((layers_dims[l], 1))
#使用断言确保我的数据格式是正确的
assert(parameters["W" + str(l)].shape == (layers_dims[l],layers_dims[l-1]))
assert(parameters["b" + str(l)].shape == (layers_dims[l],1))
return parameters
我们可以来测试一下:
parameters = initialize_parameters_random([3, 2, 1])
print("W1 = " + str(parameters["W1"]))
print("b1 = " + str(parameters["b1"]))
print("W2 = " + str(parameters["W2"]))
print("b2 = " + str(parameters["b2"]))
测试结果:
W1 = [[ 17.88628473 4.36509851 0.96497468]
[-18.63492703 -2.77388203 -3.54758979]]
b1 = [[ 0.]
[ 0.]]
W2 = [[-0.82741481 -6.27000677]]
b2 = [[ 0.]]
看起来这些参数都是比较大的,我们来看看实际运行会怎么样:
parameters = model(train_X, train_Y, initialization = "random",is_polt=True)
print("训练集:")
predictions_train = init_utils.predict(train_X, train_Y, parameters)
print("测试集:")
predictions_test = init_utils.predict(test_X, test_Y, parameters)
print(predictions_train)
print(predictions_test)
执行结果:
第0次迭代,成本值为:inf
第1000次迭代,成本值为:0.625098279396
第2000次迭代,成本值为:0.59812165967
第3000次迭代,成本值为:0.56384175723
第4000次迭代,成本值为:0.55017030492
第5000次迭代,成本值为:0.544463290966
第6000次迭代,成本值为:0.5374513807
第7000次迭代,成本值为:0.476404207407
第8000次迭代,成本值为:0.397814922951
第9000次迭代,成本值为:0.393476402877
第10000次迭代,成本值为:0.392029546188
第11000次迭代,成本值为:0.389245981351
第12000次迭代,成本值为:0.386154748571
第13000次迭代,成本值为:0.38498472891
第14000次迭代,成本值为:0.382782830835
训练集:
Accuracy: 0.83
测试集:
Accuracy: 0.86
[[1 0 1 1 0 0 1 1 1 1 1 0 1 0 0 1 0 1 1 0 0 0 1 0 1 1 1 1 1 1 0 1 1 0 0 1 1
1 1 1 1 1 1 0 1 1 1 1 0 1 0 1 1 1 1 0 0 1 1 1 1 0 1 1 0 1 0 1 1 1 1 0 0 0
0 0 1 0 1 0 1 1 1 0 0 1 1 1 1 1 1 0 0 1 1 1 0 1 1 0 1 0 1 1 0 1 1 0 1 0 1
1 0 0 1 0 0 1 1 0 1 1 1 0 1 0 0 1 0 1 1 1 1 1 1 1 0 1 1 0 0 1 1 0 0 0 1 0
1 0 1 0 1 1 1 0 0 1 1 1 1 0 1 1 0 1 0 1 1 0 1 0 1 1 1 1 0 1 1 1 1 0 1 0 1
0 1 1 1 1 0 1 1 0 1 1 0 1 1 0 1 0 1 1 1 0 1 1 1 0 1 0 1 0 0 1 0 1 1 0 1 1
0 1 1 0 1 1 1 0 1 1 1 1 0 1 0 0 1 1 0 1 1 1 0 0 0 1 1 0 1 1 1 1 0 1 1 0 1
1 1 0 0 1 0 0 0 1 0 0 0 1 1 1 1 0 0 0 0 1 1 1 1 0 0 1 1 1 1 1 1 1 0 0 0 1
1 1 1 0]]
[[1 1 1 1 0 1 0 1 1 0 1 1 1 0 0 0 0 1 0 1 0 0 1 0 1 0 1 1 1 1 1 0 0 0 0 1 0
1 1 0 0 1 1 1 1 1 0 1 1 1 0 1 0 1 1 0 1 0 1 0 1 1 1 1 1 1 1 1 1 0 1 0 1 1
1 1 1 0 1 0 0 1 0 0 0 1 1 0 1 1 0 0 0 1 1 0 1 1 0 0]]

我们来把图绘制出来,看看分类的结果是怎样的。
plt.title("Model with large random initialization")
axes = plt.gca()
axes.set_xlim([-1.5, 1.5])
axes.set_ylim([-1.5, 1.5])
init_utils.plot_decision_boundary(lambda x: init_utils.predict_dec(parameters, x.T), train_X, train_Y)
执行结果:

我们可以看到误差开始很高。这是因为由于具有较大的随机权重,最后一个激活(sigmoid)输出的结果非常接近于0或1,而当它出现错误时,它会导致非常高的损失。初始化参数如果没有很好地话会导致梯度消失、爆炸,这也会减慢优化算法。如果我们对这个网络进行更长时间的训练,我们将看到更好的结果,但是使用过大的随机数初始化会减慢优化的速度。
总而言之,将权重初始化为非常大的时候其实效果并不好,下面我们试试小一点的参数值。
抑梯度异常初始化
我们会使用到 2 上一层的维度 \sqrt{\frac{2}{\text{上一层的维度}}} 上一层的维度2这个公式来初始化参数。
def initialize_parameters_he(layers_dims):
"""
参数:
layers_dims - 列表,模型的层数和对应每一层的节点的数量
返回
parameters - 包含了所有W和b的字典
W1 - 权重矩阵,维度为(layers_dims[1], layers_dims[0])
b1 - 偏置向量,维度为(layers_dims[1],1)
···
WL - 权重矩阵,维度为(layers_dims[L], layers_dims[L -1])
b1 - 偏置向量,维度为(layers_dims[L],1)
"""
np.random.seed(3) # 指定随机种子
parameters = {}
L = len(layers_dims) # 层数
for l in range(1, L):
parameters['W' + str(l)] = np.random.randn(layers_dims[l], layers_dims[l - 1]) * np.sqrt(2 / layers_dims[l - 1])
parameters['b' + str(l)] = np.zeros((layers_dims[l], 1))
#使用断言确保我的数据格式是正确的
assert(parameters["W" + str(l)].shape == (layers_dims[l],layers_dims[l-1]))
assert(parameters["b" + str(l)].shape == (layers_dims[l],1))
return parameters
我们来测试一下这个函数:
parameters = initialize_parameters_he([2, 4, 1])
print("W1 = " + str(parameters["W1"]))
print("b1 = " + str(parameters["b1"]))
print("W2 = " + str(parameters["W2"]))
print("b2 = " + str(parameters["b2"]))
测试结果:
W1 = [[ 1.78862847 0.43650985]
[ 0.09649747 -1.8634927 ]
[-0.2773882 -0.35475898]
[-0.08274148 -0.62700068]]
b1 = [[ 0.]
[ 0.]
[ 0.]
[ 0.]]
W2 = [[-0.03098412 -0.33744411 -0.92904268 0.62552248]]
b2 = [[ 0.]]
这样我们就基本把参数W初始化到了1附近,我们来实际运行一下看看:
parameters = model(train_X, train_Y, initialization = "he",is_polt=True)
print("训练集:")
predictions_train = init_utils.predict(train_X, train_Y, parameters)
print("测试集:")
init_utils.predictions_test = init_utils.predict(test_X, test_Y, parameters)
执行结果:
第0次迭代,成本值为:0.883053746342
第1000次迭代,成本值为:0.687982591973
第2000次迭代,成本值为:0.675128626452
第3000次迭代,成本值为:0.652611776889
第4000次迭代,成本值为:0.608295897057
第5000次迭代,成本值为:0.530494449172
第6000次迭代,成本值为:0.413864581707
第7000次迭代,成本值为:0.311780346484
第8000次迭代,成本值为:0.236962153303
第9000次迭代,成本值为:0.185972872092
第10000次迭代,成本值为:0.150155562804
第11000次迭代,成本值为:0.123250792923
第12000次迭代,成本值为:0.0991774654653
第13000次迭代,成本值为:0.0845705595402
第14000次迭代,成本值为:0.0735789596268
训练集:
Accuracy: 0.993333333333
测试集:
Accuracy: 0.96

我们可以看到误差越来越小,我们来绘制一下预测的情况:
plt.title("Model with He initialization")
axes = plt.gca()
axes.set_xlim([-1.5, 1.5])
axes.set_ylim([-1.5, 1.5])
init_utils.plot_decision_boundary(lambda x: init_utils.predict_dec(parameters, x.T), train_X, train_Y)

初始化的模型将蓝色和红色的点在少量的迭代中很好地分离出来,总结一下:
-
不同的初始化方法可能导致性能最终不同
-
随机初始化有助于打破对称,使得不同隐藏层的单元可以学习到不同的参数。
-
初始化时,初始值不宜过大。
-
He初始化搭配ReLU激活函数常常可以得到不错的效果。
在深度学习中,如果数据集没有足够大的话,可能会导致一些过拟合的问题。过拟合导致的结果就是在训练集上有着很高的精确度,但是在遇到新的样本时,精确度下降会很严重。为了避免过拟合的问题,接下来我们要讲解的方式就是正则化。
正则化模型
Problem Statement: You have just been hired as an AI expert by the French Football Corporation. They would like you to recommend positions where France’s goal keeper should kick the ball so that the French team’s players can then hit it with their head.
问题描述:假设你现在是一个AI专家,你需要设计一个模型,可以用于推荐在足球场中守门员将球发至哪个位置可以让本队的球员抢到球的可能性更大。说白了,实际上就是一个二分类,一半是己方抢到球,一半就是对方抢到球,我们来看一下这个图:

读取并绘制数据集
我们来加载并查看一下我们的数据集:
train_X, train_Y, test_X, test_Y = reg_utils.load_2D_dataset(is_plot=True)
执行结果:

每一个点代表球落下的可能的位置,蓝色代表己方的球员会抢到球,红色代表对手的球员会抢到球,我们要做的就是使用模型来画出一条线,来找到适合我方球员能抢到球的位置。
我们要做以下三件事,来对比出不同的模型的优劣:
- 不使用正则化
- 使用正则化
2.1 使用L2正则化
2.2 使用随机节点删除
我们来看一下我们的模型:
- 正则化模式 - 将lambd输入设置为非零值。 我们使用“lambd”而不是“lambda”,因为“lambda”是Python中的保留关键字。
- 随机删除节点 - 将keep_prob设置为小于1的值
def model(X,Y,learning_rate=0.3,num_iterations=30000,print_cost=True,is_plot=True,lambd=0,keep_prob=1):
"""
实现一个三层的神经网络:LINEAR ->RELU -> LINEAR -> RELU -> LINEAR -> SIGMOID
参数:
X - 输入的数据,维度为(2, 要训练/测试的数量)
Y - 标签,【0(蓝色) | 1(红色)】,维度为(1,对应的是输入的数据的标签)
learning_rate - 学习速率
num_iterations - 迭代的次数
print_cost - 是否打印成本值,每迭代10000次打印一次,但是每1000次记录一个成本值
is_polt - 是否绘制梯度下降的曲线图
lambd - 正则化的超参数,实数
keep_prob - 随机删除节点的概率
返回
parameters - 学习后的参数
"""
grads = {}
costs = []
m = X.shape[1]
layers_dims = [X.shape[0],20,3,1]
#初始化参数
parameters = reg_utils.initialize_parameters(layers_dims)
#开始学习
for i in range(0,num_iterations):
#前向传播
##是否随机删除节点
if keep_prob == 1:
###不随机删除节点
a3 , cache = reg_utils.forward_propagation(X,parameters)
elif keep_prob < 1:
###随机删除节点
a3 , cache = forward_propagation_with_dropout(X,parameters,keep_prob)
else:
print("keep_prob参数错误!程序退出。")
exit
#计算成本
## 是否使用二范数
if lambd == 0:
###不使用L2正则化
cost = reg_utils.compute_cost(a3,Y)
else:
###使用L2正则化
cost = compute_cost_with_regularization(a3,Y,parameters,lambd)
#反向传播
##可以同时使用L2正则化和随机删除节点,但是本次实验不同时使用。
assert(lambd == 0 or keep_prob ==1)
##两个参数的使用情况
if (lambd == 0 and keep_prob == 1):
### 不使用L2正则化和不使用随机删除节点
grads = reg_utils.backward_propagation(X,Y,cache)
elif lambd != 0:
### 使用L2正则化,不使用随机删除节点
grads = backward_propagation_with_regularization(X, Y, cache, lambd)
elif keep_prob < 1:
### 使用随机删除节点,不使用L2正则化
grads = backward_propagation_with_dropout(X, Y, cache, keep_prob)
#更新参数
parameters = reg_utils.update_parameters(parameters, grads, learning_rate)
#记录并打印成本
if i % 1000 == 0:
## 记录成本
costs.append(cost)
if (print_cost and i % 10000 == 0):
#打印成本
print("第" + str(i) + "次迭代,成本值为:" + str(cost))
#是否绘制成本曲线图
if is_plot:
plt.plot(costs)
plt.ylabel('cost')
plt.xlabel('iterations (x1,000)')
plt.title("Learning rate =" + str(learning_rate))
plt.show()
#返回学习后的参数
return parameters
我们来先看一下不使用正则化下模型的效果:
不使用正则化
parameters = model(train_X, train_Y,is_plot=True)
print("训练集:")
predictions_train = reg_utils.predict(train_X, train_Y, parameters)
print("测试集:")
predictions_test = reg_utils.predict(test_X, test_Y, parameters)
执行结果:
第0次迭代,成本值为:0.655741252348
第10000次迭代,成本值为:0.163299875257
第20000次迭代,成本值为:0.138516424233
训练集:
Accuracy: 0.947867298578
测试集:
Accuracy: 0.915

我们可以看到,对于训练集,精确度为94%;而对于测试集,精确度为91.5%。接下来,我们将分割曲线画出来:
plt.title("Model without regularization")
axes = plt.gca()
axes.set_xlim([-0.75,0.40])
axes.set_ylim([-0.75,0.65])
reg_utils.plot_decision_boundary(lambda x: reg_utils.predict_dec(parameters, x.T), train_X, train_Y)
执行结果:

从图中可以看出,在无正则化时,分割曲线有了明显的过拟合特性。接下来,我们使用L2正则化:
使用正则化
L2正则化
避免过度拟合的标准方法称为L2正则化,它包括适当修改你的成本函数,我们从原来的成本函数(1)到现在的函数(2):
J
=
−
1
m
∑
i
=
1
m
(
y
(
i
)
log
(
a
[
L
]
(
i
)
)
+
(
1
−
y
(
i
)
)
log
(
1
−
a
[
L
]
(
i
)
)
)
(1)
J = -\frac{1}{m} \sum\limits_{i = 1}^{m} \large{(}\small y^{(i)}\log\left(a^{[L](i)}\right) + (1-y^{(i)})\log\left(1- a^{[L](i)}\right) \large{)} \tag{1}
J=−m1i=1∑m(y(i)log(a[L](i))+(1−y(i))log(1−a[L](i)))(1)
J
正
则
化
=
−
1
m
∑
i
=
1
m
(
y
(
i
)
log
(
a
[
L
]
(
i
)
)
+
(
1
−
y
(
i
)
)
log
(
1
−
a
[
L
]
(
i
)
)
)
⏟
交叉熵成本
+
1
m
λ
2
∑
l
∑
k
∑
j
W
k
,
j
[
l
]
2
⏟
L2 正则化成本
(2)
J_{正则化} = \small \underbrace{-\frac{1}{m} \sum\limits_{i = 1}^{m} \large{(}\small y^{(i)}\log\left(a^{[L](i)}\right) + (1-y^{(i)})\log\left(1- a^{[L](i)}\right) \large{)} }_\text{交叉熵成本} + \underbrace{\frac{1}{m} \frac{\lambda}{2} \sum\limits_l\sum\limits_k\sum\limits_j W_{k,j}^{[l]2} }_\text{L2 正则化成本} \tag{2}
J正则化=交叉熵成本
−m1i=1∑m(y(i)log(a[L](i))+(1−y(i))log(1−a[L](i)))+L2 正则化成本
m12λl∑k∑j∑Wk,j[l]2(2)
计算 ∑ k ∑ j W k , j [ l ] 2 \sum\limits_k\sum\limits_j W_{k,j}^{[l]2} k∑j∑Wk,j[l]2的代码为:
np.sum(np.square(Wl))
需要注意的是在前向传播中我们对 W [ 1 ] W^{[1]} W[1], W [ 2 ] W^{[2]} W[2] 和 W [ 3 ] W^{[3]} W[3]这三个项进行操作,将这三个项相加并乘以 $ \frac{1}{m} \frac{\lambda}{2} 。 在 后 向 传 播 中 , 使 用 。在后向传播中,使用 。在后向传播中,使用\frac{d}{dW} ( \frac{1}{2}\frac{\lambda}{m} W^2) = \frac{\lambda}{m} W$计算梯度。
我们下面就开始写相关的函数:
def compute_cost_with_regularization(A3,Y,parameters,lambd):
"""
实现公式2的L2正则化计算成本
参数:
A3 - 正向传播的输出结果,维度为(输出节点数量,训练/测试的数量)
Y - 标签向量,与数据一一对应,维度为(输出节点数量,训练/测试的数量)
parameters - 包含模型学习后的参数的字典
返回:
cost - 使用公式2计算出来的正则化损失的值
"""
m = Y.shape[1]
W1 = parameters["W1"]
W2 = parameters["W2"]
W3 = parameters["W3"]
cross_entropy_cost = reg_utils.compute_cost(A3,Y)
L2_regularization_cost = lambd * (np.sum(np.square(W1)) + np.sum(np.square(W2)) + np.sum(np.square(W3))) / (2 * m)
cost = cross_entropy_cost + L2_regularization_cost
return cost
#当然,因为改变了成本函数,我们也必须改变向后传播的函数, 所有的梯度都必须根据这个新的成本值来计算。
def backward_propagation_with_regularization(X, Y, cache, lambd):
"""
实现我们添加了L2正则化的模型的后向传播。
参数:
X - 输入数据集,维度为(输入节点数量,数据集里面的数量)
Y - 标签,维度为(输出节点数量,数据集里面的数量)
cache - 来自forward_propagation()的cache输出
lambda - regularization超参数,实数
返回:
gradients - 一个包含了每个参数、激活值和预激活值变量的梯度的字典
"""
m = X.shape[1]
(Z1, A1, W1, b1, Z2, A2, W2, b2, Z3, A3, W3, b3) = cache
dZ3 = A3 - Y
dW3 = (1 / m) * np.dot(dZ3,A2.T) + ((lambd * W3) / m )
db3 = (1 / m) * np.sum(dZ3,axis=1,keepdims=True)
dA2 = np.dot(W3.T,dZ3)
dZ2 = np.multiply(dA2,np.int64(A2 > 0))
dW2 = (1 / m) * np.dot(dZ2,A1.T) + ((lambd * W2) / m)
db2 = (1 / m) * np.sum(dZ2,axis=1,keepdims=True)
dA1 = np.dot(W2.T,dZ2)
dZ1 = np.multiply(dA1,np.int64(A1 > 0))
dW1 = (1 / m) * np.dot(dZ1,X.T) + ((lambd * W1) / m)
db1 = (1 / m) * np.sum(dZ1,axis=1,keepdims=True)
gradients = {"dZ3": dZ3, "dW3": dW3, "db3": db3, "dA2": dA2,
"dZ2": dZ2, "dW2": dW2, "db2": db2, "dA1": dA1,
"dZ1": dZ1, "dW1": dW1, "db1": db1}
return gradients
我们来直接放到模型中跑一下:
parameters = model(train_X, train_Y, lambd=0.7,is_plot=True)
print("使用正则化,训练集:")
predictions_train = reg_utils.predict(train_X, train_Y, parameters)
print("使用正则化,测试集:")
predictions_test = reg_utils.predict(test_X, test_Y, parameters)
执行结果:
第0次迭代,成本值为:0.697448449313
第10000次迭代,成本值为:0.268491887328
第20000次迭代,成本值为:0.268091633713
使用正则化,训练集:
Accuracy: 0.938388625592
使用正则化,测试集:
Accuracy: 0.93

我们来看一下分类的结果吧~
plt.title("Model with L2-regularization")
axes = plt.gca()
axes.set_xlim([-0.75,0.40])
axes.set_ylim([-0.75,0.65])
reg_utils.plot_decision_boundary(lambda x: reg_utils.predict_dec(parameters, x.T), train_X, train_Y)
执行结果:

λ的值是可以使用开发集调整时的超参数。L2正则化会使决策边界更加平滑。如果λ太大,也可能会“过度平滑”,从而导致模型高偏差。L2正则化实际上在做什么?L2正则化依赖于较小权重的模型比具有较大权重的模型更简单这样的假设,因此,通过削减成本函数中权重的平方值,可以将所有权重值逐渐改变到到较小的值。权值数值高的话会有更平滑的模型,其中输入变化时输出变化更慢,但是你需要花费更多的时间。L2正则化对以下内容有影响:
- 成本计算 : 正则化的计算需要添加到成本函数中
- 反向传播功能 :在权重矩阵方面,梯度计算时也要依据正则化来做出相应的计算
- 重量变小(“重量衰减”) :权重被逐渐改变到较小的值。
随机删除节点
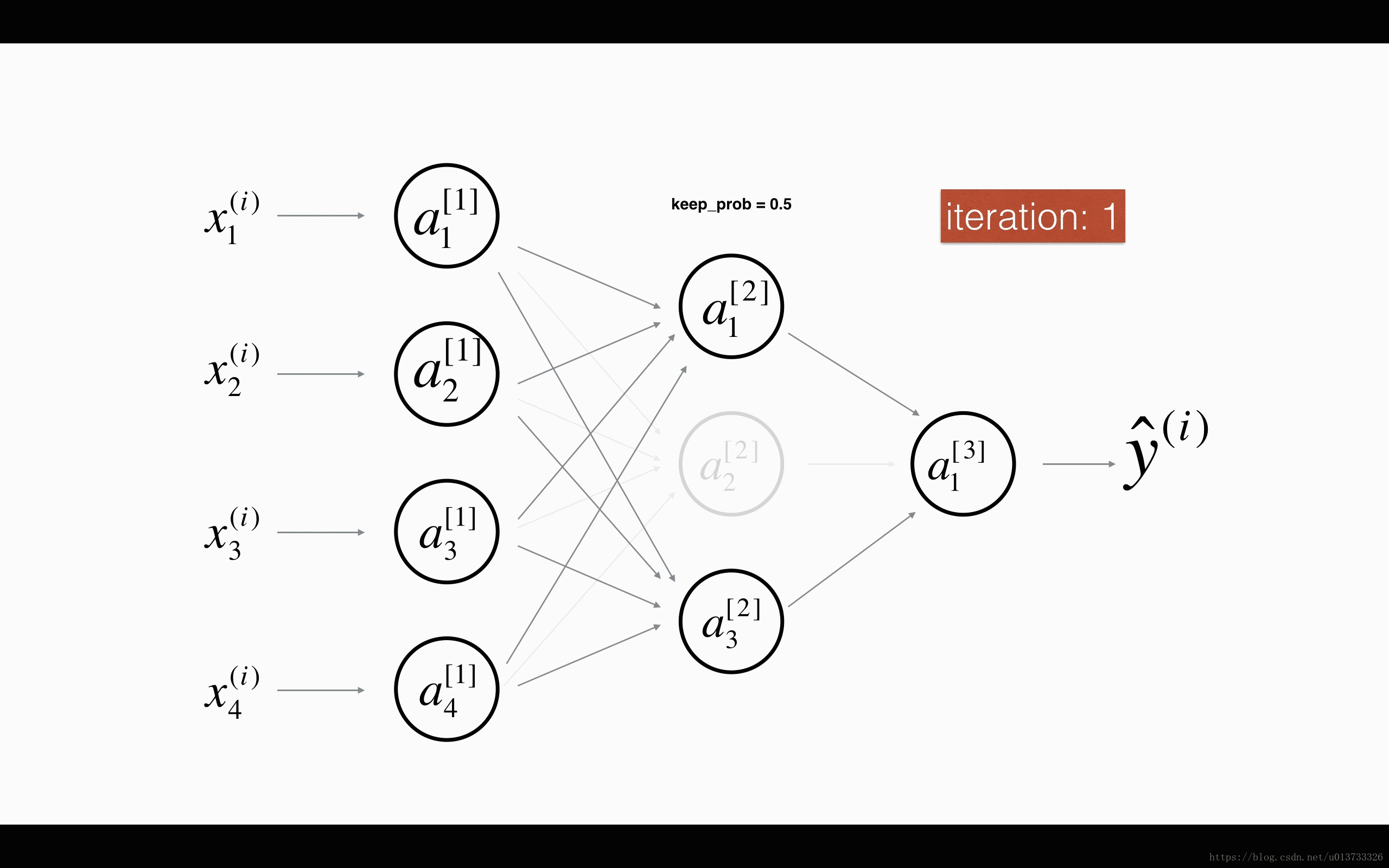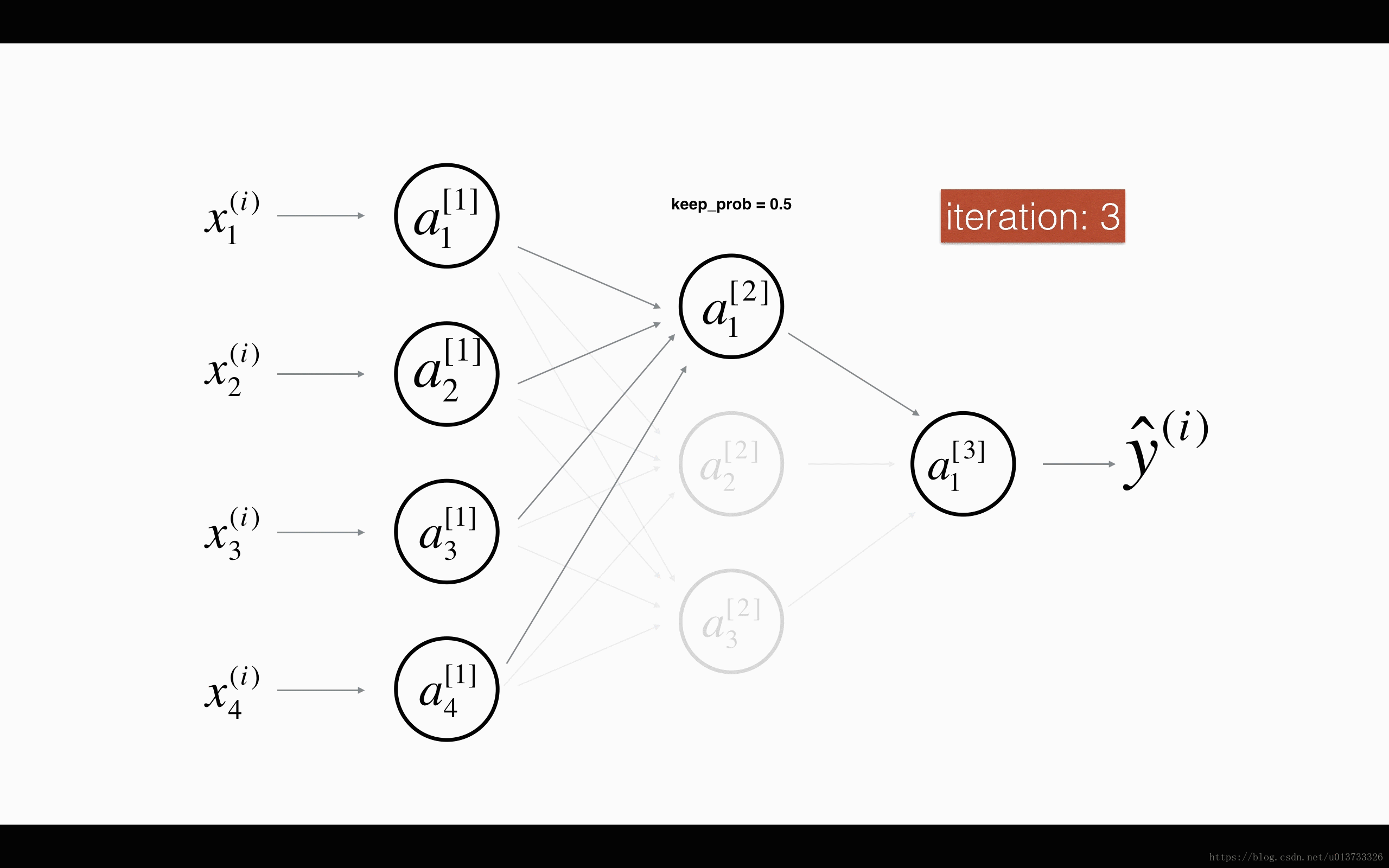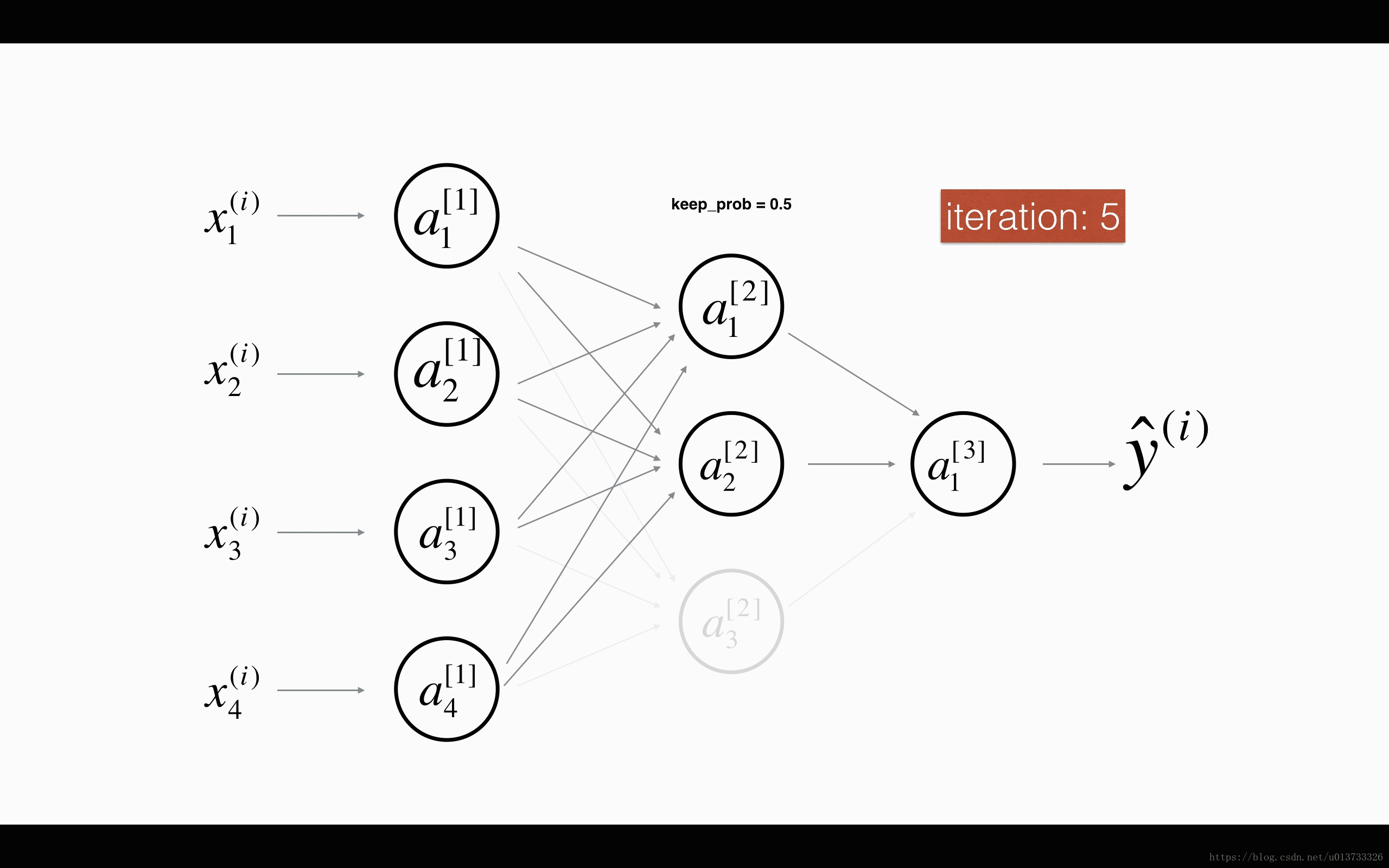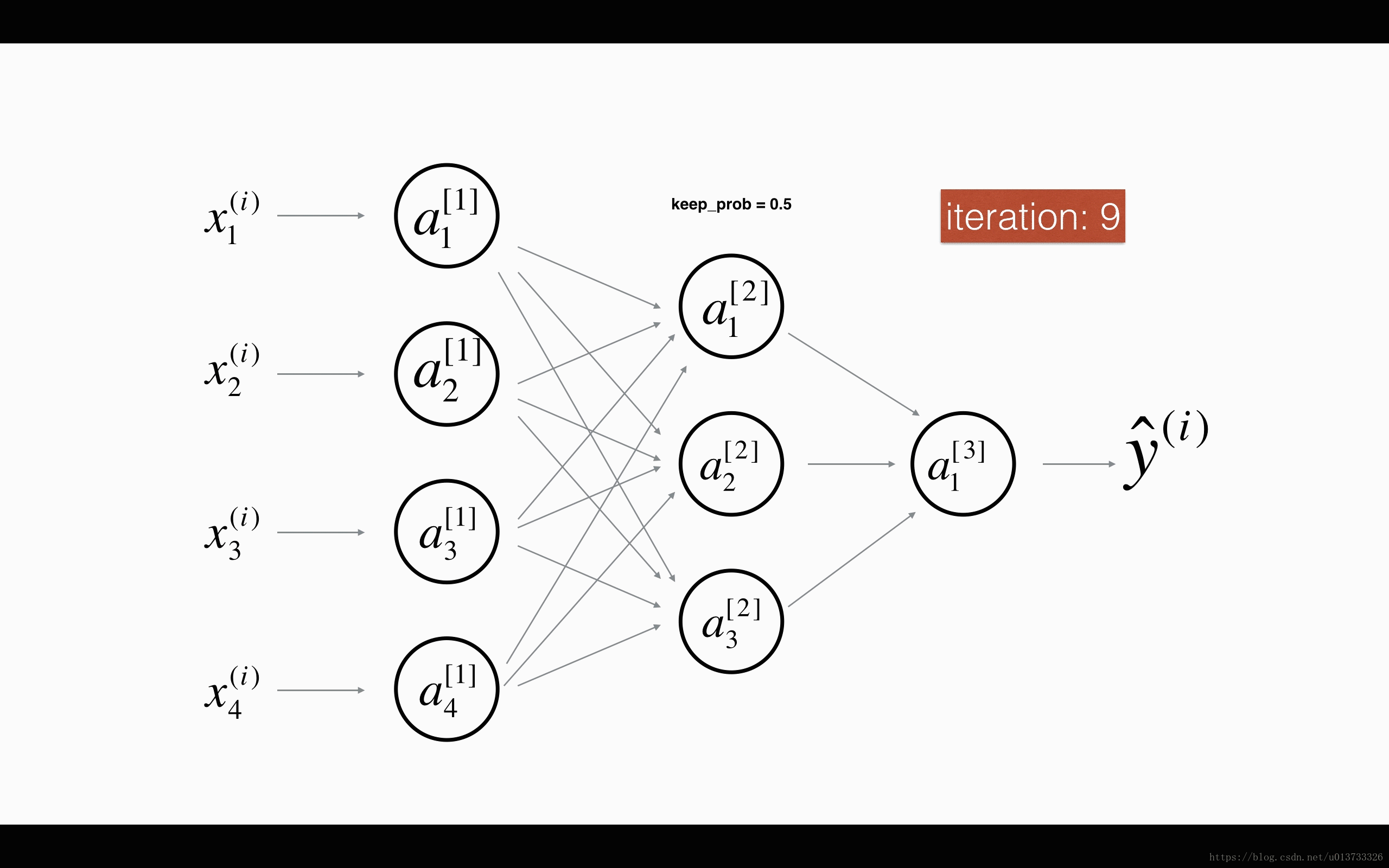
最后,我们使用Dropout来进行正则化,Dropout的原理就是每次迭代过程中随机将其中的一些节点失效。当我们关闭一些节点时,我们实际上修改了我们的模型。背后的想法是,在每次迭代时,我们都会训练一个只使用一部分神经元的不同模型。随着迭代次数的增加,我们的模型的节点会对其他特定节点的激活变得不那么敏感,因为其他节点可能在任何时候会失效。我们来看看下面两个GIF图,图有点大,加载不出来请【点我下载(11.3MB)】:
在每一次迭代中,关闭(设置为零)一层的每个神经元,概率为$1 - keep\_prob$,我们在这里保持概率为$keep\_prob$(这里为50%)。丢弃的节点都不参与迭代时的前向和后向传播。

$1^{st}$ 平均40%节点被删除, $3^{rd}$ 平均删除了20%的节点
下面我们将关闭第一层和第三层的一些节点,我们需要做以下四步:
- 在视频中,吴恩达老师讲解了使用
np.random.rand()来初始化和 a [ 1 ] a^{[1]} a[1]具有相同维度的 d [ 1 ] d^{[1]} d[1] ,在这里,我们将使用向量化实现,我们先来实现一个和 A [ 1 ] A^{[1]} A[1]相同的随机矩阵$D^{[1]} = [d^{1} d^{1} … d^{1}] $。 - 如果
D
[
1
]
D^{[1]}
D[1] 低于 (
keep_prob)的值我们就把它设置为0,如果高于(keep_prob)的值我们就设置为1。 - 把 A [ 1 ] A^{[1]} A[1] 更新为 A [ 1 ] ∗ D [ 1 ] A^{[1]} * D^{[1]} A[1]∗D[1]。 (我们已经关闭了一些节点)。我们可以使用 D [ 1 ] D^{[1]} D[1] 作为掩码。我们做矩阵相乘的时候,关闭的那些节点(值为0)就会不参与计算,因为0乘以任何值都为0。
- 使用
A
[
1
]
A^{[1]}
A[1] 除以
keep_prob。这样做的话我们通过缩放就在计算成本的时候仍然具有相同的期望值,这叫做反向dropout。
def forward_propagation_with_dropout(X,parameters,keep_prob=0.5):
"""
实现具有随机舍弃节点的前向传播。
LINEAR -> RELU + DROPOUT -> LINEAR -> RELU + DROPOUT -> LINEAR -> SIGMOID.
参数:
X - 输入数据集,维度为(2,示例数)
parameters - 包含参数“W1”,“b1”,“W2”,“b2”,“W3”,“b3”的python字典:
W1 - 权重矩阵,维度为(20,2)
b1 - 偏向量,维度为(20,1)
W2 - 权重矩阵,维度为(3,20)
b2 - 偏向量,维度为(3,1)
W3 - 权重矩阵,维度为(1,3)
b3 - 偏向量,维度为(1,1)
keep_prob - 随机删除的概率,实数
返回:
A3 - 最后的激活值,维度为(1,1),正向传播的输出
cache - 存储了一些用于计算反向传播的数值的元组
"""
np.random.seed(1)
W1 = parameters["W1"]
b1 = parameters["b1"]
W2 = parameters["W2"]
b2 = parameters["b2"]
W3 = parameters["W3"]
b3 = parameters["b3"]
#LINEAR -> RELU -> LINEAR -> RELU -> LINEAR -> SIGMOID
Z1 = np.dot(W1,X) + b1
A1 = reg_utils.relu(Z1)
#下面的步骤1-4对应于上述的步骤1-4。
D1 = np.random.rand(A1.shape[0],A1.shape[1]) #步骤1:初始化矩阵D1 = np.random.rand(..., ...)
D1 = D1 < keep_prob #步骤2:将D1的值转换为0或1(使用keep_prob作为阈值)
A1 = A1 * D1 #步骤3:舍弃A1的一些节点(将它的值变为0或False)
A1 = A1 / keep_prob #步骤4:缩放未舍弃的节点(不为0)的值
"""
#不理解的同学运行一下下面代码就知道了。
import numpy as np
np.random.seed(1)
A1 = np.random.randn(1,3)
D1 = np.random.rand(A1.shape[0],A1.shape[1])
keep_prob=0.5
D1 = D1 < keep_prob
print(D1)
A1 = 0.01
A1 = A1 * D1
A1 = A1 / keep_prob
print(A1)
"""
Z2 = np.dot(W2,A1) + b2
A2 = reg_utils.relu(Z2)
#下面的步骤1-4对应于上述的步骤1-4。
D2 = np.random.rand(A2.shape[0],A2.shape[1]) #步骤1:初始化矩阵D2 = np.random.rand(..., ...)
D2 = D2 < keep_prob #步骤2:将D2的值转换为0或1(使用keep_prob作为阈值)
A2 = A2 * D2 #步骤3:舍弃A1的一些节点(将它的值变为0或False)
A2 = A2 / keep_prob #步骤4:缩放未舍弃的节点(不为0)的值
Z3 = np.dot(W3, A2) + b3
A3 = reg_utils.sigmoid(Z3)
cache = (Z1, D1, A1, W1, b1, Z2, D2, A2, W2, b2, Z3, A3, W3, b3)
return A3, cache
改变了前向传播的算法,我们也需要改变后向传播的算法,使用存储在缓存中的掩码 D [ 1 ] D^{[1]} D[1] 和 D [ 2 ] D^{[2]} D[2]将舍弃的节点位置信息添加到第一个和第二个隐藏层。
def backward_propagation_with_dropout(X,Y,cache,keep_prob):
"""
实现我们随机删除的模型的后向传播。
参数:
X - 输入数据集,维度为(2,示例数)
Y - 标签,维度为(输出节点数量,示例数量)
cache - 来自forward_propagation_with_dropout()的cache输出
keep_prob - 随机删除的概率,实数
返回:
gradients - 一个关于每个参数、激活值和预激活变量的梯度值的字典
"""
m = X.shape[1]
(Z1, D1, A1, W1, b1, Z2, D2, A2, W2, b2, Z3, A3, W3, b3) = cache
dZ3 = A3 - Y
dW3 = (1 / m) * np.dot(dZ3,A2.T)
db3 = 1. / m * np.sum(dZ3, axis=1, keepdims=True)
dA2 = np.dot(W3.T, dZ3)
dA2 = dA2 * D2 # 步骤1:使用正向传播期间相同的节点,舍弃那些关闭的节点(因为任何数乘以0或者False都为0或者False)
dA2 = dA2 / keep_prob # 步骤2:缩放未舍弃的节点(不为0)的值
dZ2 = np.multiply(dA2, np.int64(A2 > 0))
dW2 = 1. / m * np.dot(dZ2, A1.T)
db2 = 1. / m * np.sum(dZ2, axis=1, keepdims=True)
dA1 = np.dot(W2.T, dZ2)
dA1 = dA1 * D1 # 步骤1:使用正向传播期间相同的节点,舍弃那些关闭的节点(因为任何数乘以0或者False都为0或者False)
dA1 = dA1 / keep_prob # 步骤2:缩放未舍弃的节点(不为0)的值
dZ1 = np.multiply(dA1, np.int64(A1 > 0))
dW1 = 1. / m * np.dot(dZ1, X.T)
db1 = 1. / m * np.sum(dZ1, axis=1, keepdims=True)
gradients = {"dZ3": dZ3, "dW3": dW3, "db3": db3,"dA2": dA2,
"dZ2": dZ2, "dW2": dW2, "db2": db2, "dA1": dA1,
"dZ1": dZ1, "dW1": dW1, "db1": db1}
return gradients
我们前向和后向传播的函数都写好了,现在用dropout运行模型(keep_prob = 0.86)跑一波。这意味着在每次迭代中,程序都可以24%的概率关闭第1层和第2层的每个神经元。调用的时候:
- 使用forward_propagation_with_dropout而不是forward_propagation。
- 使用backward_propagation_with_dropout而不是backward_propagation。
parameters = model(train_X, train_Y, keep_prob=0.86, learning_rate=0.3,is_plot=True)
print("使用随机删除节点,训练集:")
predictions_train = reg_utils.predict(train_X, train_Y, parameters)
print("使用随机删除节点,测试集:")
reg_utils.predictions_test = reg_utils.predict(test_X, test_Y, parameters)
执行结果:
第0次迭代,成本值为:0.654391240515
第10000次迭代,成本值为:0.0610169865749
第20000次迭代,成本值为:0.0605824357985
使用随机删除节点,训练集:
Accuracy: 0.928909952607
使用随机删除节点,测试集:
Accuracy: 0.95

我们来看看它的分类情况:
plt.title("Model with dropout")
axes = plt.gca()
axes.set_xlim([-0.75, 0.40])
axes.set_ylim([-0.75, 0.65])
reg_utils.plot_decision_boundary(lambda x: reg_utils.predict_dec(parameters, x.T), train_X, train_Y)
执行结果:

我们可以看到,正则化会把训练集的准确度降低,但是测试集的准确度提高了,所以,我们这个还是成功了。
梯度校验
You are part of a team working to make mobile payments available globally, and are asked to build a deep learning model to detect fraud–whenever someone makes a payment, you want to see if the payment might be fraudulent, such as if the user’s account has been taken over by a hacker.
But backpropagation is quite challenging to implement, and sometimes has bugs. Because this is a mission-critical application, your company’s CEO wants to be really certain that your implementation of backpropagation is correct. Your CEO says, “Give me a proof that your backpropagation is actually working!” To give this reassurance, you are going to use “gradient checking”.
假设你现在是一个全球移动支付团队中的一员,现在需要建立一个深度学习模型去判断用户账户在进行付款的时候是否是被黑客入侵的。
但是,在我们执行反向传播的计算过程中,反向传播函数的计算过程是比较复杂的。为了验证我们得到的反向传播函数是否正确,现在你需要编写一些代码来验证反向传播函数的正确性。
反向传播计算梯度 ∂ J ∂ θ \frac{\partial J}{\partial \theta} ∂θ∂J, θ \theta θ表示模型中的参数,使用前向传播和损失函数计算 J J J,因为向前传播相对容易实现,所以您确信自己得到了正确的结果,所以您几乎100%确定您正确计算了 J J J的成本。 因此,您可以使用您的代码来计算 J J J来验证计算的代码 ∂ J ∂ θ \frac{\partial J}{\partial \theta} ∂θ∂J。
让我们回头看一下导数(或梯度)的定义: ∂ J ∂ θ = lim ε → 0 J ( θ + ε ) − J ( θ − ε ) 2 ε (3) \frac{\partial J}{\partial \theta} = \lim_{\varepsilon \to 0} \frac{J(\theta + \varepsilon) - J(\theta - \varepsilon)}{2 \varepsilon} \tag{3} ∂θ∂J=ε→0lim2εJ(θ+ε)−J(θ−ε)(3)
- ∂ J ∂ θ \frac{\partial J}{\partial \theta} ∂θ∂J 是你想确保你的计算正确的值。
- 你可以计算 J ( θ + ε ) J(\theta + \varepsilon) J(θ+ε) 和 J ( θ − ε ) J(\theta - \varepsilon) J(θ−ε) (在 θ \theta θ是一个实数的情况下),因为你确信你对$J $的实现是正确的。
我们先来看一下一维线性模型的梯度检查计算过程:

##一维线性
def forward_propagation(x,theta):
"""
实现图中呈现的线性前向传播(计算J)(J(theta)= theta * x)
参数:
x - 一个实值输入
theta - 参数,也是一个实数
返回:
J - 函数J的值,用公式J(theta)= theta * x计算
"""
J = np.dot(theta,x)
return J
测试一下:
#测试forward_propagation
print("-----------------测试forward_propagation-----------------")
x, theta = 2, 4
J = forward_propagation(x, theta)
print ("J = " + str(J))
测试结果:
-----------------测试forward_propagation-----------------
J = 8
前向传播有了,我们来看一下反向传播:
def backward_propagation(x,theta):
"""
计算J相对于θ的导数。
参数:
x - 一个实值输入
theta - 参数,也是一个实数
返回:
dtheta - 相对于θ的成本梯度
"""
dtheta = x
return dtheta
测试一下:
#测试backward_propagation
print("-----------------测试backward_propagation-----------------")
x, theta = 2, 4
dtheta = backward_propagation(x, theta)
print ("dtheta = " + str(dtheta))
测试结果:
-----------------测试backward_propagation-----------------
dtheta = 2
梯度检查的步骤如下:
- θ + = θ + ε \theta^{+} = \theta + \varepsilon θ+=θ+ε
- θ − = θ − ε \theta^{-} = \theta - \varepsilon θ−=θ−ε
- J + = J ( θ + ) J^{+} = J(\theta^{+}) J+=J(θ+)
- J − = J ( θ − ) J^{-} = J(\theta^{-}) J−=J(θ−)
- g r a d a p p r o x = J + − J − 2 ε gradapprox = \frac{J^{+} - J^{-}}{2 \varepsilon} gradapprox=2εJ+−J−
接下来,计算梯度的反向传播值,最后计算误差:
d
i
f
f
e
r
e
n
c
e
=
∣
∣
g
r
a
d
−
g
r
a
d
a
p
p
r
o
x
∣
∣
2
∣
∣
g
r
a
d
∣
∣
2
+
∣
∣
g
r
a
d
a
p
p
r
o
x
∣
∣
2
(4)
difference = \frac {\mid\mid grad - gradapprox \mid\mid_2}{\mid\mid grad \mid\mid_2 + \mid\mid gradapprox \mid\mid_2} \tag{4}
difference=∣∣grad∣∣2+∣∣gradapprox∣∣2∣∣grad−gradapprox∣∣2(4)
当difference小于 1 0 − 7 10^{-7} 10−7时,我们通常认为我们计算的结果是正确的。
def gradient_check(x,theta,epsilon=1e-7):
"""
实现图中的反向传播。
参数:
x - 一个实值输入
theta - 参数,也是一个实数
epsilon - 使用公式(3)计算输入的微小偏移以计算近似梯度
返回:
近似梯度和后向传播梯度之间的差异
"""
#使用公式(3)的左侧计算gradapprox。
thetaplus = theta + epsilon # Step 1
thetaminus = theta - epsilon # Step 2
J_plus = forward_propagation(x, thetaplus) # Step 3
J_minus = forward_propagation(x, thetaminus) # Step 4
gradapprox = (J_plus - J_minus) / (2 * epsilon) # Step 5
#检查gradapprox是否足够接近backward_propagation()的输出
grad = backward_propagation(x, theta)
numerator = np.linalg.norm(grad - gradapprox) # Step 1'
denominator = np.linalg.norm(grad) + np.linalg.norm(gradapprox) # Step 2'
difference = numerator / denominator # Step 3'
if difference < 1e-7:
print("梯度检查:梯度正常!")
else:
print("梯度检查:梯度超出阈值!")
return difference
测试一下:
#测试gradient_check
print("-----------------测试gradient_check-----------------")
x, theta = 2, 4
difference = gradient_check(x, theta)
print("difference = " + str(difference))
测试结果:
-----------------测试gradient_check-----------------
梯度检查:梯度正常!
difference = 2.91933588329e-10
高维参数是怎样计算的呢?我们看一下下图:

高维
def forward_propagation_n(X,Y,parameters):
"""
实现图中的前向传播(并计算成本)。
参数:
X - 训练集为m个例子
Y - m个示例的标签
parameters - 包含参数“W1”,“b1”,“W2”,“b2”,“W3”,“b3”的python字典:
W1 - 权重矩阵,维度为(5,4)
b1 - 偏向量,维度为(5,1)
W2 - 权重矩阵,维度为(3,5)
b2 - 偏向量,维度为(3,1)
W3 - 权重矩阵,维度为(1,3)
b3 - 偏向量,维度为(1,1)
返回:
cost - 成本函数(logistic)
"""
m = X.shape[1]
W1 = parameters["W1"]
b1 = parameters["b1"]
W2 = parameters["W2"]
b2 = parameters["b2"]
W3 = parameters["W3"]
b3 = parameters["b3"]
# LINEAR -> RELU -> LINEAR -> RELU -> LINEAR -> SIGMOID
Z1 = np.dot(W1,X) + b1
A1 = gc_utils.relu(Z1)
Z2 = np.dot(W2,A1) + b2
A2 = gc_utils.relu(Z2)
Z3 = np.dot(W3,A2) + b3
A3 = gc_utils.sigmoid(Z3)
#计算成本
logprobs = np.multiply(-np.log(A3), Y) + np.multiply(-np.log(1 - A3), 1 - Y)
cost = (1 / m) * np.sum(logprobs)
cache = (Z1, A1, W1, b1, Z2, A2, W2, b2, Z3, A3, W3, b3)
return cost, cache
def backward_propagation_n(X,Y,cache):
"""
实现图中所示的反向传播。
参数:
X - 输入数据点(输入节点数量,1)
Y - 标签
cache - 来自forward_propagation_n()的cache输出
返回:
gradients - 一个字典,其中包含与每个参数、激活和激活前变量相关的成本梯度。
"""
m = X.shape[1]
(Z1, A1, W1, b1, Z2, A2, W2, b2, Z3, A3, W3, b3) = cache
dZ3 = A3 - Y
dW3 = (1. / m) * np.dot(dZ3,A2.T)
dW3 = 1. / m * np.dot(dZ3, A2.T)
db3 = 1. / m * np.sum(dZ3, axis=1, keepdims=True)
dA2 = np.dot(W3.T, dZ3)
dZ2 = np.multiply(dA2, np.int64(A2 > 0))
#dW2 = 1. / m * np.dot(dZ2, A1.T) * 2 # Should not multiply by 2
dW2 = 1. / m * np.dot(dZ2, A1.T)
db2 = 1. / m * np.sum(dZ2, axis=1, keepdims=True)
dA1 = np.dot(W2.T, dZ2)
dZ1 = np.multiply(dA1, np.int64(A1 > 0))
dW1 = 1. / m * np.dot(dZ1, X.T)
#db1 = 4. / m * np.sum(dZ1, axis=1, keepdims=True) # Should not multiply by 4
db1 = 1. / m * np.sum(dZ1, axis=1, keepdims=True)
gradients = {"dZ3": dZ3, "dW3": dW3, "db3": db3,
"dA2": dA2, "dZ2": dZ2, "dW2": dW2, "db2": db2,
"dA1": dA1, "dZ1": dZ1, "dW1": dW1, "db1": db1}
return gradients
如果想比较“gradapprox”与反向传播计算的梯度。 该公式仍然是:
KaTeX parse error: \tag works only in display equations
然而, θ \theta θ不再是标量。 这是一个名为“parameters”的字典。 我们为你实现了一个函数“dictionary_to_vector()”。 它将“parameters”字典转换为一个称为“values”的向量,通过将所有参数(W1,b1,W2,b2,W3,b3)整形为向量并将它们连接起来而获得。
反函数是“vector_to_dictionary”,它返回“parameters”字典。

这里是伪代码,可以帮助你实现梯度检查:
For i in num_parameters:
- 计算
J_plus[i]:- 把
θ
+
\theta^{+}
θ+ 设置为
np.copy(parameters_values) - 把 θ i + \theta^{+}_i θi+ 设置为 θ i + + ε \theta^{+}_i + \varepsilon θi++ε
- 使用
forward_propagation_n(x, y, vector_to_dictionary(θ + \theta^{+} θ+))来计算 J i + J^{+}_i Ji+
- 把
θ
+
\theta^{+}
θ+ 设置为
- 计算
J_minus[i]: 使用相同的方法计算 θ − \theta^{-} θ− - 计算 g r a d a p p r o x [ i ] = J i + − J i − 2 ε gradapprox[i] = \frac{J^{+}_i - J^{-}_i}{2 \varepsilon} gradapprox[i]=2εJi+−Ji−
- 计算梯度
- 计算误差: d i f f e r e n c e = ∥ g r a d − g r a d a p p r o x ∥ 2 ∥ g r a d ∥ 2 + ∥ g r a d a p p r o x ∥ 2 (4) difference = \frac {\| grad - gradapprox \|_2}{\| grad \|_2 + \| gradapprox \|_2 } \tag{4} difference=∥grad∥2+∥gradapprox∥2∥grad−gradapprox∥2(4)
def gradient_check_n(parameters,gradients,X,Y,epsilon=1e-7):
"""
检查backward_propagation_n是否正确计算forward_propagation_n输出的成本梯度
参数:
parameters - 包含参数“W1”,“b1”,“W2”,“b2”,“W3”,“b3”的python字典:
grad_output_propagation_n的输出包含与参数相关的成本梯度。
x - 输入数据点,维度为(输入节点数量,1)
y - 标签
epsilon - 计算输入的微小偏移以计算近似梯度
返回:
difference - 近似梯度和后向传播梯度之间的差异
"""
#初始化参数
parameters_values , keys = gc_utils.dictionary_to_vector(parameters) #keys用不到
grad = gc_utils.gradients_to_vector(gradients)
num_parameters = parameters_values.shape[0]
J_plus = np.zeros((num_parameters,1))
J_minus = np.zeros((num_parameters,1))
gradapprox = np.zeros((num_parameters,1))
#计算gradapprox
for i in range(num_parameters):
#计算J_plus [i]。输入:“parameters_values,epsilon”。输出=“J_plus [i]”
thetaplus = np.copy(parameters_values) # Step 1
thetaplus[i][0] = thetaplus[i][0] + epsilon # Step 2
J_plus[i], cache = forward_propagation_n(X,Y,gc_utils.vector_to_dictionary(thetaplus)) # Step 3 ,cache用不到
#计算J_minus [i]。输入:“parameters_values,epsilon”。输出=“J_minus [i]”。
thetaminus = np.copy(parameters_values) # Step 1
thetaminus[i][0] = thetaminus[i][0] - epsilon # Step 2
J_minus[i], cache = forward_propagation_n(X,Y,gc_utils.vector_to_dictionary(thetaminus))# Step 3 ,cache用不到
#计算gradapprox[i]
gradapprox[i] = (J_plus[i] - J_minus[i]) / (2 * epsilon)
#通过计算差异比较gradapprox和后向传播梯度。
numerator = np.linalg.norm(grad - gradapprox) # Step 1'
denominator = np.linalg.norm(grad) + np.linalg.norm(gradapprox) # Step 2'
difference = numerator / denominator # Step 3'
if difference < 1e-7:
print("梯度检查:梯度正常!")
else:
print("梯度检查:梯度超出阈值!")
return difference
到此为止,这篇博文就算完成了,因为我没有弄到testCase.py,所以最后这一点点的梯度检查没法做,由此带来的麻烦还望多多谅解。
#相关库代码
init_utils.py
# -*- coding: utf-8 -*-
#init_utils.py
import numpy as np
import matplotlib.pyplot as plt
import sklearn
import sklearn.datasets
def sigmoid(x):
"""
Compute the sigmoid of x
Arguments:
x -- A scalar or numpy array of any size.
Return:
s -- sigmoid(x)
"""
s = 1/(1+np.exp(-x))
return s
def relu(x):
"""
Compute the relu of x
Arguments:
x -- A scalar or numpy array of any size.
Return:
s -- relu(x)
"""
s = np.maximum(0,x)
return s
def compute_loss(a3, Y):
"""
Implement the loss function
Arguments:
a3 -- post-activation, output of forward propagation
Y -- "true" labels vector, same shape as a3
Returns:
loss - value of the loss function
"""
m = Y.shape[1]
logprobs = np.multiply(-np.log(a3),Y) + np.multiply(-np.log(1 - a3), 1 - Y)
loss = 1./m * np.nansum(logprobs)
return loss
def forward_propagation(X, parameters):
"""
Implements the forward propagation (and computes the loss) presented in Figure 2.
Arguments:
X -- input dataset, of shape (input size, number of examples)
Y -- true "label" vector (containing 0 if cat, 1 if non-cat)
parameters -- python dictionary containing your parameters "W1", "b1", "W2", "b2", "W3", "b3":
W1 -- weight matrix of shape ()
b1 -- bias vector of shape ()
W2 -- weight matrix of shape ()
b2 -- bias vector of shape ()
W3 -- weight matrix of shape ()
b3 -- bias vector of shape ()
Returns:
loss -- the loss function (vanilla logistic loss)
"""
# retrieve parameters
W1 = parameters["W1"]
b1 = parameters["b1"]
W2 = parameters["W2"]
b2 = parameters["b2"]
W3 = parameters["W3"]
b3 = parameters["b3"]
# LINEAR -> RELU -> LINEAR -> RELU -> LINEAR -> SIGMOID
z1 = np.dot(W1, X) + b1
a1 = relu(z1)
z2 = np.dot(W2, a1) + b2
a2 = relu(z2)
z3 = np.dot(W3, a2) + b3
a3 = sigmoid(z3)
cache = (z1, a1, W1, b1, z2, a2, W2, b2, z3, a3, W3, b3)
return a3, cache
def backward_propagation(X, Y, cache):
"""
Implement the backward propagation presented in figure 2.
Arguments:
X -- input dataset, of shape (input size, number of examples)
Y -- true "label" vector (containing 0 if cat, 1 if non-cat)
cache -- cache output from forward_propagation()
Returns:
gradients -- A dictionary with the gradients with respect to each parameter, activation and pre-activation variables
"""
m = X.shape[1]
(z1, a1, W1, b1, z2, a2, W2, b2, z3, a3, W3, b3) = cache
dz3 = 1./m * (a3 - Y)
dW3 = np.dot(dz3, a2.T)
db3 = np.sum(dz3, axis=1, keepdims = True)
da2 = np.dot(W3.T, dz3)
dz2 = np.multiply(da2, np.int64(a2 > 0))
dW2 = np.dot(dz2, a1.T)
db2 = np.sum(dz2, axis=1, keepdims = True)
da1 = np.dot(W2.T, dz2)
dz1 = np.multiply(da1, np.int64(a1 > 0))
dW1 = np.dot(dz1, X.T)
db1 = np.sum(dz1, axis=1, keepdims = True)
gradients = {"dz3": dz3, "dW3": dW3, "db3": db3,
"da2": da2, "dz2": dz2, "dW2": dW2, "db2": db2,
"da1": da1, "dz1": dz1, "dW1": dW1, "db1": db1}
return gradients
def update_parameters(parameters, grads, learning_rate):
"""
Update parameters using gradient descent
Arguments:
parameters -- python dictionary containing your parameters
grads -- python dictionary containing your gradients, output of n_model_backward
Returns:
parameters -- python dictionary containing your updated parameters
parameters['W' + str(i)] = ...
parameters['b' + str(i)] = ...
"""
L = len(parameters) // 2 # number of layers in the neural networks
# Update rule for each parameter
for k in range(L):
parameters["W" + str(k+1)] = parameters["W" + str(k+1)] - learning_rate * grads["dW" + str(k+1)]
parameters["b" + str(k+1)] = parameters["b" + str(k+1)] - learning_rate * grads["db" + str(k+1)]
return parameters
def predict(X, y, parameters):
"""
This function is used to predict the results of a n-layer neural network.
Arguments:
X -- data set of examples you would like to label
parameters -- parameters of the trained model
Returns:
p -- predictions for the given dataset X
"""
m = X.shape[1]
p = np.zeros((1,m), dtype = np.int)
# Forward propagation
a3, caches = forward_propagation(X, parameters)
# convert probas to 0/1 predictions
for i in range(0, a3.shape[1]):
if a3[0,i] > 0.5:
p[0,i] = 1
else:
p[0,i] = 0
# print results
print("Accuracy: " + str(np.mean((p[0,:] == y[0,:]))))
return p
def load_dataset(is_plot=True):
np.random.seed(1)
train_X, train_Y = sklearn.datasets.make_circles(n_samples=300, noise=.05)
np.random.seed(2)
test_X, test_Y = sklearn.datasets.make_circles(n_samples=100, noise=.05)
# Visualize the data
if is_plot:
plt.scatter(train_X[:, 0], train_X[:, 1], c=train_Y, s=40, cmap=plt.cm.Spectral);
train_X = train_X.T
train_Y = train_Y.reshape((1, train_Y.shape[0]))
test_X = test_X.T
test_Y = test_Y.reshape((1, test_Y.shape[0]))
return train_X, train_Y, test_X, test_Y
def plot_decision_boundary(model, X, y):
# Set min and max values and give it some padding
x_min, x_max = X[0, :].min() - 1, X[0, :].max() + 1
y_min, y_max = X[1, :].min() - 1, X[1, :].max() + 1
h = 0.01
# Generate a grid of points with distance h between them
xx, yy = np.meshgrid(np.arange(x_min, x_max, h), np.arange(y_min, y_max, h))
# Predict the function value for the whole grid
Z = model(np.c_[xx.ravel(), yy.ravel()])
Z = Z.reshape(xx.shape)
# Plot the contour and training examples
plt.contourf(xx, yy, Z, cmap=plt.cm.Spectral)
plt.ylabel('x2')
plt.xlabel('x1')
plt.scatter(X[0, :], X[1, :], c=y, cmap=plt.cm.Spectral)
plt.show()
def predict_dec(parameters, X):
"""
Used for plotting decision boundary.
Arguments:
parameters -- python dictionary containing your parameters
X -- input data of size (m, K)
Returns
predictions -- vector of predictions of our model (red: 0 / blue: 1)
"""
# Predict using forward propagation and a classification threshold of 0.5
a3, cache = forward_propagation(X, parameters)
predictions = (a3>0.5)
return predictions
reg_utils.py
# -*- coding: utf-8 -*-
#reg_utils.py
import numpy as np
import matplotlib.pyplot as plt
import scipy.io as sio
def sigmoid(x):
"""
Compute the sigmoid of x
Arguments:
x -- A scalar or numpy array of any size.
Return:
s -- sigmoid(x)
"""
s = 1/(1+np.exp(-x))
return s
def relu(x):
"""
Compute the relu of x
Arguments:
x -- A scalar or numpy array of any size.
Return:
s -- relu(x)
"""
s = np.maximum(0,x)
return s
def initialize_parameters(layer_dims):
"""
Arguments:
layer_dims -- python array (list) containing the dimensions of each layer in our network
Returns:
parameters -- python dictionary containing your parameters "W1", "b1", ..., "WL", "bL":
W1 -- weight matrix of shape (layer_dims[l], layer_dims[l-1])
b1 -- bias vector of shape (layer_dims[l], 1)
Wl -- weight matrix of shape (layer_dims[l-1], layer_dims[l])
bl -- bias vector of shape (1, layer_dims[l])
Tips:
- For example: the layer_dims for the "Planar Data classification model" would have been [2,2,1].
This means W1's shape was (2,2), b1 was (1,2), W2 was (2,1) and b2 was (1,1). Now you have to generalize it!
- In the for loop, use parameters['W' + str(l)] to access Wl, where l is the iterative integer.
"""
np.random.seed(3)
parameters = {}
L = len(layer_dims) # number of layers in the network
for l in range(1, L):
parameters['W' + str(l)] = np.random.randn(layer_dims[l], layer_dims[l-1]) / np.sqrt(layer_dims[l-1])
parameters['b' + str(l)] = np.zeros((layer_dims[l], 1))
assert(parameters['W' + str(l)].shape == layer_dims[l], layer_dims[l-1])
assert(parameters['W' + str(l)].shape == layer_dims[l], 1)
return parameters
def forward_propagation(X, parameters):
"""
Implements the forward propagation (and computes the loss) presented in Figure 2.
Arguments:
X -- input dataset, of shape (input size, number of examples)
Y -- true "label" vector (containing 0 if cat, 1 if non-cat)
parameters -- python dictionary containing your parameters "W1", "b1", "W2", "b2", "W3", "b3":
W1 -- weight matrix of shape ()
b1 -- bias vector of shape ()
W2 -- weight matrix of shape ()
b2 -- bias vector of shape ()
W3 -- weight matrix of shape ()
b3 -- bias vector of shape ()
Returns:
loss -- the loss function (vanilla logistic loss)
"""
# retrieve parameters
W1 = parameters["W1"]
b1 = parameters["b1"]
W2 = parameters["W2"]
b2 = parameters["b2"]
W3 = parameters["W3"]
b3 = parameters["b3"]
# LINEAR -> RELU -> LINEAR -> RELU -> LINEAR -> SIGMOID
z1 = np.dot(W1, X) + b1
a1 = relu(z1)
z2 = np.dot(W2, a1) + b2
a2 = relu(z2)
z3 = np.dot(W3, a2) + b3
a3 = sigmoid(z3)
cache = (z1, a1, W1, b1, z2, a2, W2, b2, z3, a3, W3, b3)
return a3, cache
def compute_cost(a3, Y):
"""
Implement the cost function
Arguments:
a3 -- post-activation, output of forward propagation
Y -- "true" labels vector, same shape as a3
Returns:
cost - value of the cost function
"""
m = Y.shape[1]
logprobs = np.multiply(-np.log(a3),Y) + np.multiply(-np.log(1 - a3), 1 - Y)
cost = 1./m * np.nansum(logprobs)
return cost
def backward_propagation(X, Y, cache):
"""
Implement the backward propagation presented in figure 2.
Arguments:
X -- input dataset, of shape (input size, number of examples)
Y -- true "label" vector (containing 0 if cat, 1 if non-cat)
cache -- cache output from forward_propagation()
Returns:
gradients -- A dictionary with the gradients with respect to each parameter, activation and pre-activation variables
"""
m = X.shape[1]
(z1, a1, W1, b1, z2, a2, W2, b2, z3, a3, W3, b3) = cache
dz3 = 1./m * (a3 - Y)
dW3 = np.dot(dz3, a2.T)
db3 = np.sum(dz3, axis=1, keepdims = True)
da2 = np.dot(W3.T, dz3)
dz2 = np.multiply(da2, np.int64(a2 > 0))
dW2 = np.dot(dz2, a1.T)
db2 = np.sum(dz2, axis=1, keepdims = True)
da1 = np.dot(W2.T, dz2)
dz1 = np.multiply(da1, np.int64(a1 > 0))
dW1 = np.dot(dz1, X.T)
db1 = np.sum(dz1, axis=1, keepdims = True)
gradients = {"dz3": dz3, "dW3": dW3, "db3": db3,
"da2": da2, "dz2": dz2, "dW2": dW2, "db2": db2,
"da1": da1, "dz1": dz1, "dW1": dW1, "db1": db1}
return gradients
def update_parameters(parameters, grads, learning_rate):
"""
Update parameters using gradient descent
Arguments:
parameters -- python dictionary containing your parameters
grads -- python dictionary containing your gradients, output of n_model_backward
Returns:
parameters -- python dictionary containing your updated parameters
parameters['W' + str(i)] = ...
parameters['b' + str(i)] = ...
"""
L = len(parameters) // 2 # number of layers in the neural networks
# Update rule for each parameter
for k in range(L):
parameters["W" + str(k+1)] = parameters["W" + str(k+1)] - learning_rate * grads["dW" + str(k+1)]
parameters["b" + str(k+1)] = parameters["b" + str(k+1)] - learning_rate * grads["db" + str(k+1)]
return parameters
def load_2D_dataset(is_plot=True):
data = sio.loadmat('datasets/data.mat')
train_X = data['X'].T
train_Y = data['y'].T
test_X = data['Xval'].T
test_Y = data['yval'].T
if is_plot:
plt.scatter(train_X[0, :], train_X[1, :], c=train_Y, s=40, cmap=plt.cm.Spectral);
return train_X, train_Y, test_X, test_Y
def predict(X, y, parameters):
"""
This function is used to predict the results of a n-layer neural network.
Arguments:
X -- data set of examples you would like to label
parameters -- parameters of the trained model
Returns:
p -- predictions for the given dataset X
"""
m = X.shape[1]
p = np.zeros((1,m), dtype = np.int)
# Forward propagation
a3, caches = forward_propagation(X, parameters)
# convert probas to 0/1 predictions
for i in range(0, a3.shape[1]):
if a3[0,i] > 0.5:
p[0,i] = 1
else:
p[0,i] = 0
# print results
print("Accuracy: " + str(np.mean((p[0,:] == y[0,:]))))
return p
def plot_decision_boundary(model, X, y):
# Set min and max values and give it some padding
x_min, x_max = X[0, :].min() - 1, X[0, :].max() + 1
y_min, y_max = X[1, :].min() - 1, X[1, :].max() + 1
h = 0.01
# Generate a grid of points with distance h between them
xx, yy = np.meshgrid(np.arange(x_min, x_max, h), np.arange(y_min, y_max, h))
# Predict the function value for the whole grid
Z = model(np.c_[xx.ravel(), yy.ravel()])
Z = Z.reshape(xx.shape)
# Plot the contour and training examples
plt.contourf(xx, yy, Z, cmap=plt.cm.Spectral)
plt.ylabel('x2')
plt.xlabel('x1')
plt.scatter(X[0, :], X[1, :], c=y, cmap=plt.cm.Spectral)
plt.show()
def predict_dec(parameters, X):
"""
Used for plotting decision boundary.
Arguments:
parameters -- python dictionary containing your parameters
X -- input data of size (m, K)
Returns
predictions -- vector of predictions of our model (red: 0 / blue: 1)
"""
# Predict using forward propagation and a classification threshold of 0.5
a3, cache = forward_propagation(X, parameters)
predictions = (a3>0.5)
return predictions
##gc_utils.py
# -*- coding: utf-8 -*-
#gc_utils.py
import numpy as np
import matplotlib.pyplot as plt
def sigmoid(x):
"""
Compute the sigmoid of x
Arguments:
x -- A scalar or numpy array of any size.
Return:
s -- sigmoid(x)
"""
s = 1/(1+np.exp(-x))
return s
def relu(x):
"""
Compute the relu of x
Arguments:
x -- A scalar or numpy array of any size.
Return:
s -- relu(x)
"""
s = np.maximum(0,x)
return s
def dictionary_to_vector(parameters):
"""
Roll all our parameters dictionary into a single vector satisfying our specific required shape.
"""
keys = []
count = 0
for key in ["W1", "b1", "W2", "b2", "W3", "b3"]:
# flatten parameter
new_vector = np.reshape(parameters[key], (-1,1))
keys = keys + [key]*new_vector.shape[0]
if count == 0:
theta = new_vector
else:
theta = np.concatenate((theta, new_vector), axis=0)
count = count + 1
return theta, keys
def vector_to_dictionary(theta):
"""
Unroll all our parameters dictionary from a single vector satisfying our specific required shape.
"""
parameters = {}
parameters["W1"] = theta[:20].reshape((5,4))
parameters["b1"] = theta[20:25].reshape((5,1))
parameters["W2"] = theta[25:40].reshape((3,5))
parameters["b2"] = theta[40:43].reshape((3,1))
parameters["W3"] = theta[43:46].reshape((1,3))
parameters["b3"] = theta[46:47].reshape((1,1))
return parameters
def gradients_to_vector(gradients):
"""
Roll all our gradients dictionary into a single vector satisfying our specific required shape.
"""
count = 0
for key in ["dW1", "db1", "dW2", "db2", "dW3", "db3"]:
# flatten parameter
new_vector = np.reshape(gradients[key], (-1,1))
if count == 0:
theta = new_vector
else:
theta = np.concatenate((theta, new_vector), axis=0)
count = count + 1
return theta








 本文深入探讨了吴恩达课程中的初始化、正则化和梯度检查技术,通过实例演示如何有效避免梯度消失或爆炸,利用L2正则化和Dropout减少过拟合,并验证反向传播的准确性。
本文深入探讨了吴恩达课程中的初始化、正则化和梯度检查技术,通过实例演示如何有效避免梯度消失或爆炸,利用L2正则化和Dropout减少过拟合,并验证反向传播的准确性。
















 646
646

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








