获取到数据集中的每一个ID
首先是测试集:testset.csv
这里测试集是这个样子的:
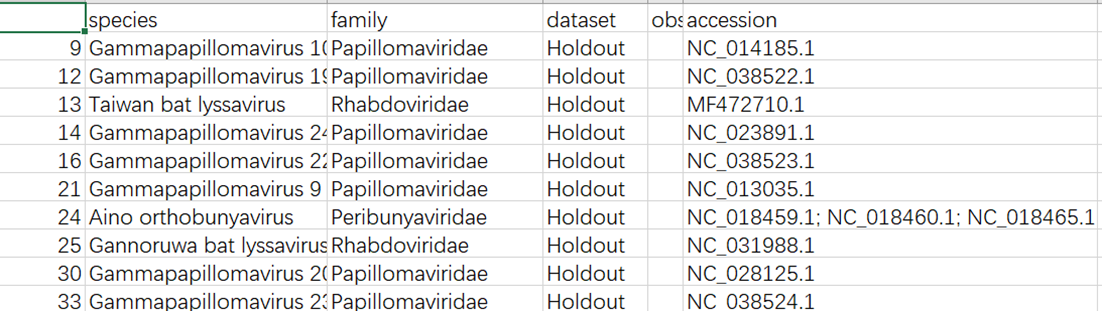
我需要根据每一个病毒的accsssion的ID去下载对应的基因文件,首先需要读取到每一个ID号
import os
import pandas as pd
from Bio import Entrez, SeqIO
from urllib.error import HTTPError
#这个函数获取到所有的NCBI id列表
def GetAccssions(CSV_path):
'''CSV_path:是csv文件的路径
'''
df = pd.read_csv(CSV_path)
#数据集中的accession列的数据转为列表
accs = df.accession.to_list()
#存放每一个ID的列表,每一个ID作为一个单独的列表元素
Accseesions = []
#accs是包含每一行的列表,不是每一个ID号的列表,进一步处理获取每个ID号的列表
for acc in accs:
#acc可以是多个ID号的字符串,中间使用分号;隔开的字符串
acc_list = acc.split(';')
#acc_list是每一行数据分割后的列表,再次遍历,去掉左右空格,
for id in acc_list:
id = id.strip()
Accseesions.append(id)
return Accseesions
调用结果:
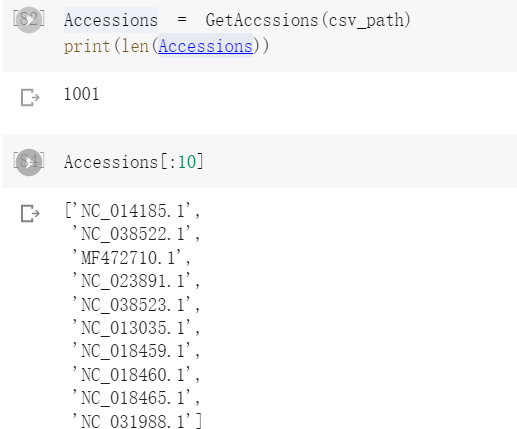
根据ID下载gb文件
拿到每一个ID后,需要下载gb文件
from posixpath import exists
def downGb_fromID(Accessions,filePath):
'''Accessions:是一个一个的id构成的列表,
filePath:文件的下载路径
'''
if not os.path.exists(filePath):
#执行到这里,目录基本不可能存在
os.makedirs(filePath)
#如果exist_ok为False(默认值),则在目标目录已存在的情况下触发FileExistsError异常;如果exist_ok为True,则在目标目录已存在的情况下不会触发FileExistsError异常。
assert os.path.exists(filePath)
os.chdir(filePath)#切换到下载目录的路径下
Entrez.tool = "ZoonosisPredictor pipeline - DownloadSequences.py"
Entrez.email = "xxjxuejian@gmail.com"
#拿到每一个NC的 ID号
for ID in Accessions:
#保存的文件名格式
FileName = "{}.gb".format(ID)
#如果文件不存在,刚开始肯定是不存在的,所以会下载
if not os.path.isfile(FileName):
try:
#这是在下载
QueryHandle = Entrez.efetch(db="nucleotide",id=ID,rettype="gb",retmode="text")
except HTTPError as Error:
if Error.code == 400: # Bad request
raise ValueError("Accession number not found: {}".format(Accessions(ID)))
else:
raise
#写入文件
with open(FileName, 'w') as WriteHandle:
WriteHandle.write(QueryHandle.read())
else:
print("{} exists, not updated".format(FileName))
到这里,就完成了所有accession的下载。
这里可以检查下路径下的所有的文件的数量,是不是和Accessions列表的长度一样,确保每一个都进行了下载。
返回每一个ID对应的碱基序列
由于我们需要的是基因的序列,AGCT这样的序列,下面需要根据每一个gb文件获取到序列信息。
这个函数是根据每一个gb文件返回对应的序列,这个序列是经过编码后的序列,之后再解码就行。
from genericpath import isfile
def gb_to_seqStr(gbPath):
'''gbPath:这个参数是每一个gb文件的路径
'''
#拿到路径直接操作
SeqRec = SeqIO.read(gbPath, format = "genbank")
# seqStr = SeqRec.seq.encode('ascii')这个方法废弃了
seqStr = bytes(SeqRec.seq)#默认是UTF-8编码
#SeqRec.id, SeqRec.name , SeqRec.description
return seqStr
#或者考虑把id,name,seq,构造成一个字典一起返回出去
测试:
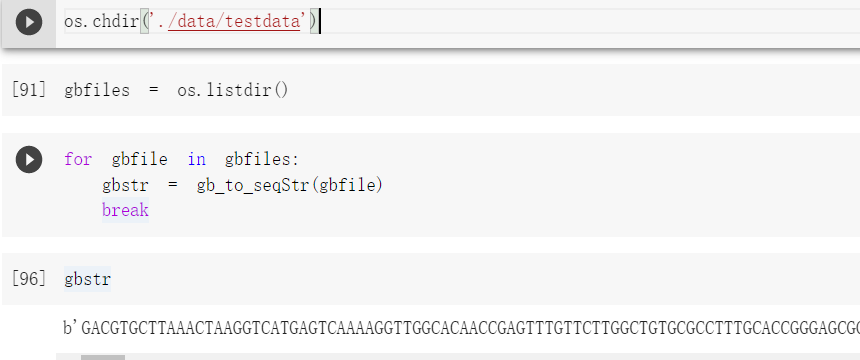
解码:

构建一个包含序列id,序列字符串等的字典
针对训练集的字典
data_train = pd.read_csv('/content/drive/MyDrive/zoonotic/trainset.csv')
data_test = pd.read_csv('/content/drive/MyDrive/zoonotic/testset.csv')
def trainset_to_dict(datas):
'''datas参数是读取到的csv对象
'''
data_dict = {}
for row in datas.iterrows():
series = row[1]
label = 1
#首先看是属于哪个类别
if series['observed_infection_class'] == 'No known human infections':
label = 0
accessions = series['accession'].split(';')
for index,value in enumerate(accessions):
value = value.strip()
accessions[index] = value
#如果大于1,说明有多个id,对每一个id都要构造一个字典
if len(accessions) == 1:
#长度就是1 的
single = {
'id':accessions[0],
'species':series['species'],
'family':series['family'],
'label':label
}
data_dict[accessions[0]] = single
else:
#长度大于1的
for index in range(len(accessions)):
single = {
'id':accessions[index],
'species':series['species'],
'family':series['family'],
'label':label
}
data_dict[accessions[index]] = single
return data_dict
针对测试集的字典
def testset_to_dict(datas):
data_dict = {}
for row in datas.iterrows():
series = row[1]
accessions = series['accession'].split(';')
#去掉空白符
for index,value in enumerate(accessions):
value = value.strip()
accessions[index] = value
# print(accessions)
# print(len(accessions))
#如果大于1,说明有多个id,对每一个id都要构造一个字典
if len(accessions) == 1:
#长度就是1 的
single = {
'id':accessions[0],
'species':series['species'],
'family':series['family'],
}
data_dict[accessions[0]] = single
else:
#长度大于1的
for index in range(len(accessions)):
single = {
'id':accessions[index],
'species':series['species'],
'family':series['family'],
}
data_dict[accessions[index]] = single
return data_dict
这个字典是这样的:

字典持久化存储
使用pickle模块把这个字典持久化的存储下来
import pickle
train_path = '/content/drive/MyDrive/zoonotic/Final_trainset.pkl'
with open(train_path,'wb') as f:
pickle.dump(train_dict,f)
构造tensorflow的输入数据格式
要把碱基序列转为one-hot矩阵,还要把标签也转为one-hot形式,还要注意数据的类型,设计好example
序列转矩阵的函数
import numpy as np
import random
import tensorflow as tf
import inspect
from typing import Any, Callable, Dict, Optional, Text, Union, Iterable
import os
from tensorflow.core.example.feature_pb2 import BytesList
# import sonnet as snt
from tqdm import tqdm
from IPython.display import clear_output
import numpy as np
import pandas as pd
import time
import pickle
#DNA序列转为one-hot编码,可以直接拿来用
def one_hot_encode(sequence: str,
alphabet: str = 'ACGT',
neutral_alphabet: str = 'N',
neutral_value: Any = 0,
dtype=np.float32) -> np.ndarray:
"""One-hot encode sequence."""
def to_uint8(string):
return np.frombuffer(string.encode('ascii'), dtype=np.uint8)
hash_table = np.zeros((np.iinfo(np.uint8).max, len(alphabet)), dtype=dtype)
hash_table[to_uint8(alphabet)] = np.eye(len(alphabet), dtype=dtype)
hash_table[to_uint8(neutral_alphabet)] = neutral_value
hash_table = hash_table.astype(dtype)
return hash_table[to_uint8(sequence)]
长度填充函数
MaxLength = 241087
def pad_to_maxLen(arr):
'''
arr:需要填充的ndarray数组
'''
length = MaxLength-arr.shape[0]
arr = np.pad(arr,((0,length),(0,0)),'constant',constant_values=(0))
return arr
写入tfr文件
#tfr文件的路径
path = '/content/drive/MyDrive/zoonotic/Trainset.tfr'
#train_dict需要提前读取到
with tf.io.TFRecordWriter(path) as writer:
for k,v in train_dict.items():
id = bytes(k,encoding='utf-8')
seq = v['seq'].decode('utf-8')
#label内的元素类型也转为float32类型
label = v['label'].astype(np.float32)
label = label.tobytes()#label也是一个矩阵,需要转为字节
#字符序列转矩阵
matrix = one_hot_encode(seq)
#填充
matrix = pad_to_maxLen(matrix)
#转为字节类型
matrix = matrix.tobytes()
#写入tfr文件
feature = {
#序列使用的是tf.train.BytesList类型
'id':tf.train.Feature(bytes_list=tf.train.BytesList(value=[id])),
'sequence':tf.train.Feature(bytes_list=tf.train.BytesList(value=[matrix])),
#'label':tf.train.Feature(int64_list=tf.train.Int64List(value=[label]))#标签单是一个数字的时候用这个
'label':tf.train.Feature(bytes_list=tf.train.BytesList(value=[label])),
}
example = tf.train.Example(features=tf.train.Features(feature=feature))
writer.write(example.SerializeToString())
读取tfr文件
#这个相当于是填充用的,占位
feature_description = {
'id':tf.io.FixedLenFeature((),tf.string),
"sequence": tf.io.FixedLenFeature((), tf.string),
"label": tf.io.FixedLenFeature((), tf.string)
}
#将 TFRecord 文件中的每一个序列化的 tf.train.Example 解码
def parse_example(example_string):
#解析之后得到的example
example = tf.io.parse_single_example(example_string,feature_description)
# id = tf.io.decode_raw(example['id'],tf.string)
id = tf.cast(example['id'],tf.string)
#example['sequence']还是字节流的形式,重新转为数字向量
sequence = tf.io.decode_raw(example['sequence'], tf.float32)
sequence = tf.reshape(sequence,(MaxLength,4)) #形状需要重塑,不然就是一个长向量
# label = tf.cast(example['label'],tf.int64) #标签对应的类型转换
label = tf.io.decode_raw(example['label'], tf.float32)
label = tf.reshape(label,(1,2))
#把整个字典返回
return {
'id':id,
'sequence':sequence,
'label': label
}
dataset = tf.data.TFRecordDataset(path)
dataset = dataset.map(parse_example)
it = iter(dataset)
example = next(it)
example

数据集的长度
由于需要设计模型的输入长度,还需要知道每一条序列的长度,也就是有多少个碱基。获取每一条序列的长度,然后比较获得最大的序列长度,根据这个长度设计模型的输入长度。
可以把每一条序列的长度都记录下来,然后使用可视化工具,或者画一个箱型图,查看数据的分布情况,设计一个合理的序列长度。
函数gb_to_seqStr()可以返回病毒的序列字符串
返回的是所有序列的长度的列表
def get_lengths(gbfiles):
'''gbfiles:参数是每一个gb文件的路径
'''
#存储每一个序列长度的列表
lengths = []
for gb in gbfiles:
gbStr = gb_to_seqStr(gb)
length = len(gbStr)
lengths.append(length)
return lengths
关于箱型图的代码:
import matplotlib.pyplot as plt
import numpy as np
x = lengths
sorted(x)
a = np.quantile(x, 0.75) # 上四分之一数
b = np.quantile(x, 0.25) # 下四分之一数
print("平均数:", np.mean(x)) # 打印均值
print("中位数:", np.median(x)) # 打印中位数
print("上四分之一数:", a) # 打印上四分之一数
print("下四分之一数:", b) # 打印下四分之一数
up = a + 1.5 * (a - b) # 异常值判断标准
down = b - 1.5 * (a - b) # 异常值判断标准
x = np.sort(x) # 对原始数据排序
shangjie = x[x < up][-1] # 除了异常值外的最大值
xiajie = x[x > down][0] # 除了异常值外的最小值
print("上界:", shangjie) # 打印上界
print("up:", up)
print("down:", down)
print("下界:", xiajie) # 打印下界
plt.grid(True) # 显示网格
y = plt.boxplot(x, meanline=True, showmeans=True,
flierprops={"marker": "o", "markerfacecolor": "red", "markersize": 15}) # 绘制箱形图,设置异常点大小、样式等
plt.show() # 显示图






















 1243
1243











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








