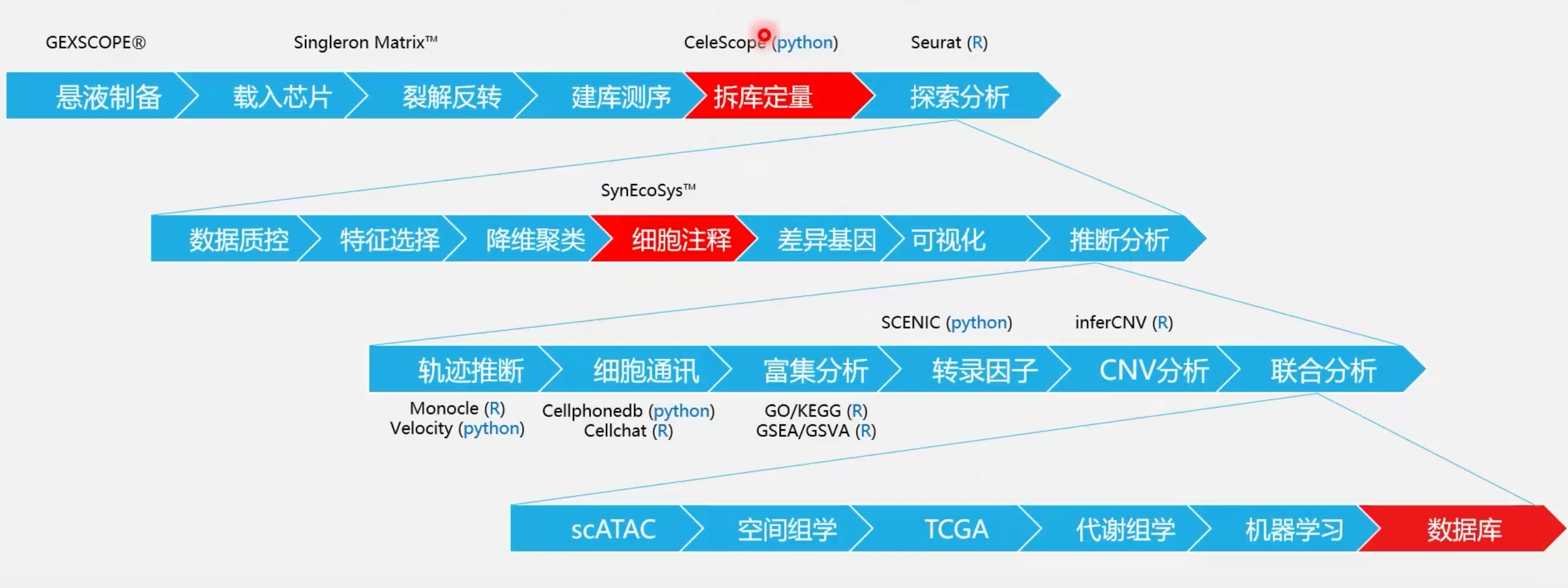
新格元-CeleScope实战
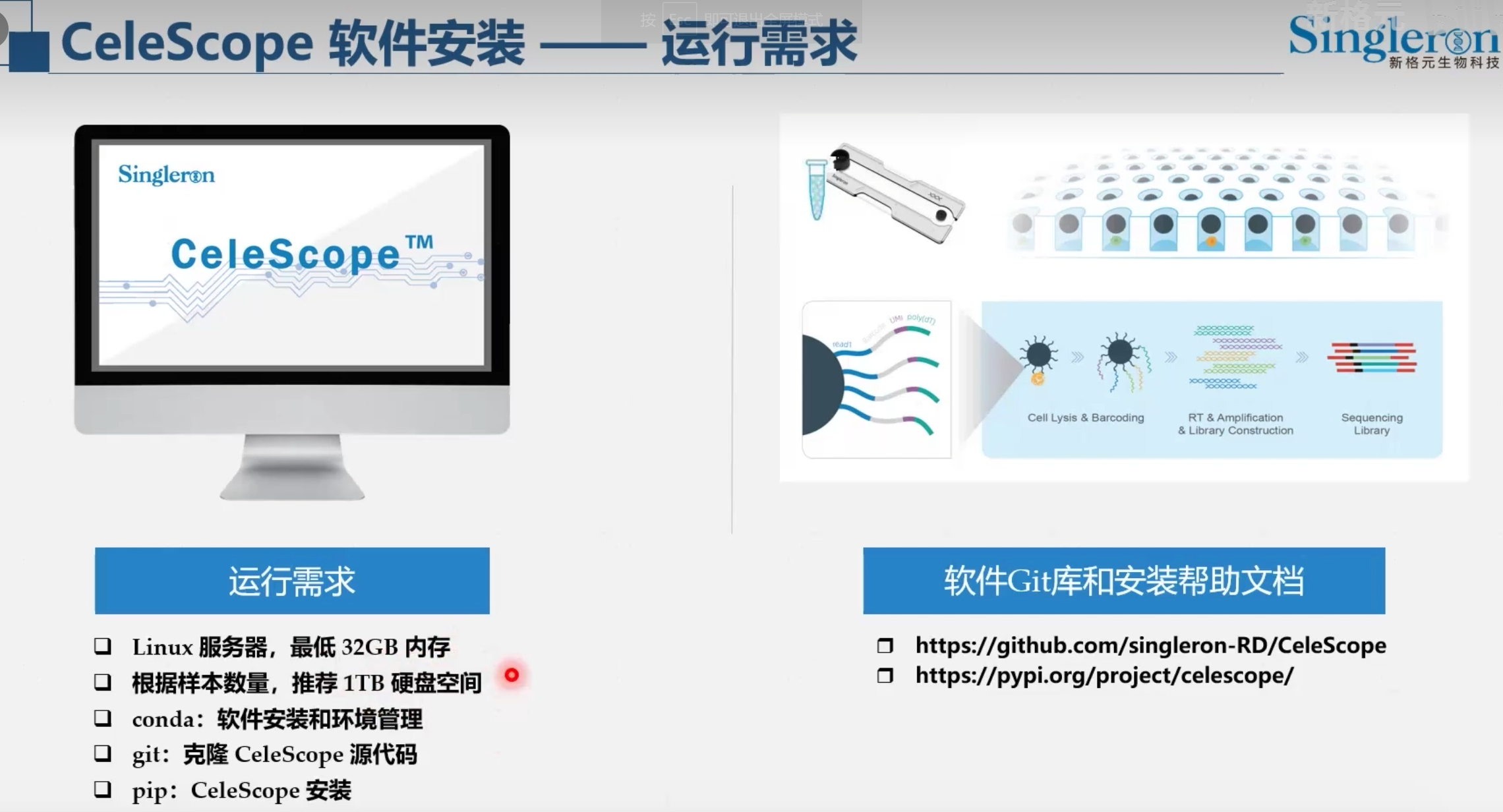
下载软件
# GitHub提供了一个conda_pkgs.txt文件,需要git clone到服务器
git clone https://github.com/singleron-RD/CeleScope.git
# 创建conda环境并安装conda包。 推荐使用mamba(是Conda的更快替代品)
conda install mamba
cd CeleScope
mamba create -n celescope -y --file conda_pkgs.txt
# 安装CeleScope
# 在运行 pip install celescope 之前,请确保您已激活 celescope conda 环境
# 依赖包很多啊,部分是conda安装,部分需要用pip
conda activate celescope
pip install celescope
整个流程:(其实就是cutadapt 和 star, featureCounts的封装)
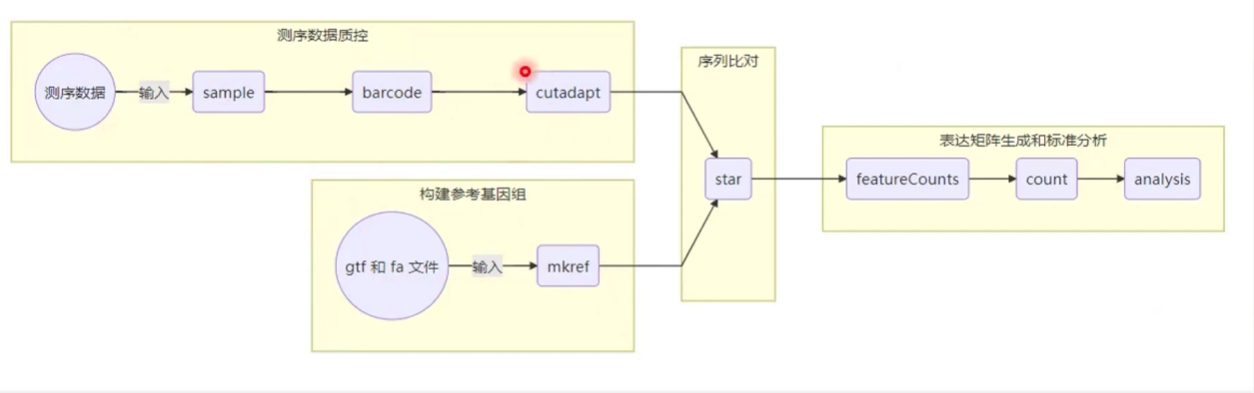
下载参考基因组文件
mkdir hs_ensembl_99
cd hs_ensembl_99
# 下载人的参考基因组fa文件与gtf文件,你是鼠的就下载鼠的然后构建就好了
wget ftp://ftp.ensembl.org/pub/release-99/fasta/homo_sapiens/dna/Homo_sapiens.GRCh38.dna.primary_assembly.fa.gz
wget ftp://ftp.ensembl.org/pub/release-99/gtf/homo_sapiens/Homo_sapiens.GRCh38.99.gtf.gz
# 解压
gunzip Homo_sapiens.GRCh38.dna.primary_assembly.fa.gz
gunzip Homo_sapiens.GRCh38.99.gtf.gz
conda activate celescope
# 构建参考基因组
nohup celescope rna mkref \
--genome_name Homo_sapiens_ensembl_99 \ #参考基因组名字
--fasta Homo_sapiens.GRCh38.dna.primary_assembly.fa \ #参考基因组文件路径
--gtf Homo_sapiens.GRCh38.99.gtf & #参考基因组注释文件路径
运行测试数据
#下载测试数据,
mkdir test_dir
cd test_dir
git clone https://github.com/singleron-RD/celescope_test_data.git
git clone https://github.com/singleron-RD/celescope_test_script.git
# 尝试运行CeleScope
cd
mkdir test_celescope
cd test_celescope
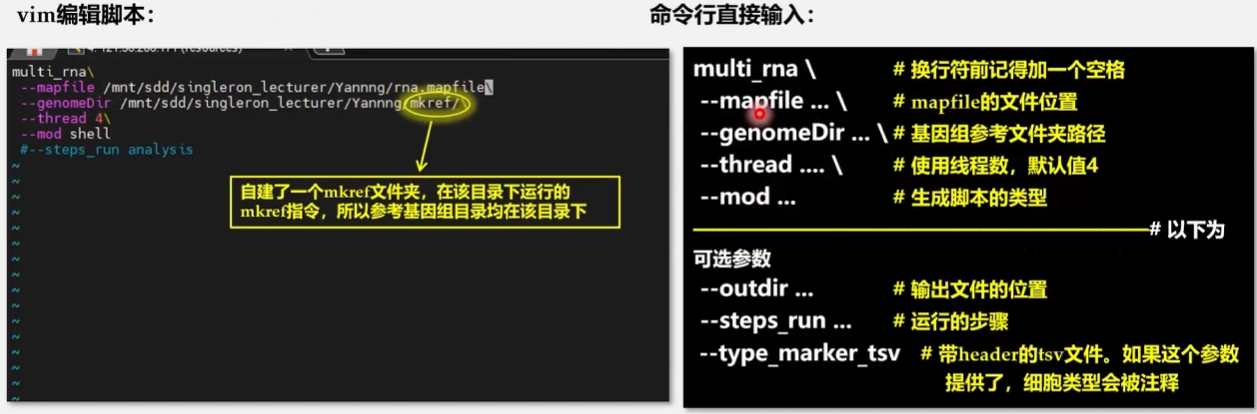
vim mymapfile
#其实就是三行命令,第一个是fastq的前缀,不用管_1或者_2,它能识别,第二个就是你的fastq的绝对路径,第三个就是输出文件的文件名,还是很简单的
# rna /home/legenddyx/CeleScope/test_dir/celescope_test_data/rna/fastqs/ rna_test
multi_rna\
--mapfile ./mymapfile\
--genomeDir /home/legenddyx/hs_ensembl_99\
--thread 4\
--mod shell\
--gzip
# 运行上面的代码之后就会生成一个shell的文件夹,里面有一个sh,直接运行这个sh脚本就可以得到结果了
sh ./shell/rna_test.sh
得到结果了
sh ./shell/rna_test.sh
[外链图片转存中...(img-B322LKok-1695313311121)]























 1522
1522

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








