FSL是牛津大学开发的十分好用的脑核磁图像处理工具,其中可以利用bedpostx和protrackx对DTI图像进行概率纤维追踪(probabilistic tractography)。但这一过程(尤其是bedpostx),在FSL给出的官方文档中被说明每张图片都需要消耗大约15小时的运算时间,好在FSL也提供了bedpostx和probtrackx2的GPU版本,稍作配置之后便可以通过命令行形式使用,效果拔群。
FSL官方文档上仅介绍了概率纤维追踪的GUI方法,命令行教程并不清晰,而GUI是无法使用GPU加速的,故本文同时给出了使用部分命令行方法的详细步骤。
配置信息
OS:Ubuntu 16.04 LTS
GPU:NVIDIA Tesla V100-PCIE-32GB
CUDA Runtime version: 9.2
Cudnn version: 7.4.1
FSL:6.0
要注意一下,根据这里,使用probtrackx2_gpu要求你的GPU至少有5GB的显存,否则在运行过程中容易出现out of memory。
配置bedpostx_gpu和probtrackx2_gpu
在官方网站上下载:bedpostx_gpu和probtrackx2_gpu,注意根据你的CUDA Runtime version选择对应版本。若不支持你的CUDA版本,则需要重新安装CUDA和Cudnn。
下载完成后解压缩
-
bedpostx_gpu解压缩后有bin和lib两个文件夹,将bin中所有文件cp到$FSLDIR/bin下,将lib文件夹中所有文件cp到$FSLDIR/lib下
-
probtrackx_gpu解压缩后仅有一个二进制文件,将其cp到$FSLDIR/bin下即可。
文件复制完成后,需要将bedpostx_postproc_gpu.sh中第一行的#!/bin/sh改为#!/bin/bash,否则会出现bug导致第13行的if分支无法进入。
bedpostx
bedpostx采用马尔可夫链蒙特卡罗采样来建立每个体素的扩散参数分布,最终生成概率纤维追踪(probabilistic tractography)所需要的所有参数文件。
数据准备
使用bedpostx_gpu需要确定你的执行目录下有:
-
data: 4D数据文件(.nii或.nii.gz),由原始数据预处理后得到。
-
nodif_brain_mask: 3D二进制掩码(.nii或.nii.gz),对结构像bet后得到。
-
bvecs: 3xN的ASCII文本文件,代表DTI图片采集时的磁场参数之一。
-
bvals: 1xN的ASCII文本文件,代表DTI图片采集时的磁场参数之一。
这是我的存放数据的位置,其余文件是我做了DTIFIT的结果。

数据检查
在执行bedpostx_gpu前要对上述的数据文件进行格式检查,各数据需要满足的格式要求为:
-
mask和data文件除mask的第四维为1以外,其它维度大小应对应相等。
-
bvecs与bvals是DTI图像采集过程中的磁场参数,每行的字数N需与data文件的第四个维度相同。
可在命令行中cd到执行文件夹后运行bedpostx_datacheck这一shell脚本来检查各数据文件是否存在且格式是否匹配。
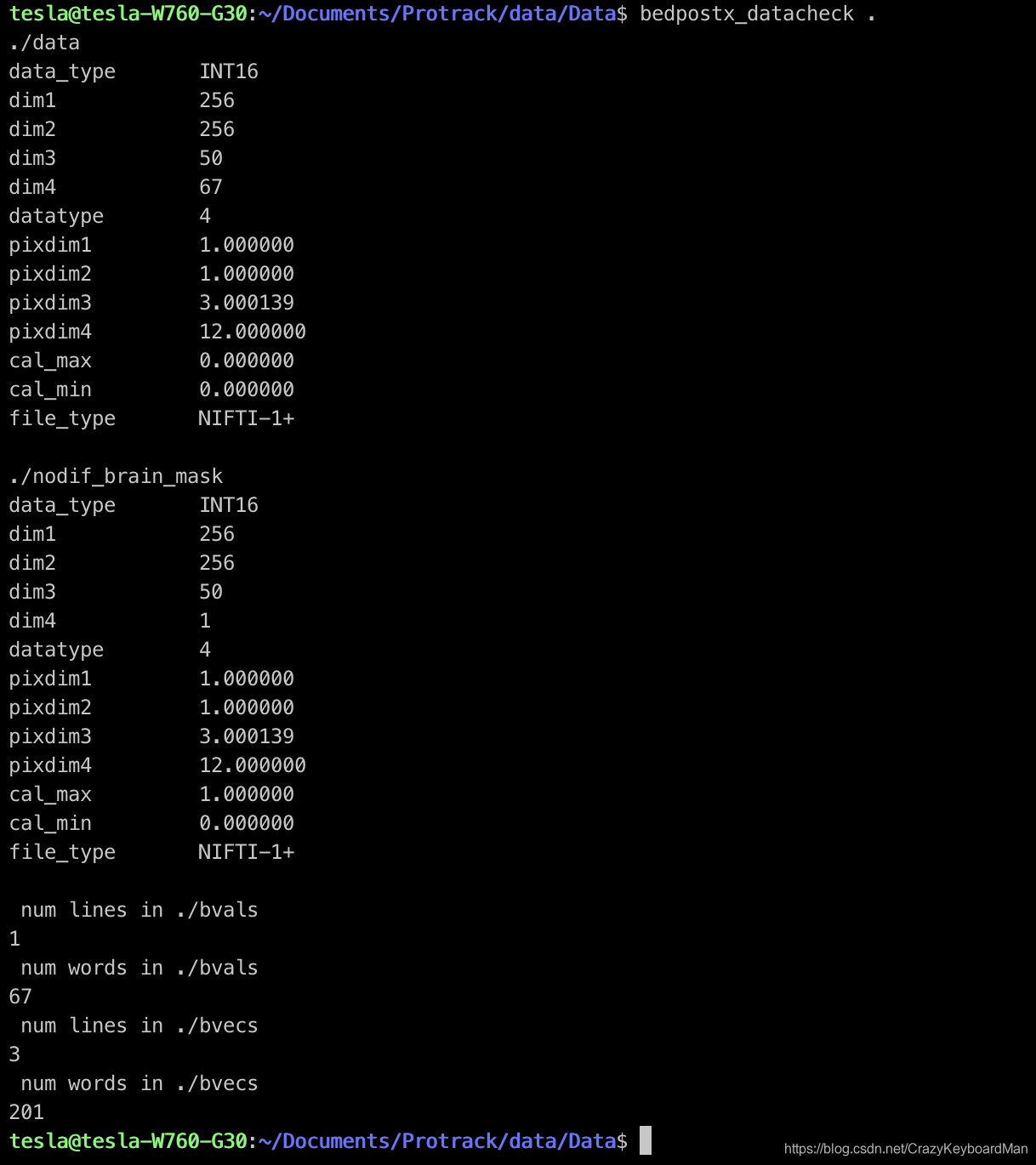
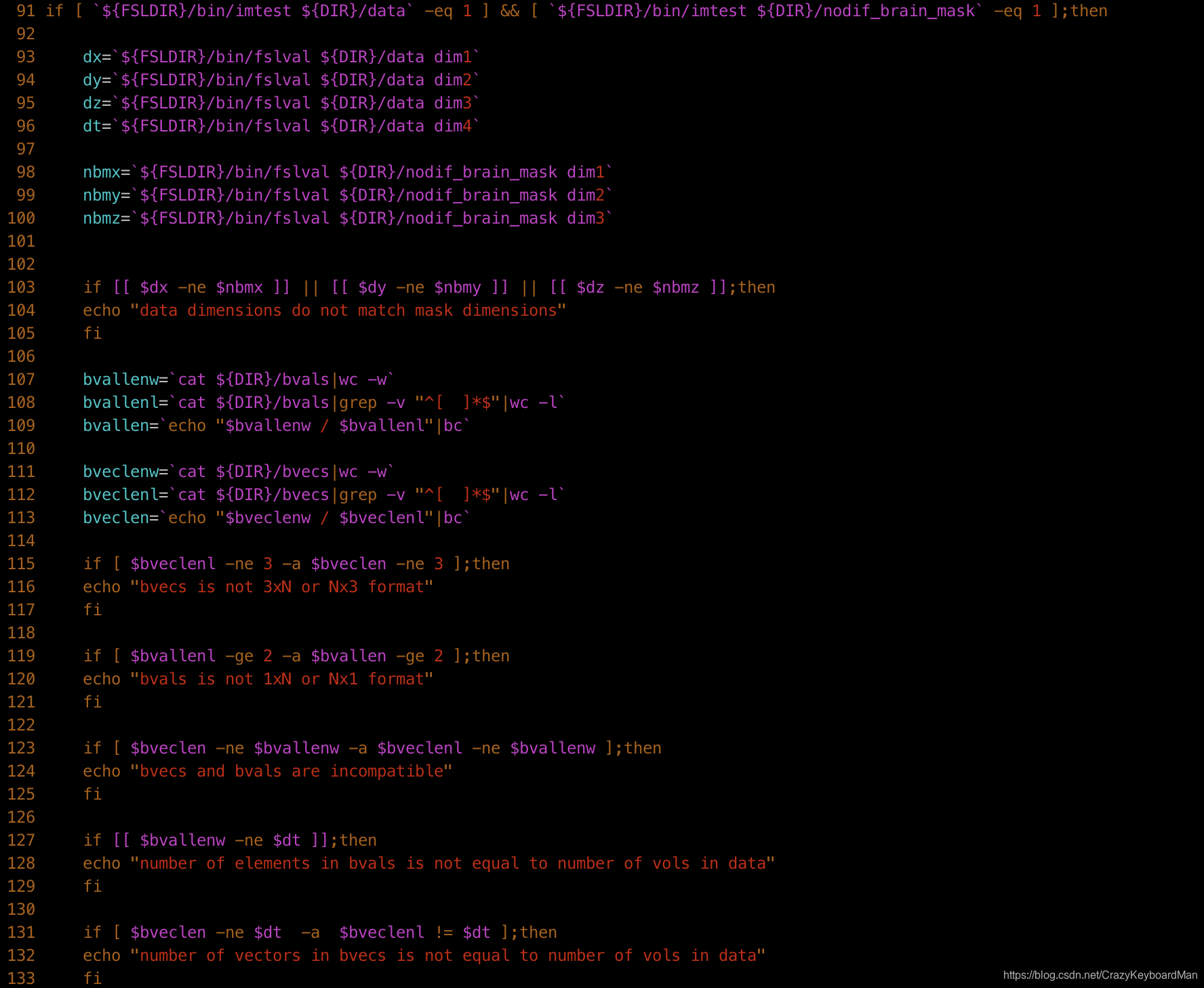
注意:在笔者的Ubuntu 16.04下运行bedpost_datacheck时,出现了部分语法错误,后经查询后发现是一些符号问题,只需对应更改脚本的103、127、131行,并同样将#!/bin/sh改为#!/bin/bash即可。
执行
将所有所需文件放好后(我是存放在~/Documents/Probtrack/data/Data,后续以我为例),只需cd到该目录,输入bedpostx_gpu .(点别忘了)即可。
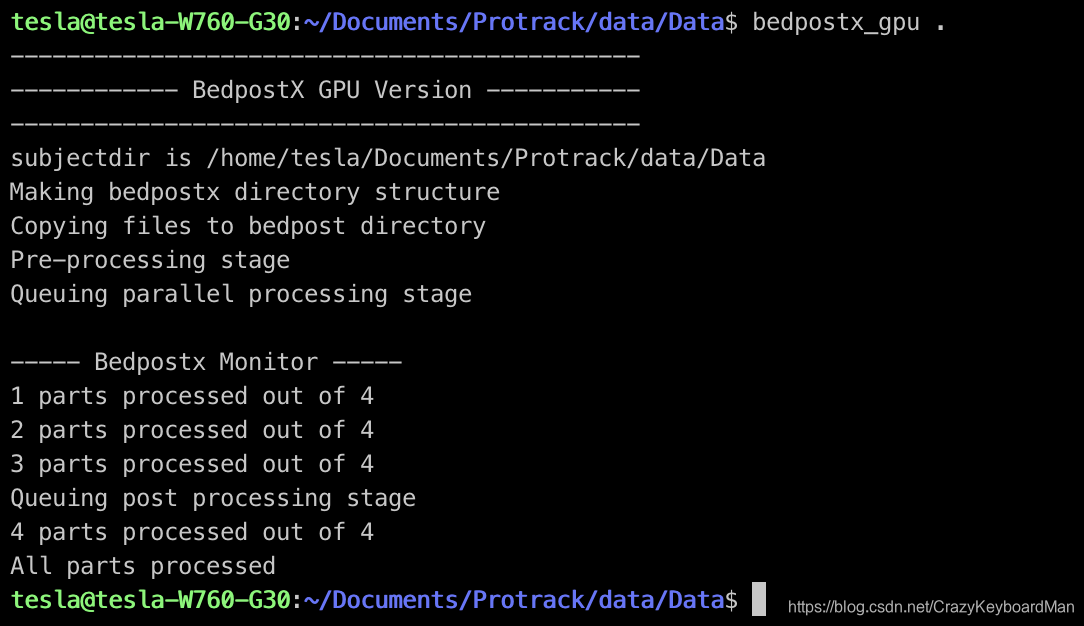
运行结果如图所示,输出目录为~/Documents/Probtrack/Data.bedpostX。
输出目录中,以merged开头的文件将是后续概率纤维追踪所需要的,具体含义参考FSL——DTI官方文档。
相比起官方文档中提到的CPU版本所需要的15小时,GPU版本的bedpostx仅耗时10分钟,可以说运算速度确实是大大提高了。
概率纤维追踪
FSL使用probtrackx2进行概率纤维追踪,其具体原理参考官方文档。
数据准备
probtrackx2_gpu需要如下数据:
-
bedpostx生成的merged。
-
nodif_brain_mask,bedpostx后会自动将其复制到Data.bedpostX文件夹。
-
根据追踪类型不同所需要的seed、target、waypoint
-
根据seed种类和seed space不同,需要的.mat或_wary.nii.gz文件(这一点很重要,稍后会解释)。
执行
说明执行步骤之前,针对上一部分所重点提到的seed种类和seed space做一点解释。
概率纤维追踪的最终结果简单来说可显示为由seed开始,经过waypoint,到termnition的纤维通路,其中seed是必须指定的。而seed可以是一个体素(single voxel),也可以是一个或多个mask。
probtrackx支持任意空间的输入输出(Diffusion、Standard或自定义),但是其过程只能在Diffusion sapce下进行,因此,在使用mask作为seed的情况下若seed space不是diff空间下,则需要提供将其线性配准到diff空间的变换矩阵.mat文件,或非线性配准到diff的正向和反向waryfiles。
具体步骤我们以这里提供的数据为例。
文件解压后,其中subj1_model2_3fibres.bedpostX文件夹为bedpostx后生成的文件夹。
Single Voxel
Single模式下,追踪计算量较小,因此probtrackx2_gpu没有无法使用–simple参数选项。若需要命令行模式运行,则使用probtrackx2即可,命令如下:
probtrackx2 --simple --seedref=nodif_brain_mask -o sigle_voxel_result -x coordinates.txt -l --onewaycondition --forcedir --opd -s merged -m nodif_brain_mask --dir=single_voxel_result
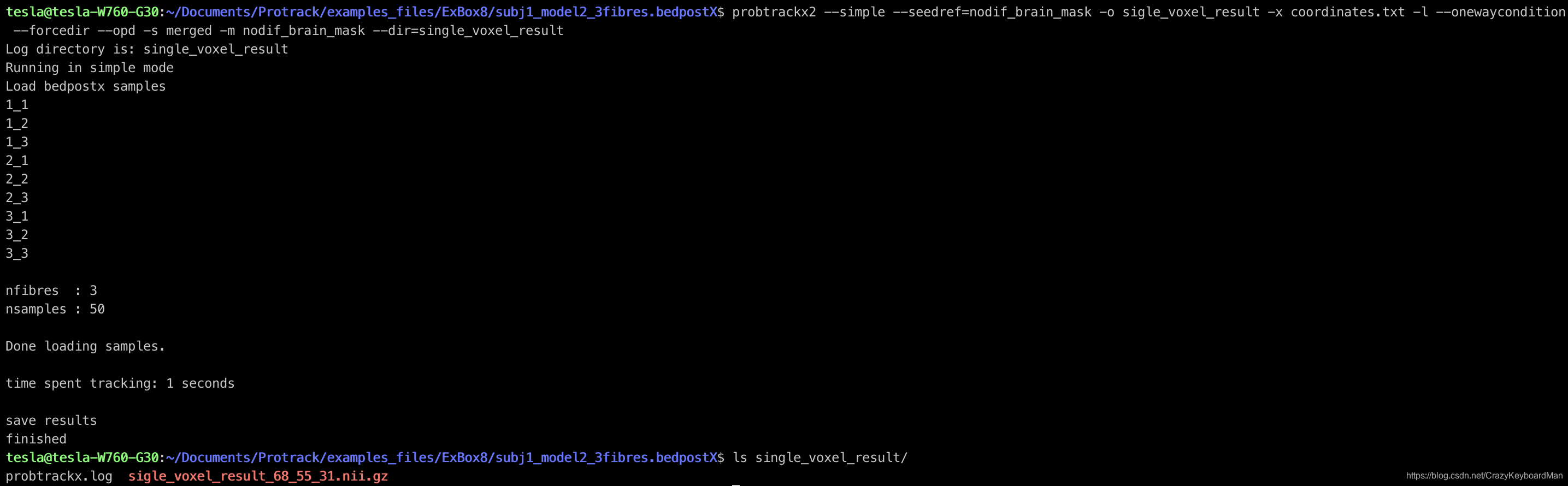
其中需要说明的是-x参数后的.txt文件是我自己创建的,内容为68 55 31,代表voxel的坐标。
用fsleyes查看追踪结果:
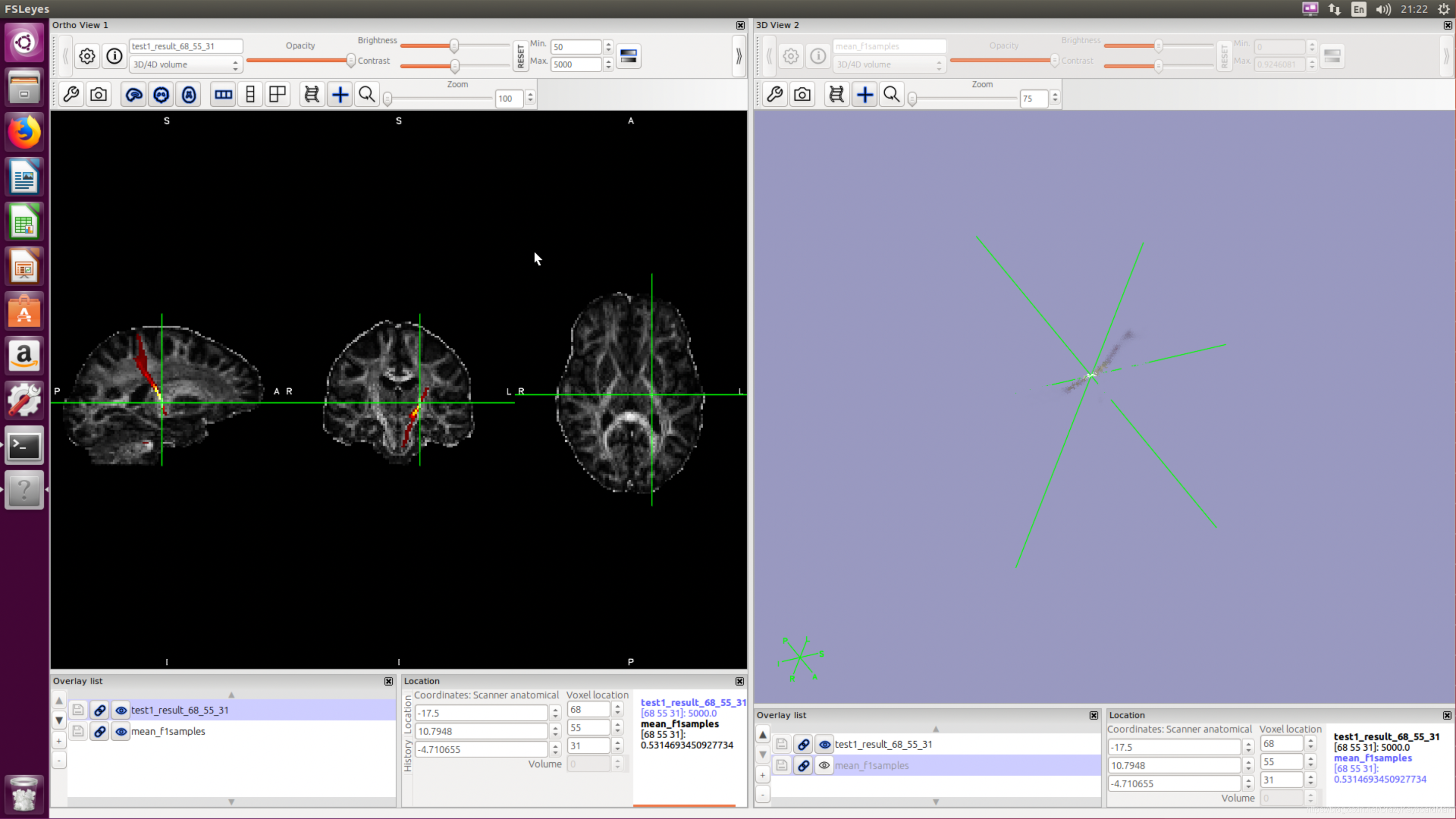
Single Mask
现在我们使用subj1_model2_3fibres.bedpostX中丘脑外侧膝状核掩码(SEED_LGN_LEFT.nii.gz)作为seed。
注意,该mask是在标准空间内,因此需要提供将其配准到diff空间的变换文件,此例中,已提供所需的.mat或waryfiles在xfms子目录下。
命令如下(使用非线性配准到diff):
probtrackx2_gpu -x SEED_LGN_LEFT.nii.gz -l --onewaycondition --xfm=xfms/standard2diff_warp.nii.gz --invxfm=xfms/diff2standard_warp.nii.gz --forcedir --opd -s merged -m nodif_brain_mask --dir=single_mask_result
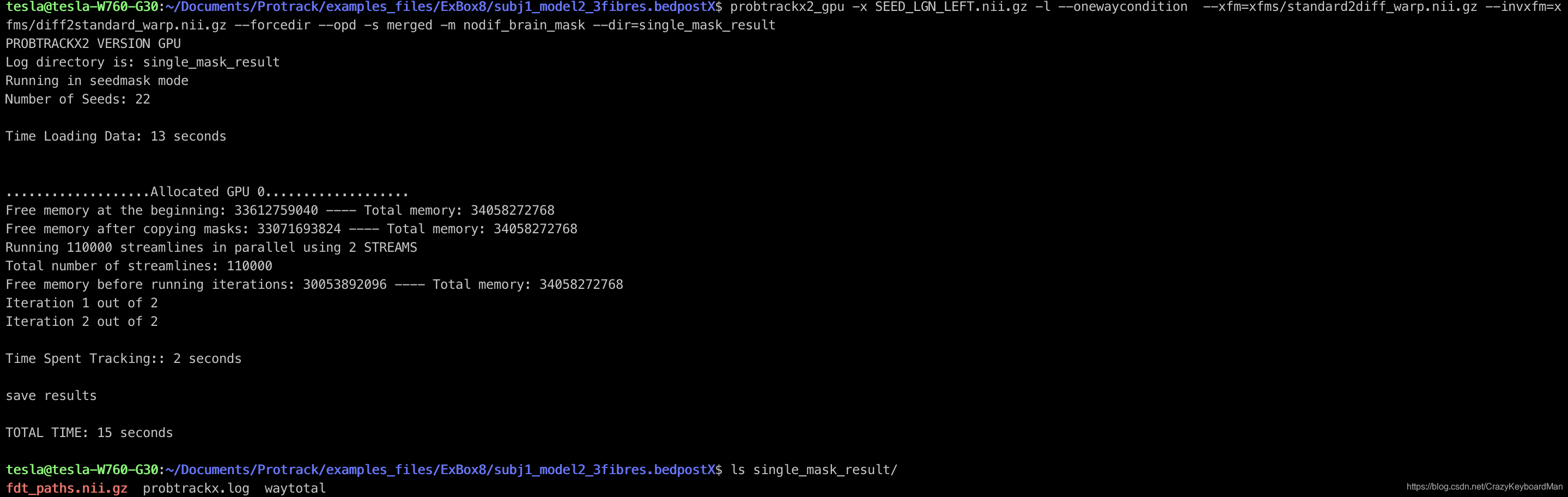
可以看出,GPU版本下,除过13s的参数加载过程,只需2s就可完成追踪。
用fsleyes查看追踪结果:
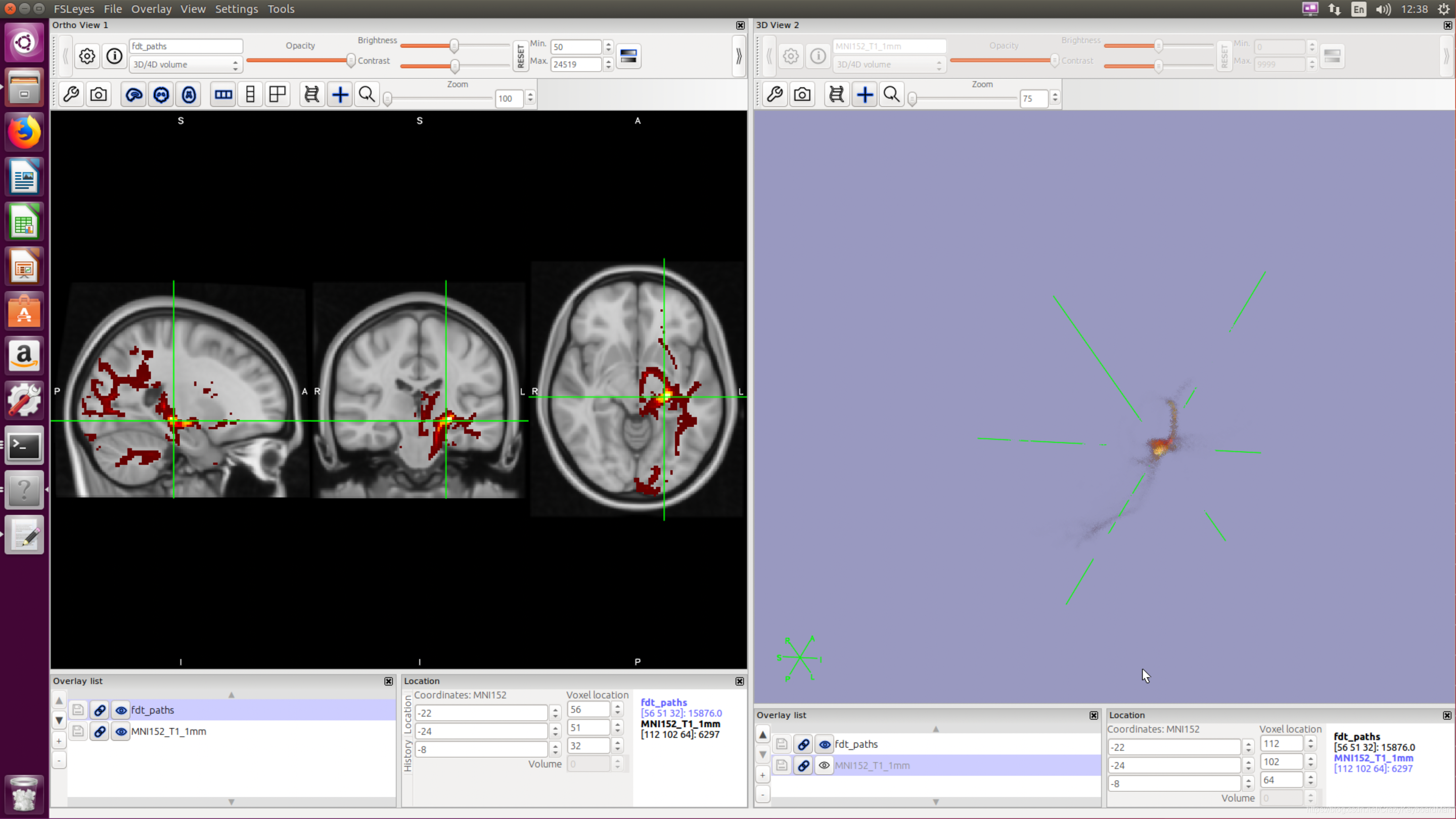
可以看出与LGN有连通的纤维被追踪到。
Including Target
probtrackx_gpu可使用额外的参数设置纤维追踪的途经点、终点等,以此来进行更具针对性的追踪,这些高级追踪模式包括:Waypoint mask、Exclusion mask、Termination mask、Classification targets。本文只简单介绍Waypoint和Termination,详细介绍请读者在官方文档中自行查阅。
使用probtrackx_gpu的--waypoints和--stop参数可设定纤维追踪的途经点和终点,用这种方法可以更加针对性地开展纤维追踪工作。
此例中,我们使用LGN作为seed,初级视皮层(primary visual cortex)掩码TARGET_V1_LEFT.nii.gz同时作为waypiont和termination,以此只追踪LGN到V1的纤维通路。
命令如下:
probtrackx2_gpu -x SEED_LGN_LEFT.nii.gz -l --onewaycondition --xfm=xfms/standard2diff_warp.nii.gz --invxfm=xfms/diff2standard_warp.nii.gz --forcedir --opd -s merged -m nodif_brain_mask --dir=waypoint_result --stop=TARGET_V1_LEFT.nii.gz --waypoints=TARGET_V1_LEFT.nii.gz --waycond=AND
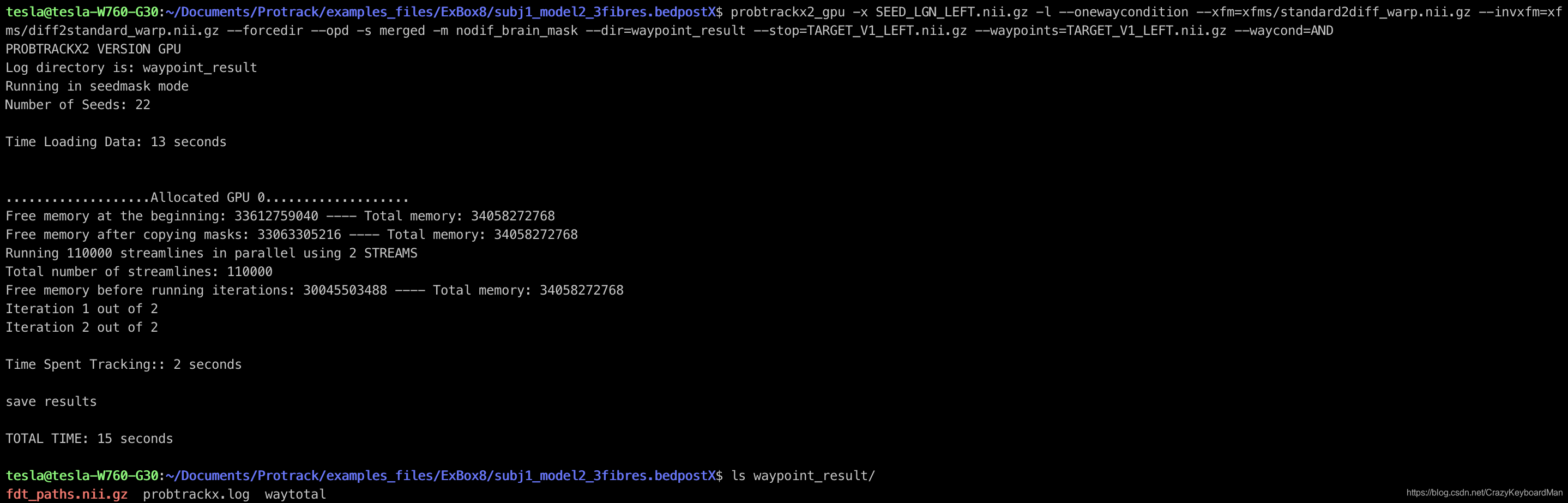
使用fsleyes查看结果:
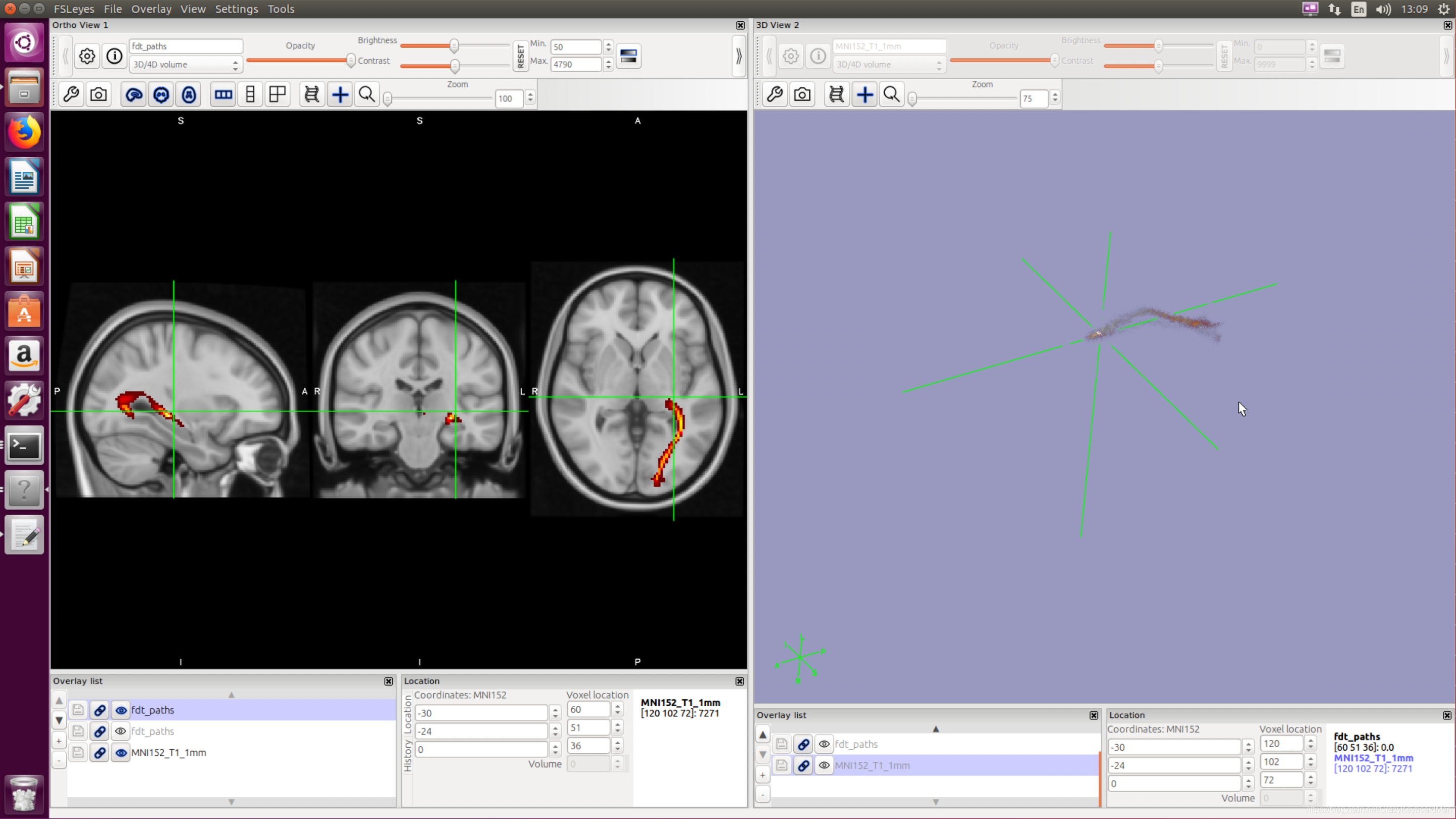
可明显看出,与不指定waypoint和termination相比,这种模式下可以更具针对性地追踪到seed到ROI的纤维通路。
后记
从接手服务器到配置环境再到尝试用FSL进行概率纤维追踪,整个过程还是踩了不少坑,好在官方文档非常详细,网络资源也很丰富,总的来说主要还是有这样额外几点总结:
-
开展工作前尽量认真地阅读官方文档。一开始我使用protrackx2_gpu时,总是报非法内存访问和out of memory(32G显存你告诉我OTM???),换了三个CUDA版本后还是不好使,后来仔细阅读了一下官方文档后发现原来是我的数据不在diff空间,我也没指定xfm和invxfm。
-
不明白命令行参数怎么设置的话,使用probtrackx2_gpu --help可以查看参数解释,实在不行就跟着官方的GUI教程跑一下CPU,直接kill掉后在输出文件夹里有log文件可以查看命令。
-
若要使用自己的seed mask、waypoint mask等,可以在脑网络组图谱中下载相应的图谱后使用MATLAB spm12工具得到特定区域的mask,只是还是要注意配准的问题。
由于笔者也是最近一段时间开始DTI图像处理相关的学习工作,故本文存在疏漏在所难免,还望大家不吝赐教,若有部分内容需要指教或讨论,请邮箱联系matrixliu@csu.edu.cn。若有转载需要,请注明出处即可。
Reference
FSL Wiki
Example Box: Tractography
Bedpostx GPU
Probtrackx GPU


























 1万+
1万+

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








