目录
1、线性可分支持向量机/硬间隔支持向量机
适用场景:训练数据线性可分
方法:通过硬间隔最大化
2、线性支持向量机/软间隔支持向量机
适用场景:训练数据近似线性可分
方法:通过软间隔最大化
3、代码
1)线性可分支持向量机的实现
2)线性支持向量机的实现以及五折交叉验证进行寻找最佳的惩罚系数C
1、线性可分支持向量机/硬间隔支持向量机
数据集:T={(x1,y1),(x2,y2),…,(xN,yN)}
(xi,yi)为一个训练样本,xi为一个实例,yi为该实例的分类。yi为1时为正例,yi为-1时为负例。
学习目标:在特征空间寻找一个分离超平面(将两类正确分类并且使得两类几何间隔最大):wx+b=0,该超平面由法向量w和截距b决定。法向量指向的一侧为正类。
相应的分类决策函数:f(x)=sign(wx+b) 称为线性可分支持向量机
间隔
函数间隔:
y(wx+b)表示分类的正确性以及确信度
(正确性:是否分类正确 y和wx+b是否同号来确定)
(确信度:|wx+b|表示当wx+b=0确定时,样本点距离超平面的远近)
超平面(w,b)关于样本点(xi,yi)的函数间隔:
ri’=yi(wxi+b)
超平面(w,b)关于数据集T的函数间隔(所有样本点中函数间隔最小值):
r‘=min(ri)=min(yi(w*xi+b))
几何间隔
超平面(w,b)关于样本点(xi,yi)的几何间隔:
ri=yi(wxi+b)//||w||
超平面(w,b)关于数据集T的几何间隔(所有样本点中几何间隔最小值):
r=min(ri)=min(yi(wxi+b))/||w||
ps:若w、b成比例的变化,即超平面不改变,此时函数间隔也会成比例变化,而几何间隔不变。
优化问题
1、希望数据集几何间隔最大,并且每一个样本点均大于这个间隔
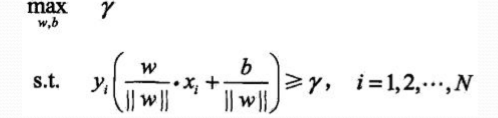
2、根据几何间隔和函数间隔的联系:
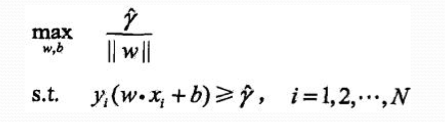
3、我们知道同比例改变w、b,函数间隔会同比例变化,故
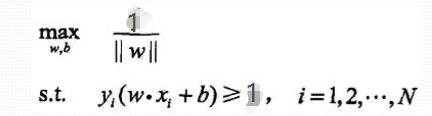
4、变求最大为求最小,则
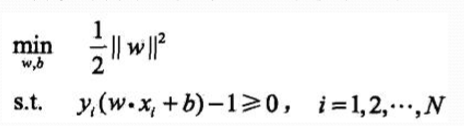
该问题是一个凸优化问题,凸优化问题定义如下:

通常转换为拉格朗日对偶问题来求解
5、学习的对偶算法

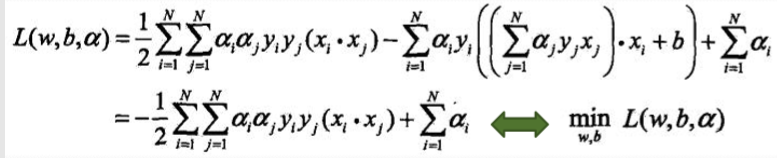
a的求解方法:
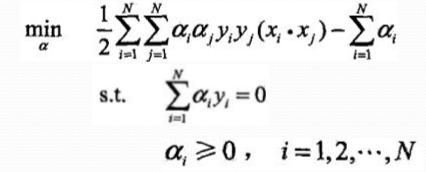
w、b的求解方法:
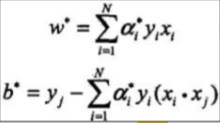
其中a的取值范围是
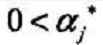
2、线性支持向量机/软间隔支持向量机
当数据中有一些奇异点,如下图中跑上来的两个红色的点。只是这极个别的点而导致的非完全线性可分。 此时,需要对每个样本点增加一个松弛变量。

这样该问题的原始问题就变成了
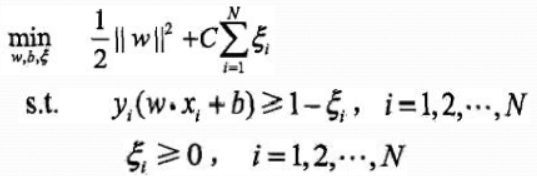
与线性可分支持向量机同样的分析过程,其对偶问题变为了
(a求解方法)

(w b求解方法)
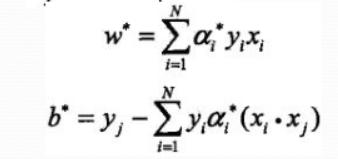
其中 a的取值范围为
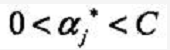
(具体原因分析KKT条件)
3、代码
重点问题:
1)因两个问题均为凸优化问题,使用cvxopt库中的solvers.qp方法进行求解a,分析其中参数得(如何寻找的大家可以对照着qp问题格式依次对应即可):
(推荐一个相关的博客,简单的举了个例子https://www.jianshu.com/p/df447c3e4efe)
求解线性可分支持向量机对应的参数

求解线性支持向量机对应的参数

2)对应线性支持向量机五折交叉验证寻找最优的C。
设置C 的范围为[1e-3,1e-2,1e-1,1,1e1,1e2,1e3]、交叉验证折数5,进行双重循环(循环C和5)执行线性支持向量机算法,对于每一个C求一次平均正确率,最终根据最高的正确率选择最优的C,再投入到线性支持向量算法中。
3)涉及到numpy和cvxopt中一些简单函数
放到另外一篇博客中
链接:https://blog.csdn.net/jichun4686/article/details/102948023
( 代码参考:https://www.cnblogs.com/buzhizhitong/p/6089070.html
https://blog.csdn.net/huakai16/article/details/78070671 整体思想相同,仅加入了我自己的理解)
代码主体如下:
import numpy as np
import matplotlib.pyplot as plt
from cvxopt import solvers
import cvxopt
def linear_kernel(x1,x2):
return np.dot(x1,x2)
class mySVM():
def __init__(self,kernel=linear_kernel,C=None):
self.kernel = kernel #这是一个函数 代指其核的运算
self.C = C
def fit(self,X,y):
n_samples = X.shape[0]
n_feature = X.shape[1]
#求凸优化问题需要的参数 P q G h A b
#先求x的核矩阵 以方便求P
K = np.zeros((n_samples,n_samples))
for i in range(n_samples):
for j in range(n_samples):
K[i][j] = self.kernel(X[i],X[j])
P = cvxopt.matrix(np.outer(y,y)*K)
q = cvxopt.matrix(np.ones(n_samples) * -1) #为列向量 √
A = cvxopt.matrix(y,(1,n_samples)) #y的转置 为行向量 (1,n_samples)表示排列为1*n_samples的矩阵
b = cvxopt.matrix(0.0)
#对于线性可分数据集
if self.C is None:
G = cvxopt.matrix(np.diag(np.ones(n_samples) * -1))
h = cvxopt.matrix(np.zeros(n_samples))
#对于软间隔
else:
arg1 = np.diag(np.ones(n_samples) * -1)
arg2 = np.diag(np.ones(n_samples))
G = cvxopt.matrix(np.vstack((arg1,arg2))) #加括号 因为vstack只需要一个参数
arg1 = np.zeros(n_samples)
arg2 = np.ones(n_samples) * self.C
h = cvxopt.matrix(np.hstack((arg1,arg2)))
solution = solvers.qp(P,q,G,h,A,b)
a = np.ravel(solution['x'])
if self.C is None:
sv = a>1e-5
else:
sv = (a > 1e-5) * (a < self.C)
index = np.arange(len(a))[sv] #a>1e-5 返回true or false的数组 取出对应为true的下标
self.a = a[sv] #大于0对应的a的值index
self.sv_X = X[sv] #支持向量的X index
self.sv_y = y[sv] #支持向量的y index
print('%d 点中有 %d 个支持向量' %( n_samples,len(self.a)))
###算 w 以及 b
#求w
self.w = np.zeros(n_feature)
for i in range(len(self.a)):
self.w += self.a[i] * self.sv_y[i] * self.sv_X[i]
# print(self.w)
#求b
self.b = 0
for i in range(len(self.a)):
self.b += self.sv_y[i]
self.b -= np.sum(self.a * self.sv_y * K[index[i]][index])
self.b /= len(self.a)
# print(self.b)
def predict(self,X_test):
return np.sign(np.dot(X_test,self.w) + self.b) #注意X_text self.w不要写反
def plot(self,X1_train,X2_train):
def f(x,w,b,c):
#w0*x0 + w1*x1 +b =c
return (-w[0] * x - b + c)/w[1]
plt.scatter(self.sv_X[:, 0], self.sv_X[:, 1], color='black', s=100)
plt.scatter(X1_train[:,0],X1_train[:,1],color='blue',label='1')
plt.scatter(X2_train[:,0],X2_train[:,1],color='red',label='-1')
#wx + b = 0 w0*x0 + w1*x1 +b =0
x0_1 = 4
y0_1 = f(x0_1,self.w,self.b,0)
x0_2 = -3
y0_2 = f(x0_2,self.w,self.b,0)
plt.plot([x0_2,x0_1],[y0_2,y0_1],'k')
#wx + b = 1 w0*x0 + w1*x1 +b = 1
x1_1 = 4
y1_1 = f(x1_1,self.w,self.b,1)
x1_2 = -3
y1_2 = f(x1_2,self.w,self.b,1)
plt.plot([x1_2,x1_1],[y1_2,y1_1],'k--')
#wx + b = -1 w0*x0 + w1*x1 +b = -1
x2_1 = 4
y2_1 = f(x2_1,self.w,self.b,-1)
x2_2 = -3
y2_2 = f(x2_2,self.w,self.b,-1)
plt.plot([x2_2,x2_1],[y2_2,y2_1],'k--')
plt.xlabel('x')
plt.ylabel('y')
plt.show()
plt.close()
def dataSelection(type):
#随机产生的数据
#随机产生的线性可分数据
mean1_1 = np.array([0, 2])
mean2_1 = np.array([2, 0])
cov_1 = np.array([[0.8, 0.6], [0.6, 0.8]])
X1_1 = np.random.multivariate_normal(mean1_1, cov_1, 100)
y1_1 = np.ones(len(X1_1)) #行向量
X2_1 = np.random.multivariate_normal(mean2_1, cov_1, 100)
y2_1 = np.ones(len(X2_1)) * -1
#随机产生的线性可分但是有部分重叠的数据
mean1_2 = np.array([0, 2])
mean2_2 = np.array([2, 0])
cov_2 = np.array([[1.7, 1.0], [1.0, 1.7]]) #原来
# cov_2 = np.array([[1, 0.5], [0.5, 1]])
X1_2 = np.random.multivariate_normal(mean1_2, cov_2, 100)
y1_2 = np.ones(len(X1_2))
X2_2 = np.random.multivariate_normal(mean2_2, cov_2, 100)
y2_2 = np.ones(len(X2_2)) * -1
#随机产生线性不可分的数据
mean1_3 = [-1, 2]
mean2_3 = [1, -1]
mean3_3 = [4, -4]
mean4_3 = [-4, 4]
cov_3 = [[1.0, 0.8], [0.8, 1.0]]
X1_3 = np.random.multivariate_normal(mean1_3, cov_3, 50)
X1_3 = np.vstack((X1_3, np.random.multivariate_normal(mean3_3, cov_3, 50)))
y1_3 = np.ones(len(X1_3))
X2_3 = np.random.multivariate_normal(mean2_3, cov_3, 50)
X2_3 = np.vstack((X2_3, np.random.multivariate_normal(mean4_3, cov_3, 50)))
y2_3 = np.ones(len(X2_3)) * -1
if type=='random_linear':
return X1_1, y1_1, X2_1, y2_1
elif type == 'random_linear_soft':
return X1_2, y1_2, X2_2, y2_2
elif type == 'random_nonlinear':
return X1_3, y1_3, X2_3, y2_3
#划分数据集测试集
def split_train_test(X1,Y1,X2,Y2,ratio):
samples_num = len(Y1)
num_train = int(samples_num * ratio)
# num_test = samples_num * (1-ratio)
X1_train = X1[:num_train]
Y1_train = Y1[:num_train]
X2_train = X2[:num_train]
Y2_train = Y2[:num_train]
X_train = np.vstack((X1_train,X2_train)) ###需要加两个括号
y_train = np.append(Y1_train,Y2_train) #用hstack也可以
X1_test = X1[num_train:]
Y1_test = Y1[num_train:]
X2_test = X2[num_train:]
Y2_test = Y2[num_train:]
X_test = np.vstack((X1_test,X2_test))
y_test = np.append(Y1_test,Y2_test)
return X_train,y_train,X_test,y_test
def test_randomLinear():
X1, y1, X2, y2 = dataSelection('random_linear')
X_train, y_train, X_test, y_test=split_train_test(X1, y1, X2, y2, 0.9)
clf = mySVM()
clf.fit(X_train,y_train)
y_predict = clf.predict(X_test)
correct = np.sum(y_predict == y_test)
print("%d 个测试样本中有%dg个预测正确" % (len(y_predict),correct))
clf.plot(X_train[y_train==1],X_train[y_train==-1])
def test_randomLinearSoft():
# X1, y1, X2, y2 = dataSelection('iris_linear')
X1, y1, X2, y2 = dataSelection('random_linear_soft')
X_train, y_train, X_test, y_test=split_train_test(X1, y1, X2, y2, 0.9)
clf = mySVM(C=10)
clf.fit(X_train,y_train)
y_predict = clf.predict(X_test)
correct = np.sum(y_predict == y_test)
print("%d 个测试样本中有%dg个预测正确" % (len(y_predict),correct))
clf.plot(X_train[y_train==1],X_train[y_train==-1])
def find_bestC(X1, y1, X2, y2):
folds = 5
cs = [-3,-2,-1,0,1,2,3]
Cs = []
for c in cs:
Cs.append(np.power(10.,c))
# Cs = [1e-3,1e-2,1e-1,1,1e1,1e2,1e3]
# X1, y1, X2, y2 = dataSelection('random_linear_soft')
X1_folds = np.vsplit(X1,folds)
X2_folds = np.vsplit(X2,folds)
y1_folds = np.hsplit(y1,folds)
y2_folds = np.hsplit(y2,folds)
accuracy_of_C = {} #字典类型
for C in Cs:
accuracy_of_C[C] = []
for i in range(folds): #fold 0 1 2 3 4
temp1 = np.vstack(X1_folds[:i]+X1_folds[i+1:])
temp2 = np.vstack(X2_folds[:i]+X2_folds[i+1:])
X_train = np.vstack((temp1,temp2))
temp1 = np.hstack(y1_folds[:i]+y1_folds[i+1:])
temp2 = np.hstack(y2_folds[:i]+y2_folds[i+1:])
y_train = np.hstack((temp1,temp2))
X_test = np.vstack((X1_folds[i],X2_folds[i]))
y_test = np.hstack((y1_folds[i],y2_folds[i]))
clf = mySVM(C=C)
clf.fit(X_train,y_train)
y_predict = clf.predict(X_test)
correct = np.sum(y_predict == y_test)
accuracy = float(correct)/len(y_test)
accuracy_of_C[C].append(accuracy)
print("当C为%f 时 第 %d 组 %d 个测试样本中有%dg个预测正确" % (C,i,len(y_predict),correct))
accuracys = []
for C in Cs:
avgacc = 0.0
for accuracy in accuracy_of_C[C]:
avgacc += accuracy
print('C = %f,accuracy = %f' %(C,accuracy))
temp = avgacc/len(accuracy_of_C[C])
accuracys.append(temp)
##求np数组的最大值的下标 np.arg(xx) 求列表最大值的下标xx.index(max(xx))
bestC_index = accuracys.index(max(accuracys))
bestC = Cs[bestC_index]
print(bestC)
plt.plot(cs,accuracys)
plt.show()
plt.close()
return bestC
# print(accuracys)
def test_randomLinearSoft2():
X1, y1, X2, y2 = dataSelection('random_linear_soft')
X_train, y_train, X_test, y_test = split_train_test(X1, y1, X2, y2, 0.9)
bestC = find_bestC( X1, y1, X2, y2)
clf = mySVM(C=bestC)
clf.fit(X_train,y_train)
y_predict = clf.predict(X_test)
correct = np.sum(y_predict == y_test)
print("%d 个测试样本中有%dg个预测正确" % (len(y_predict),correct))
clf.plot(X_train[y_train==1],X_train[y_train==-1])
def draw(datas):
plt.scatter(datas[:50,0],datas[:50,1],color='blue',label='1(iris +)')
plt.scatter(datas[50:,0],datas[50:,1],color='red',label='-1(iris -)')
plt.xlabel('SepalLengthCm')
plt.ylabel('SepalWidthCm')
plt.legend(loc='upper Data') #标签位置 左上角
plt.title('SVM_withoutC')
# x1 = 4.0
# y1 = -((self.weights[0]*x1+self.bias)/(self.weights[1]))
# x2 = 7.0
# y2 = -((self.weights[0] * x2 + self.bias) / (self.weights[1]))
# plt.plot([x1, x2], [y1, y2], 'yellow')
plt.show()
plt.close()
if __name__ == '__main__':
# dataslinear = dataSelection('linear')
# print(dataslinear)
# draw(dataslinear)
# test_randomLinear()
# test_randomLinearSoft() #指定惩罚系数
test_randomLinearSoft2() #五折交叉验证来求得最好的C后放入SVM软间隔支持向量机
# find_bestC() #五折交叉验证来求得最好的C
如有问题,请多多指正。






















 171
171











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








