library(biomaRt)
#运行下面的代码
hg_symbols<- getBM(attributes=c('ensembl_gene_id','hgnc_symbol',"chromosome_name", "start_position","end_position", "band"),
filters= 'ensembl_gene_id',
values = key_gene_ensembl,
mart = mart)
#报错如下
Error in `collect()`:
! Failed to collect lazy table.
Caused by error in `db_collect()`:
! Arguments in `...` must be used.
✖ Problematic argument:
• ..1 = Inf
ℹ Did you misspell an argument name?
Run `rlang::last_trace()` to see where the error occurred.网上指出是dbplyr(注意,不是dplyr)和Biocfilecache之间的不兼容导致的错误问题
但是采用 更新 BiocManager 版本 的方法无法解决问题
遂考虑降低dbplyr版本
解决过程:
1. 移除当前dbplyr包
R studio里面直接点这个×就行
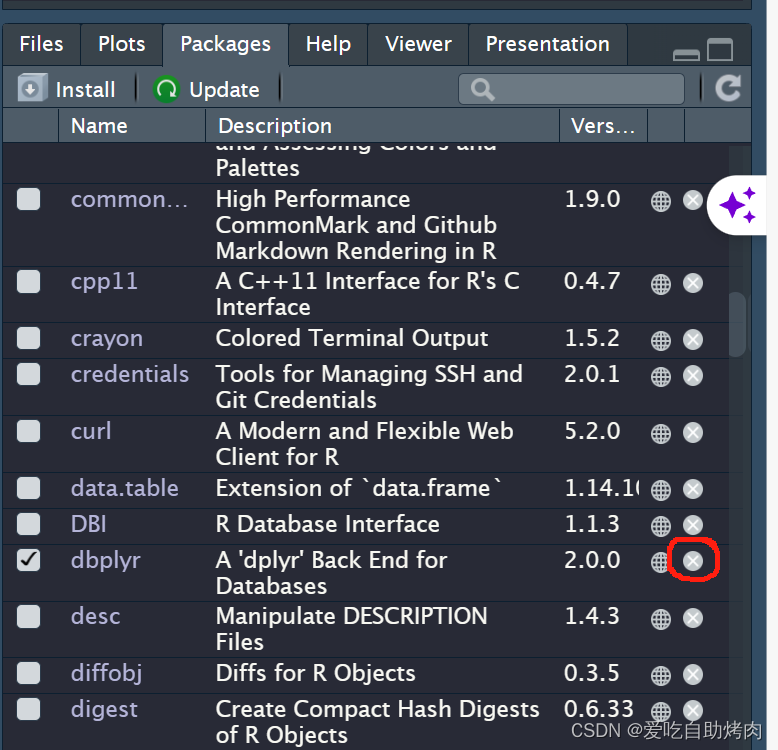
或
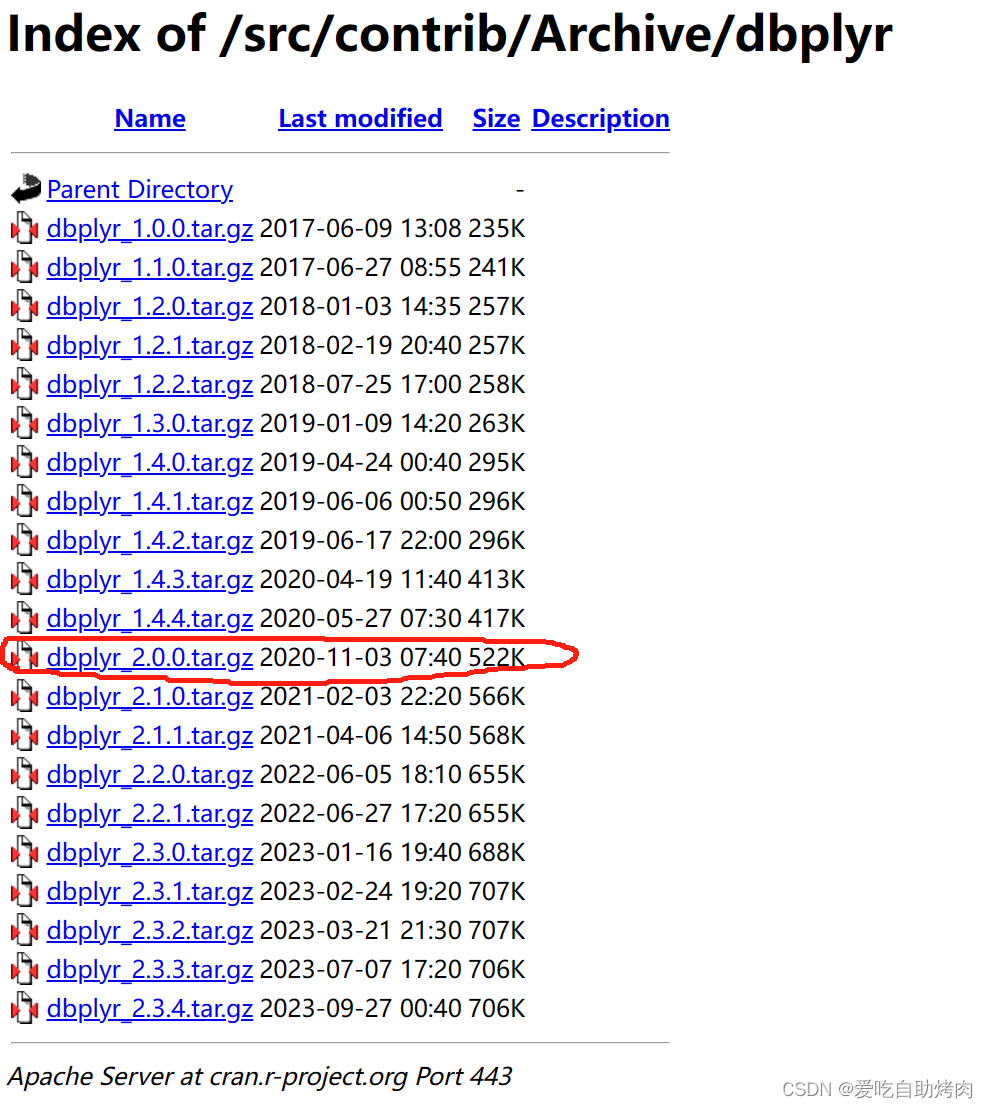
remove.packages("dbplyr")2. 下载旧版本dbplyr
进入网站:Index of /src/contrib/Archive/dbplyr (r-project.org)
下载2.0.0版本
3. 安装dbplyr
将下载的压缩包放到R包文件夹中(也可以放在其他自己能找到的地方)
点击 install
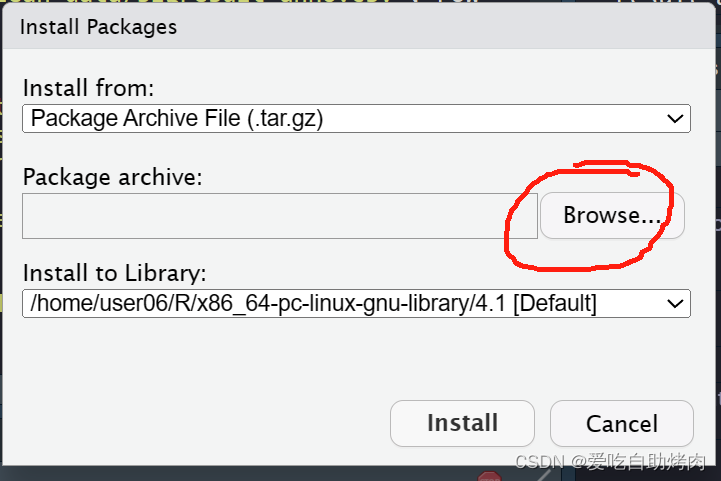
点击 Browse 找到R包位置点开即可安装
如果报错,注意是看一下是不是哪个依赖包没有安装上,直接install.packages()安装上,再重复上面步骤即可。
问题解决,不再报错了























 6513
6513

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








