点云库PCL从入门到精通
提示:这里可以添加系列文章的所有文章的目录,目录需要自己手动添加
例如:第一章
RANSAC随机采样一致性算法
基本假设:
- 数据由“局内点(inliers)”组成,例如:数据的分布可以用一些模型参数来解释
- “局外点(outliers)”是不能适应该模型的数据
- 除此之外的数据属于噪声
局外点产生的原因有:噪声的极值、错误的测量方法、对数据的错误假设。
基本原理:
从样本中随机抽选出一个样本子集,使用最小方差估计算法对这个子集计算规模参数,然后计算所有样本与改模型的偏差,在使用一个预先设定好的阈值与偏差比较。通过反复选择数据中的一组随机子集来达成目标,被选取的子集被假设为局内点,并用下述方法进行验证:
- 假设有一个模型适应于最多的局内点,即所有的未知参数都能从假设的局内点计算得出
- 从样本总体中随机抽取一部分样本,作为样本子集,使用某一算法(如最小方差估计算法)计算1中假设的模型的参数,然后计算所有样本与该模型的偏差
- 使用一个预先设定好的阈值与得到的每个点的偏差做比较,当偏差小于阈值时,该样本点属于模型局内点,否则属于模型局外点
- 然后,记录当前的局内点个数和模型参数
- 重复上述过程,每一次重复,都纪律当前最多局内点的的模型参数。
在每次迭代的末尾,都要根据期望的误差率、
best_ninliers、总样本个数、当前迭代次数,来计算一个迭代结束评判因子,据此判定迭代是否结束。
存在的问题:
- 区分局内点和局外点的阈值有时候很难事先设定
- 算法的迭代次数是运行期决定的,在算法执行之前,无法预知算法需要迭代的确切次数(只能知道一个大概的范围)
- 只能从一个特定的数据集中估计一个模型,当两个及以上个模型存在时,
RANSAC不能找到别的模型
一个简单例子:
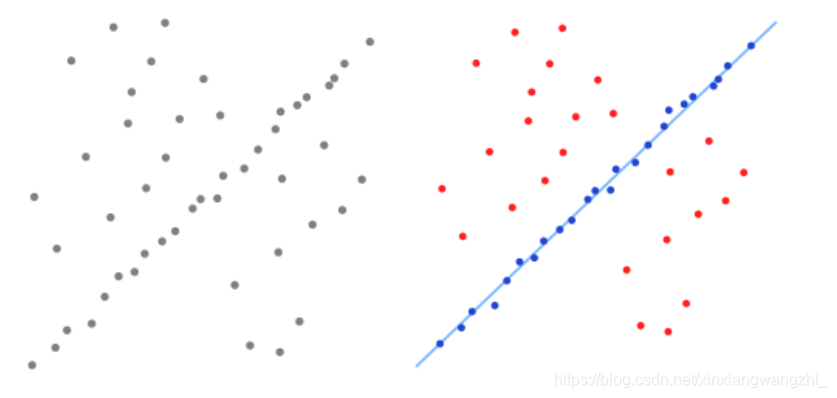
如上图,左侧图像表示一组既包含局内点又包含局外点的数据集;右侧图像中,所有的局外点都被标为红色,局内点标为蓝色,蓝色线条就是基于RANSAC算法得到的结果(简单的最小二乘法不能找到适应于局内点的直线,原因是最小二乘法尽量去适应包括局外点在内的所有点,当然,RANSAC算法也不能保证结果的绝对正确,在执行算法时,必须设置选择参数)。
LMedS最小中值方差估计算法
基本原理:从样本中随机抽出N个样本子集,使用最大似然(通常是最小二乘)对每个子集计算模型参数和该模型的偏差,记录该模型参数及子集中所有样本中偏差居中的那个样本的偏差(即Med偏差),重复该过程N次,最后选取N个样本子集中Med偏差最小的所对应的模型参数作为我们要估计的模型参数。
该算法中的迭代次数N是由样本子集的个数、期望的模型误差、事先估计的样本中outliers的比例所决定的。
优点:
- 不用事先设定阈值
- 迭代次数可以事先确定
缺点:当outliers在样本中所占比例达到或超过50%时,该算法不再适用(LMedS每次迭代记录的是Med偏差值)。
一个简单的示例
std::vector<int> inliers; // 存储局内点集合的点的索引的向量
// 创建随机采样一致性
pcl::SampleConsensusModelSphere<pcl::PointXYZ>::Ptr
model_s(new pcl::SampleConsensusModelSphere<pcl::PointXYZ>(cloud)); // 针对球模型的对象
pcl::SampleConsensusModelPlane<pcl::PointXYZ>::Ptr
model_p(new pcl::SampleConsensusModelPlane<pcl::PointXYZ>(cloud)); // 针对平面模型的对象
if (pcl::console::find_argument(argc, argv, "-f") >= 0)
{
// 根据命令行参数,来随机估算对应的平面模型,并存储估计的局内点
pcl::RandomSampleConsensus<pcl::PointXYZ> ransac(model_p);
ransac.setDistanceThreshold(.01); // 与平面距离小于0.01的点作为局内点考虑
ransac.computeModel(); // 执行随机参数估计
ransac.getInliers(inliers); // 存储估计所获得的局内点
}
else if (pcl::console::find_argument(argc, argv, "-sf") >= 0)
{
// 根据命令行参数,来随机估算对应的球面模型,并存储估计的局内点
pcl::RandomSampleConsensus<pcl::PointXYZ> ransac(model_s);
ransac.setDistanceThreshold(.01);
ransac.computeModel();
ransac.getInliers(inliers);
}






















 6369
6369











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








