Mixed effects models 回顾(二)
A.F. Zuur et al., Mixed Effects Models and Extensions in Ecology with R, 11 Statistics
###写在Chapter 4, 5, 6前
在一般 (general) 线性模型以及一般加性模型的模型验证时,总会碰到一系列问题,诸如异质性、嵌套数据、数据时空相关等。对这些问题的处理,可以通过添加随机部分 (random part) 的形式解决:

我们不能简单的将上述数学模型统称为混合效应模型,这是不严谨的。对于异质性问题解决的模型,应被称为广义最小二乘法 (generalised least squares, GLS) 模型,其本质上是一种加权 (weights) 的线性回归。
##Chapter 4 广义最小二乘法(GLS): 处理模型异质性问题
Smith et al.(2005)报道了乌贼产卵(reproductive)及体细胞组织(somatic tissues)的季节变换模式,以此为例,构建睾丸重量(testis weight)与胴背长(dorsal mantle length)及月份关系的模型,线性回归模型为:
T e s t i s w e i g h t i = i n t e r c e p t + D M L i + M o n t h i + D M L i : M o n t h i + ε i Testisweight_i = intercept + DML_i + Month_i + DML_i:Month_i + ε_i Testisweighti=intercept+DMLi+Monthi+DMLi:Monthi+εi
ε i ( 0 , σ 2 ) ε_i ~ (0, σ^2) εi (0,σ2)
在该模型中,index i是观测数(1-768),εi的特征,var(εi) = σ2。
M1 <- lm(Testisweight ~ DML*fMONTH, data = Squid)
plot(M1, which = c(1), col = 1, add.smooth = FALSE, caption = "")
plot(Squid$fMONTH, resid(M1), xlab = "Month", ylab = "Residuals")
plot(Squid$DML, resid(M1), xlab = "DML", ylab = "Residuals")
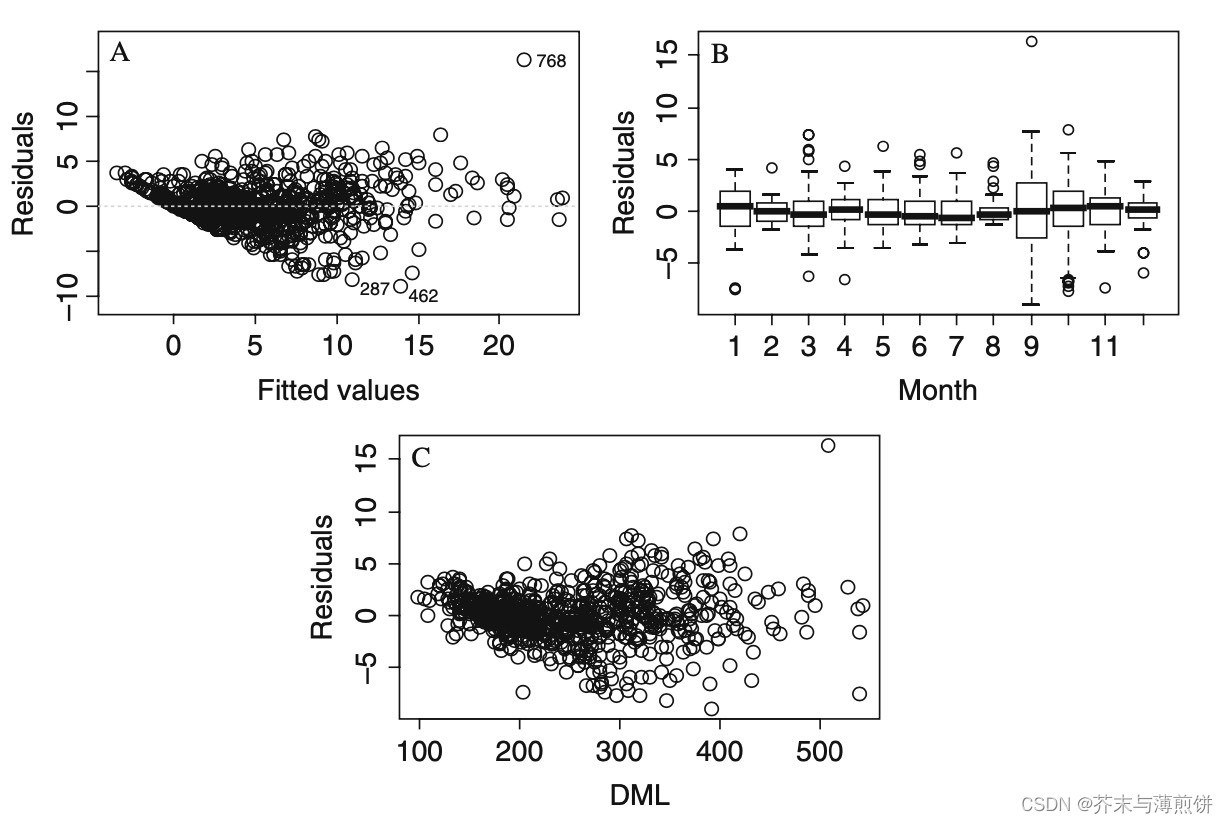
Panel A中残差随着Fitted values的增大而增大,违反了同质性假设。另一个明显的模式是,Panel C中,残差随着DML的增大而增大,且不同月份的残差也明显不同。因此,与其假设var(εi) = σ2,不如允许var(εi) 是解释变量的函数。
用于残差方差的解释变量称为方差协变量 (variance covariate),找到适合εij的**方差协变量结构 (variance covariate structure)**是关键。常见的方差协变量结构如下表所示:
| Names of the Function in R | What does it do? |
|---|---|
| VarFixed | Fixed variance |
| VarIdent | Different variances per stratum |
| VarPower | Power of the variance covariate |
| VarExp | Exponential of the variance covariate |
| VarConstPower | Constant plus power of the variance covariate |
| VarComb | A combination of variance functions |
###Fixed Variance Structure
Fix variance structure,该结构假设:
T e s t i s w e i g h t i = i n t e r c e p t + D M L i + M o n t h i + D M L i : M o n t h i + ε i Testisweight_i = intercept + DML_i + Month_i + DML_i:Month_i + ε_i Testisweighti=intercept+DMLi+Monthi+DMLi:Monthi+εi
( ε i ∼ N ( 0 , σ 2 × D M L i ) (ε_i ∼ N(0, σ^2 \times DML_i) (εi∼N(0,σ2×DMLi)
在该模型中,index i是观测数(1-768), 允许残差与DML呈正比例变化。
library(nlme)
M.lm <- gls(Testisweight ∼ DML * fMONTH, data=Squid)
vf1Fixed <- varFixed(∼DML) #允许残差与DML呈正比例变化。
M.gls1 <- gls(Testisweight ∼ DML * fMONTH, weights = vf1Fixed, data = Squid)
anova(M.lm, M.gls1)
Model df AIC BIC logLik
M.lm 1 25 3752.084 3867.385 -1851.042
M.gls1 2 25 3620.898 3736.199 -1785.449
###The VarIdent Variance Structure
VarIdent Variance Structure,该结构假设:
T e s t i s w e i g h t i j = i n t e r c e p t + D M L i j + M o n t h j + D M L i j : M o n t h j + r e s i d u a l s i j Testisweight_{ij} = intercept + DML_{ij} + Month_j + DML_{ij}:Month_j + residuals_{ij} Testisweightij=intercept+DMLij+Monthj+DML








 最低0.47元/天 解锁文章
最低0.47元/天 解锁文章















 76
76











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








