👨🎓个人主页:研学社的博客
💥💥💞💞欢迎来到本博客❤️❤️💥💥
🏆博主优势:🌞🌞🌞博客内容尽量做到思维缜密,逻辑清晰,为了方便读者。
⛳️座右铭:行百里者,半于九十。
📋📋📋本文目录如下:🎁🎁🎁
目录
💥1 概述
创建合取子句进化算法 (CCEA) 和析取范式进化算法 (DNFEA) 是为了找到与具有名义和可能的有序输出的真实世界数据相关的复杂交互。CCEA 和 DNFEA 执行监督学习,以发现与特定目标结果(例如疾病)的复杂多变量相关性。CCEA 能够在具有噪声、缺失数据和/或多种数据类型(即连续、有序和标称)的数据集中查找特征(上位)交互。CCEA 还能够使用特征敏感度函数来帮助防止过拟合特征交互的存档。DNFEA 在 CCEA 之后用于查找异构组合,这些组合可能与输出类别的相关性比任何单个连接子句更强。CCEA 和 DNFEA 都使用超几何概率质量函数作为适应度函数。
概述: 我们提出了一种新的进化方法,用于从批次数据中发现复杂分类问题中的因果规则。关键方面包括:(a) 使用超几何概率质量函数作为评估适合度的原则统计量,量化给定子句与目标类之间观察到的关联是由于偶然性的概率,同时考虑到数据集的大小、缺失的数据量和结果类别的分布, (b)串联年龄分层进化算法,用于演化连词的简约档案,以及这些连词的析取,每个连词都与结果类具有概率显着关联,以及(c)不同顺序的子句的单独档案箱,具有动态调整的顺序特定阈值。该方法在多数和多路复用器基准问题上进行了验证,这些问题表现出异质性、上位性、重叠、类关联噪声、缺失数据、无关特征和不平衡类的各种组合。我们还在更真实的合成基因组数据集上进行了验证,该数据集具有异质性、上位性、外来特征和噪声。在所有合成上位基准中,我们始终如一地恢复用于生成数据的真实因果规则集。最后,我们讨论了在复杂的真实世界调查数据集中的应用,该数据集旨在为恰加斯病的可能生态健康干预措施提供信息。
📚2 运行结果
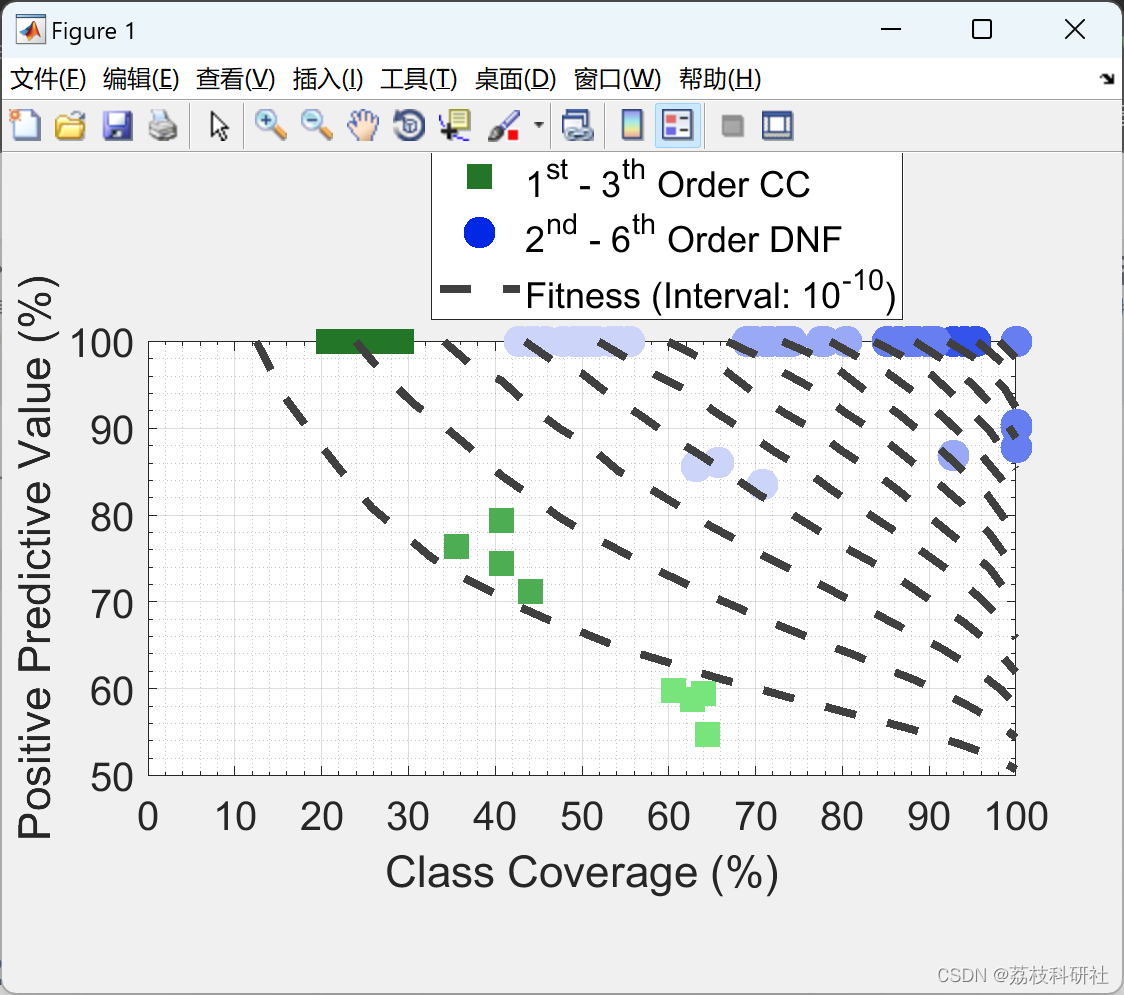
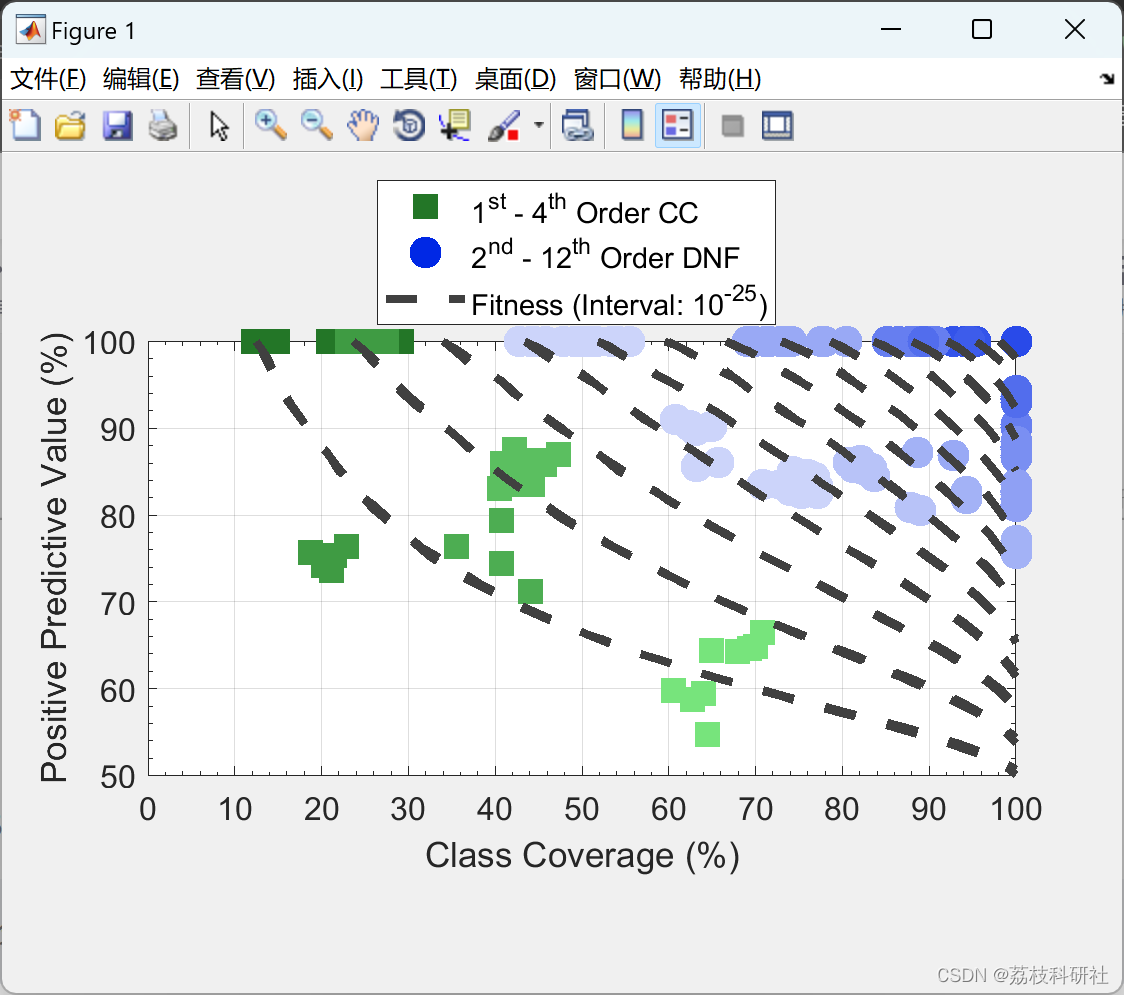
部分代码:
% Now try plotting the countour lines
for i=1:length(FitnessLevels)
CurCov=Boundaries{i,1};
CurPPV=Boundaries{i,4};
PlotCov=[CurCov(1:8:end); CurCov(end)];
PlotPPV=[CurPPV(1:8:end); CurPPV(end)];
% Extract the boundaries and plot
plot(PlotCov,PlotPPV,'--','Color',[0.25 0.25 0.25],...
'LineWidth',3)
hold on
clear CurCov
clear CurPPV
end
% For the legend
h1=plot(0,0,'s','MarkerFaceColor',CC_Green(end,:),...
'MarkerSize',12,'MarkerEdgeColor','none');
h2=plot(0,0,'o','MarkerFaceColor',DNF_Blue(end,:),...
'MarkerSize',12,'MarkerEdgeColor','none');
hf1=plot([-10 -20],[-10 -20],'--','Color',[0.25 0.25 0.25],...
'LineWidth',3);
% Plot settings
set(gca,'FontSize',12)
xlabel('Class Coverage (%)')
axis equal
ylabel('Positive Predictive Value (%)')
set(gca,'XTick',0:10:100)
set(gca,'YTick',50:10:100)
ylim([50 100])
xlim([0 100])
set(gca,'XMinorTick','on','YMinorTick','on')
% Write the legend captions
h1cap=[num2str(min(UniCC)) '^{st} - ' num2str(max(UniCC)) '^{th} Order CC'];
h2cap=[num2str(min(UniDNF)) '^{nd} - ' num2str(max(UniDNF)) '^{th} Order DNF'];
h3cap=['Fitness (Interval: 10^{-' num2str(FitInt) '})'];
legend([h1 h2 hf1],{h1cap,h2cap,h3cap},'Location','SouthWest')
grid on
grid minor
%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%%
% Finally, it may be helpful to see the values for each of the features
% The Bin2Cell function converts the conjunctive clauses to extract the CCs
% in the most-fit DNF
% First make a mask for the 10th-order DNF
OrdMask=DNFEA_A.DNForder==10;
Best10thOrd=min(DNFEA_A.DNFfit(OrdMask));
DNFmask=OrdMask&DNFEA_A.DNFfit==Best10thOrd;
% Now exctract the best 10th-order DNF
BestDNF=DNFEA_A.DNF(DNFmask,:);
% Select the first Best 10th order DNF
[CCsinDNF]=Bin2Cell(CCEA_A.CCs(BestDNF(1,:),:),...
CCEA_A.CCFeats(BestDNF(1,:),:),Param);
🎉3 参考文献
部分理论来源于网络,如有侵权请联系删除。
[1]Hanley, J.P., Rizzo, D.M., Buzas, J.S., and Eppstein, M.J. "A Tandem Evolutionary Algorithm for Identifying Causal Rules from Complex Data.", Evolutionary Computation, accepted subject to final editorial review, 2019.
























 6494
6494











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










