最全的Linux教程,Linux从入门到精通
======================
-
linux从入门到精通(第2版)
-
Linux系统移植
-
Linux驱动开发入门与实战
-
LINUX 系统移植 第2版
-
Linux开源网络全栈详解 从DPDK到OpenFlow

第一份《Linux从入门到精通》466页
====================
内容简介
====
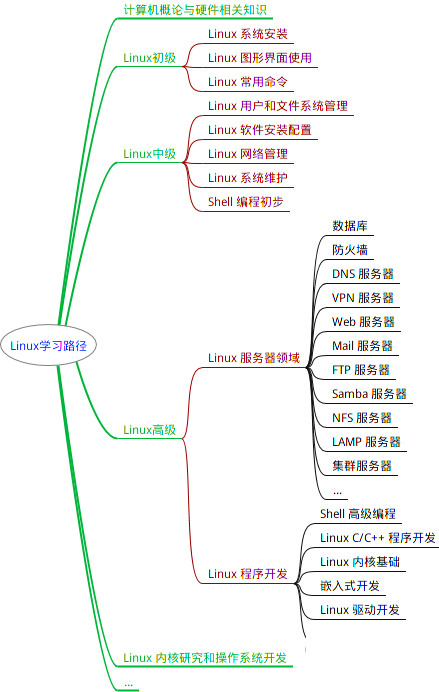
本书是获得了很多读者好评的Linux经典畅销书**《Linux从入门到精通》的第2版**。本书第1版出版后曾经多次印刷,并被51CTO读书频道评为“最受读者喜爱的原创IT技术图书奖”。本书第﹖版以最新的Ubuntu 12.04为版本,循序渐进地向读者介绍了Linux 的基础应用、系统管理、网络应用、娱乐和办公、程序开发、服务器配置、系统安全等。本书附带1张光盘,内容为本书配套多媒体教学视频。另外,本书还为读者提供了大量的Linux学习资料和Ubuntu安装镜像文件,供读者免费下载。

本书适合广大Linux初中级用户、开源软件爱好者和大专院校的学生阅读,同时也非常适合准备从事Linux平台开发的各类人员。
需要《Linux入门到精通》、《linux系统移植》、《Linux驱动开发入门实战》、《Linux开源网络全栈》电子书籍及教程的工程师朋友们劳烦您转发+评论
网上学习资料一大堆,但如果学到的知识不成体系,遇到问题时只是浅尝辄止,不再深入研究,那么很难做到真正的技术提升。








 本文介绍了全面的Linux教程,包括《Linux从入门到精通》第二版,涉及系统移植、驱动开发、网络全栈等内容。强调了系统化学习的重要性,推荐MetaWRAP工具和IT技术面试题集锦,鼓励读者加入技术交流社区以促进深度学习和职业发展。
本文介绍了全面的Linux教程,包括《Linux从入门到精通》第二版,涉及系统移植、驱动开发、网络全栈等内容。强调了系统化学习的重要性,推荐MetaWRAP工具和IT技术面试题集锦,鼓励读者加入技术交流社区以促进深度学习和职业发展。
 最低0.47元/天 解锁文章
最低0.47元/天 解锁文章















 8万+
8万+

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








