1. K-Means算法介绍
K-Means作为聚类算法中的典型代表,比较容易实现。
聚类算法又叫做“无监督分类”,其目的是将数据划分成有意义或有用的组(或簇)。这种划分可以基于业务需求或建模需求来完成,也可以单纯地帮助我们探索数据的自然结构和分布。比如在商业中,如果手头有大量的当前和潜在客户的信息,可以使用聚类将客户划分为若干组,以便进一步分析和开展营销活动。再比如,聚类可以用于降维和矢量量化,可以将高维特征压缩到一列当中,常常用于图像、声音和视频等非结构化数据,可以大幅度压缩数据量。
K-Means的工作原理:
K-Means算法是将一组N个样本的特征矩阵划分为K个无交集的簇;直观上是一组一组聚类
在一起的数据,在一个簇中的数据就是同一类。簇就是聚类的结果表现。
簇中所有数据的均值即:“簇的质心”。
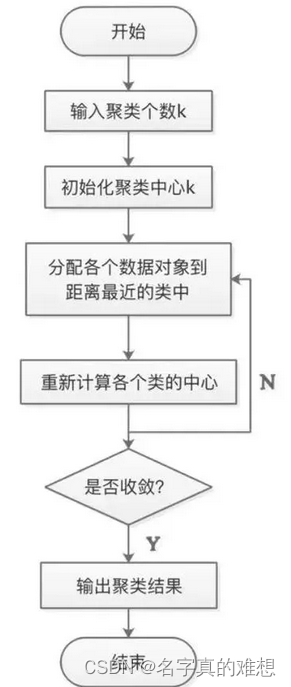
在K-Means算法中,簇的个数K是一个超参数,需要人为输入来确定。K-Means的核心任务就是根据设定好的K,找出K个最优的质心,并将离这些质心最近的数据分别分配到这些质心代表的簇中去。具体过程可以总结如下:
1.首先随机选取样本中的K个点作为聚类中心;
2.分别算出样本中其他样本距离这K个聚类中心的距离,并把这些样本分别作为自己最近的那个聚类中心的类别;
3.对上述分类完的样本再进行每个类别求平均值,求解出新的聚类质心;
4.与前一次计算得到的K个聚类质心比较,如果聚类质心发生变化,转过程b,否则转过程e;
5.当质心不发生变化时(当我们找到一个质心,在每次迭代中被分配到这个质心上的样本都是一致的,即每次新生成的簇都是一致的,所有的样本点都不会再从一个簇转移到另一个簇,质心就不会变化了),停止并输出聚类结果。流程图如下:
簇内误差平方和的定义:
聚类算法聚出的类有什么含义呢?这些类有什么样的性质?
我们认为,被分在同一个簇中的数据是有相似性的,而不同簇中的数据是不同的,当聚类完毕之后,接下来需要分别研究每个簇中的样本都有什么样的性质,从而根据业务需求制定不同的商业或者科技策略。聚类算法追求“簇内差异小,簇外差异大”。而这个 “差异”便是通过样本点到其簇质心的距离来衡量。
对于一个簇来说,所有样本点到质心的距离之和越小,便认为这个簇中的样本越相似,簇内差异越小。而距离的衡量方法有多种,令x表示簇中的一个样本点,μ表示该簇中的质心,n表示每个样本点中的特征数目,i表示组成点x的每个特征,则该样本点到质心的距离可以由以下距离来度量:

采用欧几里德距离,那么同一个簇中样本点到质心的距离平方和为:

其中,m为一个簇中样本的个数,j是每个样本的编号。这个公式被称为簇内平方和(Cluster Sum of Square),又叫做Inertia。而将一个数据集中的所有簇的簇内平方和相加,就得到了整体平方和(Total Cluster Sum of Square),又叫做Total Inertia。
Total Inertia越小,代表着每个簇内样本越相似,聚类的效果就越好。因此K-Means追求的是:求解能够让Inertia最小化的质心。实际上,在质心不断变化不断迭代的过程中,总体平方和是越来越小的。我们可以通过数学来证明,当整体平方和达到最小值的时候,质心就不再发生变化了。如此,K-Means的求解过程,就变成了一个最优化问题。
在K-Means中,在一个固定的簇数K条件下,最小化总体平方和来求解最佳质心,并基于质心的存在去进行聚类。两个过程十分相似,并且整体距离平方和的最小值其实可以使用梯度下降来求解。
Inertia是基于欧几里得距离的计算公式得来的。实际上,也可以使用其他距离,每个距离都有自己对应的Inertia。在过去的经验中,已经总结出不同距离所对应的质心选择方法和Inertia,
在K-Means中,只要使用了正确的质心和距离组合,无论使用什么距离,都可以达到不错的聚类效果。
因此,K-Means可以被用在很多数据最优化的问题当中。
参考了文章:
2. K-Means_C++实现
K_Means的C++代码如下:
#include<iostream>
#include<vector>
#include<map>
#include<cstdlib>
#include<algorithm>
#include<fstream>
#include<stdio.h>
#include<string.h>
#include<string>
#include<time.h> //for srand
#include<limits.h> //for INT_MIN INT_MAX
using namespace std;
template<typename T>
class KMEANS
{
private:
vector< vector<T> > dataSet;//the data set
vector< T > mmin,mmax;
int colLen,rowLen;//colLen:the dimension of vector;rowLen:the number of vectors
int k;
vector< vector<T> > centroids;
typedef struct MinMax
{
T Min;
T Max;
MinMax(T min , T max):Min(min),Max(max) {}
}tMinMax;
typedef struct Node
{
int minIndex; //the index of each node
double minDist;
Node(int idx,double dist):minIndex(idx),minDist(dist) {}
}tNode;
vector<tNode> clusterAssment;
/*split line into numbers*/
void split(char *buffer , vector<T> &vec);
tMinMax getMinMax(int idx);
void setCentroids(tMinMax &tminmax , int idx);
void initClusterAssment();
double distEclud(vector<T> &v1 , vector<T> &v2);
public:
KMEANS(int k);
void loadDataSet(char *filename);
void randCent();
void print();
void kmeans();
};
template<typename T>
void KMEANS<T>::initClusterAssment()
{
tNode node(-1,-1);
for(int i=0;i<rowLen;i++)
{
clusterAssment.push_back(node);
}
}
template<typename T>
void KMEANS<T>::kmeans()
{
initClusterAssment();
bool clusterChanged = true;
//the termination condition can also be the loops less than some number such as 1000
while( clusterChanged )
{
clusterChanged = false;
//step one : find the nearest centroid of each point
cout<<"find the nearest centroid of each point : "<<endl;
for(int i=0;i<rowLen;i++)
{
int minIndex = -1;
double minDist = INT_MAX;
for(int j=0;j<k;j++)
{
double distJI = distEclud( centroids[j],dataSet[i] );
if( distJI < minDist )
{
minDist = distJI;
minIndex = j;
}
}
if( clusterAssment[i].minIndex != minIndex )
{
clusterChanged = true;
clusterAssment[i].minIndex = minIndex;
clusterAssment[i].minDist = minDist ;
}
}
//step two : update the centroids
cout<<"update the centroids:"<<endl;
for(int cent=0;cent<k;cent++)
{
vector<T> vec(colLen,0);
int cnt = 0;
for(int i=0;i<rowLen;i++)
{
if( clusterAssment[i].minIndex == cent )
{
++cnt;
//sum of two vectors
for(int j=0;j<colLen;j++)
{
vec[j] += dataSet[i].at(j);
}
}
}
//mean of the vector and update the centroids[cent]
for(int i=0;i<colLen;i++)
{
if( cnt!=0 ) vec[i] /= cnt;
centroids[cent].at(i) = vec[i];
}
}//for
print();//update the centroids
}//while
#if 0
typename vector<tNode> :: iterator it = clusterAssment.begin();
while( it!=clusterAssment.end() )
{
cout<<(*it).minIndex<<"\t"<<(*it).minDist<<endl;
it++;
}
#endif
}
template<typename T>
KMEANS<T>::KMEANS(int k)
{
this->k = k;
}
template<typename T>
void KMEANS<T>::setCentroids(tMinMax &tminmax,int idx)
{
T rangeIdx = tminmax.Max - tminmax.Min;
for(int i=0;i<k;i++)
{
/* generate float data between 0 and 1 */
centroids[i].at(idx) = tminmax.Min + rangeIdx * ( rand() / (double)RAND_MAX ) ;
}
}
//get the min and max value of the idx column
template<typename T>
typename KMEANS<T>::tMinMax KMEANS<T>::getMinMax(int idx)
{
T min , max ;
dataSet[0].at(idx) > dataSet[1].at(idx) ? ( max = dataSet[0].at(idx),min = dataSet[1].at(idx) ) : ( max = dataSet[1].at(idx),min = dataSet[0].at(idx) ) ;
for(int i=2;i<rowLen;i++)
{
if( dataSet[i].at(idx) < min ) min = dataSet[i].at(idx);
else if( dataSet[i].at(idx) > max ) max = dataSet[i].at(idx);
else continue;
}
tMinMax tminmax(min,max);
return tminmax;
}
template<typename T>
void KMEANS<T>::randCent()
{
//init centroids
vector<T> vec(colLen,0);
for(int i=0;i<k;i++)
{
centroids.push_back(vec);
}
//set values by column
srand( time(NULL) );
for(int j=0;j<colLen;j++)
{
tMinMax tminmax = getMinMax(j);
setCentroids(tminmax,j);
}
}
template<typename T>
double KMEANS<T>::distEclud(vector<T> &v1 , vector<T> &v2)
{
T sum = 0;
int size = v1.size();
for(int i=0;i<size;i++)
{
sum += (v1[i] - v2[i])*(v1[i] - v2[i]);
}
return sum;
}
template<typename T>
void KMEANS<T>::split(char *buffer , vector<T> &vec)
{
char *p = strtok(buffer," \t");
while(p!=NULL)
{
vec.push_back( atof(p) );
p = strtok( NULL," " );
}
}
template<typename T>
void KMEANS<T>::print()
{
ofstream fout;
fout.open("res.txt");
if(!fout)
{
cout<<"file res.txt open failed"<<endl;
exit(0);
}
#if 0
typename vector< vector<T> > :: iterator it = centroids.begin();
while( it!=centroids.end() )
{
typename vector<T> :: iterator it2 = (*it).begin();
while( it2 != (*it).end() )
{
//fout<<*it2<<"\t";
cout<<*it2<<"\t";
it2++;
}
//fout<<endl;
cout<<endl;
it++;
}
#endif
typename vector< vector<T> > :: iterator it = dataSet.begin();
typename vector< tNode > :: iterator itt = clusterAssment.begin();
for(int i=0;i<rowLen;i++)
{
typename vector<T> :: iterator it2 = (*it).begin();
while( it2!=(*it).end() )
{
fout<<*it2<<"\t";
it2++;
}
fout<<(*itt).minIndex<<endl;
itt++;
it++;
}
}
template<typename T>
void KMEANS<T>:: loadDataSet(char *filename)
{
FILE *pFile;
pFile = fopen(filename,"r");
if( !pFile )//读取整个文件的名称
{
printf("open file %s failed...\n",filename);
exit(0);
}
//init dataSet
char *buffer = new char[100];
vector<T> temp;
while( fgets(buffer,100,pFile) )
{
temp.clear();
split(buffer,temp);
dataSet.push_back(temp);
}
//init colLen,rowLen
colLen = dataSet[0].size();
rowLen = dataSet.size();
}
int main( int argc , char *argv[])
{
if(argc!=3)
{
cout<<"Usage : ./a.out filename k"<<endl;
exit(0);
}
char *filename = argv[1];
int k = atoi(argv[2]);//将字符串变为整数
KMEANS<double> kms(k);//自定义类型为double的KMEAS对象
kms.loadDataSet(filename);
kms.randCent();
kms.kmeans();
return 0;
}然后我是在Linux系统下,使用的CMake工程进行编译的。
编译完成后,使用:
./生成的可执行文件名 数据集 将数据划分为几类
在我的电脑上,是这样执行的:
./K_Means ../1.txt 3
然后将会生成一个结果文件,具体如下:
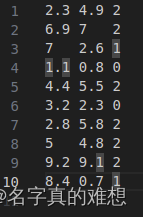
将会对数据进行分类。可视化可以使用python进行处理,在这里不演示。
数据集比较小:
(2.3, 4.9), (6.9, 7), (7, 2.6), (1.1, 0.8), (4.4, 5.5), (3.2, 2.3), (2.8, 5.8), (5, 4.8), (9.2, 9.1), (8.4, 0.7)
参考文章如下:





















 2963
2963











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








