由于网络原因,常常使用getGEO函数可能会出错,下载不了文件。可以从GEO官网下载矩阵(部分可能没有矩阵)
读取矩阵
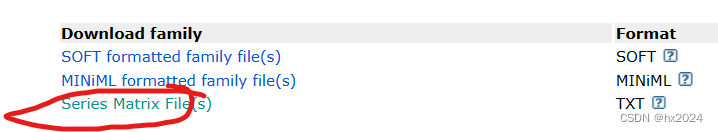
然后进行R读取进行ID转换分析等
#第一步对下载的文件解压
#解压一个txt 文件,并且有相关GSE样本的注释(可选择删除注释,转换为CSV格式进行读取:麻烦)
##这里直接读取txt文件
exprSet <- read.table("GSE文件_series_matrix.txt",
comment.char="!", #comment.char="!" 意思是!后面的内容不要读取
stringsAsFactors=F,
header=T)
class(exprSet)##查看数据类型
rownames(exprSet) <- exprSet[,1] #把第一列的值变为行名
exprSet <- exprSet[,-1] #把第一列去掉
##后续进行ID转换和分析读取GPL探针文件
rm(list=ls())
GPL <- read.delim("GPL570.annot",stringsAsFactors=FALSE,skip = 27 )
##下载的GPL文件的前27行是基本信息,这个基本每个文件都一样,不一样的自己微调
GSE临床数据下载
#临床信息下载整理:方法1
rm(list = ls())
library(GEOquery)
eSet <- getGEO("GSE84437", #获取相关GEO信息
destdir = '.', #下载在当前目录
getGPL = F) #平台信息不要
pdata1 <- pData(eSet[[2]])#提取第一个平台的临床数据
pdata2 <- pData(eSet[[1]])#提取第二个平台的临床数据
#pdata<-pData(eSet) #pData用于提取临床信息出现报错下载不了怎么解决?
Error in downloadFile(url, destfile = destfile, mode = "wb") : (应该是网络下载相关的问题)
或者直接从GEO网页下载数据
GEOquery只下载临床信息如何只查看geo的临床信息而不下载矩阵_easygeo-CSDN博客
GEO生信数据挖掘(五)提取临床信息构建分组,分组数据可视化(绘制层次聚类图,绘制PCA图)_geo数据库 层次聚类-CSDN博客







 本文讲述了在网络不稳定时处理getGEO函数下载文件的问题,介绍了从GEO官网手动下载矩阵的方法,以及如何使用R读取、解压和处理GSE文件,包括ID转换、GPL探针文件读取,以及GEO临床数据的下载和处理技巧。
本文讲述了在网络不稳定时处理getGEO函数下载文件的问题,介绍了从GEO官网手动下载矩阵的方法,以及如何使用R读取、解压和处理GSE文件,包括ID转换、GPL探针文件读取,以及GEO临床数据的下载和处理技巧。

















 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








