基本原理:对片段对的概念。所谓片段对是指两个给定序列中的一对子序列,它们长度相等,且可形成无空位完全匹配。
种类:
- Blastp:蛋白质序列去蛋白质数据库。
- Blastn:核酸序列去核酸数据库。
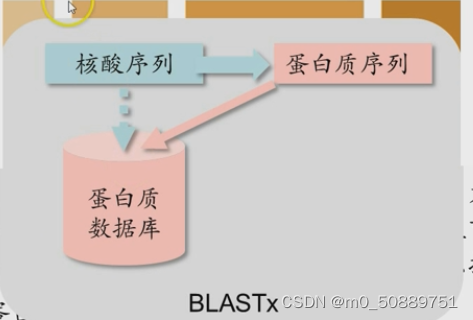
- Blastx:将核酸按照6条翻译成蛋白质序列再在蛋白质里进行搜索。
应用:主要对于核酸未知的序列,将其翻译成蛋白质序列再在蛋白质数据库搜索。
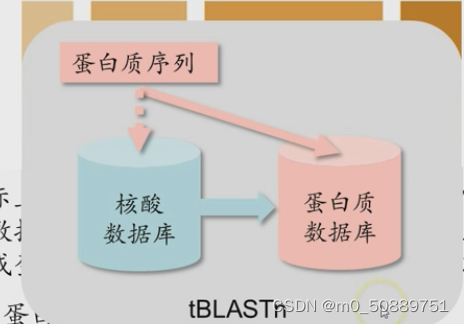
- tblastn:用蛋白质序列搜索核酸序列数据库,核酸数据库中按照6条翻译链翻译成蛋白质序列搜索。
应用:主要对未知的蛋白质序列进行搜索。蛋白质库中没有该序列,但是核酸数据库中可能有。
- tblastx:将核酸序列按照6条链翻译成蛋白质序列后搜索核酸序列数据库,数据库的中核酸序列按照6条链翻译成蛋白质序列再进行搜索。
应用:对于未知的核酸序列(利用6条链翻译成蛋白质序列a),利用核酸数据库进行翻译,然后得到蛋白质数据库(核酸数据库通过6条链翻译成蛋白质数据库A),再用a 在B中查找。与tblastn不同的是需要转义一步。

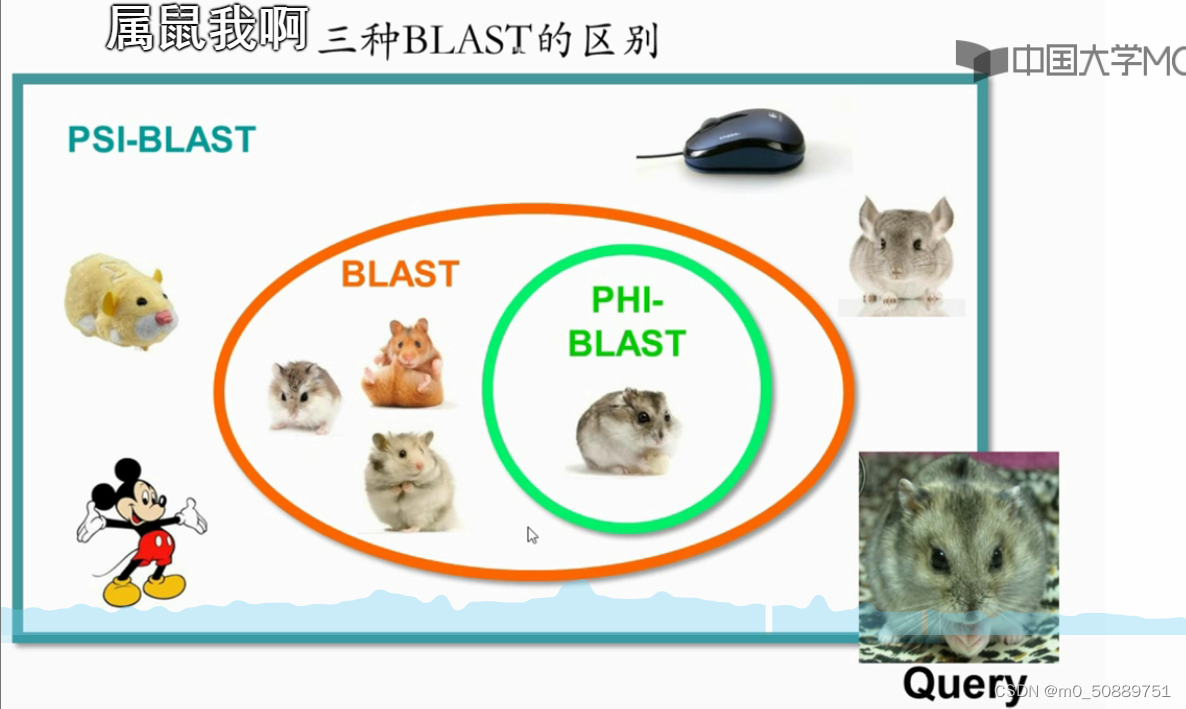
标准BLAST,PSI-BLAST(就近搜索,不断进行迭代),PHI-BLAST之间的示意图:





















 9120
9120











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








