MOCAT2的一些常见模块及其输出结果文件的内容展示和介绍:
1. mocat_preprocessing 模块:
- 输出文件:
clean_reads_1.fastq、clean_reads_2.fastq: 经过质量控制和预处理后的测序数据。summary_statistics.txt: 包含关于质量控制步骤的统计信息,如序列数目、质量分数统计等。
2. mocat_assembly 模块:
- 输出文件:
contigs.fasta: 组装得到的contigs序列。assembly_stats.txt: 包含有关组装质量和性能的统计信息,如N50、最大/最小contig长度等。
3. mocat_analysis 模块:
- 输出文件:
blast_results.txt:包含BLAST注释的结果,显示序列与参考数据库的相似性。gene_catalog.fasta:根据比对结果生成的基因目录序列。functional_annotation.txt:功能注释的结果文件,包括基因或序列的功能描述、KEGG或COG注释等信息。classification_results.txt:分类结果,显示序列或基因的分类信息,如菌株、属、门水平的分类等。
4. mocat_metaquant 模块(可选,用于定量分析):
- 输出文件:
gene_abundance_table.txt:基因丰度表,显示每个基因在样本中的丰度估算。transcript_abundance_table.txt:转录本丰度表,显示转录本在样本中的丰度估算。- 其他可能包含样本丰度信息的文件。
注意事项:
- 每个模块生成的输出文件格式和内容可能会因应用不同参数和实验设计而有所不同。
- 结果文件中包含的信息可以帮助研究人员了解数据质量、序列注释信息、组装质量和功能注释等方面的信息。
- 输出文件中的数据通常以文本或FASTA等格式呈现,可以使用文本编辑器或专业的生物信息学软件进行查看和进一步分析。
MOCAT2 使用流程:
数据准备:
- 获得宏基因组/宏转录组测序数据(FASTQ格式)。
- 准备参考数据库,如基因组数据库或功能注释数据库。
运行 MOCAT2:
MOCAT2的主要模块和使用示例命令如下:
mocat_preprocessing:进行质量控制和预处理。
mocat_preprocessing -t 4 -o output_directory --input-files reads_1.fastq,reads_2.fastq
mocat_assembly:执行序列组装。
mocat_assembly -t 4 -o output_directory --input-files reads_1.fastq,reads_2.fastq
mocat_analysis:进行功能注释和分类分析。
mocat_analysis -t 4 -o output_directory --input-files assembly.fa
这里的 -t 选项用于指定线程数,-o 用于指定输出目录,--input-files 用于指定输入文件。
结果解释和分析:
MOCAT2生成的输出文件包括装配得到的序列、注释结果、分类信息等。可以使用其他工具或分析流程进一步解释和分析这些结果。
示例代码:
以下是一个使用MOCAT2的简单Shell脚本示例,演示了一个简单的分析流程:
# 质量控制和预处理
mocat_preprocessing -t 4 -o preprocessing_output --input-files reads_1.fastq,reads_2.fastq
# 序列组装
mocat_assembly -t 4 -o assembly_output --input-files preprocessing_output/clean_reads_1.fastq,preprocessing_output/clean_reads_2.fastq
# 功能注释和分类分析
mocat_analysis -t 4 -o analysis_output --input-files assembly_output/contigs.fasta
注意事项:
- MOCAT2提供了丰富的功能和模块,具体的使用方法和参数设置需要根据数据类型和实验设计进行调整。
- 分析过程可能需要较长的时间和较大的计算资源,特别是对于大规模的宏基因组/宏转录组数据。
- 根据数据类型和分析需求,可能需要进一步的后续分析和解释。
MOCAT.pl全参数帮助信息
MOCAT.pl --help
===============================================================================
MOCAT - Metagenomics Analysis Toolkit v2.1.3
by Jens Roat Kultima, Luis Pedro Coelho, Shinichi Sunagawa @ Bork Group, EMBL
===============================================================================
Full manual & FAQ: MOCAT.pl -man
How to cite MOCAT: MOCAT.pl -cite
Have you tried the wrapper runMOCAT.sh? Try it!
Usage: MOCAT.pl -sf|sample_file 'FILE' [Pipeline, Statistics, & Additional Options]
'FILE'
Contains the list of folder names (sample names), one per line,
in which the raw sample data is located
Examples
Process, Assemble, Revise Assembly, Predict Genes, cluster genes into gene catalog, annotate gene catalog, profile against gene catalog
MOCAT.pl -sf my.samples -rtf
MOCAT.pl -sf my.samples -a
MOCAT.pl -sf my.samples -gp assembly
MOCAT.pl -sf my.samples -make_gene_catalog -assembly_type assembly
MOCAT.pl -sf my.samples -annotate_gene_catalog
MOCAT.pl -sf my.samples -s my.samples.padded -identity 95
MOCAT.pl -sf my.samples -f my.samples.padded -identity 95
MOCAT.pl -sf my.samples -p my.samples.padded -identity 95 -mode functional
Assemble and predict genes: MOCAT.pl -sf my.samples -rtf
(no screen) MOCAT.pl -sf my.samples -a
MOCAT.pl -sf my.samples -gp assembly
fetch marker genes: MOCAT.pl -sf my.samples -fmg assembly
MOCAT.pl -sf my.samples -ss
Assemble and predict genes: MOCAT.pl -sf my.samples -rtf
(DB screen) MOCAT.pl -sf my.samples -s hg19 -screened_files -identity 90
MOCAT.pl -sf my.samples -a -r hg19
MOCAT.pl -sf my.samples -gp assembly -r hg19
MOCAT.pl -sf my.samples -ss
Assemble and predict genes: MOCAT.pl -sf my.samples -rtf
(remove eg. adapters MOCAT.pl -sf my.samples -sff adapters.fa -screened_files
and then DB screen) MOCAT.pl -sf my.samples -bwa hg19 -r adapters.fa -screened_files
MOCAT.pl -sf my.samples -a -r screened.adapters.fa.on.hg19
MOCAT.pl -sf my.samples -gp assembly -r screened.adapters.fa.on.hg19
MOCAT.pl -sf my.samples -ss
Pipeline Options
-r|reads ['reads.processed', 'DATABASE' or 'FASTA FILE']
Required for all pipeline options, except rtf|read_trim_filter
Specify whether processing trim & filtered, or screened reads.
A default value to this setting can also be specified in config file
-e|extracted
Optional for all pipeline options, except rtf|read_trim_filter, see full manual
-rtf|read_trim_filter
performs trimming and filtering of reads
-a|assembly
Performs assembly of reads
-ar|assembly_revision
Further improves assemblies
-gp|gene_prediction ['assembly', 'assembly.revised']
Predicts protein coding genes on assemblies
-fmg|fetch_mg ['assembly', 'assembly.revised']
Extracts marker genes among the predicted genes
-soap|bwa ['DB1 DB2 ...',s,c,f,r]
Screen, extract and map reads against a reference databse (hg19 is provided) or (s)acftigs,
(c)ontigs, sca(f)folds from an assembly, or scaftigs from a (r)evised assembly.
This mapping step uses SOAPaligner2 (soap) or BWA (bwa).
Additional options:
-screened_files : If set, screened read files are generated, these are reads not matching the DB
-extracted_files : If set, extracted read files are generated, these are reads matching the DB
-use_mem : If set, copies the DB into memory for faster loading
-sff|screen_fastafile 'FASTA FILE'
Same as 's|screen' above, but uses USearch, rather than SOAPaligner2.
-fsoap ['DB1 DB2 ...',s,c,f,r]
Filter screened reads, (s)caftigs, (c)ontigs, sca(f)folds or (r)evised assembly scaftigs
at higher %ID and length cutoff. This step has to be run before calculating profiles if the option soap was used
Additional options:
-shm : If set, faster, but saves data for the filtering step in /dev/shm/<USER>
-psoap|pbwa ['DB1 DB2 ...',s,c,f,r] -m|mode [gene, NCBI, mOTU, functional] -o [OUTPUT FOLDER]
Generate gene, mOTU, NCBI or functional profiles on filtered reads,
(s)caftigs, (c)ontigs, sca(f)folds or (r)evised assembly scaftigs.
If -mode is set to either NCBI or mOTU, it is expected that the
reads have been correctly mapped to the corresponding databases.
Specify psoap if you used the command 'soap' previously, and 'pbwa' if you used 'bwa'.
Additional options:
-no_horizontal : No not calculate horizontal gene & functional coverages
-verbose : Prints extra information about status of profiling steps
-shm : Faster, but saves 2-5 GB of data for the profiling step in /dev/shm/<USER>
-uniq : Specify this flag if you find duplicated row names
(e.g. if you have mapped to a DB where the same reference appears multiple times)
Available modules
These are installed in the folder /nfs/data/Downloads/mocat2/stable/2.1.3/mod
Each module requires a NAME.sh and NAME.cfg file inside the NAME folder
-annotate_gene_catalog [leave empty for using sample file generated catalog or enter full path to catalog; use amino acid sequence file]
Required options:
-blasttype [should be "blastp" normally for amino acid sequences, but can be set to "blastx"]
-make_gene_catalog [samples specifed in sample file will be used ot generate catalog]
Required options:
-assembly_type [asembly or assembly.revised]
Statistics Options
-sfq|stats_fastqc
Produces statistics for each lane with raw reads using the FastQC toolkit
-ss|sample_status
Prints a simple view how the processing status of each sample,
and stores this in <sample_file>.status
Additional Options
-cfg|config [file]
Specify another config file than MOCAT.cfg
-x|no_execute
Only create job scripts, but don't execute them
-nt|no_temp
Overrides any specified temp folders config file
-cpus [integer]
Not recommended, but specifies a fixed number of cores for each job,
please read the full manual using MOCAT.pl -man
-host [hostname]
Runs the jobs on a different host machine
-identity [integer]
Overrides any percentage cutoff setting in cfg file
-length [integer]
Overrides any length cutoff setting in cfg file
**自我介绍一下,小编13年上海交大毕业,曾经在小公司待过,也去过华为、OPPO等大厂,18年进入阿里一直到现在。**
**深知大多数Linux运维工程师,想要提升技能,往往是自己摸索成长或者是报班学习,但对于培训机构动则几千的学费,着实压力不小。自己不成体系的自学效果低效又漫长,而且极易碰到天花板技术停滞不前!**
**因此收集整理了一份《2024年Linux运维全套学习资料》,初衷也很简单,就是希望能够帮助到想自学提升又不知道该从何学起的朋友,同时减轻大家的负担。**





**既有适合小白学习的零基础资料,也有适合3年以上经验的小伙伴深入学习提升的进阶课程,基本涵盖了95%以上Linux运维知识点,真正体系化!**
**由于文件比较大,这里只是将部分目录大纲截图出来,每个节点里面都包含大厂面经、学习笔记、源码讲义、实战项目、讲解视频,并且后续会持续更新**
**如果你觉得这些内容对你有帮助,可以添加VX:vip1024b (备注Linux运维获取)**

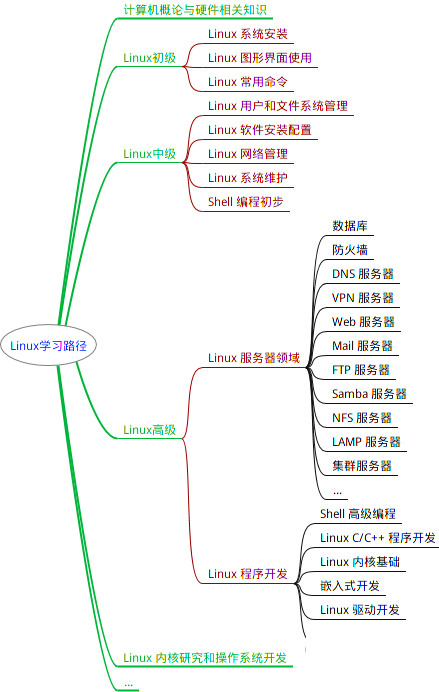
最全的Linux教程,Linux从入门到精通
======================
1. **linux从入门到精通(第2版)**
2. **Linux系统移植**
3. **Linux驱动开发入门与实战**
4. **LINUX 系统移植 第2版**
5. **Linux开源网络全栈详解 从DPDK到OpenFlow**

第一份《Linux从入门到精通》466页
====================
内容简介
====
本书是获得了很多读者好评的Linux经典畅销书**《Linux从入门到精通》的第2版**。本书第1版出版后曾经多次印刷,并被51CTO读书频道评为“最受读者喜爱的原创IT技术图书奖”。本书第﹖版以最新的Ubuntu 12.04为版本,循序渐进地向读者介绍了Linux 的基础应用、系统管理、网络应用、娱乐和办公、程序开发、服务器配置、系统安全等。本书附带1张光盘,内容为本书配套多媒体教学视频。另外,本书还为读者提供了大量的Linux学习资料和Ubuntu安装镜像文件,供读者免费下载。

**本书适合广大Linux初中级用户、开源软件爱好者和大专院校的学生阅读,同时也非常适合准备从事Linux平台开发的各类人员。**
> 需要《Linux入门到精通》、《linux系统移植》、《Linux驱动开发入门实战》、《Linux开源网络全栈》电子书籍及教程的工程师朋友们劳烦您转发+评论
**一个人可以走的很快,但一群人才能走的更远。不论你是正从事IT行业的老鸟或是对IT行业感兴趣的新人,都欢迎扫码加入我们的的圈子(技术交流、学习资源、职场吐槽、大厂内推、面试辅导),让我们一起学习成长!**

6a92edea27b825e59aa1f2c54.png)
**本书适合广大Linux初中级用户、开源软件爱好者和大专院校的学生阅读,同时也非常适合准备从事Linux平台开发的各类人员。**
> 需要《Linux入门到精通》、《linux系统移植》、《Linux驱动开发入门实战》、《Linux开源网络全栈》电子书籍及教程的工程师朋友们劳烦您转发+评论
**一个人可以走的很快,但一群人才能走的更远。不论你是正从事IT行业的老鸟或是对IT行业感兴趣的新人,都欢迎扫码加入我们的的圈子(技术交流、学习资源、职场吐槽、大厂内推、面试辅导),让我们一起学习成长!**
[外链图片转存中...(img-QMDMXEZy-1712901457529)]






















 1763
1763











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








