新手发布,如果有错误或者补充,欢迎捉虫~
dpabi view的使用及多重比较矫正
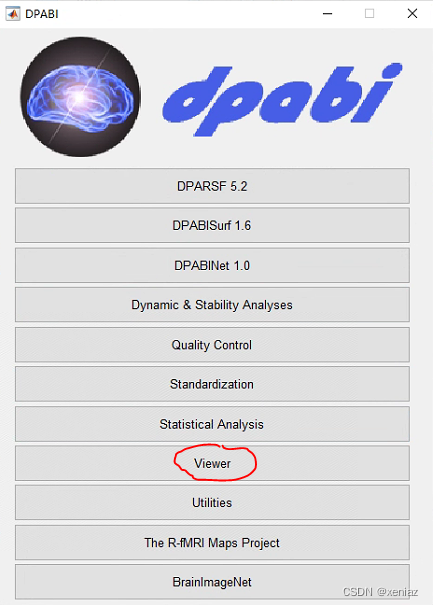
打开dpabi,点击Viewer,进入dpabi view界面
基本介绍:
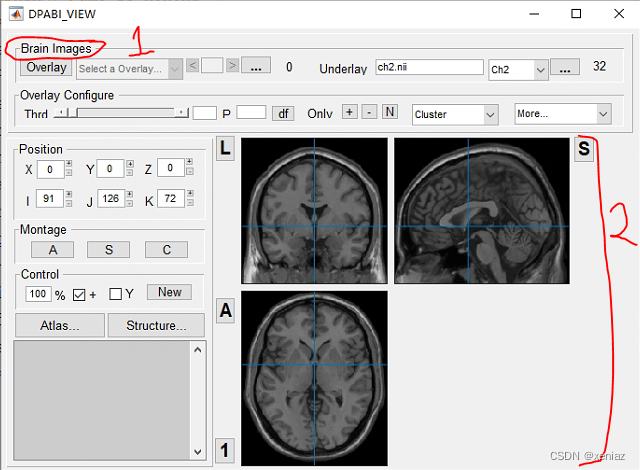
1、Brain Images: 选择要展示的Brain Image
2、图像显示界面: 显示图像的界面
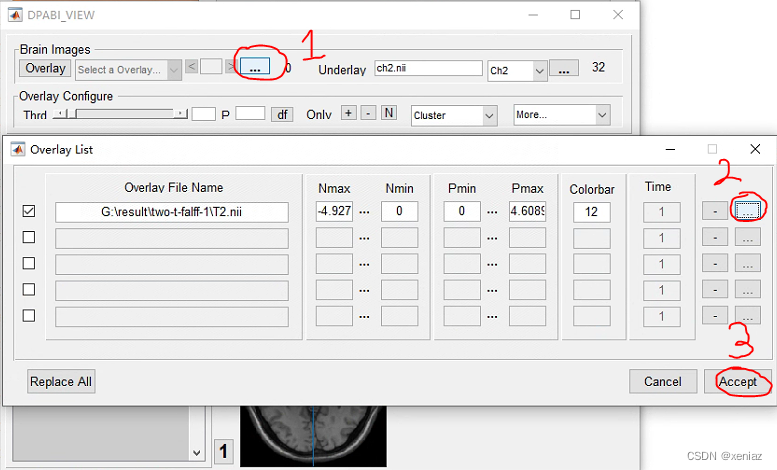
导入图像:
1、overlay: 点击overlay后的“…”,打开overlay list
**2、overlay File: **点击2所示的“…”,选择要查看的图像,这里我选择的是falff双样本t检验之后算出的图像“T2”(不要选算出的另一个)【更多双样本t检验内容看上篇】
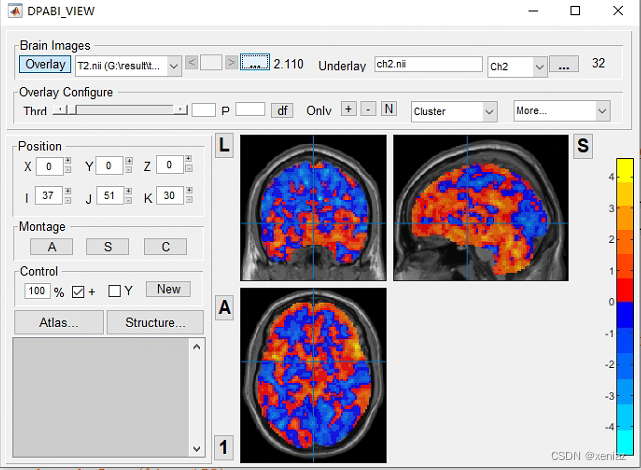
3、Accept: 点击确定,出现如下图所示花花绿绿的图像是正常的
多重比较矫正(基于Cluster)
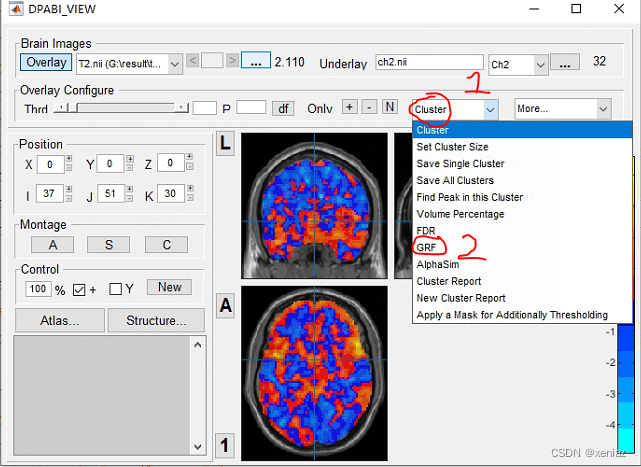
1、Cluster: 点击Cluster进行多重比较矫正
2、GRF: 选择GRF矫正,矫正严格程度:FDR>GRF>AlphaSim,个人更建议使用spm做FWE或FDR的矫正,不建议单独使用AlphaSim矫正,可信度低。
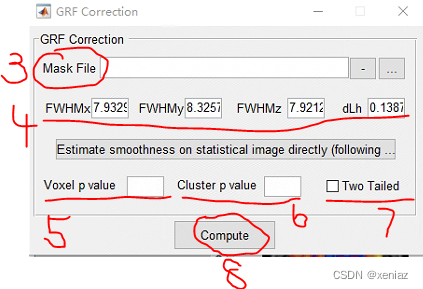
3、Mask File: 选择之前双样本t检验选择的Mask
4、FWHM: 如果是使用dpabi做的预处理这里会直接显示,如果是其他软件做的预处理要填写平滑核,注意这里的平滑核和smooth输入的平滑核不一样,因为在smooth之后有进行了计算操作等等,我这里是直接用dpabi做的预处理,严老师好像有出相关计算参考,可以查一下【这里不输入结果会出错】
5、Voxel p value: 使用基于Cluster的多重比较矫正,填写0.001【有关多重比较矫正原理可能会出一篇新文章说明】
6、Cluster p value: 填写0.05或0.01
7、Two Tailed: 一般要勾选,意思是为了保证最终假阳性率小于0.05,使得groupA-groupB的假阳性小于0.025且groupB-groupA的假阳性小于0.025,所以总假阳性率小于0.05
8、Compute: 点击Compute运行查看结果
脑区显示

1、Atlas: 点击Atlas出现w_AtlasSelect界面
2、Select Atlas to Add: 点击Select Atlas to Add选择需要的模板(可选择多个)
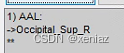
3、Accept: 点击Accept出现上图结果
结果汇报
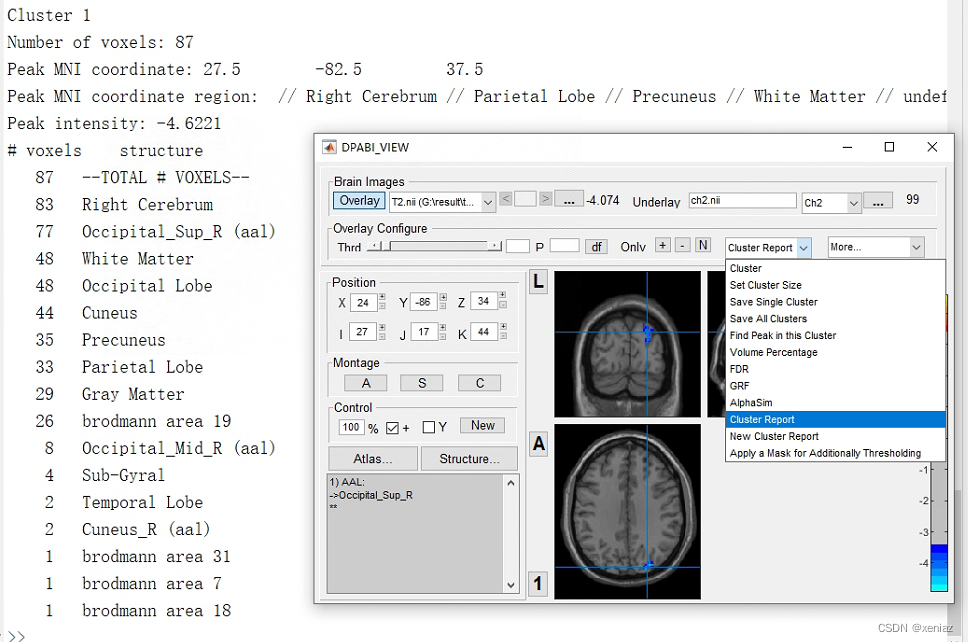
点击Cluster Report,在MATLAB中会出现结果值
结果提值
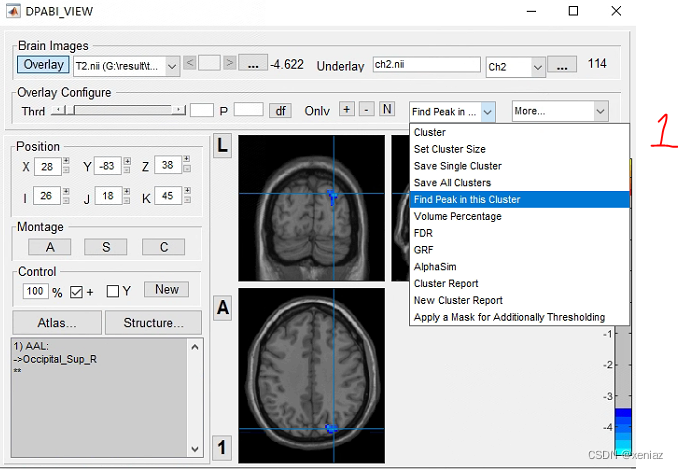
1、Find Peak in this Cluster: 点击Find Peak in this Cluster,将十字光标定位在peak值上
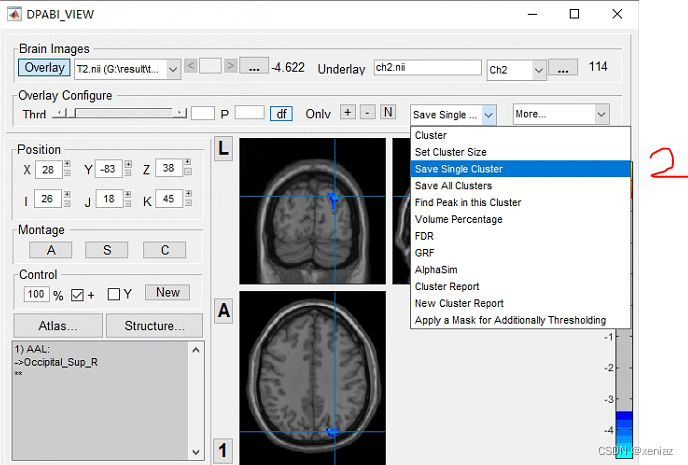
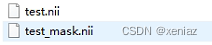
2、Save Single Cluster: 点击Save Single Cluster,会生成两个文件,其中test_mask就是提值结果(nii)
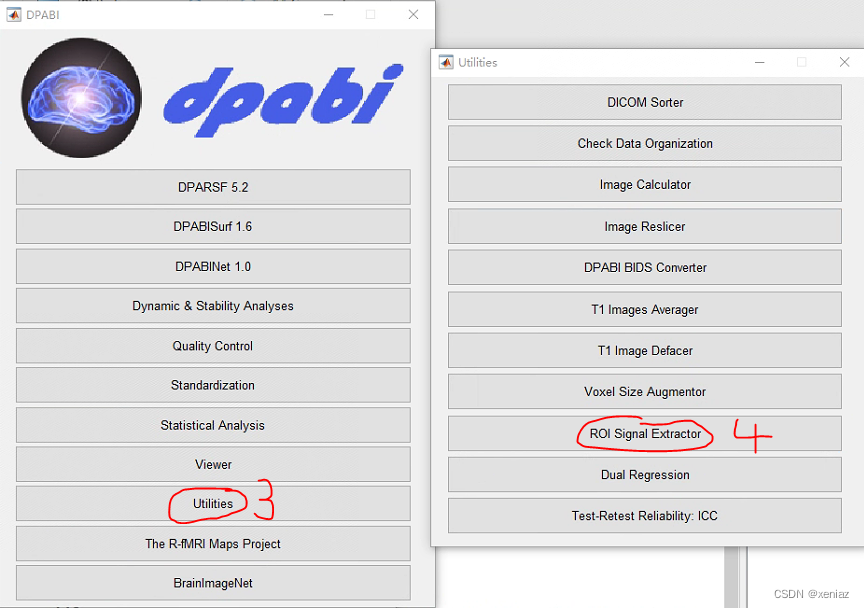
3、打开dpabi点击Utilities
4、在Utilities中点击ROI Signal Extractor
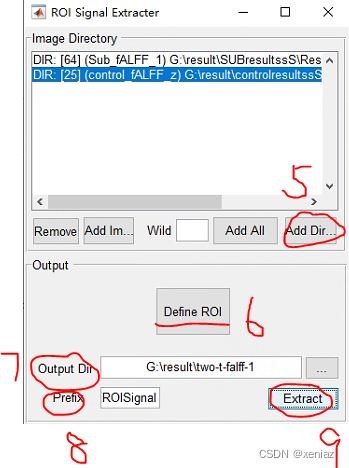
5、Add Dir: 选择处理后的nii图像所在文件夹
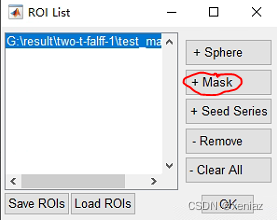
6、Define ROI: 点击Define ROI,点击+Mask,选择之前提值生成的Mask
7、Output Dir: 选择输出路径
8、Prefix: 选择输出名称
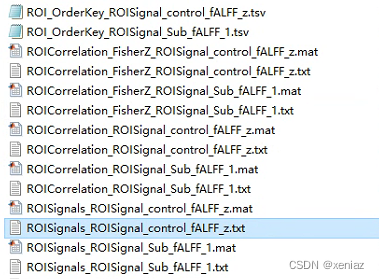
9、Extract: 运行生成如上文件,结合量表进一步进行分析








 本文详细介绍了如何在dpabiview中导入图像,进行多重比较矫正(基于Cluster的GRF),选择脑区模板,以及如何汇报和提值结果的过程。重点强调了FDR和Clusterpvalue的选择以及结果分析的步骤。
本文详细介绍了如何在dpabiview中导入图像,进行多重比较矫正(基于Cluster的GRF),选择脑区模板,以及如何汇报和提值结果的过程。重点强调了FDR和Clusterpvalue的选择以及结果分析的步骤。
















 3516
3516

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








