一 背景
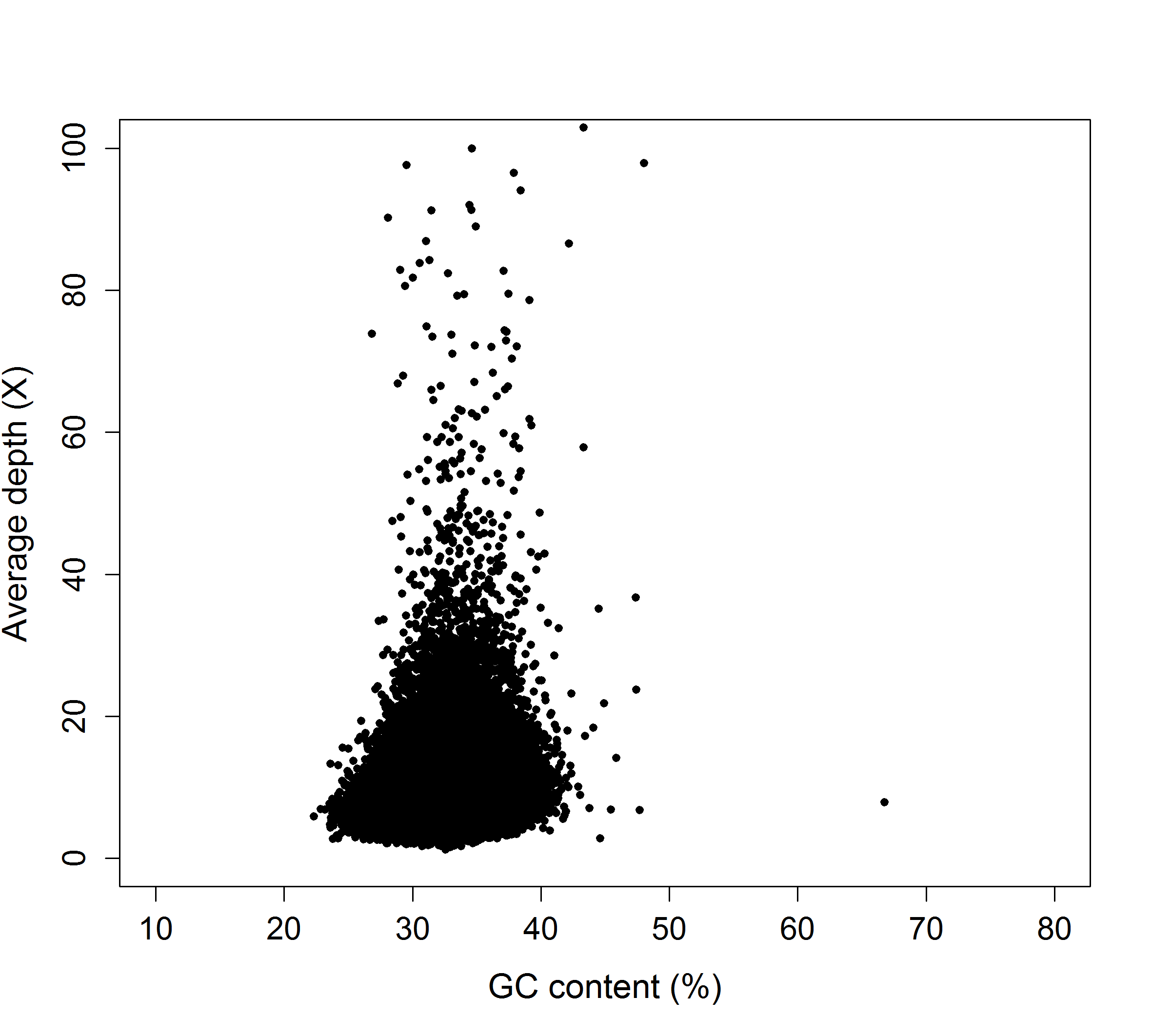
基因组组装完成后,需要对组装结果进行评估,其中GC_depth图是一个比较重要的指标。该图的横坐标是GC含量,纵坐标是平均深度。以30k为窗口(window)无overlap计算其GC含量和平均深度。如果存在样品污染,通常能够从GC含量分析中呈现出来。
下文探索了几种绘制GC_depth散点图的方法思路。
二 具体方法
2.1 直接生成散点图
由于数据点太多,且相互重合,弱化了想要传达给读者的重要信息。
df <- read.table("result.txt", header = TRUE)
png("GC_depth.png", width = 20, height = 18, units = "cm", res = 300)
plot(df, ylab="Average depth (X)", xlab="GC content (%)", cex.lab = 1.4, cex.axis = 1.3, pch = 20, ylim = c(0,100), xlim = c(10,80))
dev.off()2.2 通过透明度展示点密度
可能是点太多,调试了多次无法达到理想的效果。
df <- read.table("result.txt", header = TRUE)
MyGray <- rgb(t(col2rgb("black")), alpha=50, maxColorValue=255)
png("GC_depth_alpha.png", width = 20, height = 18, units = "cm", res = 300)
plot(df, ylab="Average depth (X)", xlab=<







 最低0.47元/天 解锁文章
最低0.47元/天 解锁文章















 4454
4454

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








