官方文档:
https://docs.ultralytics.com/yolov5/tutorials/hyperparameter_evolution/#1-initialize-hyperparameters
Hyperparameter evolution超参数演化是一种使用遗传算法(GA)进行优化的超参数优化方法。ML 中的超参数控制训练的各个方面,为它们找到最佳值可能是一个挑战。由于 1) 高维搜索空间 2) 维度之间的未知相关性,以及 3) 评估每个点的适应度的昂贵性质,网格搜索等传统方法很快就会变得难以处理,这使得 GA 成为超参数搜索的合适候选者。
以上是官方文档的介绍:Hyperparameter Evolution,其实简单的来说,就是使用遗传算法来对超参数已经交叉变异以获得更好的结果,而不需要传统的网格搜索。这个想法其实在之前yolov3-spp中也介绍过,对于anchor聚类结果使用遗传算法来获取更好的anchor设置,笔记见:使用kmeans与遗传算法聚类anchor
至此,在整个yolov5项目中,其实对遗传算法使用了在两个地方中,一个是对anchor进行变异优化;另外一个就是这篇笔记所介绍的,对超参数进行变异优化。
1. 遗传算法介绍
遗传算法是用于解决最优化问题的一种搜索算法。从名字来看,遗传算法借用了生物学里达尔文的进化理论:”适者生存,不适者淘汰“,将该理论以算法的形式表现出来就是遗传算法的过程。
问题引入
上面提到遗传算法是用来解决最优化问题的,下面我将以求二元函数:
def F(x, y):
return 3*(1-x)**2*np.exp(-(x**2)-(y+1)**2)- 10*(x/5 - x**3 - y**5)*np.exp(-x**2-y**2)- 1/3**np.exp(-(x+1)**2 - y**2)
在
x
∈
[
−
3
,
3
]
,
y
∈
[
−
3
,
3
]
x\in[-3, 3], y\in[-3, 3]
x∈[−3,3],y∈[−3,3]范围里的最大值为例子来详细讲解遗传算法的每一步。该函数的图像如下图:
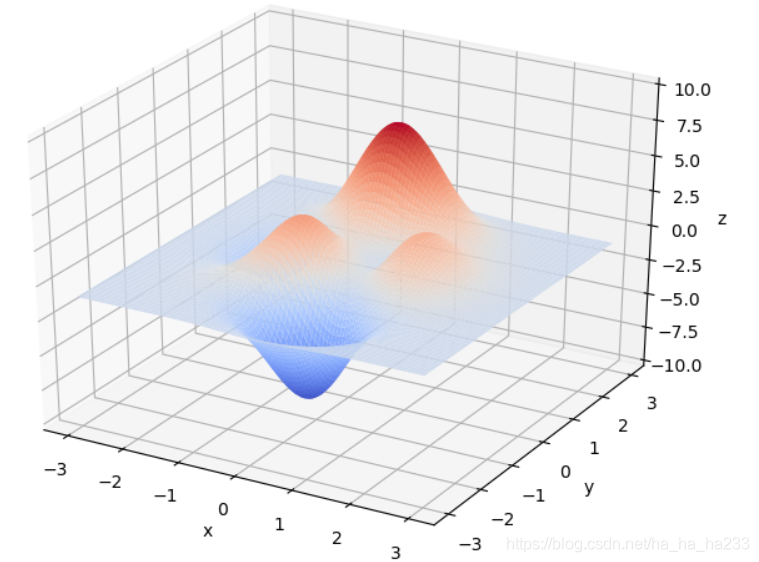
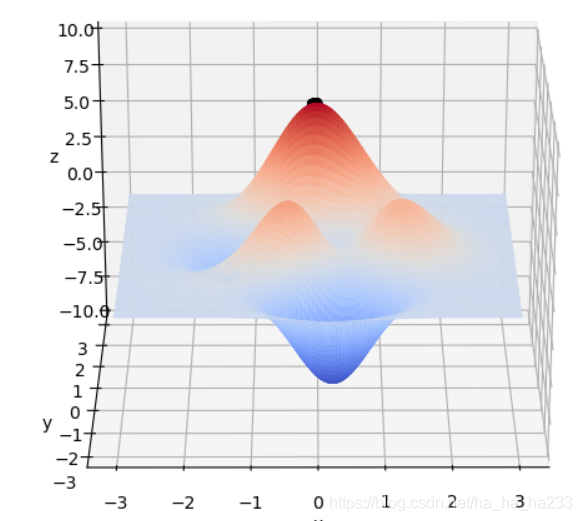
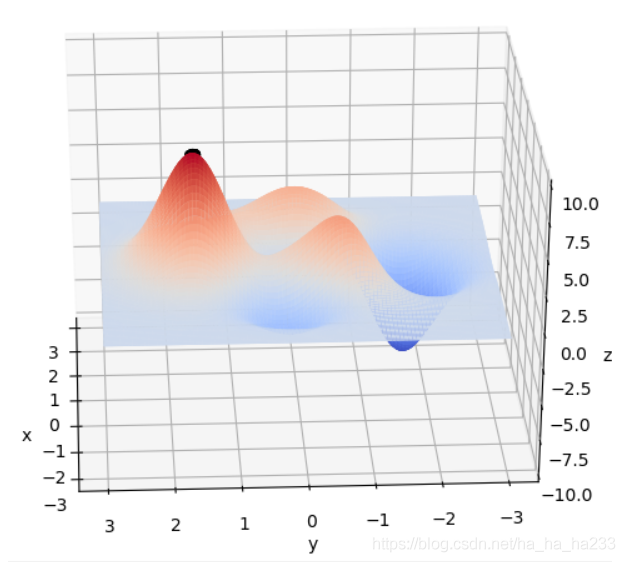
通过旋转视角可以发现,函数在这个局部的最大值大概在当
x
≈
0
,
y
≈
1.5
x \approx 0,y\approx1.5
x≈0,y≈1.5时,函数值取得最大值,这里的
x
,
y
x,y
x,y的取值就是我们最后要得到的结果。
算法详解
先直观看一下算法过程:
寻找最小值:
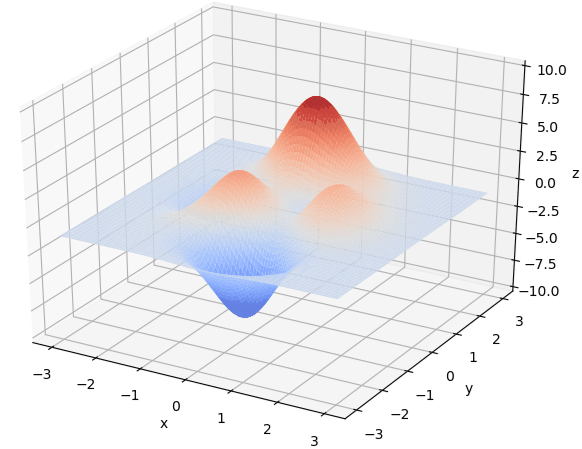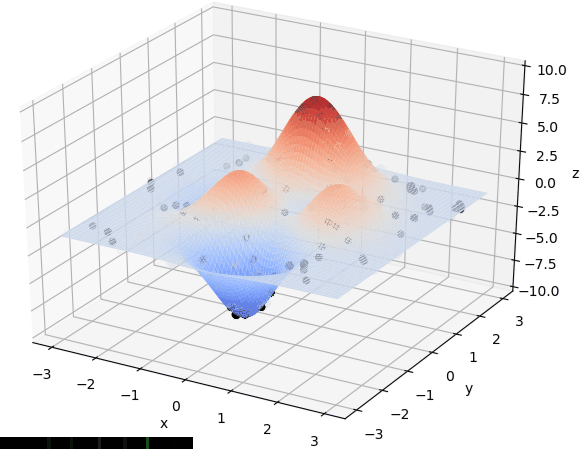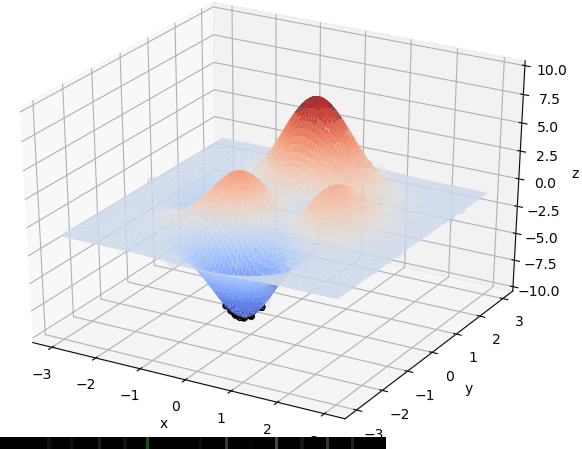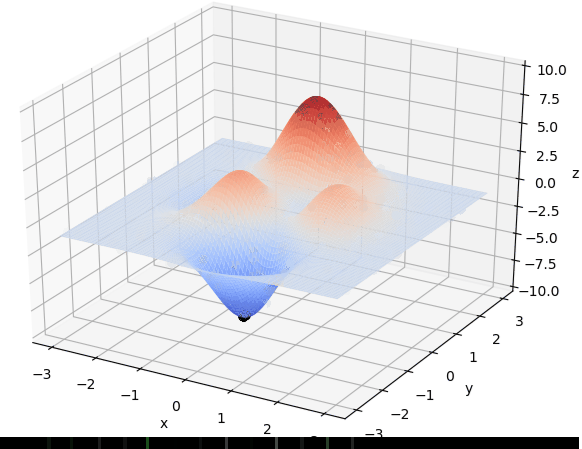
寻找最大值
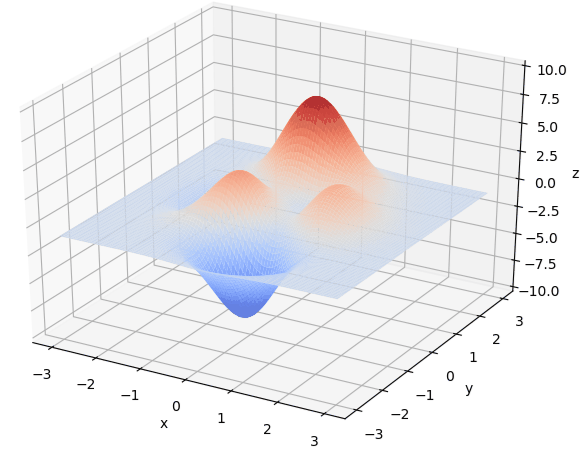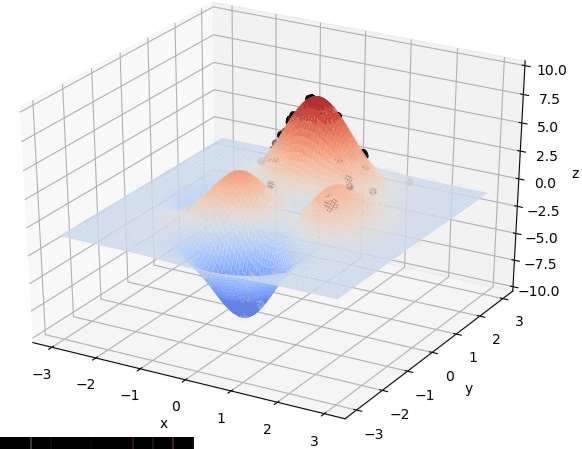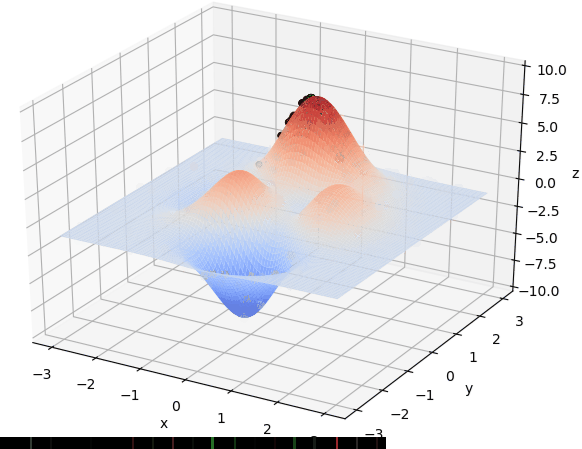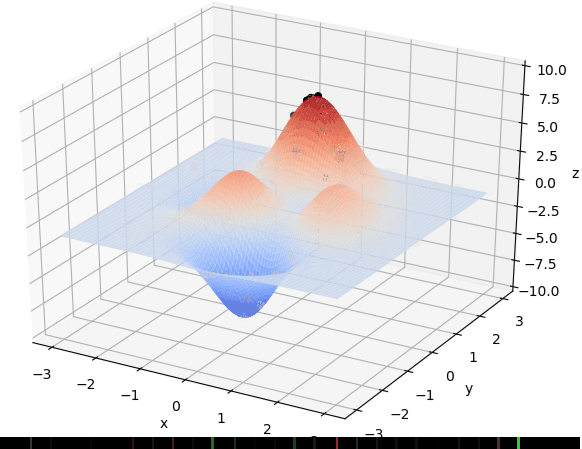
首先我们生成了200个随机的(x,y)对,将(x, y)坐标对带入要求解的函数F(x,y)中,根据适者生存,我们定义使得函数值F(x,y)越大的(x,y)对越适合环境,从而这些适应环境的(x,y)对更有可能被保留下来,而那些不适应该环境的(x,y)则有很大几率被淘汰,保留下来的点经过繁殖产生新的点,如此进化下去最后留下的大部分点都是试应环境的点,即在最高点附近。下图为算法执行结果,和上面的分析 x ≈ 0 , y ≈ 1.5 x \approx 0,y\approx1.5 x≈0,y≈1.5相近。
种群和个体的概念
遗传算法启发自进化理论,而我们知道进化是由种群为单位的,种群是什么呢?维基百科上解释为:在生物学上,是在一定空间范围内同时生活着的同种生物的全部个体。显然要想理解种群的概念,又先得理解个体的概念,在遗传算法里,个体通常为某个问题的一个解,并且该解在计算机中被编码为一个向量表示! 我们的例子中要求最大值,所以该问题的解为一组可能的(x, y)的取值。比如 ( x = 2.1 , y = 0.8 ) , ( x = − 1.5 , y = 2.3 ) . . . (x=2.1,y=0.8), (x=-1.5, y=2.3)... (x=2.1,y=0.8),(x=−1.5,y=2.3)...就是求最大值问题的一个可能解,也就是遗传算法里的个体,把这样的一组一组的可能解的集合就叫做种群 ,比如在这个问题中设置100个这样的x,y 的可能的取值对,这100个个体就构成了种群。
编码、解码与染色体的概念
在上面个体概念里提到个体(也就是一组可能解)在计算机程序中被编码为一个向量表示,而在我们这个问题中,个体是 x , y x,y x,y的取值,是两个实数,所以问题就可以转化为如何将实数编码为一个向量表示,可能有些朋友有疑惑,实数在计算机里不是可以直接存储吗,为什么需要编码呢?这里编码是为了后续操作(交叉和变异)的方便。实数如何编码为向量这个问题找了很多博客,写的都是很不清楚,看了莫烦python的教学代码,终于明白了一种实数编码、解码的方式。
生物的DNA有四种碱基对,分别是ACGT,DNA的编码可以看作是DNA上碱基对的不同排列,不同的排列使得基因的表现出来的性状也不同(如单眼皮双眼皮)。在计算机中,我们可以模仿这种编码,但是碱基对的种类只有两种,分别是0,1。只要我们能够将不同的实数表示成不同的0,1二进制串表示就完成了编码,也就是说其实我们并不需要去了解一个实数对应的二进制具体是多少,我们只需要保证有一个映射
y
=
f
(
x
)
,
x
i
s
d
e
c
i
m
a
l
s
y
s
t
e
m
,
y
i
s
b
i
n
a
r
y
s
y
s
t
e
m
y=f(x), x \ is\ decimal \ system, y \ is \ binary\ system
y=f(x),x is decimal system,y is binary system
能够将十进制的数编码为二进制即可,至于这个映射是什么,其实可以不必关心。将个体(可能解)编码后的二进制串叫做染色体,染色体(或者有人叫DNA)就是个体(可能解)的二进制编码表示。为什么可以不必关心映射f(x) 呢?因为其实我们在程序中操纵的都是二进制串,而二进制串生成时可以随机生成,如:
#pop表示种群矩阵,一行表示一个二进制编码表示的DNA,矩阵的行数为种群数目,DNA_SIZE为编码长度,不理解乘2的看后文
pop = np.random.randint(2, size=(POP_SIZE, DNA_SIZE*2)) #matrix (POP_SIZE, DNA_SIZE*2)
实际上是没有需求需要将一个十进制数转化为一个二进制数,而在最后我们肯定要将编码后的二进制串转换为我们理解的十进制串,所以我们需要的是 y = f ( x ) y=f(x) y=f(x)的逆映射,也就是将二进制转化为十进制,这个过程叫做解码(很重要,感觉初学者不容易理解),理解了解码编码还难吗?先看具体的解码过程如下。
首先我们限制二进制串的长度为10(长度自己指定即可,越长精度越高),例如我们有一个二进制串(在程序中用数组存储即可)
[
0
,
1
,
0
,
1
,
1
,
1
,
0
,
1
,
0
,
1
]
[0,1,0,1,1,1,0,1,0,1]
[0,1,0,1,1,1,0,1,0,1]
,这个二进制串如何转化为实数呢?不要忘记我们的
x
,
y
∈
[
−
3
,
3
]
x,y\in[-3,3]
x,y∈[−3,3]这个限制,我们目标是求一个逆映射将这个二进制串映射到
x
,
y
∈
[
−
3
,
3
]
x,y\in[-3,3]
x,y∈[−3,3]即可,为了更一般化我们将x,y的取值范围用一个变量表示,在程序中可以用python语言写到:
X_BOUND = [-3, 3] #x取值范围
Y_BOUND = [-3, 3] #y取值范围
为将二进制串映射到指定范围,首先先将二进制串按权展开,将二进制数转化为十进制数,我们有 0 ∗ 2 9 + 1 ∗ 2 8 + 0 ∗ 2 7 + . . . + 0 ∗ 2 0 + 1 ∗ 2 0 = 373 0*2^9+1*2^8+0*2^7+...+0*2^0+1*2^0=373 0∗29+1∗28+0∗27+...+0∗20+1∗20=373 ,然后将转换后的实数压缩到[0,1]之间的一个小数, 373 / ( 2 10 − 1 ) ≈ 0.36461388074 373 / (2^{10}-1) \approx 0.36461388074 373/(210−1)≈0.36461388074通过以上这些步骤所有二进制串表示都可以转换为 [0,1]之间的小数,现在只需要将[0,1]区间内的数映射到我们要的区间即可。假设区间[0,1] 内的数称为num,转换在python语言中可以写成:
#X_BOUND,Y_BOUND是x,y的取值范围 X_BOUND = [-3, 3], Y_BOUND = [-3, 3],
x_ = num * (X_BOUND[1] - X_BOUND[0]) + X_BOUND[0] #映射为x范围内的数
y_ = num * (Y_BOUND[1] - Y_BOUND[0]) + Y_BOUND[0] #映射为y范围内的数
通过以上这些标记为蓝色的步骤我们完成了将一个二进制串映射到指定范围内的任务(解码)。

以下为解码过程的python代码:
这里我设置DNA_SIZE=24(一个实数DNA长度),两个实数x,y一共用48位二进制编码,我同时将x和y编码到同一个48位的二进制串里,每一个变量用24位表示,奇数24列为x的编码表示,偶数24列为y的编码表示。
def translateDNA(pop):#pop表示种群矩阵,一行表示一个二进制编码表示的DNA,矩阵的行数为种群数目
x_pop = pop[:,1::2]#奇数列表示X
y_pop = pop[:,::2] #偶数列表示y
#pop:(POP_SIZE,DNA_SIZE)*(DNA_SIZE,1) --> (POP_SIZE,1)完成解码
x = x_pop.dot(2**np.arange(DNA_SIZE)[::-1])/float(2**DNA_SIZE-1)*(X_BOUND[1]-X_BOUND[0])+X_BOUND[0]
y = y_pop.dot(2**np.arange(DNA_SIZE)[::-1])/float(2**DNA_SIZE-1)*(Y_BOUND[1]-Y_BOUND[0])+Y_BOUND[0]
return x,y
适应度和选择
我们已经得到了一个种群,现在要根据适者生存规则把优秀的个体保存下来,同时淘汰掉那些不适应环境的个体。现在摆在我们面前的问题是**如何评价一个个体对环境的适应度?*在我们的求最大值的问题中可以*直接用可能解(个体)对应的函数的函数值的大小来评估,这样可能解对应的函数值越大越有可能被保留下来,以求解上面定义的函数F的最大值为例,python代码如下:
def get_fitness(pop):
x,y = translateDNA(pop)
pred = F(x, y)
return (pred - np.min(pred)) + 1e-3 #减去最小的适应度是为了防止适应度出现负数,通过这一步fitness的范围为[0, np.max(pred)-np.min(pred)],最后在加上一个很小的数防止出现为0的适应度
pred是将可能解带入函数F中得到的预测值,因为后面的选择过程需要根据个体适应度确定每个个体被保留下来的概率,而概率不能是负值,所以减去预测中的最小值把适应度值的最小区间提升到从0开始,但是如果适应度为0,其对应的概率也为0,表示该个体不可能在选择中保留下来,这不符合算法思想,遗传算法不绝对否定谁也不绝对肯定谁,所以最后加上了一个很小的正数。
有了求最大值的适应度函数求最小值适应度函数也就容易了,python代码如下:
def get_fitness(pop):
x,y = translateDNA(pop)
pred = F(x, y)
return -(pred - np.max(pred)) + 1e-3
因为根据适者生存规则在求最小值问题上,函数值越小的可能解对应的适应度应该越大,同时适应度也不能为负值,先将适应度减去最大预测值,将适应度可能取值区间压缩为 [ n p . m i n ( p r e d ) − n p . m a x ( p r e d ) , 0 ] [np.min(pred)-np.max(pred), 0] [np.min(pred)−np.max(pred),0],然后添加个负号将适应度变为正数,同理为了不出现0,最后在加上一个很小的正数。
有了评估的适应度函数,下面可以根据适者生存法则将优秀者保留下来了。选择则是根据新个体的适应度进行,但同时不意味着完全以适应度高低为导向(选择top k个适应度最高的个体,容易陷入局部最优解),因为单纯选择适应度高的个体将可能导致算法快速收敛到局部最优解而非全局最优解,我们称之为早熟。作为折中,遗传算法依据原则:适应度越高,被选择的机会越高,而适应度低的,被选择的机会就低。 在python中可以写做:
def select(pop, fitness): # nature selection wrt pop's fitness
idx = np.random.choice(np.arange(POP_SIZE), size=POP_SIZE, replace=True,
p=(fitness)/(fitness.sum()) )
return pop[idx]
不熟悉numpy的朋友可以查阅一下这个函数,主要是使用了choice里的最后一个参数p,参数p描述了从np.arange(POP_SIZE)里选择每一个元素的概率,概率越高约有可能被选中,最后返回被选中的个体即可。
交叉、变异
通过选择我们得到了当前看来“还不错的基因”,但是这并不是最好的基因,我们需要通过繁殖后代(包含有交叉+变异过程)来产生比当前更好的基因,但是繁殖后代并不能保证每个后代个体的基因都比上一代优秀,这时需要继续通过选择过程来让试应环境的个体保留下来,从而完成进化,不断迭代上面这个过程种群中的个体就会一步一步地进化。
具体地繁殖后代过程包括交叉和变异两步。交叉是指每一个个体是由父亲和母亲两个个体繁殖产生,子代个体的DNA(二进制串)获得了一半父亲的DNA,一半母亲的DNA,但是这里的一半并不是真正的一半,这个位置叫做交配点,是随机产生的,可以是染色体的任意位置。通过交叉子代获得了一半来自父亲一半来自母亲的DNA,但是子代自身可能发生变异,使得其DNA即不来自父亲,也不来自母亲,在某个位置上发生随机改变,通常就是改变DNA的一个二进制位(0变到1,或者1变到0)。
需要说明的是交叉和变异不是必然发生,而是有一定概率发生。先考虑交叉,最坏情况,交叉产生的子代的DNA都比父代要差(这样算法有可能朝着优化的反方向进行,不收敛),如果交叉是有一定概率不发生,那么就能保证子代有一部分基因和当前这一代基因水平一样;而变异本质上是让算法跳出局部最优解,如果变异时常发生,或发生概率太大,那么算法到了最优解时还会不稳定。交叉概率,范围一般是0.6~1,突变常数(又称为变异概率),通常是0.1或者更小。
python实现如下:
def crossover_and_mutation(pop, CROSSOVER_RATE = 0.8):
new_pop = []
for father in pop: #遍历种群中的每一个个体,将该个体作为父亲
child = father #孩子先得到父亲的全部基因(这里我把一串二进制串的那些0,1称为基因)
if np.random.rand() < CROSSOVER_RATE: #产生子代时不是必然发生交叉,而是以一定的概率发生交叉
mother = pop[np.random.randint(POP_SIZE)] #再种群中选择另一个个体,并将该个体作为母亲
cross_points = np.random.randint(low=0, high=DNA_SIZE*2) #随机产生交叉的点
child[cross_points:] = mother[cross_points:] #孩子得到位于交叉点后的母亲的基因
mutation(child) #每个后代有一定的机率发生变异
new_pop.append(child)
return new_pop
def mutation(child, MUTATION_RATE=0.003):
if np.random.rand() < MUTATION_RATE: #以MUTATION_RATE的概率进行变异
mutate_point = np.random.randint(0, DNA_SIZE) #随机产生一个实数,代表要变异基因的位置
child[mutate_point] = child[mutate_point]^1 #将变异点的二进制为反转
上面这些步骤即为遗传算法的核心模块,将这些模块在主函数中迭代起来,让种群去进化
pop = np.random.randint(2, size=(POP_SIZE, DNA_SIZE*2)) #生成种群 matrix (POP_SIZE, DNA_SIZE)
for _ in range(N_GENERATIONS): #种群迭代进化N_GENERATIONS代
pop = np.array(crossover_and_mutation(pop, CROSSOVER_RATE)) #种群通过交叉变异产生后代
fitness = get_fitness(pop) #对种群中的每个个体进行评估
pop = select(pop, fitness) #选择生成新的种群
完整代码
import numpy as np
import matplotlib.pyplot as plt
from matplotlib import cm
from mpl_toolkits.mplot3d import Axes3D
DNA_SIZE = 24
POP_SIZE = 200
CROSSOVER_RATE = 0.8
MUTATION_RATE = 0.005
N_GENERATIONS = 50
X_BOUND = [-3, 3]
Y_BOUND = [-3, 3]
# 定义的一个优化问题
def F(x, y):
return 3 * (1 - x) ** 2 * np.exp(-(x ** 2) - (y + 1) ** 2) - 10 * (x / 5 - x ** 3 - y ** 5) * np.exp(
-x ** 2 - y ** 2) - 1 / 3 ** np.exp(-(x + 1) ** 2 - y ** 2)
# 绘制3D图像
def plot_3d(ax):
X = np.linspace(*X_BOUND, 100)
Y = np.linspace(*Y_BOUND, 100)
X, Y = np.meshgrid(X, Y)
Z = F(X, Y)
ax.plot_surface(X, Y, Z, rstride=1, cstride=1, cmap=cm.coolwarm)
ax.set_zlim(-10, 10)
ax.set_xlabel('x')
ax.set_ylabel('y')
ax.set_zlabel('z')
plt.pause(3)
plt.show()
# 解码过程
# 说明: 设置DNA_SIZE=24(一个实数DNA长度),两个实数x,y一共用48位二进制编码,我同时将x和y编码到同一个48位的二进制串里,每一个变量用24位表示
# 奇数24列为x的编码表示,偶数24列为y的编码表示
def translateDNA(pop): # pop表示种群矩阵,一行表示一个二进制编码表示的DNA,矩阵的行数为种群数目
x_pop = pop[:, 1::2] # 奇数列表示X
y_pop = pop[:, ::2] # 偶数列表示y
# pop:(POP_SIZE,DNA_SIZE)*(DNA_SIZE,1) --> (POP_SIZE,1)
x = x_pop.dot(2 ** np.arange(DNA_SIZE)[::-1]) / float(2 ** DNA_SIZE - 1) * (X_BOUND[1] - X_BOUND[0]) + X_BOUND[0]
y = y_pop.dot(2 ** np.arange(DNA_SIZE)[::-1]) / float(2 ** DNA_SIZE - 1) * (Y_BOUND[1] - Y_BOUND[0]) + Y_BOUND[0]
return x, y
# 交叉变异操作
# 说明: 交叉是指每一个个体是由父亲和母亲两个个体繁殖产生,子代个体的DNA(二进制串)获得了一半父亲的DNA,一半母亲的DNA.
# 但是这里的一半并不是真正的一半,这个位置叫做交配点,是随机产生的,可以是染色体的任意位置。通过交叉子代获得了一半来自父亲一半来自母亲的DNA
def crossover_and_mutation(pop, CROSSOVER_RATE=0.8):
new_pop = []
for father in pop: # 遍历种群中的每一个个体,将该个体作为父亲
child = father # 孩子先得到父亲的全部基因(这里我把一串二进制串的那些0,1称为基因)
if np.random.rand() < CROSSOVER_RATE: # 产生子代时不是必然发生交叉,而是以一定的概率发生交叉
mother = pop[np.random.randint(POP_SIZE)] # 再种群中选择另一个个体,并将该个体作为母亲
cross_points = np.random.randint(low=0, high=DNA_SIZE * 2) # 随机产生交叉的点
child[cross_points:] = mother[cross_points:] # 孩子得到位于交叉点后的母亲的基因
mutation(child) # 每个后代有一定的机率发生变异
new_pop.append(child)
return new_pop
# 变异操作
# 说明: 在交叉过程外,子代自身可能发生变异,使得其DNA即不来自父亲,也不来自母亲,在某个位置上发生随机改变
# 通常就是改变DNA的一个二进制位(0变到1,或者1变到0)
def mutation(child, MUTATION_RATE=0.003):
if np.random.rand() < MUTATION_RATE: # 以MUTATION_RATE的概率进行变异
mutate_point = np.random.randint(0, DNA_SIZE * 2) # 随机产生一个实数,代表要变异基因的位置
child[mutate_point] = child[mutate_point] ^ 1 # 将变异点的二进制为反转
# 适应度
# 说明: 求最大值的问题中可以直接用可能解(个体)对应的函数的函数值的大小来评估,这样可能解对应的函数值越大越有可能被保留下来
def get_fitness(pop):
x, y = translateDNA(pop) # 解码, 将二进制串映射到指定范围内(也就是区间[-3, 3])
# pred是将可能解带入函数F中得到的预测值,因为后面的选择过程需要根据个体适应度确定每个个体被保留下来的概率,而概率不能是负值,所以减去预测中的最小值把适应度值的最小区间提升到从0开始
# 但是如果适应度为0,其对应的概率也为0,表示该个体不可能在选择中保留下来,这不符合算法思想,遗传算法不绝对否定谁也不绝对肯定谁,所以最后加上了一个很小的正数。
pred = F(x, y)
return (pred - np.min(
pred)) + 1e-3 # 减去最小的适应度是为了防止适应度出现负数,通过这一步fitness的范围为[0, np.max(pred)-np.min(pred)],最后在加上一个很小的数防止出现为0的适应度
# 种群选择
# 说明: 选择则是根据新个体的适应度进行,但同时不意味着完全以适应度高低为导向(选择top k个适应度最高的个体,容易陷入局部最优解)
# 因为单纯选择适应度高的个体将可能导致算法快速收敛到局部最优解而非全局最优解,我们称之为早熟
# 作为折中,遗传算法依据原则:适应度越高,被选择的机会越高,而适应度低的,被选择的机会就低
def select(pop, fitness): # nature selection wrt pop's fitness
# 这里主要是使用了choice里的最后一个参数p,参数p描述了从np.arange(POP_SIZE)里选择每一个元素的概率,概率越高约有可能被选中
idx = np.random.choice(np.arange(POP_SIZE), size=POP_SIZE, replace=True,
p=(fitness) / (fitness.sum())) # 返回的是被选择种群的所以,这里可能是重复的索引
# 最后返回被选中的个体即可
return pop[idx]
# 打印相关信息
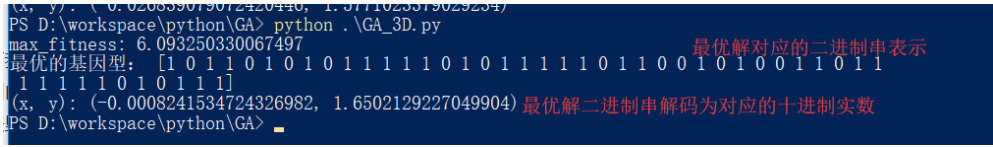
def print_info(pop):
fitness = get_fitness(pop)
max_fitness_index = np.argmax(fitness)
print("max_fitness:", fitness[max_fitness_index])
x, y = translateDNA(pop)
print("最优的基因型:", pop[max_fitness_index])
print("(x, y):", (x[max_fitness_index], y[max_fitness_index]))
if __name__ == "__main__":
fig = plt.figure()
ax = Axes3D(fig)
plt.ion() # 将画图模式改为交互模式,程序遇到plt.show不会暂停,而是继续执行
plot_3d(ax)
pop = np.random.randint(2, size=(POP_SIZE, DNA_SIZE * 2)) # matrix (POP_SIZE, DNA_SIZE)
for _ in range(N_GENERATIONS): # 迭代N代
x, y = translateDNA(pop)
if 'sca' in locals():
sca.remove()
sca = ax.scatter(x, y, F(x, y), c='black', marker='o');
plt.show();
plt.pause(0.1)
pop = np.array(crossover_and_mutation(pop, CROSSOVER_RATE))
# F_values = F(translateDNA(pop)[0], translateDNA(pop)[1])#x, y --> Z matrix
fitness = get_fitness(pop)
pop = select(pop, fitness) # 选择生成新的种群
print_info(pop)
plt.ioff()
plot_3d(ax)
plt.savefig("results.png")
以上为完整的代码,解码、适应度与选择、交叉变异这些步骤是遗传算法的核心模块,将这些模块在主函数中迭代起来,让种群去进化,核心的迭代代码如下所示:
# 随机生成种群 matrix (POP_SIZE, DNA_SIZE)
pop = np.random.randint(2, size=(POP_SIZE, DNA_SIZE*2))
for _ in range(N_GENERATIONS): # 种群迭代进化N_GENERATIONS代
crossover_and_mutation(pop, CROSSOVER_RATE) # 种群通过交叉变异产生后代
fitness = get_fitness(pop) # 对种群中的每个个体进行评估
pop = select(pop, fitness) # 选择生成新的种群
后记:很多人评论最后最大适应度很小是不是没收敛,我说一下我的理解,请注意最大适应度和F(x,y)不等价,最大适应度小不能说明没有拟合,认真观察适应度咋算的,是F(x,y) - min(F(x,y)),这个值小,F(x,y)的最大值和最小值很接近,方差很小,反而可能是表明收敛了
2. 遗传算法进化超参数
yolov5中包含差不多30个超参数来对训练过程进行设置,如此多的超参数如果使用网格搜索来获得最佳结果是比较困难的,所以这里作者使用了遗传算法来求出一个局部最优解——获得较好的超参数结果。
2.1 实现思路
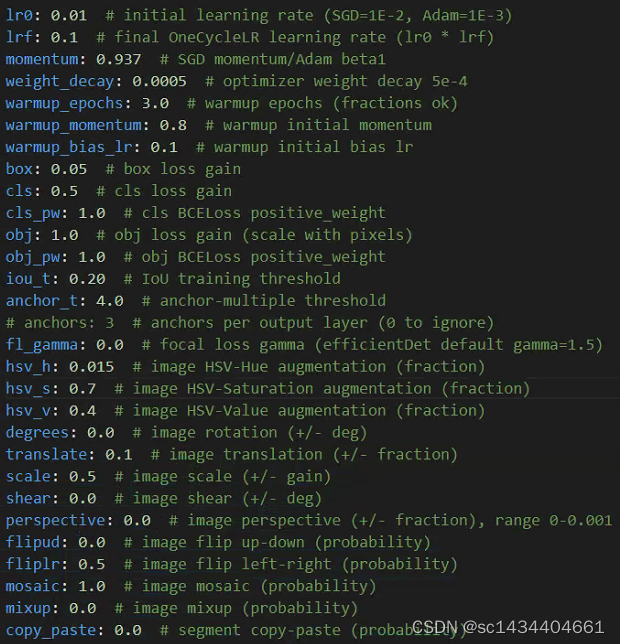
这里一般用对COCO训练的默认超参数作为初始(演化前)的超参数:hyp.scratch.yaml,其内容如下所示:
# YOLOv5 🚀 by Ultralytics, GPL-3.0 license
# Hyperparameters for COCO training from scratch
# python train.py --batch 40 --cfg yolov5m.yaml --weights '' --data coco.yaml --img 640 --epochs 300
# See tutorials for hyperparameter evolution https://github.com/ultralytics/yolov5#tutorials
lr0: 0.01 # initial learning rate (SGD=1E-2, Adam=1E-3) 基础/初始学习率
lrf: 0.01 # final OneCycleLR learning rate (lr0 * lrf) 学习率变化过程的变换最终收敛的权重值: 每次的更新学习率=lr0*c_lrf, c_lrf是从1.0->lrf的一个变化值
momentum: 0.937 # SGD momentum/Adam beta1 动量法的系数
weight_decay: 0.0005 # optimizer weight decay 5e-4 L2惩罚项系数
warmup_epochs: 3.0 # warmup epochs (fractions ok) 给定warmup操作的epoch的阈值
warmup_momentum: 0.8 # warmup initial momentum 给定warmup操作的动态法系数的初始值
warmup_bias_lr: 0.1 # warmup initial bias lr 进行warmup操作的时候的基础学习率(bias的基础学习率)
box: 0.05 # box loss gain 边框回归损失的加权系数
cls: 0.5 # cls loss gain 边框分类损失的加权系数
cls_pw: 1.0 # cls BCELoss positive_weight 给定类别判断损失中,正样本(属于这个类别)的权重,没有加权
obj: 1.0 # obj loss gain (scale with pixels) 边框是否有物体分类损失的加权系数
obj_pw: 1.0 # obj BCELoss positive_weight 给定是否有物体判断损失中,正样本(有物体)的权重
iou_t: 0.20 # IoU training threshold
anchor_t: 2.0 # 4.0 anchor-multiple threshold 自动计算anchor box时候的高度和宽度比例的阈值 为啥是4? --> 因为现在的推理的边框高宽转换公式为:(2*sigmoid(tw))**2 * Pw
# anchors: 3 # anchors per output layer (0 to ignore)
fl_gamma: 0.0 # focal loss gamma (efficientDet default gamma=1.5) 是否使用FocalLoss
hsv_h: 0.015 # image HSV-Hue augmentation (fraction) h增强的参数/范围
hsv_s: 0.7 # image HSV-Saturation augmentation (fraction) s增强的参数/范围
hsv_v: 0.4 # image HSV-Value augmentation (fraction) v增强的参数/范围
degrees: 10.0 # 0.0 image rotation (+/- deg) 图像旋转允许的角度大小
translate: 0.1 # image translation (+/- fraction) 图像允许的平移大小
scale: 0.5 # image scale (+/- gain) 图像允许的缩放大小
shear: 10.0 # 0.0 image shear (+/- deg) 图像的旋转剪切
perspective: 0.0 # 0.0 image perspective (+/- fraction), range 0-0.001 透视变换的超参数
flipud: 0.0 # image flip up-down (probability) 控制上下交换的阈值
fliplr: 0.5 # image flip left-right (probability) 控制左右交换的阈值
mosaic: 1.0 # image mosaic (probability) 控制mosaic数据增强的阈值
mixup: 0.0 # image mixup (probability) 控制mixup数据增强的阈值
copy_paste: 0.0 # segment copy-paste (probability) 是否基于mosaic之后的图像分割数据重新规划目标检测的labels信息 -- 概率阈值
可以看见,这一系列的超参数是控制训练过程中的一些参数设置,所以可以将其看成是一个自变量x。对这些超参数x进行训练会得到一个结果y,这个y返回了7个结果,分别是:'metrics/precision', 'metrics/recall', 'metrics/mAP_0.5', 'metrics/mAP_0.5:0.95', 'val/box_loss', 'val/obj_loss', 'val/cls_loss'
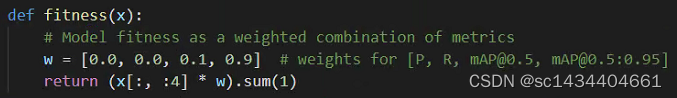
对于这个输入x需要判断其效果,也就是需要定义一个适应度fitness,这里定义的fitness是精确度R,召回率R,以及mAP_0.5与mAP_0.5:0.95的分数加权和,与Loss部分无关(当然可以自行改动这个fitness的定义),如下所示:
def fitness(x):
# Model fitness as a weighted combination of metrics
w = [0.0, 0.0, 0.1, 0.9] # weights for [P, R, mAP@0.5, mAP@0.5:0.95]
return (x[:, :4] * w).sum(1)
那么如果进行变异后的x,所返回的结果y,计算得到其适应度是比当前要高的,那么就说明当前的变异是对效果是提升的,变异后的参数是可取的。这里会默认会变异300次,然后每一次变异选择当前之前变异效果最好的前n个超参数x’来作为下一次的变异结果。
这里yolov5提供了两个不同进化方式获得base hyp
- single方式: 根据每个hyp的权重随机选择一个之前的hyp作为base hyp
- weighted方式: 根据每个hyp的权重对之前所有的hyp进行融合获得一个base hyp
根据前n次效果最好的超参数x来进行变异处理,获得下一个待输入的x’,依次反复迭代300次,变异300回来获得效果最好的x。
2.2 实现代码
yolov5实现代码参考如下:
def main(opt, callbacks=Callbacks()):
...
# Resume
if opt.resume and not check_wandb_resume(opt) and not opt.evolve: # resume an interrupted run
ckpt = opt.resume if isinstance(opt.resume, str) else get_latest_run() # specified or most recent path
assert os.path.isfile(ckpt), 'ERROR: --resume checkpoint does not exist'
with open(Path(ckpt).parent.parent / 'opt.yaml', errors='ignore') as f:
opt = argparse.Namespace(**yaml.safe_load(f)) # replace
opt.cfg, opt.weights, opt.resume = '', ckpt, True # reinstate
LOGGER.info(f'Resuming training from {ckpt}')
else:
opt.data, opt.cfg, opt.hyp, opt.weights, opt.project = \
check_file(opt.data), check_yaml(opt.cfg), check_yaml(opt.hyp), str(opt.weights), str(opt.project) # checks
assert len(opt.cfg) or len(opt.weights), 'either --cfg or --weights must be specified'
if opt.evolve:
opt.project = str(ROOT / 'runs/evolve')
opt.exist_ok, opt.resume = opt.resume, False # pass resume to exist_ok and disable resume
opt.save_dir = str(increment_path(Path(opt.project) / opt.name, exist_ok=opt.exist_ok))
...
# Train
if not opt.evolve:
train(opt.hyp, opt, device, callbacks)
if WORLD_SIZE > 1 and RANK == 0:
LOGGER.info('Destroying process group... ')
dist.destroy_process_group()
# Evolve hyperparameters (optional)
else:
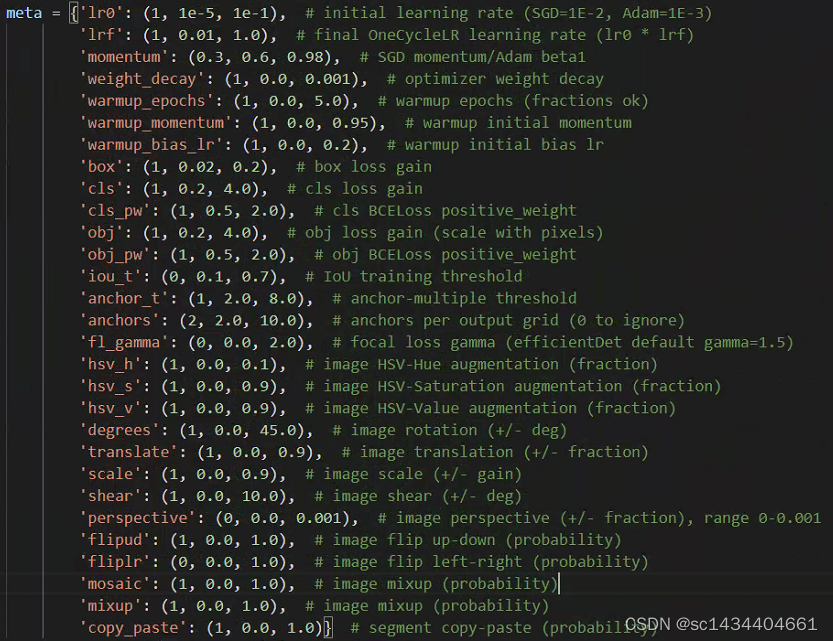
# Hyperparameter evolution metadata (mutation scale 0-1, lower_limit, upper_limit)
# 三个数值分别对应着: 变异初始概率, 最低限值, 最大限值
meta = {'lr0': (1, 1e-5, 1e-1), # initial learning rate (SGD=1E-2, Adam=1E-3)
'lrf': (1, 0.01, 1.0), # final OneCycleLR learning rate (lr0 * lrf)
'momentum': (0.3, 0.6, 0.98), # SGD momentum/Adam beta1
'weight_decay': (1, 0.0, 0.001), # optimizer weight decay
'warmup_epochs': (1, 0.0, 5.0), # warmup epochs (fractions ok)
'warmup_momentum': (1, 0.0, 0.95), # warmup initial momentum
'warmup_bias_lr': (1, 0.0, 0.2), # warmup initial bias lr
'box': (1, 0.02, 0.2), # box loss gain
'cls': (1, 0.2, 4.0), # cls loss gain
'cls_pw': (1, 0.5, 2.0), # cls BCELoss positive_weight
'obj': (1, 0.2, 4.0), # obj loss gain (scale with pixels)
'obj_pw': (1, 0.5, 2.0), # obj BCELoss positive_weight
'iou_t': (0, 0.1, 0.7), # IoU training threshold
'anchor_t': (1, 2.0, 8.0), # anchor-multiple threshold
'anchors': (2, 2.0, 10.0), # anchors per output grid (0 to ignore)
'fl_gamma': (0, 0.0, 2.0), # focal loss gamma (efficientDet default gamma=1.5)
'hsv_h': (1, 0.0, 0.1), # image HSV-Hue augmentation (fraction)
'hsv_s': (1, 0.0, 0.9), # image HSV-Saturation augmentation (fraction)
'hsv_v': (1, 0.0, 0.9), # image HSV-Value augmentation (fraction)
'degrees': (1, 0.0, 45.0), # image rotation (+/- deg)
'translate': (1, 0.0, 0.9), # image translation (+/- fraction)
'scale': (1, 0.0, 0.9), # image scale (+/- gain)
'shear': (1, 0.0, 10.0), # image shear (+/- deg)
'perspective': (0, 0.0, 0.001), # image perspective (+/- fraction), range 0-0.001
'flipud': (1, 0.0, 1.0), # image flip up-down (probability)
'fliplr': (0, 0.0, 1.0), # image flip left-right (probability)
'mosaic': (1, 0.0, 1.0), # image mixup (probability)
'mixup': (1, 0.0, 1.0), # image mixup (probability)
'copy_paste': (1, 0.0, 1.0)} # segment copy-paste (probability)
with open(opt.hyp, errors='ignore') as f:
hyp = yaml.safe_load(f) # load hyps dict
if 'anchors' not in hyp: # anchors commented in hyp.yaml
hyp['anchors'] = 3
opt.noval, opt.nosave, save_dir = True, True, Path(opt.save_dir) # only val/save final epoch
# ei = [isinstance(x, (int, float)) for x in hyp.values()] # evolvable indices
evolve_yaml, evolve_csv = save_dir / 'hyp_evolve.yaml', save_dir / 'evolve.csv'
if opt.bucket:
os.system(f'gsutil cp gs://{opt.bucket}/evolve.csv {save_dir}') # download evolve.csv if exists
# 默认迭代演化300次, 每次变异都需要训练一次要查看效果result, 所以计算量呈倍数递增
# 官方建议至少进行 300 代进化以获得最佳结果, 而基础场景被训练了数百次, 可能需要数百或数千个GPU小时
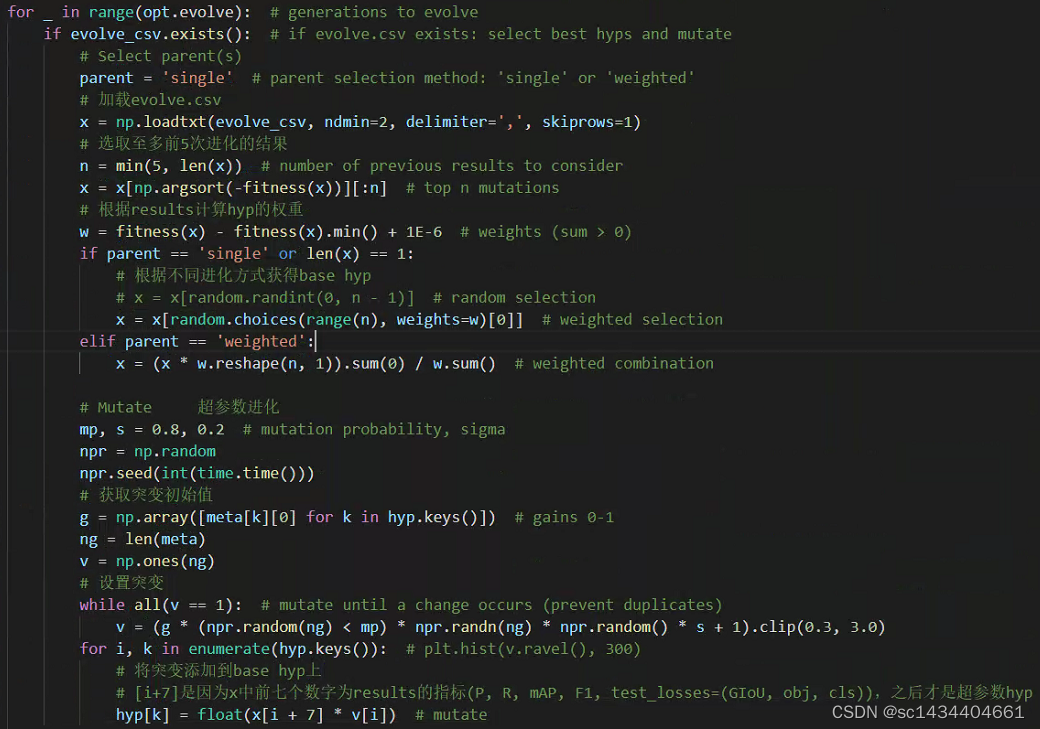
for _ in range(opt.evolve): # generations to evolve
if evolve_csv.exists(): # if evolve.csv exists: select best hyps and mutate
# Select parent(s):选择超参进化方式 只用single和weighted两种
parent = 'single' # parent selection method: 'single' or 'weighted'
# 加载evolve.csv文件, skiprows=1跳过第一行, delimiter加载文件分隔符
x = np.loadtxt(evolve_csv, ndmin=2, delimiter=',', skiprows=1)
# 最多选择5个最好的变异结果来挑选
n = min(5, len(x)) # number of previous results to consider
# np.argsort只能从小到大排序, 添加负号实现从大到小排序, 算是排序的一个代码技巧
# 挑选出适应度最好的前n个样本数据, 每个样本包含29个超参数变异结构{array:29}
x = x[np.argsort(-fitness(x))][:n] # top n mutations
# 根据(mp, mr, map50, map)的加权和来作为权重
w = fitness(x) - fitness(x).min() + 1E-6 # weights (sum > 0)
# 根据不同进化方式获得base hyp
# single方式: 根据每个hyp的权重随机选择一个之前的hyp作为base hyp
# weighted方式: 根据每个hyp的权重对之前所有的hyp进行融合获得一个base hyp
if parent == 'single' or len(x) == 1:
# 根据权重的几率随机挑选适应度历史前5的其中一个
# x = x[random.randint(0, n - 1)] # random selection
x = x[random.choices(range(n), weights=w)[0]] # weighted selection
elif parent == 'weighted':
# 对hyp乘上对应的权重融合层一个hpy, 再取平均(除以权重和)
x = (x * w.reshape(n, 1)).sum(0) / w.sum() # weighted combination
# Mutate 超参进化
mp, s = 0.8, 0.2 # mutation probability, sigma 设置突变概率与方差
npr = np.random
npr.seed(int(time.time()))
# 获取突变初始值, 也就是meta三个值的第一个数据
# 三个数值分别对应着: 变异初始概率, 最低限值, 最大限值(mutation scale 0-1, lower_limit, upper_limit)
g = np.array([meta[k][0] for k in hyp.keys()]) # gains 0-1
ng = len(meta)
v = np.ones(ng) # 确保至少其中有一个超参变异了
# 其实这里的v都是1附近的一个数值, 也就是对超参进行一个1附近微亮的变异
while all(v == 1): # mutate until a change occurs (prevent duplicates)
v = (g * (npr.random(ng) < mp) * npr.randn(ng) * npr.random() * s + 1).clip(0.3, 3.0)
for i, k in enumerate(hyp.keys()): # plt.hist(v.ravel(), 300)
# [i+7]是因为x中前7个数字为results的指标(P,R,mAP,F1,test_loss=(box,obj,cls)),之后才是超参数hyp
hyp[k] = float(x[i + 7] * v[i]) # mutate 超参变异
# Constrain to limits 限制超参范围
for k, v in meta.items():
hyp[k] = max(hyp[k], v[1]) # lower limit
hyp[k] = min(hyp[k], v[2]) # upper limit
hyp[k] = round(hyp[k], 5) # significant digits: 有效数字为5, 也就是留5个小数
# Train mutation: result{tuple 7}: mp, mr, map50, map, box, obj, cls
# 具体返回的是: 'metrics/precision', 'metrics/recall', 'metrics/mAP_0.5', 'metrics/mAP_0.5:0.95',
# 'val/box_loss', 'val/obj_loss', 'val/cls_loss'
results = train(hyp.copy(), opt, device, callbacks)
# Write mutation results
# 将每一代的演化结果与训练结果记录在evolve.csv文件中
print_mutation(results, hyp.copy(), save_dir, opt.bucket)
# Plot results
# 绘图: 每个超参数有一个子图, 显示适应度(y 轴)与超参数值(x 轴).黄色表示更高的浓度
plot_evolve(evolve_csv)
print(f'Hyperparameter evolution finished\n'
f"Results saved to {colorstr('bold', save_dir)}\n"
f'Use best hyperparameters example: $ python train.py --hyp {evolve_yaml}')
# 适应度的计算(用来挑选变异结果)
def fitness(x):
# Model fitness as a weighted combination of metrics
w = [0.0, 0.0, 0.1, 0.9] # weights for [P, R, mAP@0.5, mAP@0.5:0.95]
return (x[:, :4] * w).sum(1)
# 将每一代的演化结果与训练结果记录在evolve.csv文件中
def print_mutation(results, hyp, save_dir, bucket):
# keys/vals: (mp, mr, map50, map, box, obj, cls) + (lr0, lr1, ... , copy_paste, anchors)
evolve_csv, results_csv, evolve_yaml = save_dir / 'evolve.csv', save_dir / 'results.csv', save_dir / 'hyp_evolve.yaml'
keys = ('metrics/precision', 'metrics/recall', 'metrics/mAP_0.5', 'metrics/mAP_0.5:0.95',
'val/box_loss', 'val/obj_loss', 'val/cls_loss') + tuple(hyp.keys()) # [results + hyps]
keys = tuple(x.strip() for x in keys)
vals = results + tuple(hyp.values())
n = len(keys)
# Download (optional)
if bucket:
url = f'gs://{bucket}/evolve.csv'
if gsutil_getsize(url) > (os.path.getsize(evolve_csv) if os.path.exists(evolve_csv) else 0):
os.system(f'gsutil cp {url} {save_dir}') # download evolve.csv if larger than local
# Log to evolve.csv:记录当前代目的演化超参数数据与训练数据
s = '' if evolve_csv.exists() else (('%20s,' * n % keys).rstrip(',') + '\n') # add header
with open(evolve_csv, 'a') as f:
f.write(s + ('%20.5g,' * n % vals).rstrip(',') + '\n')
# Print to screen
print(colorstr('evolve: ') + ', '.join(f'{x.strip():>20s}' for x in keys))
print(colorstr('evolve: ') + ', '.join(f'{x:20.5g}' for x in vals), end='\n\n\n')
# Save yaml
with open(evolve_yaml, 'w') as f:
data = pd.read_csv(evolve_csv)
data = data.rename(columns=lambda x: x.strip()) # strip keys
# 根据曾经所有训练测试的结果: mp, mr, map50, map来计算适应度(fitness)
# 挑选出其中适应度最强的代目(其实就是根据mp, mr, map50, map的权重和分数, 越高适应度最强)
i = np.argmax(fitness(data.values[:, :7]))
# 将适应度最好的那一代的相关结果写在hyp_evolve.yaml文件的注释中
f.write('# YOLOv5 Hyperparameter Evolution Results\n' +
f'# Best generation: {i}\n' +
f'# Last generation: {len(data)}\n' +
'# ' + ', '.join(f'{x.strip():>20s}' for x in keys[:7]) + '\n' +
'# ' + ', '.join(f'{x:>20.5g}' for x in data.values[i, :7]) + '\n\n')
# 保存当前的演化超参数hpy在hyp_evolve.yaml文件
yaml.safe_dump(hyp, f, sort_keys=False)
if bucket:
os.system(f'gsutil cp {evolve_csv} {evolve_yaml} gs://{bucket}') # upload
具体过程见注释。
3. Hyperparameter Evolution使用
简单实现
使用方式其实很简单,就是设置一些evolve参数即可
python train.py --epochs 10 --data coco128.yaml --weights yolov5s.pt --cache --evolve
或者我对args进行了改动,使得可以设定迭代演化次数:
parser.add_argument('--evolve', type=int, default=300, help='evolve hyperparameters for x generations')
...
python train.py --epochs 10 --data coco128.yaml --weights yolov5s.pt --cache --evolve 10
Hyperparameter Evolution主要的遗传算子是交叉和变异。在这项工作中,使用突变,以 80% 的概率和 0.04 的方差基于所有前几代最好的父母的组合来创造新的后代。这里结果被记录到runs/evolve/exp/evolve.csv中,最高适应度的后代被保存为每一代runs/evolve/hyp_evolved.yaml
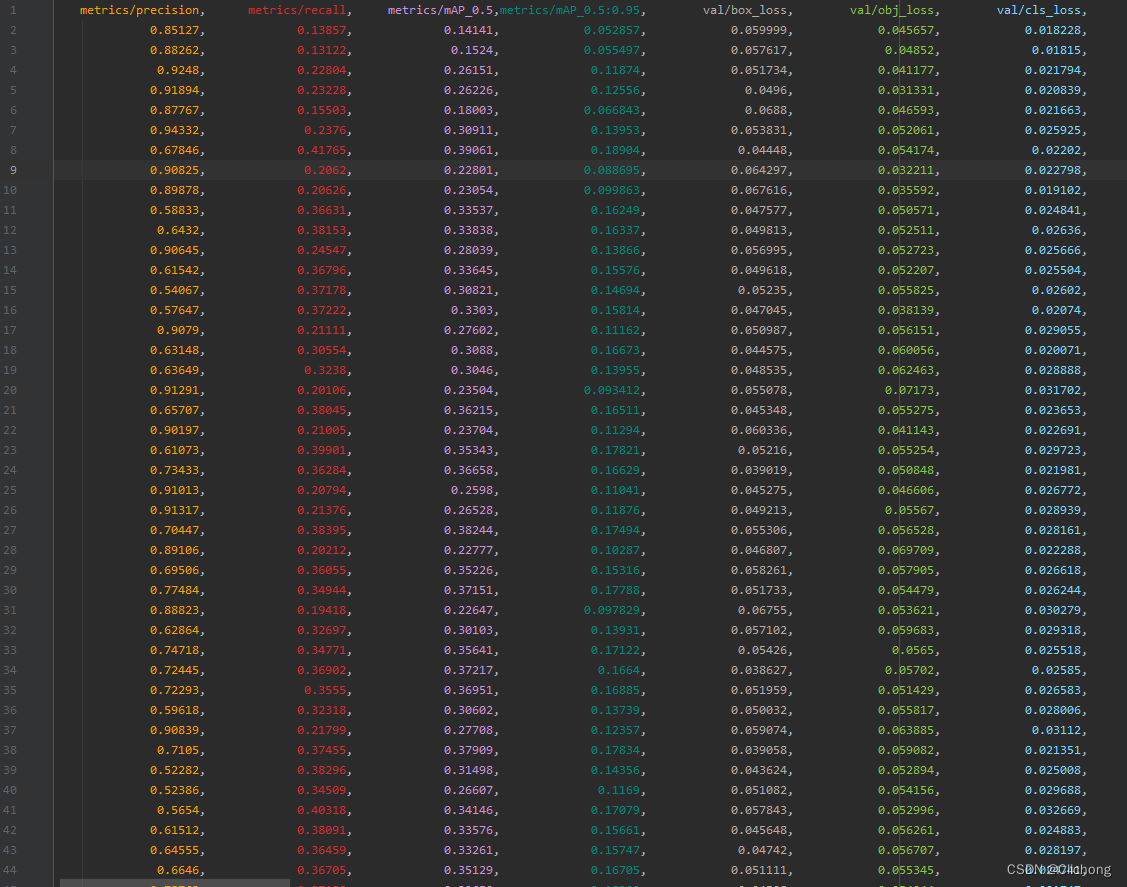
- evolve.csv展示:
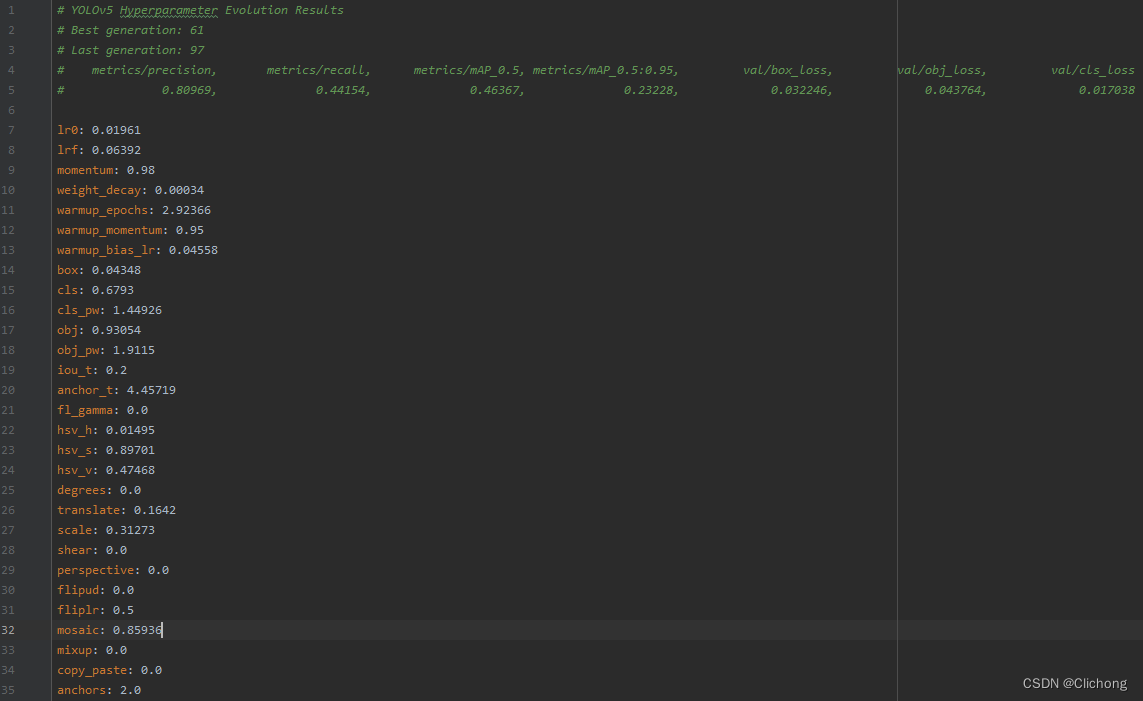
- hyp_evolved.yaml展示:
详细实现
YOLOv5(v6.1)解析(四)超参数进化
YOLOv5(v6.1)解析(四)超参数进化
本文对YOLOv5项目的超参数算法进行详细阐述,笔者以后会定期讲解关于模型的其他的模块与相关技术,笔者也建立了一个关于目标检测的交流群:781334731,欢迎大家踊跃加入,一起学习鸭!
1.项目地址
源码地址:https://github.com/ultralytics/yolov5
打开网址后,点击master可选取不同版本的分支,本文对Yolov5最新版本v6.1解析
2.环境搭建
在配置Conda环境后就可以进入项目了,可以通过作者提供的requirements.txt文件进行快速安装,即在终端中键入如下指令:pip install -r requirements.txt
3.代码运行
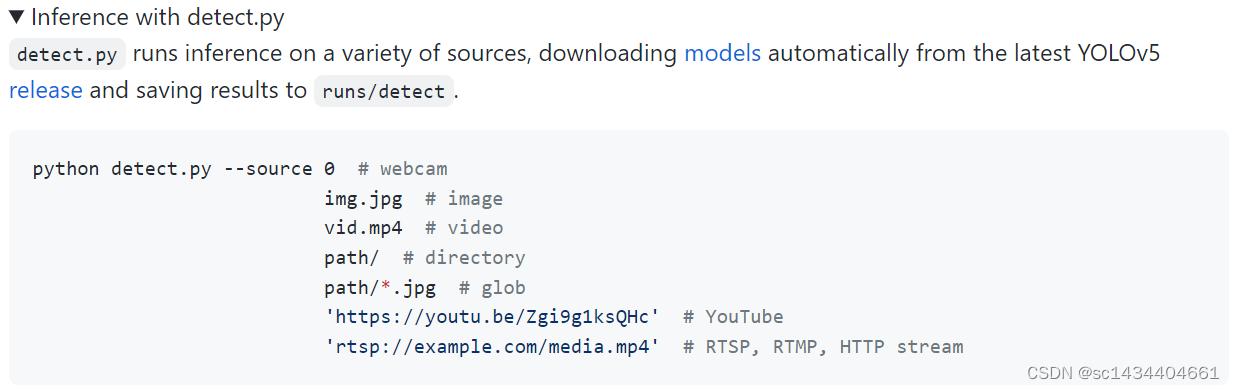
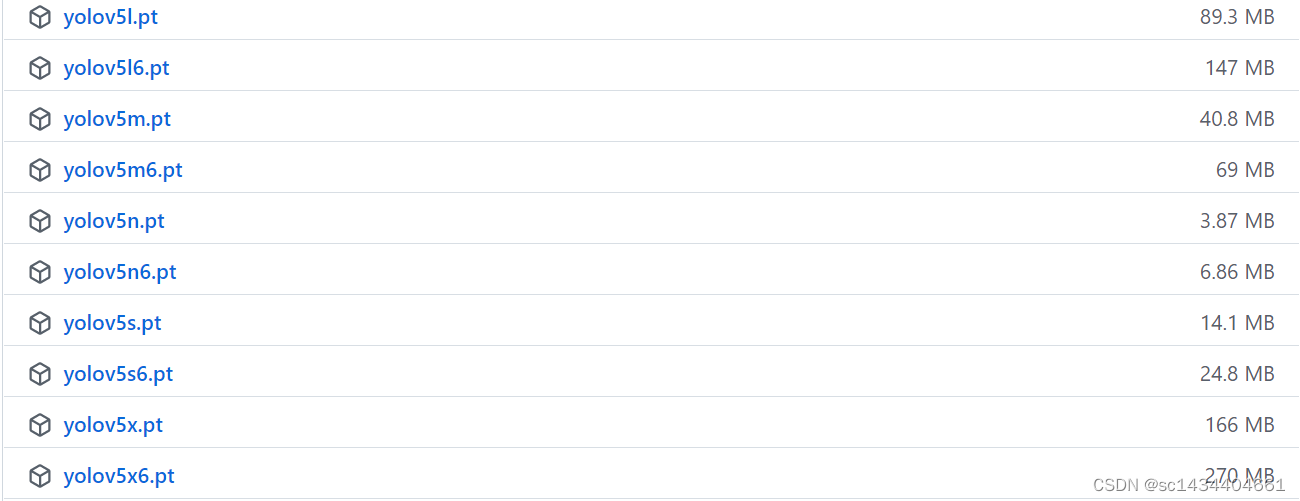
如上是官方给出的代码运行方式,我们可利用Yolov5模型预测图像、视频、摄像头、网站视频、RTSP流文件等,模型会自动下载权重文件(yolov5s.pt、yolov5m.pt、yolov5l.pt等),预测后的结果会自动保存到runs/detect/exp目录下,下次运行结果会保存在runs/detect/exp1目录下,依次类推;下图给出yolov5模型的权重和尺寸,更具体信息请参考:https://github.com/ultralytics/yolov5/releases
4.模型推理
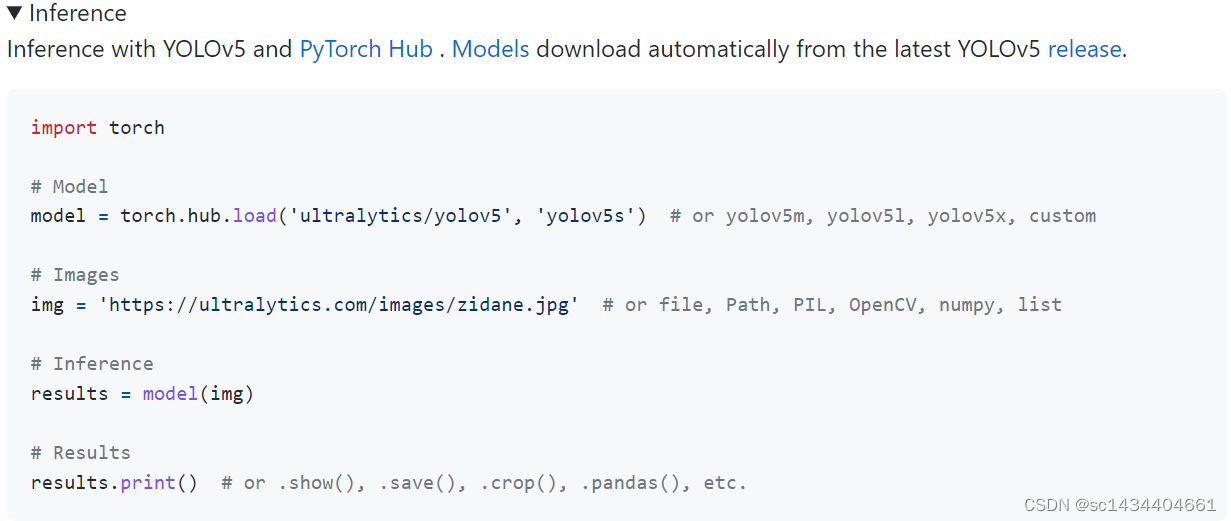
首先我们可以利用PyTorch Hub工具加载Yolov5模型(如果没下载,会自动下载模型权重到根目录下),之后加载需要检测的图片,最后利用封装好的模型推理检测结果,下图给出具体的实现步骤。
5. 检测结果
我们可以直接运行detect.py文件试试效果,运行后系统会把检测结果保存在runs\detect\exp3路径下(之前自己跑过试试)
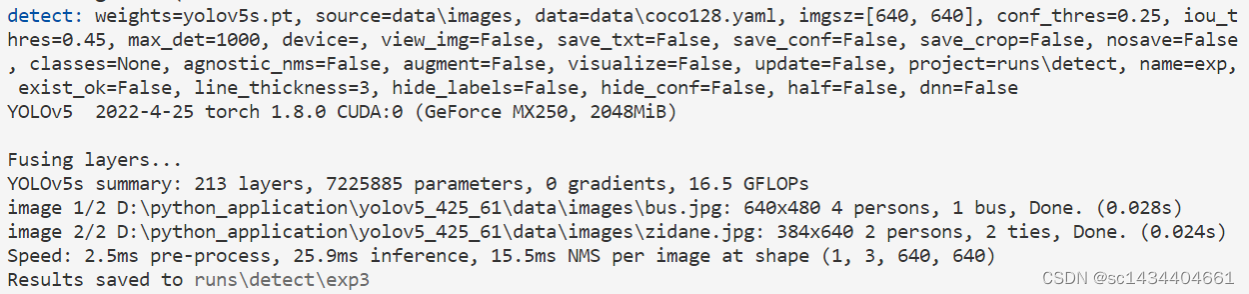
下图就是检测结果:

6. 超参数进化Hyperparameter Evolution
yolov5提供了一种超参数优化的方法Hyperparameter Evolution,即超参数进化;超参数进化是一种利用遗传算法(GA) 进行超参数优化的方法,我们可以通过该方法选择更加合适自己的超参数;模型提供的默认参数是通过在COCO数据集上使用超参数进化得来的(由于超参数进化会耗费大量的资源和时间,如果默认参数训练出来的结果能满足你的使用,使用默认参数也是不错的选择)
6.1 初始化超参数
YOLOv5有28个用于各种训练设置的超参数,它们定义在/data/hyps目录下的yaml文件中;好的初始参数值将产生更好的最终结果,因此在演进之前正确初始化这些值是很重要的;如果有不清楚怎么初始化,只需使用默认值,这些值是针对COCO训练优化得到的(如yolov5/data/hyps/hyp.scratch.yaml文件)
6.2 参考指标
在YOLOv5模型中,定义了一个fitness函数对各项指标进行加权得到当前拟合度
6.3 超参数进化
yolov5/train.py文件中的超参数进化列表,括号里分别为(突变规模, 最小值,最大值#pic_center)
超参数进化算法:
根据之前训练时的hyp来确定一个base hyp再进行突变,再通过之前每次进化得到的results来确定之前每个hyp的权重,得到每个hyp和每个hyp的权重之后有两种进化方式:
- 根据每个hyp的权重随机选择一个之前的hyp作为base hyp,random.choices(range(n), weights=w)
- 根据每个hyp的权重对之前所有的hyp进行融合获得一个base hyp,(x * w.reshape(n, 1)).sum(0) / w.sum()
evolve.txt会记录每次进化之后的results+hyp,每次进化时,hyp会根据之前的results进行从大到小的排序,再根据fitness函数计算之前每次进化得到的hyp的权重;再确定哪一种进化方式,从而进行进化
6.4 超参数进化实验
设置每75轮进化一次,epoch为300:python train.py --evolve 75 ;在进化之后可得到28个超参数的值
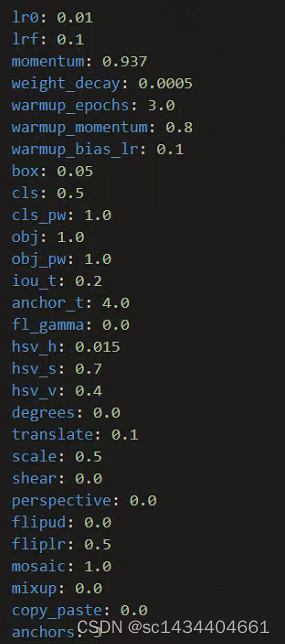
这些超参数的值也会保存在/runs/evolve/exp/hyp.evolve.yaml文件中(好像也没啥变化,一定是我数据集的问题。。。)
官方资料:https://github.com/ultralytics/yolov5/issues/607



























 6653
6653











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










