Plink常见命令
1) --bfie
输入的二进制Plink文件,由三个相互链接的文件组成,example.bim,example.bed、example.fam。
2)--freq
计算等位基因频率
3)--out
输出文件
4)--recode
将二进制文件转换为人类可读的文件集
plink --bfile hapmap-ceu --recode --out hapmap-ceu
(1) 输出过程
[外链图片转存失败,源站可能有防盗链机制,建议将图片保存下来直接上传(img-9xUIqyNI-1663504756125)(https://files.catbox.moe/hahq61.png)]
Warning: 59 het. haploid genotypes present (see hapmap-ceu.hh ); many commands treat these as missing.,一个warming,这通常与X染色体伪常染色体区域的雄性杂合子calling有关。建议是检查.hh文件中的变异,如果它们都靠近X染色体的开头或结尾,使用命令——split-x来解决这个问题。
慎用,用之后报错。
(2) 生成四个文件
- hapmap-ceu.map
- hapmap-ceu.ped
- hapmap-ceu.log
- hapmap-ceu.hh
5) --make-bed
将其他类型的数据转换成plink二进制文件。
例如,将vcf文件转换为二进制文件。
plink --vcf ALL.chr21.vcf.gz --make-bed --out test_vcf
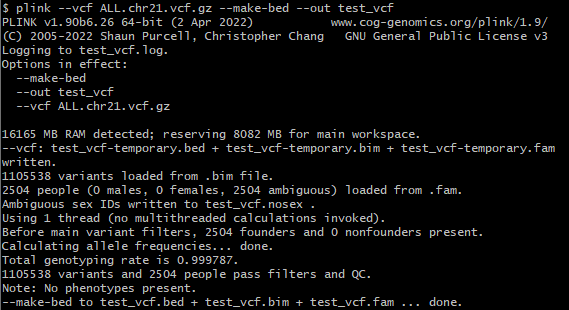
我们提供了一个命令列表用于从不同的软件导入数据
(1) Oxford格式(do not run this example)
plink --gen oxford_example.gen\
--sample oxford_example.sample\
--make-bed --out oxford_example
(2) Bgen (do not run this example)
plink --ben bgen_example \
--make-bed --out bgen_example
(3) 23andme(do not run this example)
plink --23fle 23andme_example \
--make-bed --out 23andme_example























 2万+
2万+











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










