一、哔哔两句
本来这篇文章没有报着去写的态度的,但是我遇见的这个bug目前国内还是搜索不出来,那就捯饬捯饬,做个记录吧。
二、上报错
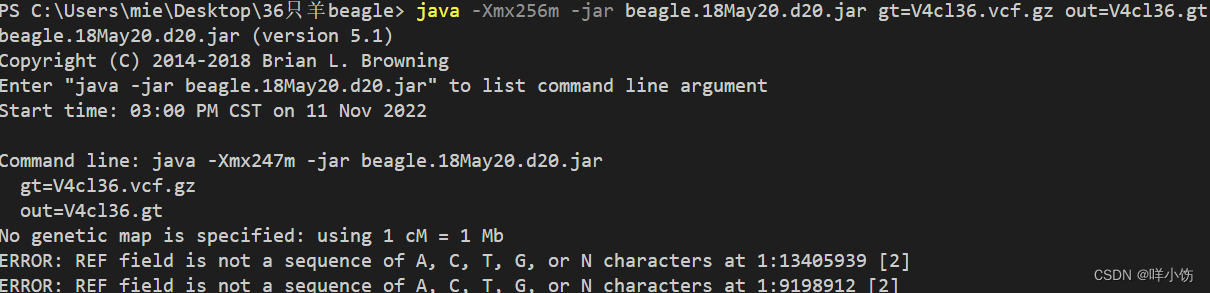
今天在做beagle时遇见了这么个问题。就是说除了ATCG变体意外还有其他的。那就。。。
删除呗。。。
三、解决过程
No genetic map is specified: using 1 cM = 1 Mb
ERROR: REF field is not a sequence of A, C, T, G, or N characters at 1:47721496 [1]
ERROR: REF field is not a sequence of A, C, T, G, or N characters at 1:16800804 [2]
ERROR: REF field is not a sequence of A, C, T, G, or N characters at 1:60911674 [2]
解决方案:
删除非 A、T、C、G 变体:
plink --bfile V4cl36 --list-duplicate-vars ids-only suppress-first
plink --bfile V4cl36 --alleleACGT --snps-only just-acgt --exclude plink.dupvar --make-bed --out V4cl36-acgt






















 8565
8565











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








