简介
多位点序列分型(multilocus sequence typing, MLST)是一种基于核酸序列测定的细菌分型方法。这种方法通过PCR扩增多个管家基因内部片段并测定其序列,分析菌株的变异。MLST操作简单,结果能快速得到并且便于不同实验室的比较,已经用于多种细菌的流行病学监测和进化研究。随着测序速度的加快和成本的降低,以及分析软件的发展,MLST逐渐成为细菌的常规分型方法。随着二代测序技术提供了快速、经济高效的细菌基因组测序方法,以及分析软件的发展,全基因组多位点序列分型(wgMLST)技术逐渐取代了传统的MLST Sanger测序技术。在wgMLST分型分析中考虑了更多的位点(通常为1500 – 4000),因此可以获得更高的分型分辨率。全基因组多位点序列分型被用于研究细菌的流行病学,群体生物学,致病性和进化等研究领域。
应用领域
- 在流行病学研究中揭示细菌毒力与基因型之间的关系。
- 追溯耐药菌株的来源和传播进程。
- 通过对管家基因序列特征分析,研究大量具有代表性的菌株的流行病学和进化特征,从而为阻止病原菌的传播提供依据。
分析流程
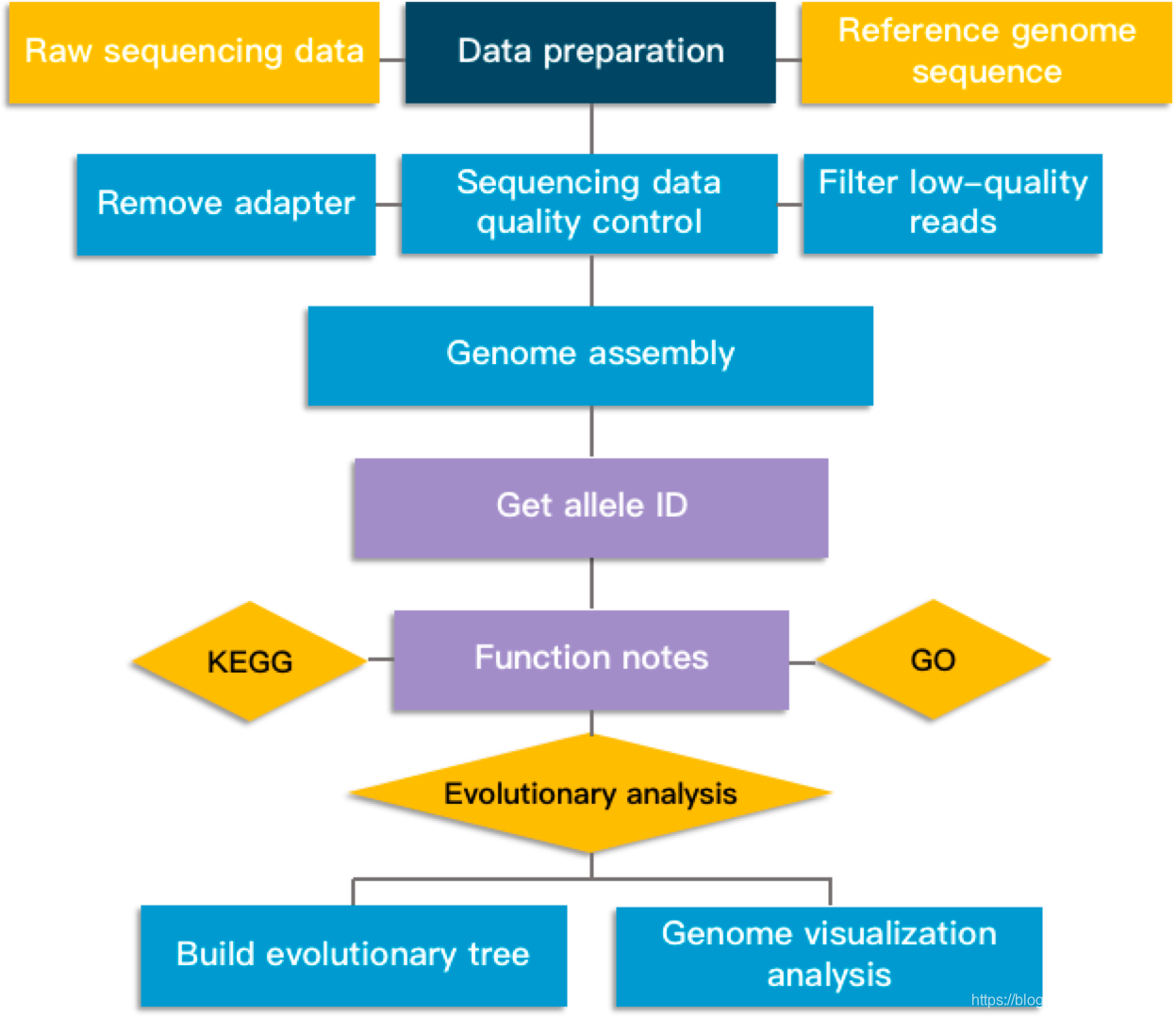
1.原始下机数据处理:此步骤过滤测序质量值低的reads,保留高质量reads,进行数据质控。
2.基因组组装:使用Velvet算法进行基因组组装,得到能反映样品基因组基本情况的序列文件,并对组装结果进行评价。
3.获取等位基因ID:基于Assemblybased和Assembly free两种算法对基因组内的基因位点进行等位基因ID号的获取。
4.功能注释:针对编码基因序列进行不同数据库的功能注释和致病及耐药分析等。
5.进化分析:利用wgMLST数据构建高分辨率物种分型结果,对传染病的爆发进行解释,分析目标菌种的群体结构和进化规律,为疾病预防和控制提供数据基础。
6.基因组可视化分析:结合基因组组分分析结果和功能注释结果,展示基因组的基础研究结果。
参考文献:
- 张少敏, 徐建国. 多位点序列分型及其应用[J]. 疾病监测, 2008, 23(010):648-650.




























 4155
4155

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










