公众号:生信漫谈,获取最新科研信息!
Seqlogo图用途很广,Chip-seq测序完后转录因子结合元件图、蛋白的单个motif图、启动子预测上游转录因子结合元件图等等,怎么快速绘制不求人,大家看下以下三种方法,总有一种你喜欢的!
R语言绘制
#代码如下
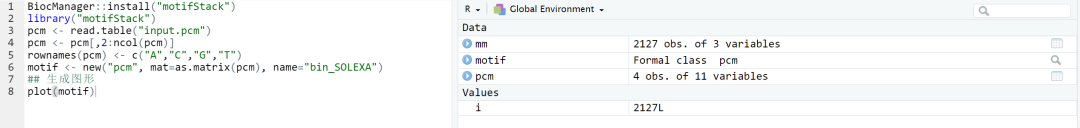
BiocManager::install("motifStack")
library("motifStack")
pcm <- read.table("input.pcm")
pcm <- pcm[,2:ncol(pcm)]
rownames(pcm) <- c("A","C","G","T")
motif <- new("pcm", mat=as.matrix(pcm), name="bin_SOLEXA")
## 生成图形
plot(motif)
其中input.pcm是配置文件,格式如下:
#格式如下,其中的数值代表出现的次数
A 0 1 16 1 0 0 0 0 16 0 0
C 0 0 0 0 0 0 16 16 0 0 0
G 0 8 0 15 0 0 0 0 0 16 16
T 16 7 0 0 16 16 0 0 0 0 0具体R语言中界面如下:
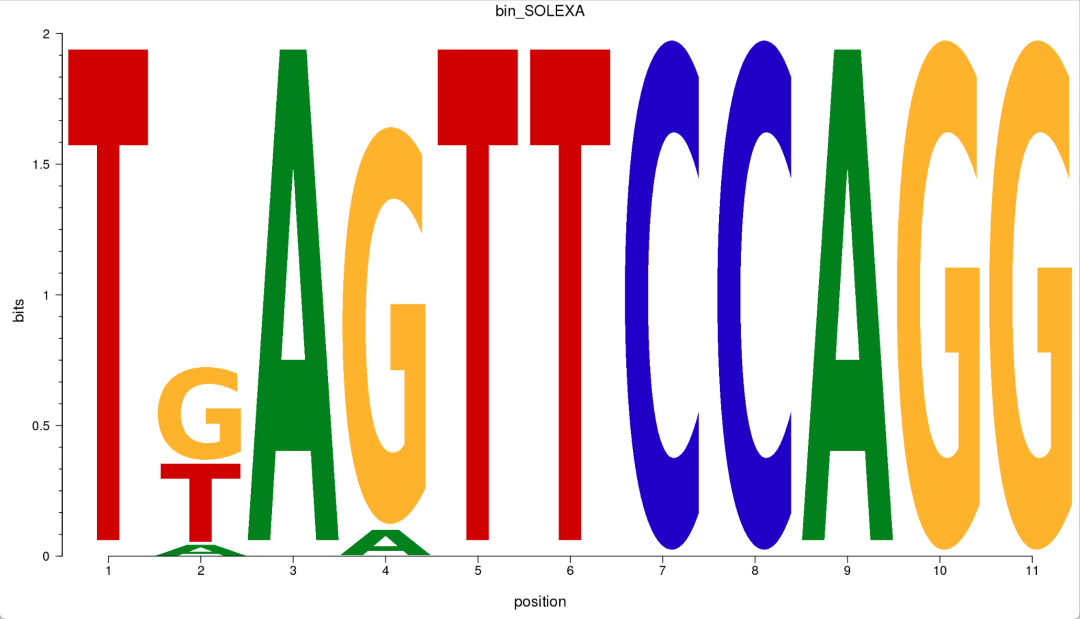
结果可以非常清晰的展示:
Weblogo
![]()
WebLogo是一个在线网站,其网站地址如下所示:
https://weblogo.threeplusone.com
打开网页如下图:
点击红色框框进行绘制图片:
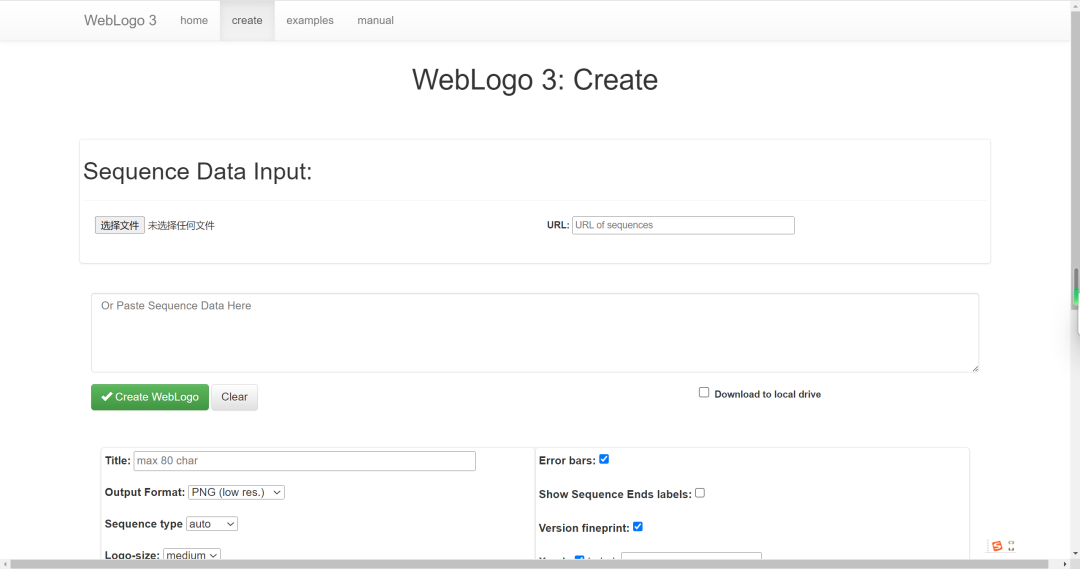
在中间的白色框内粘贴对齐的序列:
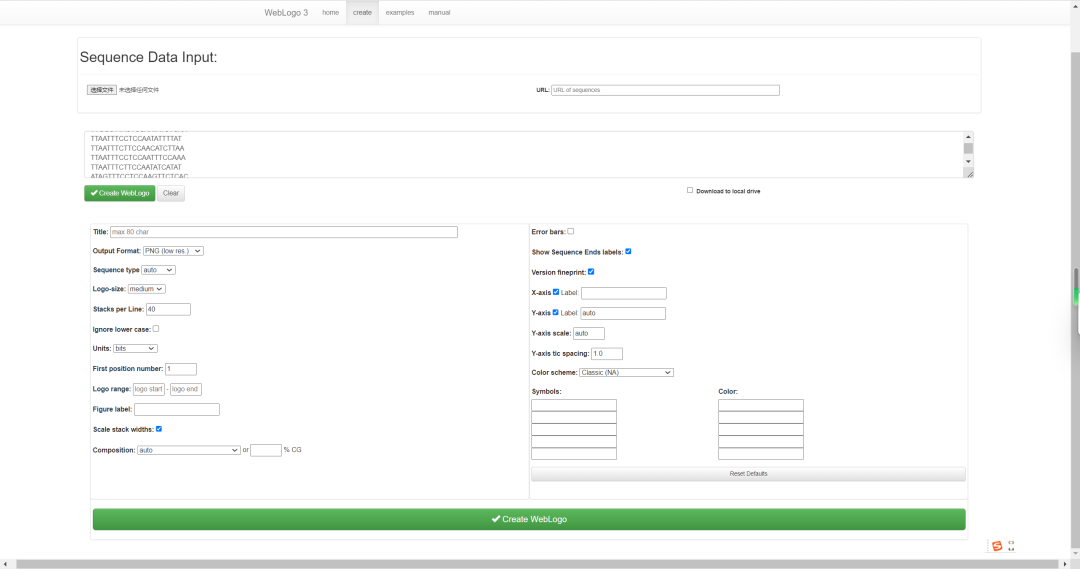
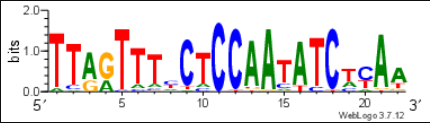
根据具体需要,创建Seqlog图:
Tbtools
![]()
相信好多小伙伴都知道tbtools工具了,它也有这个seqlogo图绘制功能,图片还非常不错,支持多种格式下载。
点击Seqlogo模块,输入如下序列,一定要是对齐的,没对齐记得先进行多序列比对对齐即可:
TTAATATTCCCCAATACCCCAG
TTGGTTTGCTCCAATATCTTAA
TTGGTTTGCTCCAATATCCCAT
TTGGTTTTCTCCAATATCACAA
ATAGTTTCATCCAATATCTTAA
TCAGTAAACTCCAAAATCTCAT
TTAGTCAACTCCAACATCTCAT
TTGGCTTACTCCAATATCTCAA
TTAATTTCCTCCAATATTTTAT
TTAATTTCTTCCAACATCTTAA
TTAATTTCCTCCAATTTCCAAA
TTAATTTCTTCCAATATCATAT
ATAGTTTCCTCCAAGTTCTCAC
TTAATCATCCCCAATATCTTAA
TTGGTTTTCTCCAATATCACAA
TTGGTTTTCTCCAATATCACAA
TTGGTTTTCTCCAATATCACAA
TTAATATTCCCCAATACCCCAG
TTAATTTTCTCCAATATCACAA
TAAGTTTCCTCCCATATCTCTA
TTAGTTTTCACCAATATCTCGA
TTGGTTTTCTCCAATATCACAA
TTGGTTTTCTCCAATATCACAA
TCAGTTTCCTCCGACTTCTTAA
TTAATTTCCTCCAATTTCCAAA
TTAGTTCACACCAATATCTTAT
TTAGTTCACACCAATATCTTAT
TTAGTTTCCTCCTACATCTCAA
TTAGTTGCCTCCAAAACCTTAA
TCAGTTTCCTCTAGCATCTAAG
得到图片也非常漂亮,基本可以直接使用了。
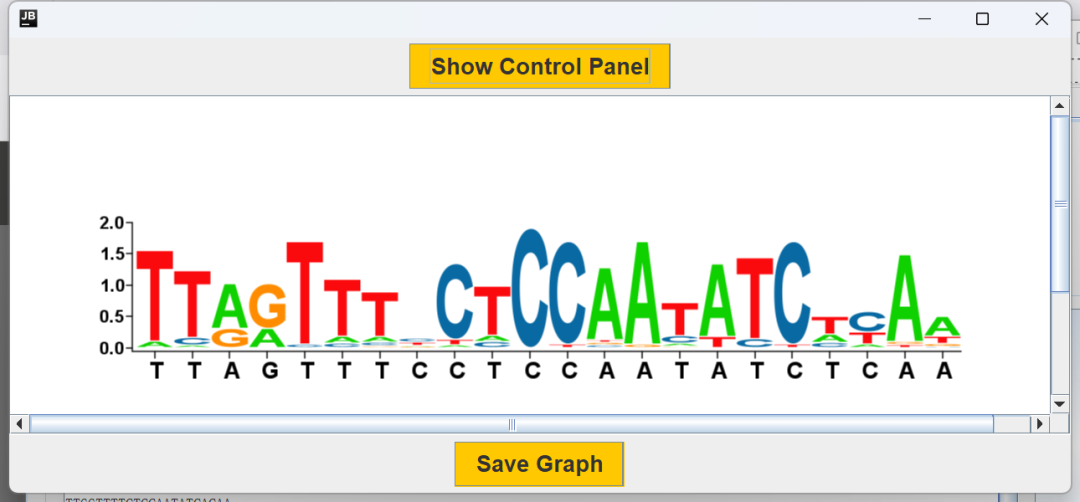
以上三种方法均是免费的,是不是get到了新知识了!
小伙伴们,是不是超级方便,导师再问你seqlogo图怎么绘制,再也不用傻傻的花钱找人绘制了吧!现在你应该知道绘制了吧,学会了吗?学会了不要忘了转发朋友圈,点赞点赞噢!
回顾往期内容
11、如果浙江大学李兰娟院士在MDPI杂志发表的SCI论文结果不能复现,会怎么样?
12、为什么浙江大学李兰娟院士选择在MDPI杂志发表SCI论文
13、施一公为什么没有推荐颜宁/柴继杰成院士候选人,李兰娟推荐了谁?
16、清华大学施一公团队为什么选择《International Journal of Molecular Sciences》发表SCI
17、西湖大学施一公团队在国际著名杂志IJMS发表重要论文给予我们的启示
18、可以在施一公团队投稿的《International Journal of Molecular Sciences》上发表文章吗?
通过以上步骤是否学会了呢?关注我们,学习更多生信干货,原创不易,请各位多多点赞加转发朋友圈进行分享!
今天就先给大家介绍到这里,希望大家的科研能有所帮助!祝您科研顺利快乐!

生信漫谈
生信漫谈,认识生信,学习生信,跨越生信入门路上的障碍,从而利用生信技术解决科研学习路上的绊脚石!






















 6001
6001

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








