使用SingleR自动进行细胞注释
软件下载和使用
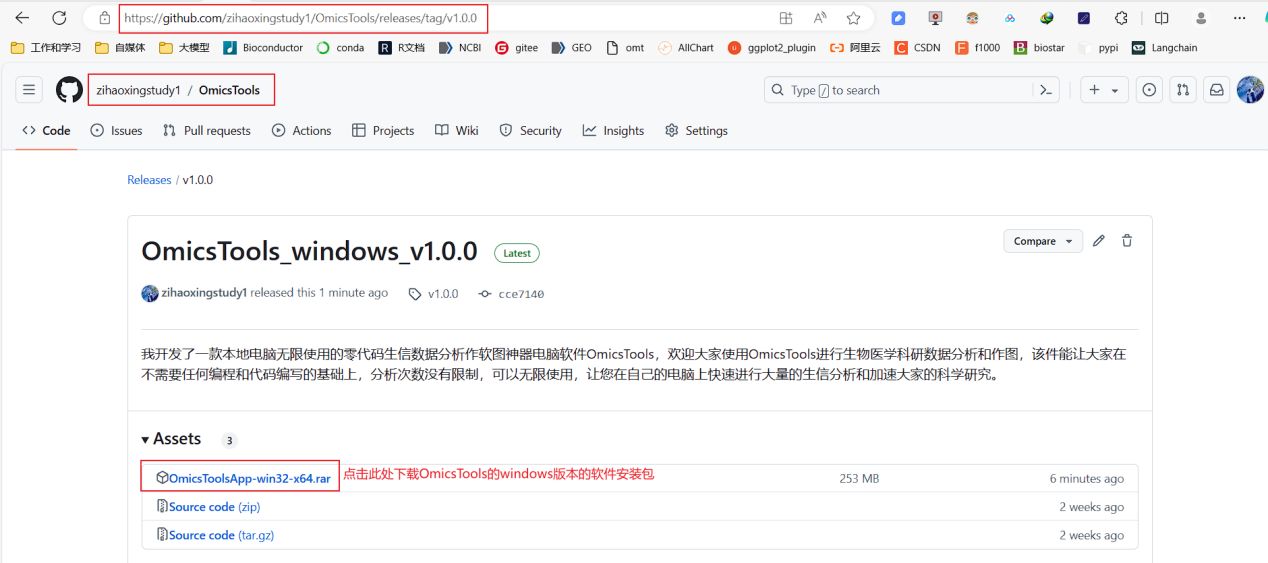
我开发了一款本地电脑无限使用的零代码生信数据分析作软图神器电脑软件OmicsTools,欢迎大家使用OmicsTools进行生物医学科研数据分析和作图,该软件件能让大家在不需要任何编程和代码编写的基础上,分析次数没有限制,可以无限使用,让您在自己的电脑上快速进行大量的生信分析和加速大家的科学研究。
我开发的本地电脑无限使用无限分析作图的生信零代码一键分析电脑软件神器OmicsTools 软件在github上的zihaoxingstudy1/OmicsTools仓库 中,大家可以下载安装OmicsTools进行各种生信分析和可视化作图。
软件下载官方网址: https://github.com/zihaoxingstudy1/OmicsTools ,大家可以下载安装OmicsTools进行各种生信分析和可视化作图。

参数解释:
func_ref__file: 参考数据集文件路径
func_save__file__prefix: 结果保存的文件名前缀
func_rare__cell__threshold: 设置低于阈值数量的细胞类型统一被命名为Rare Cells
nested_function: 是否嵌套函数
run_file_path: 前面缩放和PCA降维处理好后的结果文件
run_read_file: 是否要读取文件
run_add__res__dir: 是否要新建一个res_dir存储结果文件
run_add_save_file_prefix: 是否要添加结果保存文件的前缀
提交
参数的默认值
func_ref__file: D:/omics_tools/demo_data/human_primary_cell_atlas.rds ;
func_save__file__prefix:D:/omics_tools/demo_data/res_dir/renal_cancer/GSE159115/7.cell_anno/step7_cell_anno ;
func_rare__cell__threshold: 10 ;
nested_function: TRUE ;
run_file_path:D:/omics_tools/demo_data/res_dir/renal_cancer/GSE159115/4.scale_pca/step4_scale_pca_scrnaseq_after_scaled_runpca.rds ;
run_read_file: FALSE ;
run_add__res__dir: FALSE ;
run_add_save_file_prefix: FALSE
运行窗口展示

运行中的显示信息
执行中,请稍后, 运行结果保存的目录位置为: D:/omics_tools/demo_data/res_dir/renal_cancer/GSE159115/4.scale_pca; 分析结果日志保存的路径为: D:/omics_tools/demo_data/res_dir/renal_cancer/GSE159115/4.scale_pca\step4_scale_pca_scrnaseq_after_scaled_runpca_last_final_run_res_log.csv
运行完成显示信息
执行已完成,运行结果保存的目录位置为: D:/omics_tools/demo_data/res_dir/renal_cancer/GSE159115/4.scale_pca; 分析结果日志保存的路径为: D:/omics_tools/demo_data/res_dir/renal_cancer/GSE159115/4.scale_pca\step4_scale_pca_scrnaseq_after_scaled_runpca_last_final_run_res_log.csv
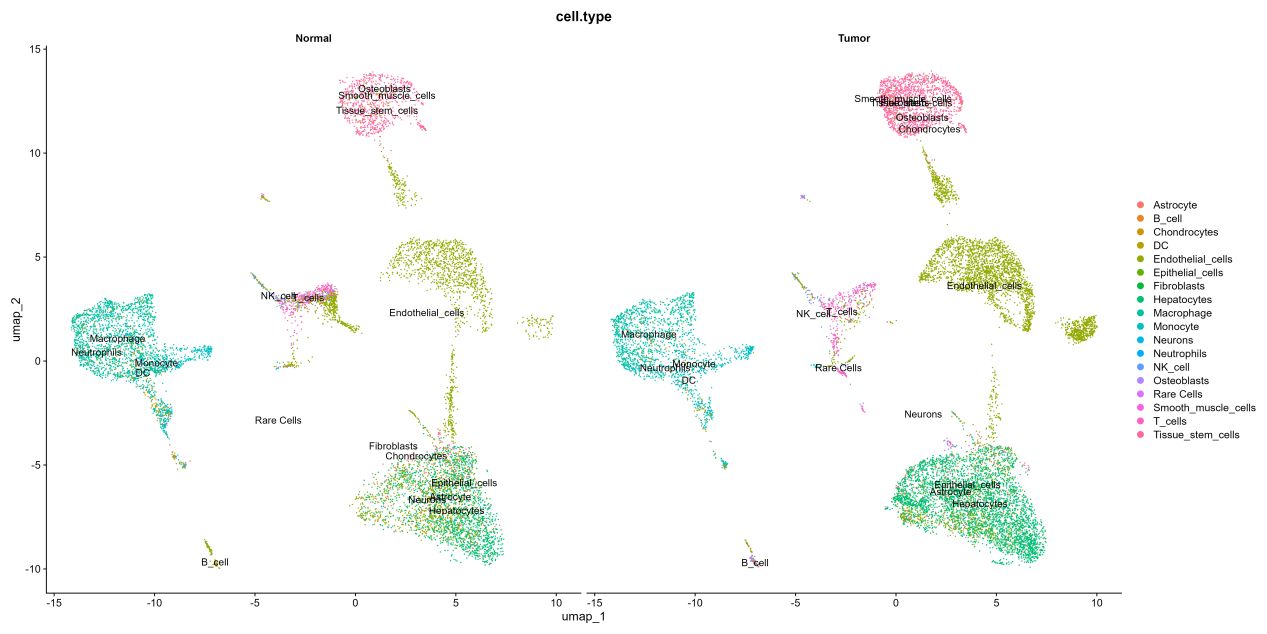
singleR自动注释运行完成的细胞注释聚类UMAP结果图

singleR自动注释运行完成的细胞注释聚类UMAP结果图
详细的视频教学教程讲解和运行参数及结果解读见下方的教学视频:
https://www.bilibili.com/video/BV1ex4y1Y71G/























 4981
4981











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










