💥💥💞💞欢迎来到本博客❤️❤️💥💥
🏆博主优势:🌞🌞🌞博客内容尽量做到思维缜密,逻辑清晰,为了方便读者。
⛳️座右铭:行百里者,半于九十。
📋📋📋本文目录如下:🎁🎁🎁
目录
💥1 概述
区间多目标优化算法(Interval Pareto-based Multi-Objective Evolutionary Algorithm, 简称IP-MOEA)是面向具有不确定性因素的多目标优化问题的一种进化算法。这种类型的算法旨在处理问题的解不是一个确定的值,而是一个区间,以此来表征解的不确定性。这种不确定性可能源于系统参数的测量误差、模型的简化或预测的不确定性等因素。IP-MOEA通过寻找一组解来逼近理想的Pareto前沿,这组解在考虑了不确定性因素后,仍能够尽量满足多个目标的优化。
IP-MOEA的核心特点和实现步骤通常包括:
1. **初始化**: 生成一个初始种群,种群中的每一个个体不仅代表了一个潜在的解,而且还包含了解的不确定性(即区间值)。
2. **适应度评估**: 对于每一个个体,根据其性能和不确定性范围对其进行评估。这一步骤需要特殊的适应度评估函数,能够同时考虑目标优化性能和不确定性。
3. **选择**: 根据个体的适应度,采用一种基于区间Pareto支配的选择机制,选择出表现较好的个体进行繁殖。在这个过程中,不仅比较个体间目标函数的性能,也比较其不确定性的大小,以此来判断哪些个体更有可能成为Pareto最优解。
4. **交叉和变异**: 模拟生物进化中的遗传过程,通过交叉和变异操作生成新个体,这些操作既要保证解的多样性,也要确保能在解空间中有效搜索。
5. **环境选择**: 从当前种群和新生成的后代种群中,根据一定的规则选择一定数量的个体组成新一代种群。这一步旨在保留优秀的解,同时维持种群的多样性。
6. **迭代终止条件**: 设置终止条件,这可以是达到最大迭代次数、解的质量达到一定水平或其他准则。满足终止条件后,算法结束。
研究IP-MOEA意味着探索这些算法步骤的最佳实现方式,以及如何针对特定类型的不确定性问题设计和调整算法的各个方面。这包括如何更准确地估计不确定性、如何设计更有效的区间Pareto支配机制等。随着复杂系统模型的不确定性不断增加,IP-MOEA及相关研究对于工程优化、财务管理等领域具有重要的理论和实践意义。

📚2 运行结果
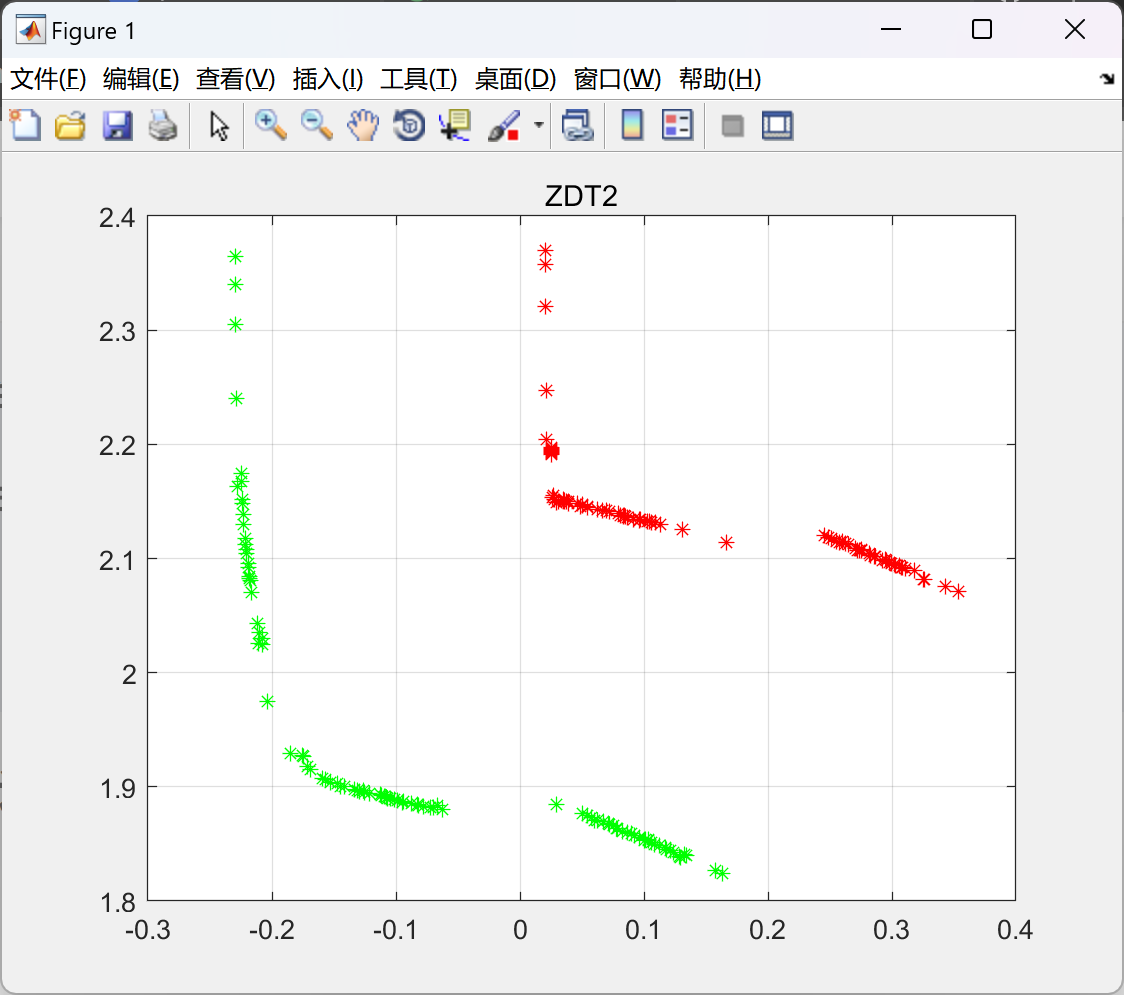
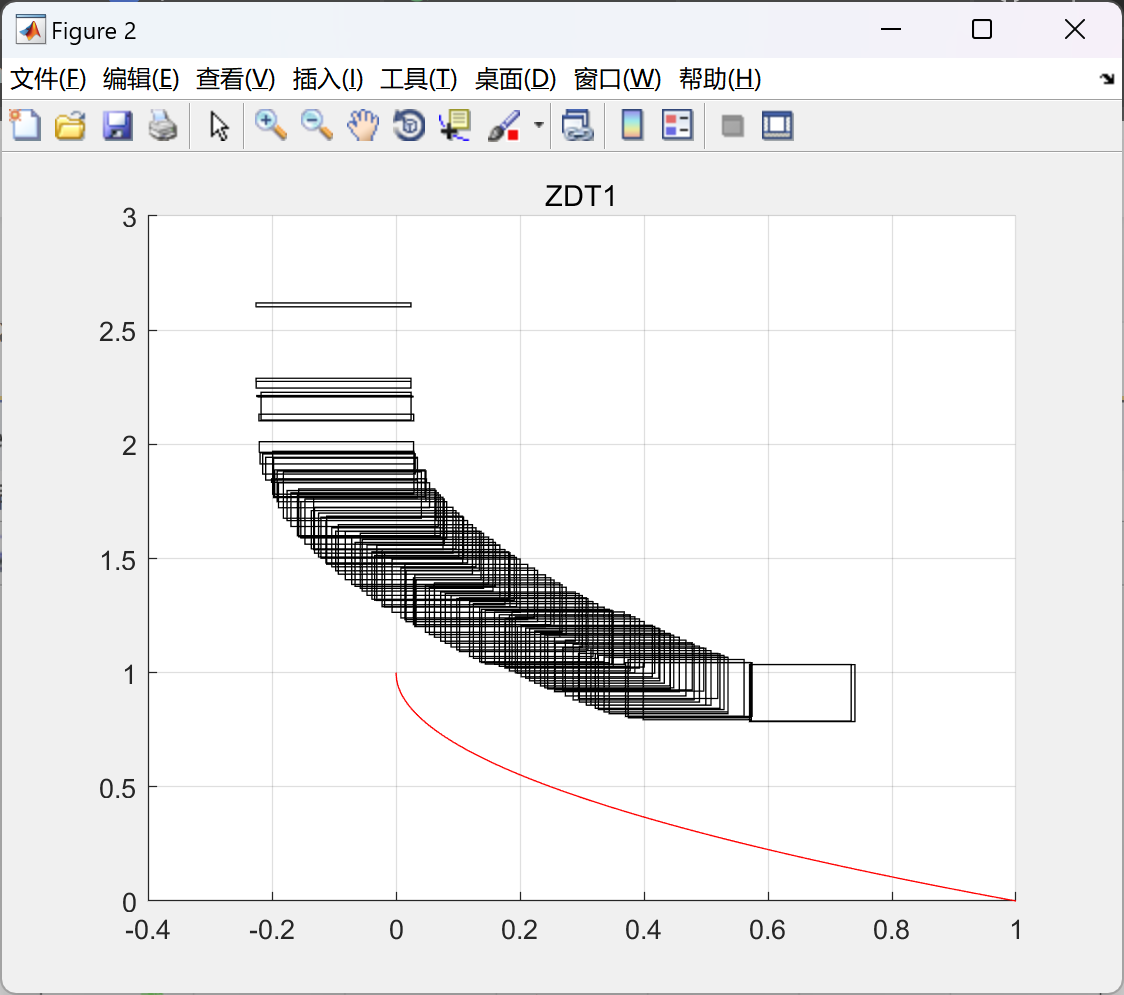
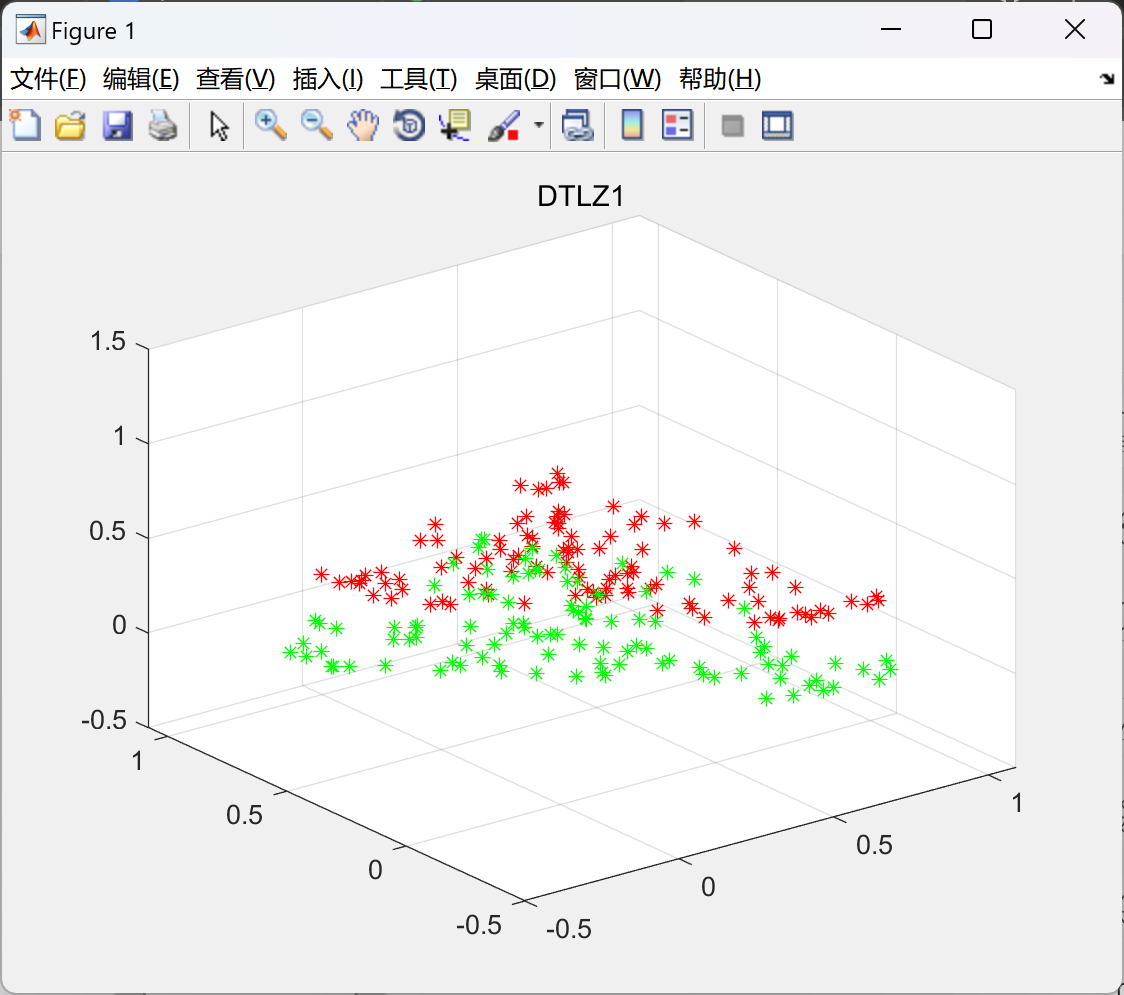
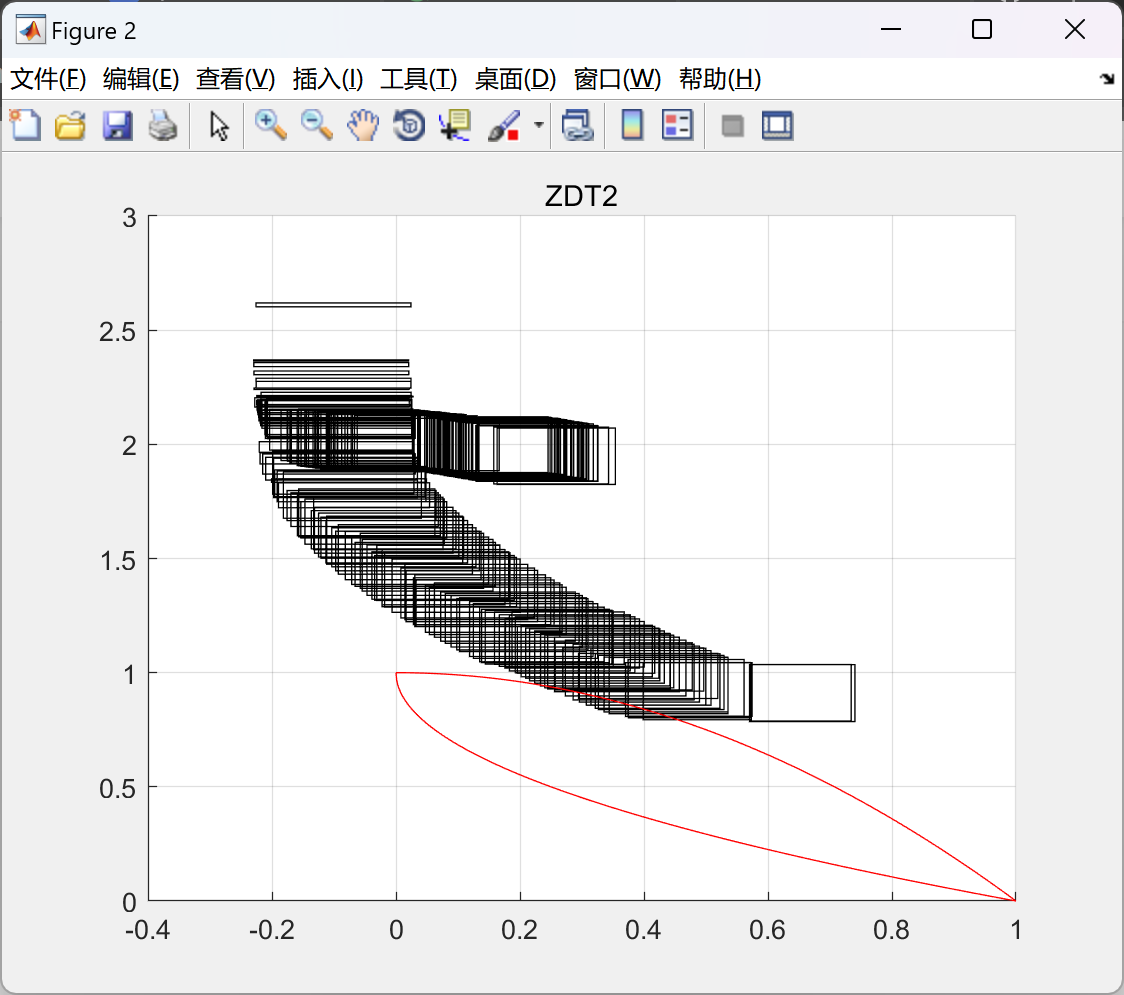
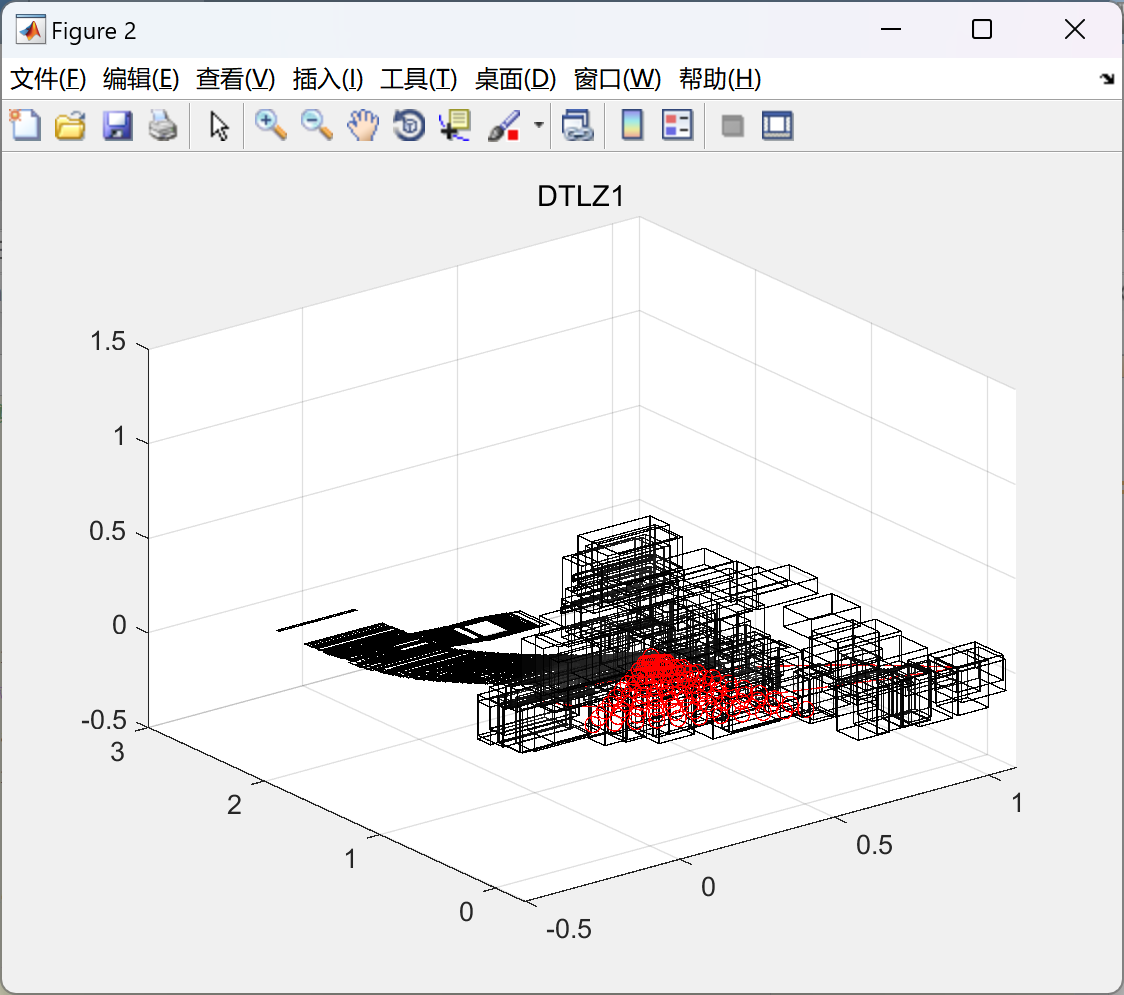
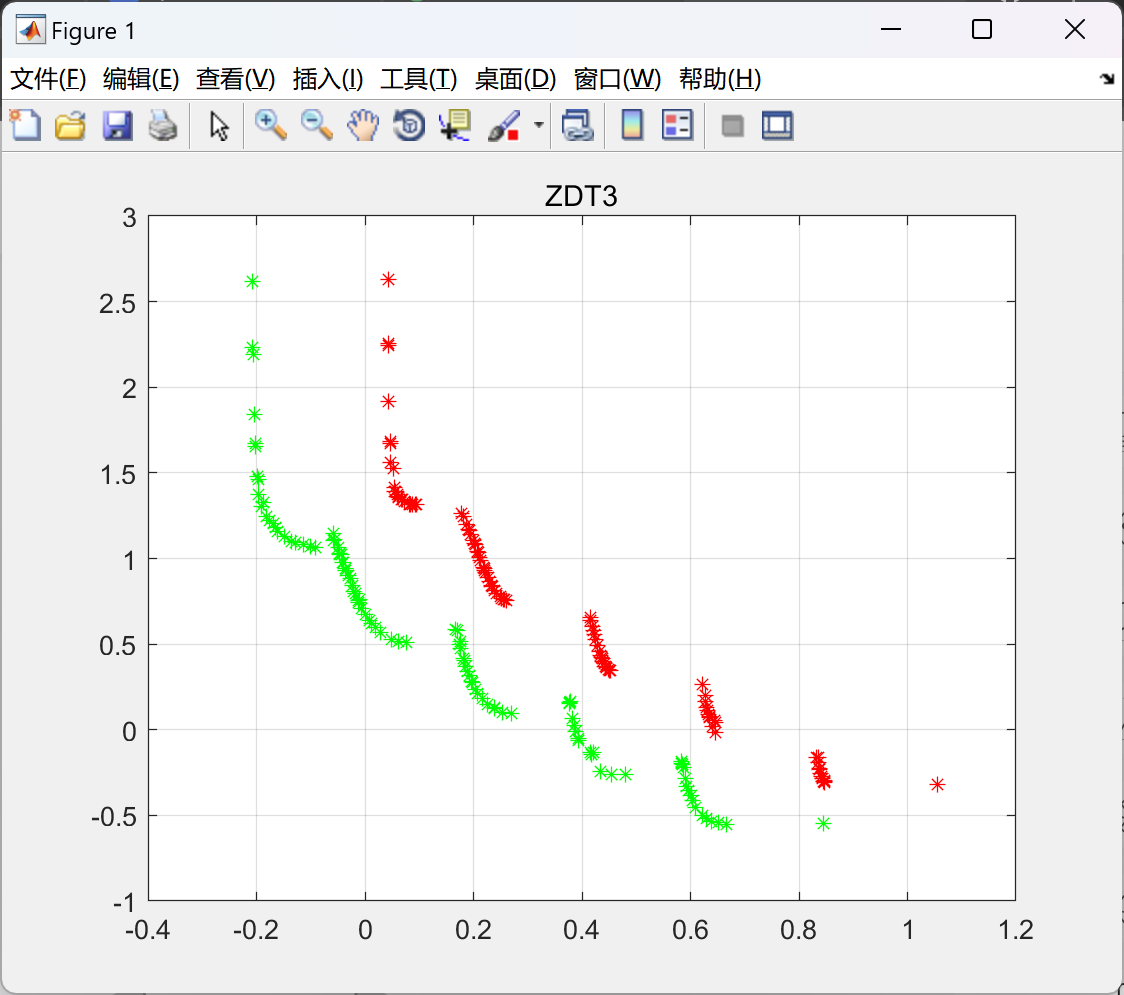
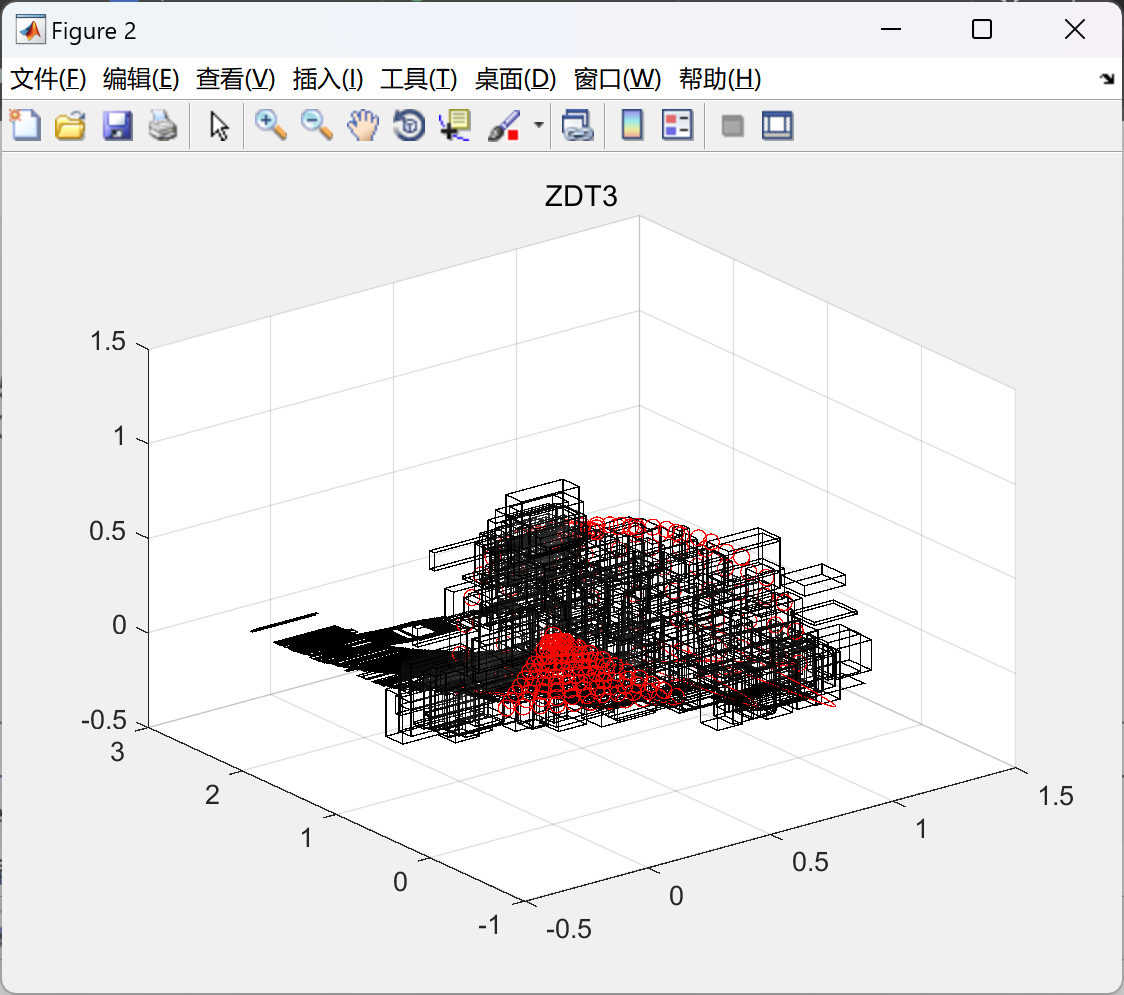
部分代码:
function [indices,archive]=IMOEA(name,nVar,pop,gen,runs)
pop = round(pop);
gen = round(gen);
[nObj,xbounds,ybounds]= objective_description_function(name,nVar);
M=nObj;
V=nVar;
min_range=xbounds(:,1);
max_range=xbounds(:,2);
chromosome = initialize_variables(name,pop,nObj,nVar,min_range,max_range);
fprintf(2,name),fprintf(2,'_循环次数:'),fprintf(2,'%d\n',runs);
%% 进化操作
tic
for i = 1 : gen
pool = round(pop/2);
tour = 2;
parent_chromosome = tournament_selection(chromosome, pool, tour);
mu = 20;
mum = 20;
offspring_chromosome =...
genetic_operator2(name,parent_chromosome,nObj, nVar, mu, mum, min_range, max_range);
[main_pop,~] = size(chromosome);
[offspring_pop,~] = size(offspring_chromosome);
intermediate_chromosome(1:main_pop,:) = chromosome;
intermediate_chromosome(main_pop + 1 : main_pop + offspring_pop,1 : M+V) = ...
offspring_chromosome;
intermediate_chromosome = ...
u_non_domination_sort_mod(intermediate_chromosome, M, V);
chromosome = replace_chromosome(intermediate_chromosome, nObj, nVar, pop);
archive(i,1).xy=chromosome;
if ~mod(i,100)
fprintf('%d generations completed\n',i);
end
end
chromosome=chromosome(1:max(find(chromosome(:,nVar+nObj+1)==1)),:);
toc
time = toc;
%归档集
%% *******************性能指标的计算***************
indices = metric(name,chromosome, nObj, nVar, ybounds,1);
indices.time(1) = time;
plot_figure(name,chromosome,nObj, nVar);
hold on
fit=ptrue(name);
if M == 4
plot(fit(:,1),fit(:,2),'r-');
elseif M==6
plot3(fit(:,1),fit(:,2),fit(:,3),'ro');
end
end
🎉3 参考文献
文章中一些内容引自网络,会注明出处或引用为参考文献,难免有未尽之处,如有不妥,请随时联系删除。
Introduction to Interval Analysis - 百度学术







 本文介绍了区间多目标优化算法IP-MOEA,一种处理带有不确定性因素的多目标优化问题的进化算法。它通过考虑解的区间值,寻找接近理想Pareto前沿的解决方案。文章详细阐述了IP-MOEA的关键步骤,包括初始化、适应度评估、选择、交叉变异等,并提供了MATLAB代码示例。
本文介绍了区间多目标优化算法IP-MOEA,一种处理带有不确定性因素的多目标优化问题的进化算法。它通过考虑解的区间值,寻找接近理想Pareto前沿的解决方案。文章详细阐述了IP-MOEA的关键步骤,包括初始化、适应度评估、选择、交叉变异等,并提供了MATLAB代码示例。














 1446
1446

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








