构建瘤胃微生物脲酶的靶向宏蛋白质组方法
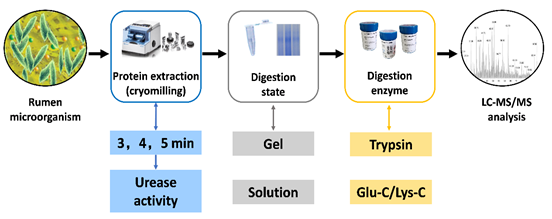
中国农业科学院北京畜牧兽医研究所奶业创新团队在奶牛瘤胃微生物脲酶蛋白多样性方面取得新进展,建立了一种分析瘤胃微生物脲酶的靶向宏蛋白质组方法,不仅为揭示瘤胃脲酶蛋白多样性,也为发展完善靶向宏蛋白质组学方法提供了指导。相关研究成果发表在《微生物前沿(Frontiers in Microbiology)》上。
宏蛋白质组学方法是研究微生物群落功能的重要技术方法,对于连接上游宏基因组和下游宏代谢组具有重要意义。靶向宏蛋白质组方法是指针对某一类功能微生物的某个或几个蛋白或酶,通过宏蛋白质组学方法体系,研究某一类功能微生物的多样性与功能调控的方法,具有功能靶向性强、表型关联性高和调控机制明显等优势。但是,目前靶向宏蛋白质组方法应用的较少,尤其是在瘤胃微生物功能研究方面鲜有报道。脲酶是瘤胃微生物生态系统中的重要酶,在尿素氮循环利用和微生物蛋白质合成中扮演重要角色,但是目前仍缺乏蛋白质水平的脲酶多样性研究。
为了构建瘤胃微生物脲酶的靶向宏蛋白质组方法,研究人员通过检测脲酶活性优化了奶牛瘤胃微生物蛋白质提取(冷冻珠磨时间)条件,分析了瘤胃微生物酶解效率高的酶解方法(胶条、溶液),优化了适合脲酶蛋白的消化酶种类(胰蛋白酶、蛋白内切酶谷氨酸-C、蛋白内切酶赖氨酸-C)。结果表明,液氮冷冻珠磨4分钟时可提取到最高脲酶活性的蛋白质,胶内结合胰蛋白酶酶解方式能鉴定到最多的脲酶肽段。利用已知脲酶蛋白数据库进行鉴定分析,发现瘤胃中存在大量新的未被认识的脲酶蛋白,并且脲酶蛋白多样性较高。在鉴定的脲酶蛋白中,发现他们主要来自于原绿球菌和螺杆菌等。该研究成果对于解析瘤胃微生物脲酶蛋白特征,发展完善靶向宏蛋白质学方法提供了重要指导。
该研究得到国家重点研发计划、中国农业科学院重大任务和现代农业产业技术体系等项目资助。张晓音为文章第一作者,赵圣国和王加启为文章通讯作者。
原文链接:https://doi.org/10.3389/fmicb.2020.573414
猜你喜欢
10000+:菌群分析 宝宝与猫狗 梅毒狂想曲 提DNA发Nature Cell专刊 肠道指挥大脑
文献阅读 热心肠 SemanticScholar Geenmedical
16S功能预测 PICRUSt FAPROTAX Bugbase Tax4Fun
生物科普: 肠道细菌 人体上的生命 生命大跃进 细胞暗战 人体奥秘
写在后面
为鼓励读者交流、快速解决科研困难,我们建立了“宏基因组”专业讨论群,目前己有国内外5000+ 一线科研人员加入。参与讨论,获得专业解答,欢迎分享此文至朋友圈,并扫码加主编好友带你入群,务必备注“姓名-单位-研究方向-职称/年级”。PI请明示身份,另有海内外微生物相关PI群供大佬合作交流。技术问题寻求帮助,首先阅读《如何优雅的提问》学习解决问题思路,仍未解决群内讨论,问题不私聊,帮助同行。

学习16S扩增子、宏基因组科研思路和分析实战,关注“宏基因组”
点击阅读原文,跳转最新文章目录阅读























 703
703

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








