最近想尝试突变是否会改变蛋白质结构,想起来之前安装的Pymol有蛋白质可视化功能,所以小小记录一下。
tips: Pymol的fetch +ID只能可视化在RCSB PDB中有3D 结构的蛋白质。
OK,介绍 1b27蛋白质第73个残基由E变成W的过程
1. fetch 1b27
右下角S,出现序列
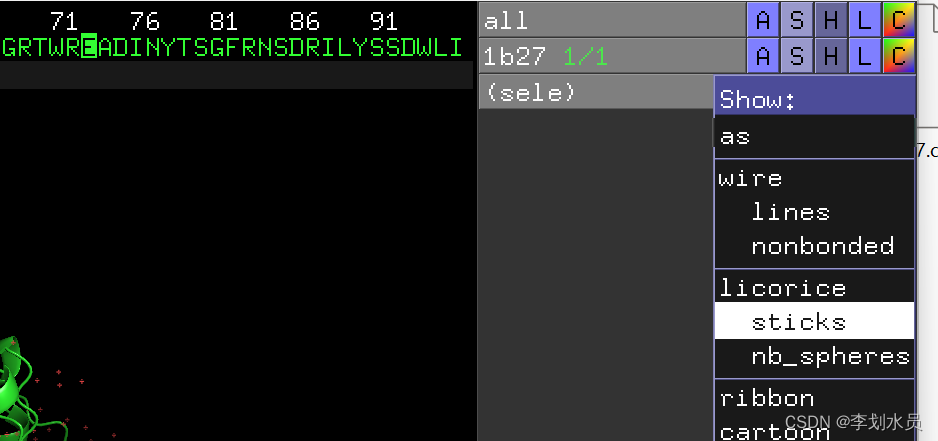
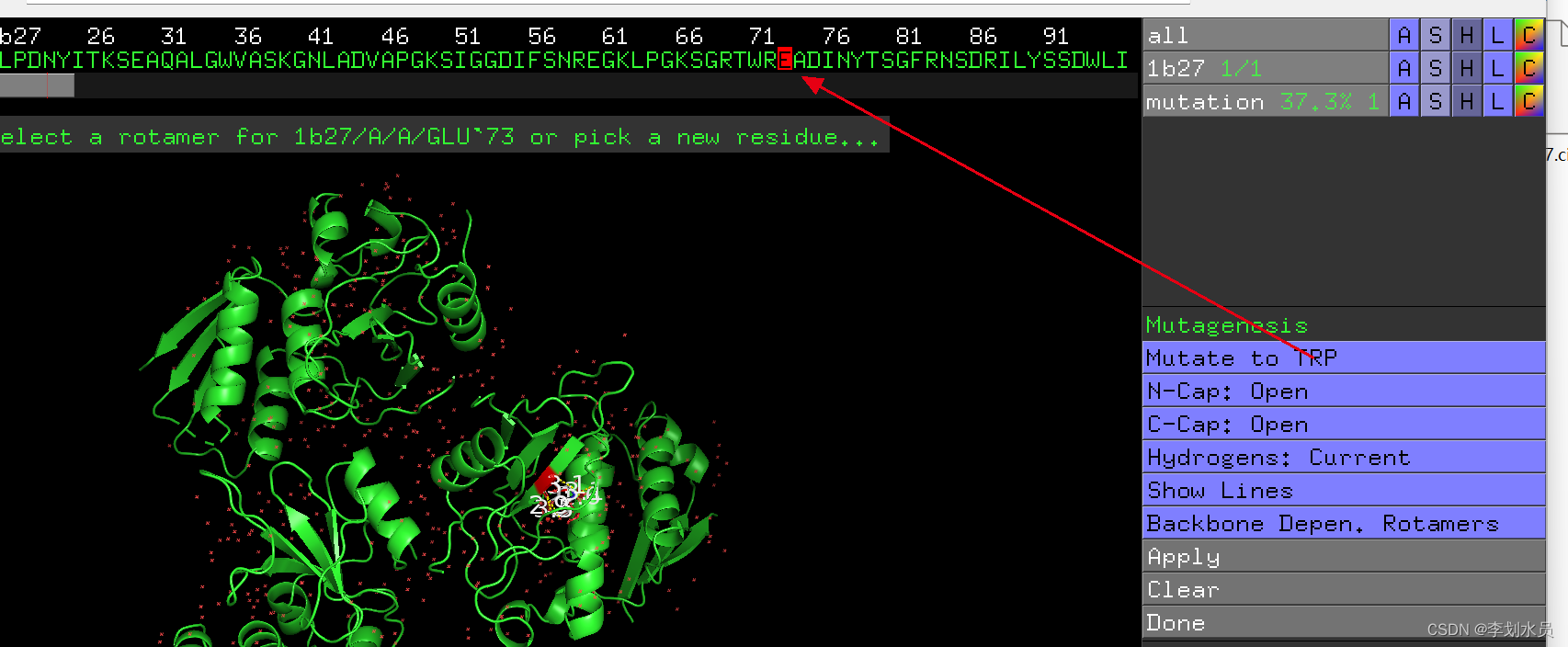
2. 找到73氨基酸E; 点show->stick; 点Color->red标红;可以看到该氨基酸E在Pymol被标记成红色而且可以显示侧链:
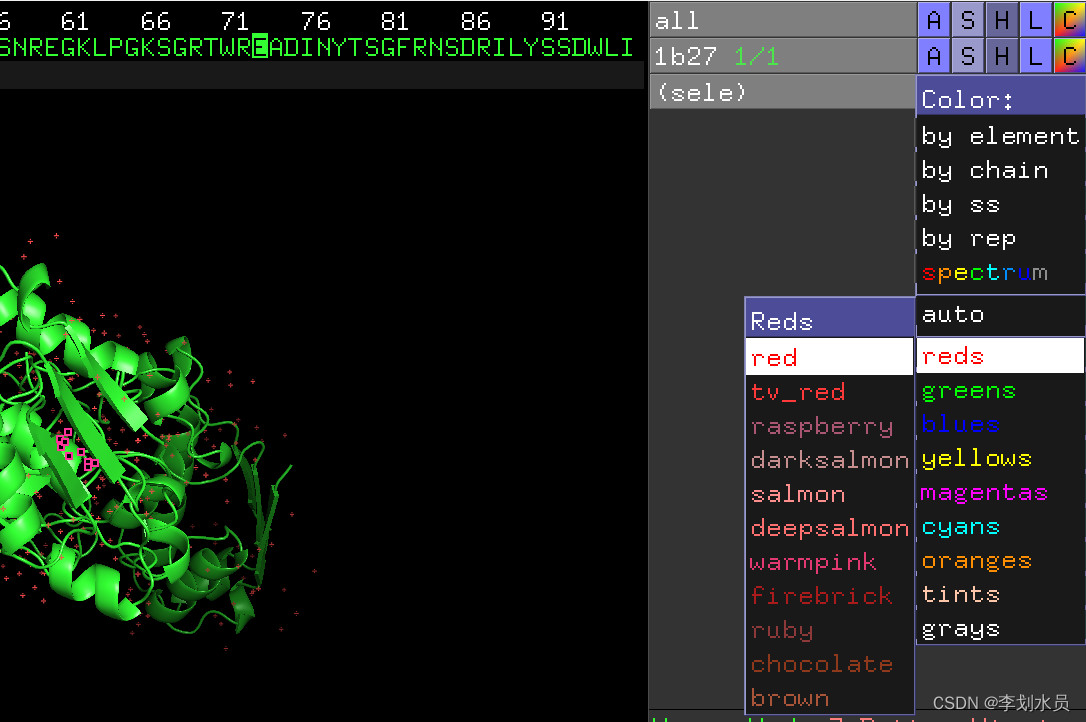
转一下:

3. 点Wizard->Mutagenesis->protein;
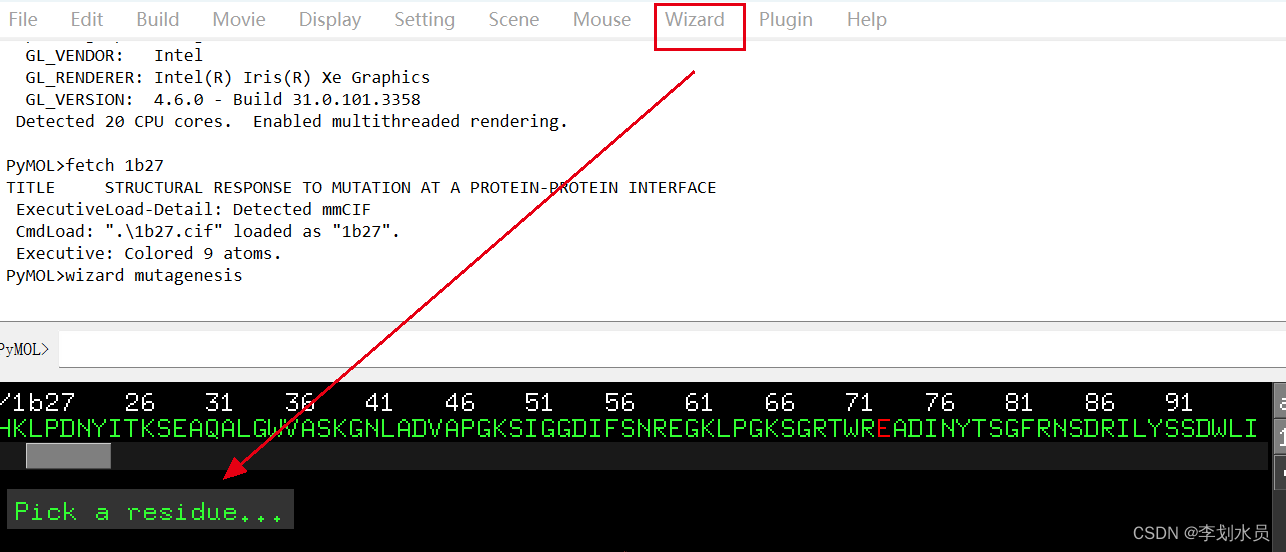
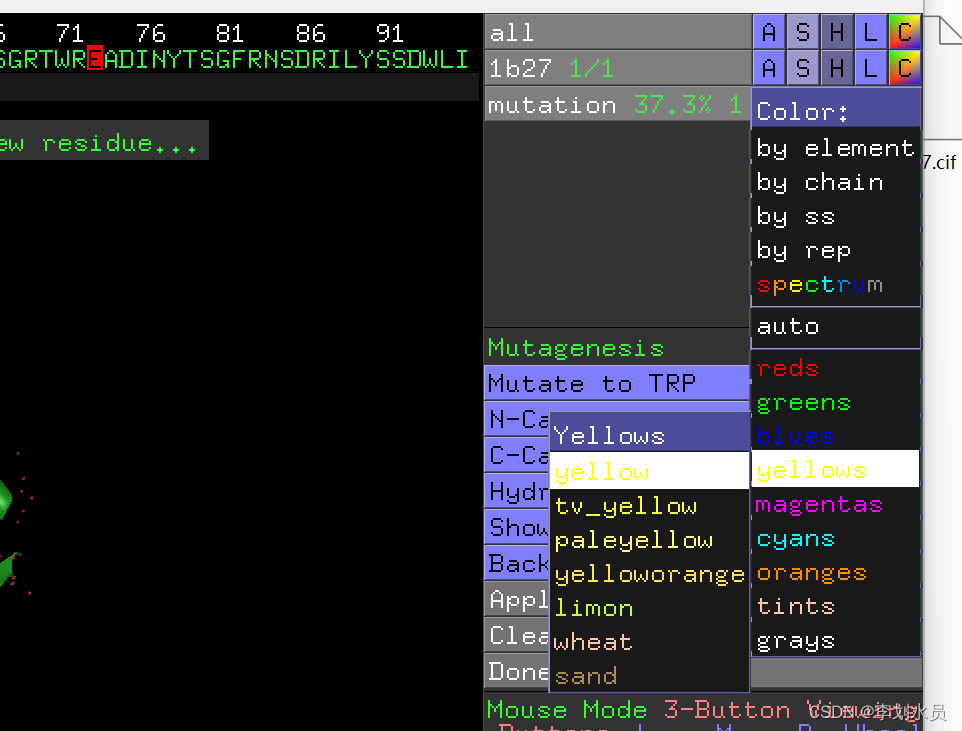
4. 点 右侧NO-MUTATION, 选择色氨酸 Trp W;Pick-#73 Glu, Color->yellow, 可以看到黄色是点突变以后Trp, 红色是原来的Glu. 点击Apply保存就只剩下黄色的Trp了。
5.现在我想放大查看
摁住鼠标右键,向左滑,然后左键调整角度
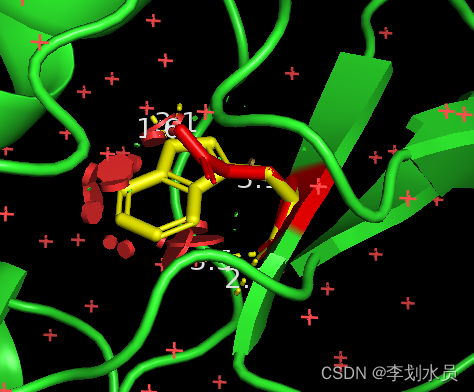
OK 看到了~
可以看到,做完点突变后,周围残基并没有发生构象上的变化,意味着pymol不会自动做能量最小化处理。
参考文档:





















 3052
3052











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








