欢迎关注”生信修炼手册”!
在之前的文章中,我们介绍过CPC和CNCI这两款软件,可以用于预测lncRNA序列。其中CPC基于序列比对的方式,对于注释信息相对全面的物种分类效果较好,但是运行速度相对较慢,CNCI基于序列的三联体碱基组成来区分编码和非编码转录本,对于注释信息缺乏的物种,效果也不错,但是当序列中存在插入缺失时,其分类效果就变得很差。
在高通量测序产生的数据中,会存在一定的测序错误,虽然比例很低,但是基于这样的序列组装得到转录本然后去预测lncRNA, 对于CNCI这个软件而言,就会造成相当大的影响。
为了克服上述问题,需要一款运行速度又快,又可以一定程度上降低测序错误影响的lncRNA预测软件,PLEK软件就是基于这样的出发点进行开发的。PLEK软件通过序列的kmer构成来区分编码和非编码转录本,不需要通过比对来完成,所以运行速度较快,同时其性能受到测序错误的影响的概率较低,比较稳定。
在论文中,开发者评估了测序错误对各个软件准确度的影响,结果如下所示
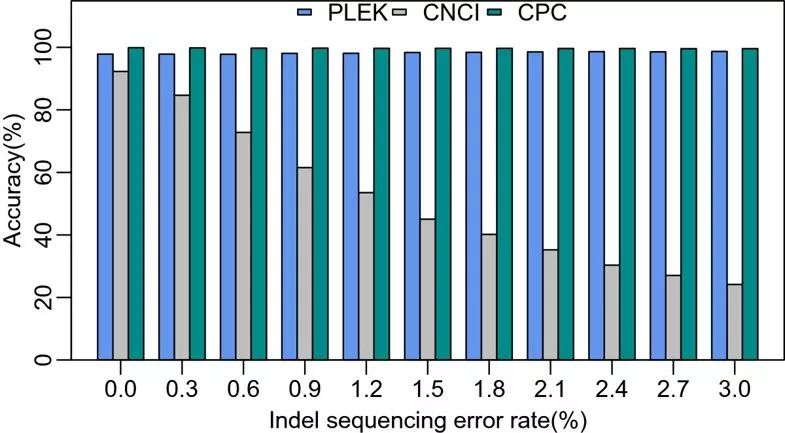
可以看到,随着测序错误比例的上升,CNCI的准确度急剧下降,而PLEK和CPC的结果都相对稳定。
同时利用小鼠的转录本数据,评估了各个软件分类的准确性,结果如下所示








 PLEK是一款快速且受测序错误影响较小的lncRNA预测软件,通过序列kmer构成区分编码和非编码转录本。在准确性与速度方面,它介于CPC和CNCI之间,尤其在处理测序错误时表现出优势。论文结果显示,随着测序错误增加,CNCI准确度显著下降,而PLEK和CPC保持稳定。PLEK的源代码可在SourceForge上获取,提供简单的安装和使用教程。
PLEK是一款快速且受测序错误影响较小的lncRNA预测软件,通过序列kmer构成区分编码和非编码转录本。在准确性与速度方面,它介于CPC和CNCI之间,尤其在处理测序错误时表现出优势。论文结果显示,随着测序错误增加,CNCI准确度显著下降,而PLEK和CPC保持稳定。PLEK的源代码可在SourceForge上获取,提供简单的安装和使用教程。
 最低0.47元/天 解锁文章
最低0.47元/天 解锁文章

















 1460
1460

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








