摘要
最近不断做项目,闲暇之余也优化了某些项目流程。这次要补充的是分析miRNA时要对reads_length进行统计。一般定义的miRNA长度大约在18-24bp,如果你的统计结果在这个范围内,说明reads是可靠的,可以进一步分析。
环境与方法
R version 3.6.1 (2019-07-05)
绘图包,ggplot2
原始数据
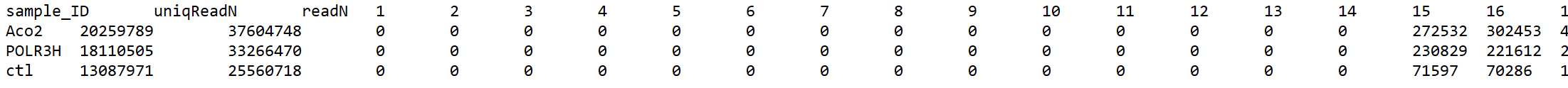
我设置了过滤,14之前是没有reads的,咱们后面需要统计的也是15-24bp的数据。
使用代码
library(ggplot2) #调用ggplot2包,没有的话需要自己安装install.packages("ggplot2")
count = read.table












 订阅专栏 解锁全文
订阅专栏 解锁全文



















 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










