官网:https://surfer.nmr.mgh.harvard.edu/fswiki/PetSurfer
参考博客:https://blog.csdn.net/qq_28480795/article/details/117200025
文章目录
第一步 gtmseg
使用文件
在使用该命令之前,需要使用freesurfer处理T1W图像,而且要求T1W的图像是高质量的。这里使用的T1图像质量是3T。
命令中的
subject
这是一个文件,文件要求是经过t1-freesurfer处理后的t1文件,里面包括mir等一系列文件夹。
使用探讨
在使用这个命令的时候,我是直接在t1的目录里面打开,一直报错:
ERROR: cannot find T1_0143
我就纳闷为什么会报错。然后经过反复实验在发现问题所在:问题在于安装Freesurfer后的SUBJECTS_DIR。
如果按照官方给的文档以及推荐安装位置,那么在打开终端显示的是这个样子:
Setting up environment for FreeSurfer/FS-FAST (and FSL)
FREESURFER_HOME /usr/local/freesurfer
FSFAST_HOME /usr/local/freesurfer/fsfast
FSF_OUTPUT_FORMAT nii
SUBJECTS_DIR /usr/local/freesurfer/subjects
MNI_DIR /usr/local/freesurfer/mni
不管你在哪个目录下输出命令,Freesurfer寻找你的subject永远是在
$SUBJECTS_DIR/你的路径
就好比我上面的输入文件,它就会在
/usr/local/freesurfer/subjects/T1_0143
这个路径下进行寻找,同样找不到文件所以就会报错。
这里提供两个解决方法:
1、(如果只是需要分析文件则不推荐)
将T0001移动到$Freesurfer下。这样做的话移动过去的文件权限:
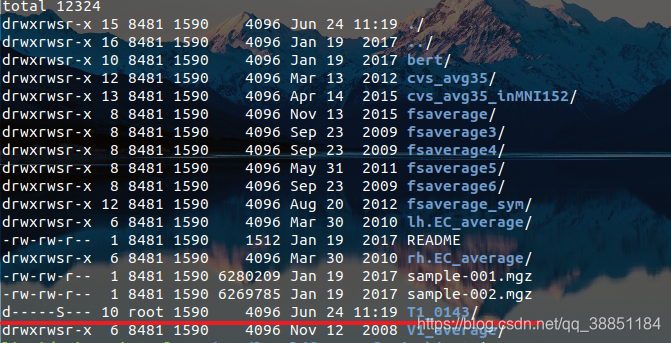
而且T1_0143里面的文件只有读权限,也需要进行更改权限。这样对文件来说比较安全,但是对于处理就不那么友好了。
2、(只分析文件推荐方法)
这里回到官方给的安装步骤中(以ubuntu 18.0.4 为例,其它系统有对应的):
## bash
$> export FREESURFER_HOME=/usr/local/freesurfer
$> source $FREESURFER_HOME/SetUpFreeSurfer.sh
我们发现并没有给出SUBJECTS_DIR的路径,也就是说SUBJECTS_DIR 的路径是在$FREESURFER_HOME/SetUpFreeSurfer.sh这个脚本文件中。注意:这里需要进行脚本文件的更改,请使用管理员权限
sudo vim /usr/local/freesurfer/SetUpFreeSurfer.sh
找到这一行,即是问题所在,这里是我更改过得文件路径(把自己名字抹去,嘿嘿~)
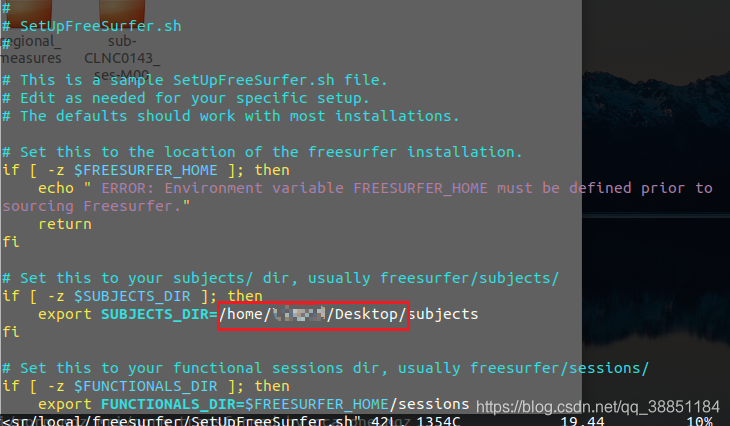
改完之后使用
sh SetUpFreeSurfer.sh
这样做会报个错,但是不用管它。直接关闭终端再重新打开就可以了。
这样的改法一劳永逸,只需要把处理文件放在相应目录下并且不需要更改权限~。但是之后的一些别的需要用到SUBJECTS_DIR的路径会不会报错就不知道了,这个问题是成功解决了。
解决完这个问题,那么我们就可以再脚本或者python语言中使用路径进行petSurface第一步处理了。
PS:之后的第二步中有个检查的步骤,需要用到mri文件下的lh.nii和rh.nii,如果找不到文件,方法如上所示。
输出结果
在mri文件夹下会输出
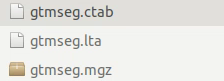
这三个文件,大概需要一两个小时。
第二步 Register your PET image with the anatomical
命令分析
这个步骤要执行两个命令,第一个命令是产生模板。
mri_convert pet.nii.gz --frame frameno template.nii.gz
这个命令分两种情况(每种情况下具体的命令都不一样,需要结合文档查看):
1、如果PET是动态数据,那么需要将动态帧创建模板(官方建议进行时间加权平均,在MATLAB中进行)。
2、如果是静态,那么直接创建模板即可。
第二个命令才是:
mri_coreg --s subject --mov template.nii.gz --reg template.reg.lta
这里需要用到第一步产生的模板。为了方便起见,我选择将模板放到pet.nii.gz目录下。
然后是可以进行注册查看,这一步可以不使用官方文档上的命令,当运行完第二步的时候,会在终端打印出查看注册的命令,直接复制即可查看(该图像结果应该是左右半脑的白质+绿红染色)。
第三步 Apply Partial Volume Correction
这一步需要用到第一步产生的 gtmseg.mgz文件和第二步产生的文件,并且输出的文件是在PET_Data文件夹下。
第四步 Kinetic Modeling (KM). KM is done with either MRTM1 or MRTM2. To run MRTM1
这一步是动态PET图像需要进行操作的步骤,如果是PET静态图那么这步可以进行跳过
第五步 组分析
这一步里有需要注意的点:
1、先进行mri_vol2surf命令,产生 lh.mgx.ctxgm.fsaverage.sm00.nii.gz文件
2、由于静态图并没有进行第四步,所以需要进行把所有的文件链接起来,然后表皮平滑,分析。
注意:这里的文件链接,是链接需要分析的不同组。

























 2369
2369

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?










